Clear Sky Science · fr
Modèle de génération de légendes par IA pour la pathologie numérique de l’adénocarcinome en histopathologie endoscopique utilisant des mécanismes d’attention multi‑instance
Pourquoi convertir des lames en mots importe
Lorsque les médecins suspectent un cancer de l’estomac, de petits échantillons de tissu sont prélevés de la muqueuse gastrique et examinés au microscope. L’interprétation de ces lames est une tâche experte et chronophage pour les pathologistes, et le rapport écrit qu’ils produisent oriente toutes les décisions thérapeutiques ultérieures. Cette étude présente un système d’intelligence artificielle (IA) qui accomplit quelque chose de surprenamment humain : il examine des images numériques de lames de biopsie gastrique et rédige automatiquement de courtes descriptions structurées semblables à un compte rendu de pathologiste.
De la lame de verre à l’assistant numérique
L’adénocarcinome gastrique, forme courante et mortelle de cancer de l’estomac, est actuellement diagnostiqué et gradé par des pathologistes qui étudient visuellement les prélèvements biopsiques. Au cours de la dernière décennie, de nombreux hôpitaux ont commencé à numériser les lames de verre en très grandes images numériques, ouvrant la porte à des outils d’IA susceptibles d’assister le diagnostic. Les systèmes antérieurs se concentraient surtout sur des questions binaires, comme la présence ou non de cancer, ou sur l’attribution d’une catégorie. Or, les rapports pathologiques réels sont narratifs : ils décrivent la morphologie cellulaire, les motifs tissulaires et le degré d’agressivité apparent de la tumeur. Seuls quelques travaux de recherche ont tenté de générer directement ces légendes descriptives à partir d’images de lames entières, et beaucoup d’entre eux dépendent d’étiquettes supplémentaires indiquant des sous‑types prédéfinis, lesquelles sont coûteuses et pas toujours disponibles.
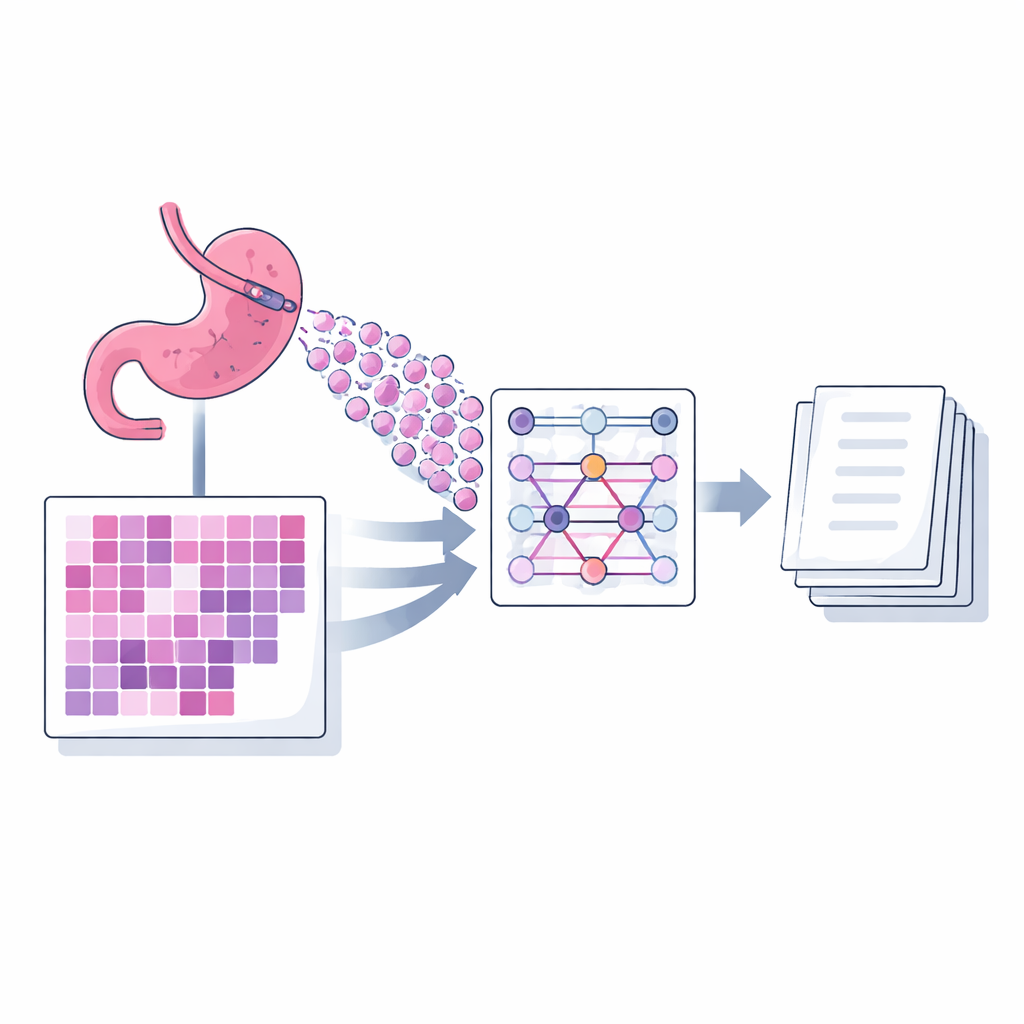
Une nouvelle façon pour l’IA de lire de nombreux petits morceaux
Les auteurs présentent un modèle de légendage appelé MIAC (Multi‑instance Attention Captioning) conçu spécialement pour les lames de biopsie d’adénocarcinome gastrique. Une seule lame numérique est bien trop grande pour être fournie au modèle d’un seul tenant, elle est donc découpée en de nombreuses petites images carrées, ou patchs. MIAC utilise une approche connue sous le nom d’apprentissage multi‑instance : au lieu de traiter ces patchs comme une séquence ordonnée, il les considère comme un ensemble, permettant que le nombre et la disposition des patchs varient d’une lame à l’autre comme c’est le cas en pratique courante. Un puissant réseau d’analyse d’images extrait d’abord des caractéristiques visuelles de chaque patch. Ensuite, un mécanisme d’auto‑attention, construit sans information de position, apprend l’importance relative de chaque patch pour le résumé final. Le modèle combine ces signaux en une représentation compacte de la lame entière, qui alimente ensuite un module linguistique générant une légende diagnostique de la longueur d’une phrase, mot par mot.
Entraînement sur des rapports réels, test dans un hôpital différent
Pour entraîner MIAC, les chercheurs ont utilisé un jeu de données public appelé PatchGastricADC22, qui contient près d’un millier de lames de biopsie numérisées provenant d’un hôpital japonais. Chaque lame est associée à une courte phrase diagnostique extraite du rapport pathologique original et convertie en terminologie standardisée. Les lames ont été découpées en centaines de patchs, et le modèle a été entraîné à reproduire la légende originale lorsqu’on lui fournissait un sous‑ensemble de ces patchs. Les performances ont été mesurées avec des scores linguistiques standards qui évaluent la proximité entre les descriptions générées par l’IA et le texte d’expert. MIAC a surpassé une méthode antérieure à la pointe dans toutes les métriques, en particulier lorsqu’on lui a permis de voir davantage de patchs par lame pendant l’entraînement, ce qui suggère qu’il capturait mieux la vision d’ensemble à partir de vues locales éparses.

Gérer les différences entre hôpitaux
Une question majeure pour tout système d’IA médicale est de savoir s’il fonctionne encore lorsque les données proviennent d’un nouvel environnement. L’équipe a donc testé MIAC sur un ensemble indépendant de lames de biopsie gastrique collectées dans un hôpital différent, avec des légendes rédigées par un autre pathologiste. Ces images différaient en couleur en raison des pratiques locales de coloration et de numérisation, un problème courant qui peut déstabiliser les modèles basés sur l’image. Les chercheurs ont appliqué une technique de normalisation des couleurs largement utilisée, qui ajuste les teintes des colorations pour les rapprocher de celles des lames d’entraînement. Même sans ajustement supplémentaire, MIAC a produit des légendes cliniquement pertinentes sur ce jeu de données externe, et ses performances se sont améliorées lorsque la normalisation des couleurs a été appliquée et lorsque davantage de patchs ont été échantillonnés par lame.
Ce que cela pourrait signifier pour la prise en charge des patients
MIAC n’a pas vocation à remplacer les pathologistes ; il vise plutôt à rédiger des descriptions concises et standardisées que les spécialistes peuvent rapidement relire et modifier. Dans des cliniques surchargées ou des régions avec un accès limité aux spécialistes, un tel outil pourrait raccourcir le temps de rédaction des rapports, réduire la variabilité de formulation et signaler les cas présentant des motifs complexes pour une attention particulière. L’étude souligne aussi les limites actuelles : les performances diminuent encore lorsque le modèle est confronté à des lames provenant de nouvelles institutions ou présentant des motifs tissulaires inhabituels, et les scores linguistiques automatisés ne reflètent pas entièrement l’utilité clinique. Les auteurs soutiennent que des jeux de données plus riches et multicentriques, des méthodes plus intelligentes pour choisir les patchs à analyser et des retours directs des pathologistes seront nécessaires avant que de tels systèmes de génération de légendes puissent être intégrés en toute sécurité aux flux de travail diagnostiques quotidiens.
Citation: Lee, Y., Bai, K., Kim, Y. et al. AI caption generation model for digital pathology of adenocarcinoma in endoscopic histopathology using multi-instance attention mechanisms. Sci Rep 16, 13244 (2026). https://doi.org/10.1038/s41598-026-37455-5
Mots-clés: cancer gastrique, pathologie numérique, IA médicale, génération de légendes d’images, histopathologie