Clear Sky Science · de
RAG-basierte Architekturen zur Abfrage von Arzneimittelnebenwirkungen mit kompakten LLMs
Warum das für die tägliche Medizin wichtig ist
Wer schon einmal ein neues Rezept bekommen hat, hat sich vermutlich gefragt: „Könnte diese Tablette meine Kopfschmerzen oder meinen Hautausschlag verursachen?“ Ärztinnen, Ärzte und Patientinnen und Patienten sehen sich täglich Tausende Male mit derselben Frage konfrontiert, doch die Antworten stecken in sperrigen Handbüchern und Datenbanken. Diese Studie untersucht, wie kleinere, effizientere KI-Systeme auf einen bestehenden Katalog bekannter Arzneimittelnebenwirkungen zugreifen können, um schnelle, präzise und evidenzbasierte Antworten zu liefern — ohne Dinge zu erfinden.

Die Herausforderung bei der Verfolgung von Nebenwirkungen
Arzneimittelnebenwirkungen sind weltweit eine wichtige Ursache für Erkrankungen, Krankenhausaufenthalte und sogar Todesfälle. Neue Medikamente kommen schneller auf den Markt, als beschäftigte Kliniker ihre Risiken auswendig lernen können, und Patienten haben zunehmend komplexe Behandlungsverläufe. Traditionelle Hilfsmittel — gedruckte Handbücher, elektronische Krankenakten und Meldesysteme — sind mächtig, aber in einer hektischen Klinik oft langsam durchsuchbar. Große Sprachmodelle, die hinter Chatbots stehen, scheinen ideal, weil sie Fragen in Alltagssprache beantworten können. Doch bei konkreten Fragen wie „Verursacht dieses Medikament diese bestimmte Nebenwirkung?“ neigen Standardmodelle, selbst sehr große, dazu zu raten oder zu halluzinieren und liefern Antworten, die nicht mit den besten verfügbaren Belegen übereinstimmen.
KI beibringen, nachzuschlagen statt zu raten
Die Autorinnen und Autoren gehen das Problem an, indem sie ändern, wie die KI auf Informationen zugreift, statt nur die Modelle größer zu machen. Sie beginnen mit einer kuratierten Ressource namens SIDER, einer Datenbank, die aufführt, welche zugelassenen Medikamente mit welchen Nebenwirkungen in Verbindung gebracht wurden. Darauf aufbauend bauen sie zwei "Open-Book"-Systeme, die statt sich auf das während des Trainings Gelernte zu verlassen, zur Fragezeit gezielt relevante Fakten nachschlagen und diese einem kompakten Sprachmodell übergeben. In einem textbasierten Ansatz werden Informationen zu Arzneimittel–Nebenwirkungs-Paaren als schriftliche Einträge gespeichert und mittels eines Ähnlichkeits-Engines durchsucht, die die relevantesten Textausschnitte findet. In einem graphbasierten Ansatz namens GraphRAG sind jedes Arzneimittel und jede Nebenwirkung ein Knoten in einem Netzwerk; eine Kante zwischen ihnen bedeutet, dass für dieses Medikament die Nebenwirkung berichtet wurde. Beide Systeme schließen damit ab, dass ein kleines Sprachmodell eine einfache JA- oder NEIN-Antwort sowie eine kurze Erklärung liefert, die ausschließlich auf den abgerufenen Belegen beruht.
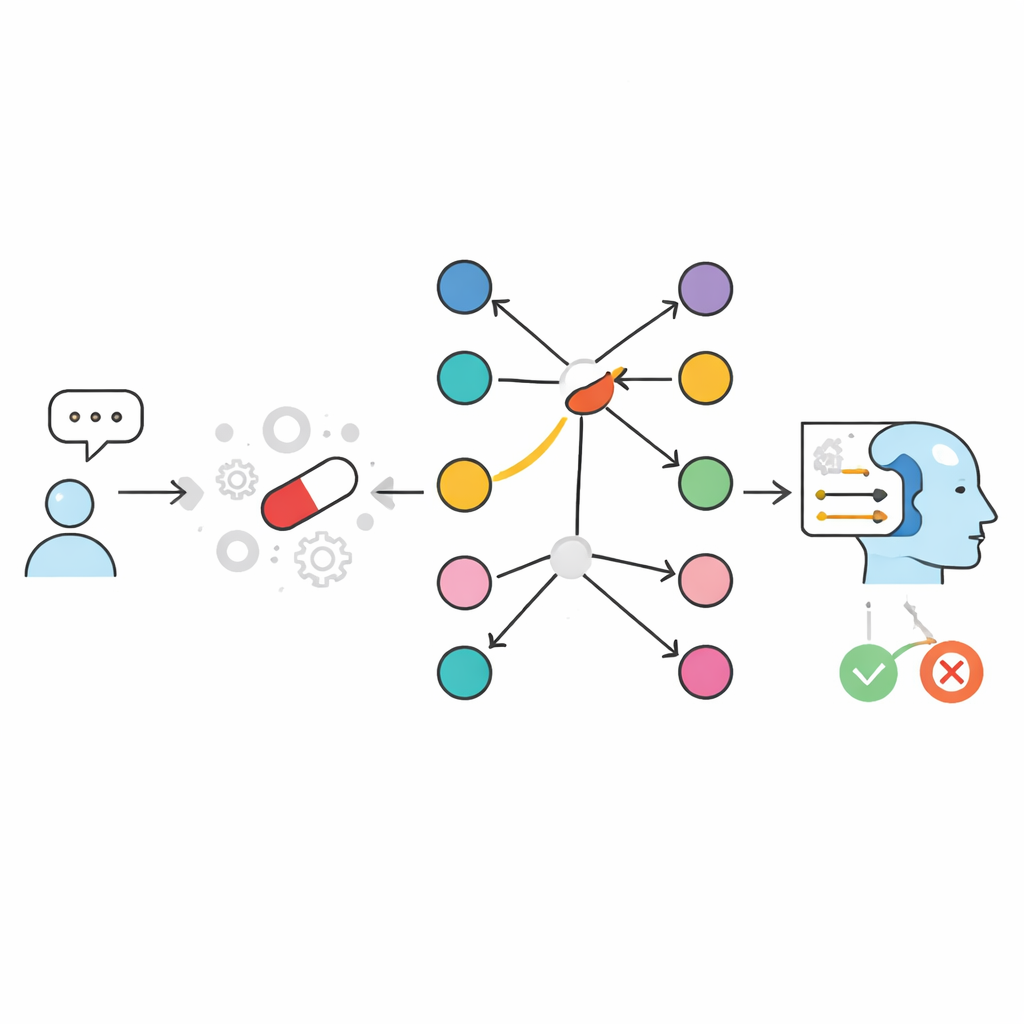
Wie der Graph-Ansatz das Spiel verändert
Zur Prüfung dieser Entwürfe erstellte das Team ein großes, ausgewogenes Benchmark mit nahezu zwanzigtausend Arzneimittel–Nebenwirkungs-Paaren, abgeleitet aus SIDER. Für jedes Medikament wurden einige Nebenwirkungen aufgenommen, die damit verknüpft sind, und andere, die es nicht sind. Kompakte Sprachmodelle, die ohne Nachschlagen arbeiteten, erreichten nur etwa zwei Drittel der korrekten Antworten — ähnlich wie oder schlechter als verbreitete, allgemein einsetzbare Chatbots. Sobald die Retrieval-Komponente hinzugefügt wurde, stieg die Leistung deutlich. Ein textbasiertes System, das pro Arzneimittel–Nebenwirkungs-Paar einen Satz speicherte, erreichte rund 98–99 % Genauigkeit. Der graphbasierte GraphRAG ging noch weiter und erreichte praktisch perfekte Werte: in fast jedem Fall antwortete das System JA, wenn die Verbindung in SIDER existierte, und NEIN, wenn sie nicht existierte. Die wenigen verbleibenden Fehler kamen von der abschließenden Formulierung des Sprachmodells, nicht vom zugrunde liegenden Nachschlagen.
Alle Medikamente zu einem Symptom finden
Die Autorinnen und Autoren untersuchten auch die umgekehrte Frage, die Kliniker oft interessiert: „Welche Medikamente sind dafür bekannt, diese spezielle Nebenwirkung zu verursachen?“ Hier muss das System statt einer einzelnen Ja/Nein-Entscheidung alle passenden Medikamente auflisten. Auch hier glänzte der graphbasierte Ansatz. Da er einfach vom Knoten der Nebenwirkung zu allen verbundenen Medikamenten-Knoten expandiert, liefert er die exakte Liste mit sehr geringer Latenz, selbst wenn Hunderte von Medikamenten beteiligt sind. Ein starkes textbasiertes Verfahren könnte eine ähnliche Vollständigkeit erreichen, jedoch nur, indem es viele einzelne Textstücke durchsucht und zusammensetzt, was es deutlich langsamer machte. Das Team fügte außerdem einen kleinen Normalisierungsschritt hinzu, bei dem ein kompaktes Sprachmodell häufige Rechtschreibfehler von Medikamentennamen korrigiert, bevor die Suche erfolgt — was die Robustheit gegenüber realen Anfragen wie „floxetine" statt „fluoxetine" erheblich verbesserte.
Was das für Patientinnen, Patienten und Klinikpersonal bedeutet
Einfache gesagt zeigt diese Arbeit, dass der klügste Weg, KI für Fragen zu Arzneimittelnebenwirkungen sicherer zu machen, nicht darin besteht, immer größere Modelle zu bauen, sondern kleinere Modelle mit gut organisierten medizinischen Wissensbeständen zu verbinden. Indem bekannte Arzneimittel–Nebenwirkungs-Verknüpfungen als einfacher Graph dargestellt werden und die KI gezwungen wird, ihre Antworten auf diese Struktur zu stützen, können die Autorinnen und Autoren das Raten bei katalogisierten Assoziationen nahezu eliminieren. Das Ergebnis ist ein System, das Ärztinnen, Ärzten oder Patientinnen und Patienten schnell sagen kann, ob ein berichtetes Symptom in einer autoritativen Nebenwirkungs-Liste erscheint und welche Medikamente damit verbunden sind — und dies in verständlicher Sprache erläutert. Zwar entdeckt es keine neuen Nebenwirkungen und ersetzt nicht das sorgfältige klinische Urteil, doch dieser Ansatz bietet eine praktikable, skalierbare Grundlage für vertrauenswürdige, interaktive Werkzeuge, die Menschen helfen, die Risiken der von ihnen verwendeten Medikamente zu verstehen.
Zitation: Nygren, S., Erdogan, O., Avci, P. et al. RAG-based architectures for drug side effect retrieval using compact LLMs. Sci Rep 16, 12754 (2026). https://doi.org/10.1038/s41598-026-41495-2
Schlüsselwörter: Arzneimittelnebenwirkungen, medizinische KI, Wissensgraphen, retrieval-augmented generation, Pharmakovigilanz