Clear Sky Science · zh
近端粒到端粒的石鳅(Traccatichthys pulcher)基因组装配
一条有着重要遗传故事的亮眼小鱼
石鳅 Traccatichthys pulcher 是一种小型淡水鱼,因其闪烁的绿色条纹和鲜明的黑色鳍缘而深受家庭水族爱好者喜爱。但在这色彩斑斓的外表下,藏着一套能揭示河流鱼类如何适应急流、物种如何形成以及我们如何更好地保护和繁育它们的遗传蓝图。本研究提供了几乎完整的该蓝图图谱,让科学家可以非常细致地从染色体一端看到另一端的石鳅 DNA。
这种溪流鱼的分布及其重要性
Traccatichthys pulcher 属于生活在中国南部及东南亚部分地区岩石溪流中的石鳅群体。它的种群分布在岛屿、河流流域和沿海集水区之间呈碎片化,这使其成为研究地理和水流如何塑造演化过程的理想模型。同时,这种鱼鲜艳的颜色也使其在观赏贸易中颇具价值。然而,直到现在,研究人员仍缺乏一份高质量的参考基因组——即其 DNA 序列的“主副本”——来回答有关其起源、自然变异以及如何管理野生与人工饲养种群的问题。
构建近端到端的基因组图谱
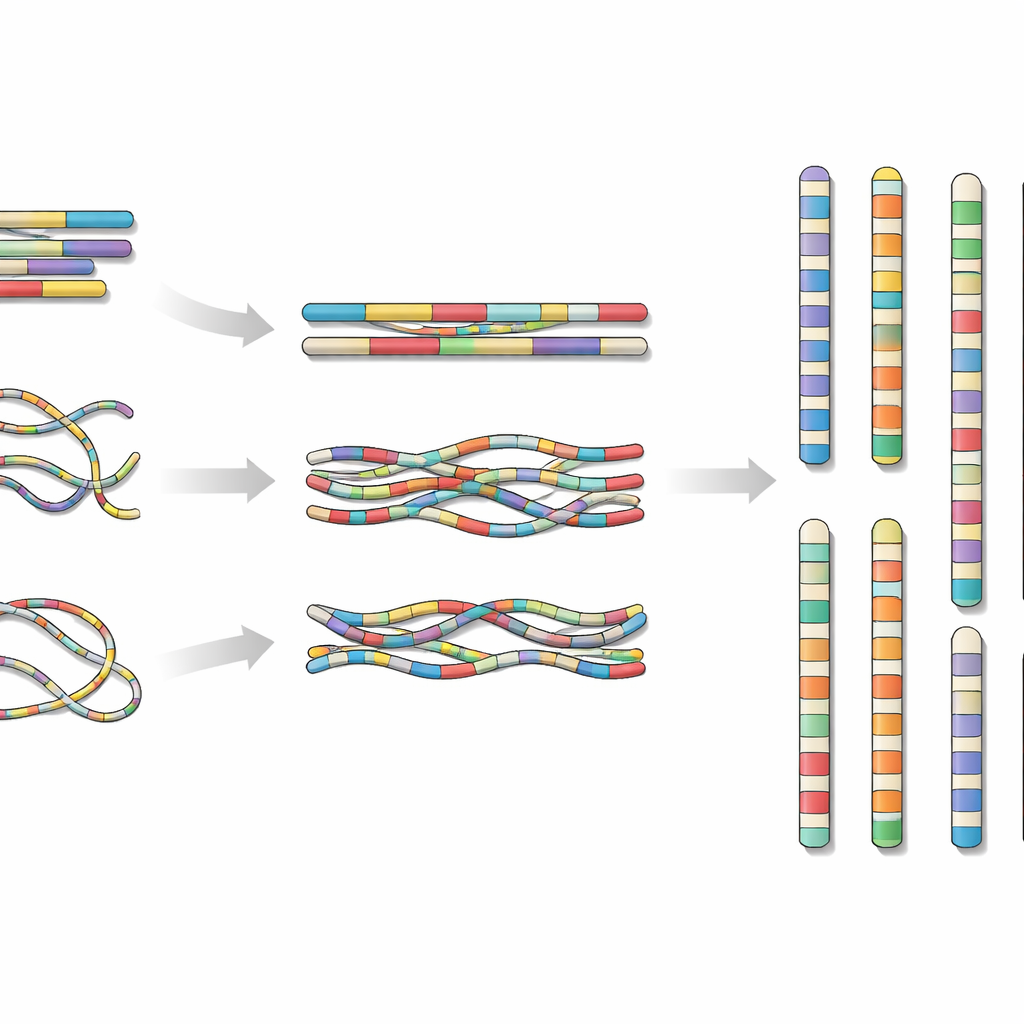
为了解决这一问题,团队在海南岛采集了一条石鳅并从其组织中提取了 DNA 和 RNA。他们结合了三种前沿测序策略:一种平台提供的高准确度长读长测序、另一种平台的超长读长测序,以及一种称为 Hi‑C 的技术,用于揭示 DNA 在细胞核中如何物理排列。通过将这些不同来源的数据输入专门的组装软件,并仔细检查和修正错误,他们将该鱼的 DNA 拼接成 24 条染色体尺度的片段,覆盖约 6.24 亿个遗传“字母”。
检验缺口与隐藏的重复序列
最终的基因组几乎完全连续。23 条染色体完全没有缺口,最后一条染色体仅在一段高度重复的非编码 DNA 区域中保留了一个微小的未解析区域。研究者还寻找了端粒——染色体末端的保护帽,发现在 8 条染色体的两端均检测到端粒,而大多数染色体的另一端也检测到端粒,这表明组装非常接近真实的染色体末端。他们还编目了重复元素,如活动的移动 DNA 序列,这些序列合计约占基因组的五分之一,并绘制了基因相对于这些重复序列的聚集分布。
发现并验证基因
接着,团队把这条长长的 DNA 序列转化为一份功能部件清单。他们通过多种方式预测基因:直接识别序列中的常见基因模式、将序列与相关鱼类的已知基因进行比对,以及利用显示哪些 DNA 区段在体内被主动表达的 RNA 数据。通过合并这些证据,他们鉴定出近 2.4 万个蛋白编码基因,并且针对一组标准保守鱼类基因的测试显示超过 97% 的基因是存在的。额外的比对检查证明这些染色体与相关石鳅物种的染色体很好地对应,进一步支持了新基因组的准确性。
这份新基因组带来的可能性
对普通读者而言,最终成果相当于一本尽可能完整的 Traccatichthys pulcher 参考手册。拥有这份近端到端的基因组后,科学家现在可以寻找决定石鳅颜色和花纹的基因,追踪其零散种群之间的亲缘关系,以及探索溪流鱼类如何应对不断变化的山地环境。保护规划者将获得监测野外遗传健康的强大工具,育种者可以利用这些信息开发可持续的观赏鱼品系。本质上,这项研究将一条漂亮的观赏鱼转变为一个在演化、生态学和淡水生物多样性可持续利用方面都更为明确的研究模型。
引用: Du, LN., Wang, ZC., Chen, ZN. et al. Near telomere-to-telomere genome assembly of the stone loach (Traccatichthys pulcher). Sci Data 13, 492 (2026). https://doi.org/10.1038/s41597-026-06849-5
关键词: 基因组装配, 石鳅, 淡水鱼, 保护遗传学, 观赏鱼育种