Clear Sky Science · ja
イシモチウオ(Traccatichthys pulcher)のテロメアからテロメアまでに迫るゲノムアセンブリ
小さく鮮やかな魚が語る大きな遺伝学的物語
イシモチウオ Traccatichthys pulcher は、きらめく緑色の縞と際立つ黒いひれ縁で家庭用水槽で人気の小型淡水魚です。しかしその色鮮やかな体表の下には、急流に適応する過程や新種の誕生の仕組み、さらには保護や育種の改善に役立つ遺伝設計図が隠されています。本研究はその設計図のほぼ完全な地図を提示し、染色体の端から端までローチのDNAを極めて詳細に示しています。
この渓流魚の生息域とその重要性
Traccatichthys pulcher は、南中国や東南アジアの一部に広がる岩場の渓流に生息するイシモチ類に属します。集団は島々、流域、沿岸の水系に点在しており、地理と水の流れが進化にどう影響するかを研究するモデルとして魅力的です。同時に、その鮮やかな体色は観賞魚市場での価値も高めます。しかしこれまで、起源や自然変異、野生・養殖個体群の管理に答えるための高品質な参照ゲノム、すなわちDNA配列のマスターコピーは存在しませんでした。
ほぼ端から端までのゲノム地図を作る
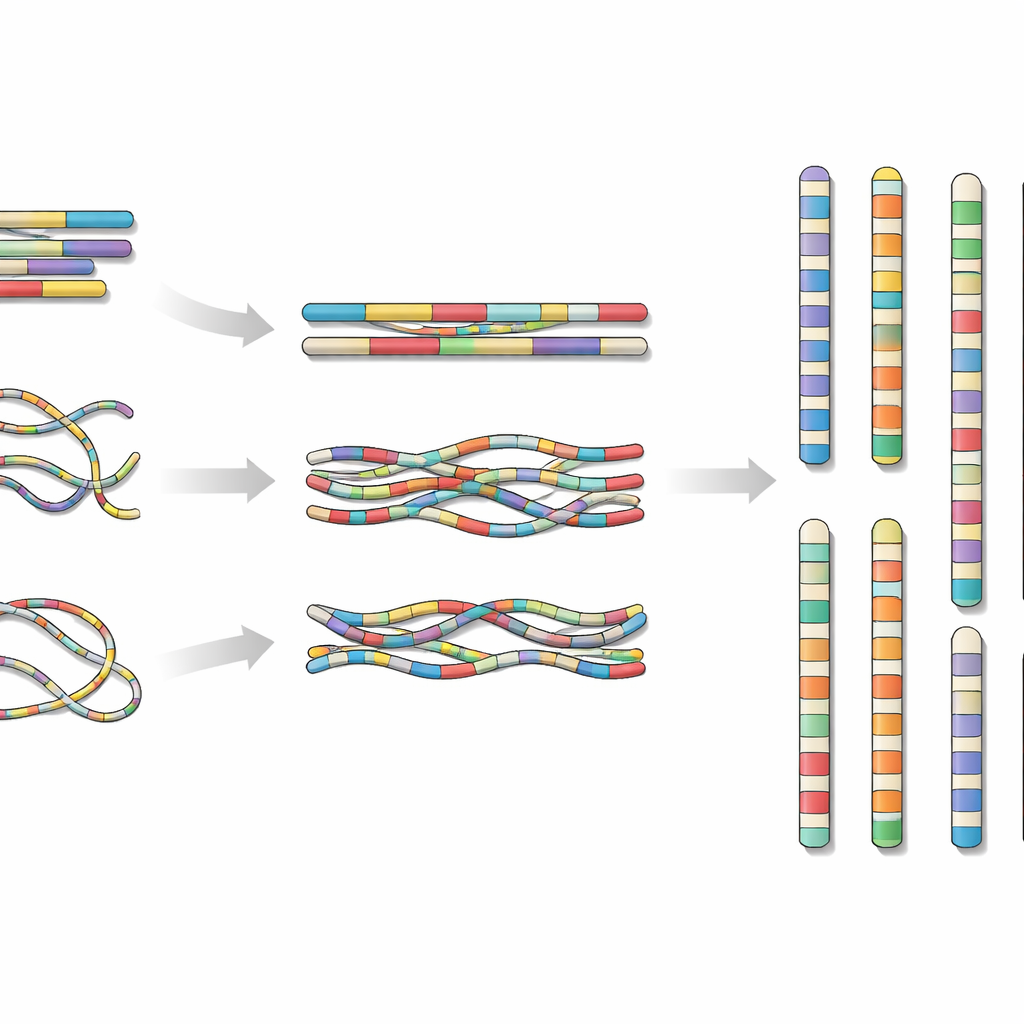
これに対処するため、研究チームは海南島で単一個体のローチを採取し、組織からDNAとRNAを抽出しました。彼らは三つの最先端シーケンシング手法を組み合わせました:一つのプラットフォームによる高精度の長鎖リード、別のプラットフォームによる超長鎖リード、そして細胞核内でDNA断片がどのように配置されているかを示すHi‑Cという技術です。これら異なるデータの流れを専門のアセンブリソフトに投入し、エラーを入念に検査・修正することで、約6億2400万塩基に相当する配列を24本の染色体スケール断片に縫い合わせました。
ギャップと隠れた反復配列の確認
得られたゲノムはほぼ連続していました。23本の染色体にはギャップが全くなく、最後の1本も非コードの高反復領域に小さな未解決領域が一つあるのみでした。研究者たちはまた、染色体末端を保護するテロメアを探索し、8本の染色体の両端および多くの染色体の片方の末端で検出しました。これはアセンブリが実際の染色体端に非常に近づいていることを示します。可動性DNA配列などの反復要素を分類すると、これらはゲノムの約5分の1を占め、遺伝子がこれらの反復に対してどのようにクラスタリングしているかもマッピングしました。
遺伝子の同定と検証
次にチームは、長いDNA配列を機能的な部品リストに変換しました。遺伝子を予測するために複数の方法を用いました:配列内の一般的な遺伝子パターンの認識、関連する魚類の既知遺伝子との比較、そしてどのDNA領域が体内で実際に利用されているかを示すRNAデータの利用です。これらの証拠を統合することで、約24,000のタンパク質コード遺伝子を特定し、保存性の高い魚類遺伝子の標準セットに対する検査では97%以上が存在することが示されました。追加の確認により、染色体は関連する別種のローチと良好に整列し、新しいゲノムの正確性がさらに支持されました。
この新しいゲノムが切り開くもの
一般読者にとって、この成果は現行の技術で到達可能な限りにおいて完成度の高い Traccatichthys pulcher の参照マニュアルです。このほぼ端から端までのゲノムを手に、研究者はローチの色や模様を形作る遺伝子を探索し、分散した個体群の系統関係を追跡し、渓流性魚類が山地環境の変化にどう対処するかを調べることができます。保全計画担当者は野生個体群の遺伝的健全性を監視する強力なツールを得て、育種者は持続可能な観賞魚系統の開発にこの情報を活用できます。本質的に、この研究は美しい観賞魚を進化・生態学・淡水生物多様性の慎重な利用のためのよく理解されたモデルへと変えました。
引用: Du, LN., Wang, ZC., Chen, ZN. et al. Near telomere-to-telomere genome assembly of the stone loach (Traccatichthys pulcher). Sci Data 13, 492 (2026). https://doi.org/10.1038/s41597-026-06849-5
キーワード: ゲノムアセンブリ, イシモチウオ, 淡水魚, 保全遺伝学, 観賞魚の育種