Clear Sky Science · pl
Prawie telomera-do-telomera złożenie genomu ciernika (Traccatichthys pulcher)
Jasna mała rybka z wielką genetyczną historią
Ciernik Traccatichthys pulcher to mała ryba słodkowodna ceniona w akwariach domowych za opalizujące zielone paski i ostre czarne krawędzie płetw. Pod jej kolorową skórą kryje się jednak plan genetyczny, który może ujawnić, jak ryby rzeczne przystosowują się do wartkiego nurtu, jak powstają nowe gatunki i jak możemy lepiej je chronić i rozmnażać. W tym badaniu powstała prawie kompletna mapa tego planu, dając naukowcom wyjątkowo szczegółowy wgląd w DNA ciernika od jednego końca chromosomów do drugiego.
Gdzie żyje ta ryba rzeczna i dlaczego to ważne
Traccatichthys pulcher należy do grupy cierników żyjących w kamienistych potokach południowych Chin i części Azji Południowo-Wschodniej. Jego populacje są rozproszone po wyspach, zlewniach rzecznych i przybrzeżnych dorzeczach, co czyni go atrakcyjnym modelem do badania, jak geografia i przepływ wody kształtują ewolucję. Jednocześnie jaskrawe barwy ryby zwiększają jej wartość w handlu ozdobnym. Do tej pory jednak badaczom brakowało wysokiej jakości genomu referencyjnego — wzorcowej kopii sekwencji DNA — niezbędnej do odpowiadania na pytania o pochodzenie, naturalną zmienność i najlepsze metody zarządzania populacjami dzikimi i hodowlanymi.
Budowa prawie kompletnej mapy genomu
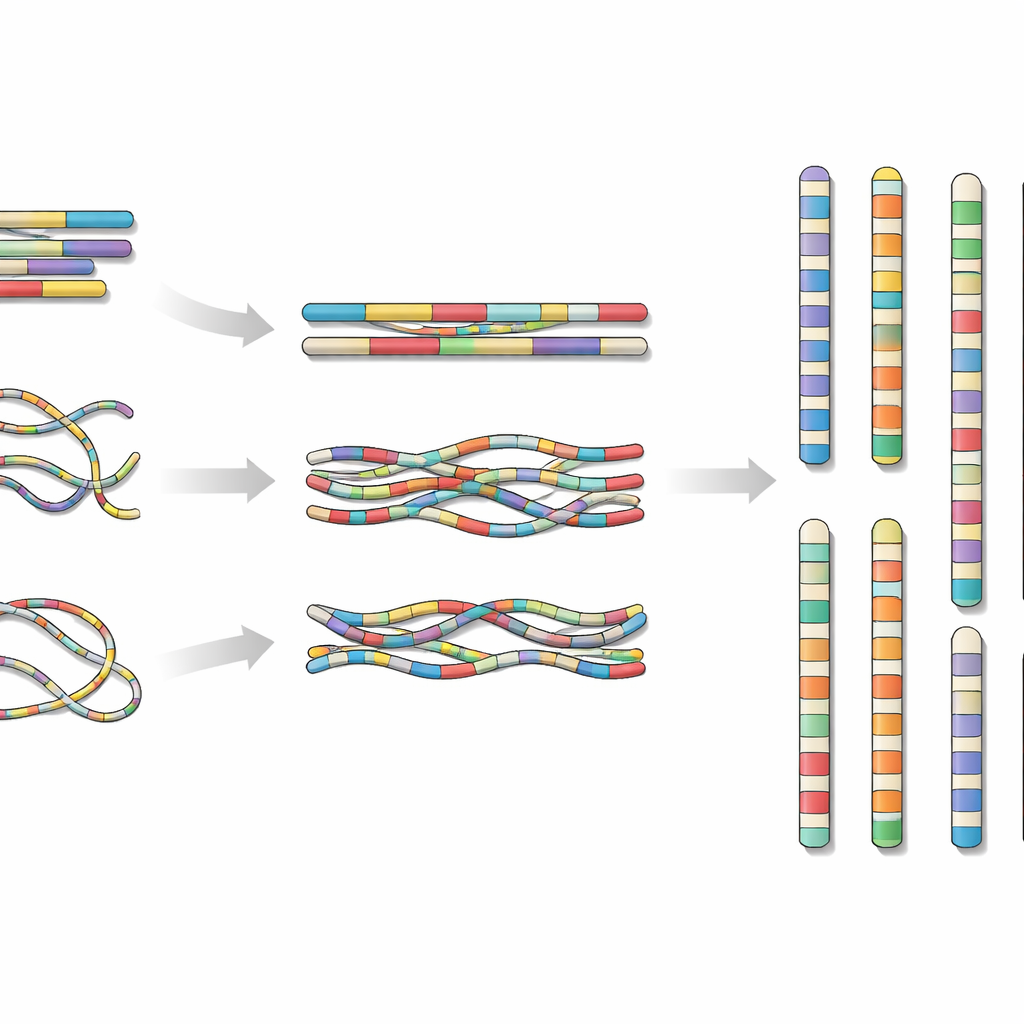
Aby to osiągnąć, zespół pobrał jednego ciernika z wyspy Hainan i wyekstrahował DNA oraz RNA z jego tkanek. Połączyli trzy nowoczesne podejścia sekwencjonowania: bardzo dokładne długie odczyty z jednej platformy, ultradługie odczyty z innej oraz technikę Hi-C, która ujawnia, jak fragmenty DNA są fizycznie rozmieszczone w jądrze komórkowym. Wprowadzając te różne strumienie danych do specjalistycznego oprogramowania składającego i skrupulatnie sprawdzając oraz poprawiając błędy, scalili DNA ryby w 24 fragmenty na poziomie chromosomów, obejmujące około 624 milionów "liter" kodu genetycznego.
Sprawdzanie przerw i ukrytych powtórzeń
Uzyskany genom był niemal całkowicie ciągły. Dwadzieścia trzy chromosomy nie zawierały żadnych przerw, a ostatni chromosom zawierał tylko jeden niewielki nierozwiązany odcinek w silnie powtarzalnym fragmencie niekodującego DNA. Naukowcy poszukali także telomerów — ochronnych czapeczek na końcach chromosomów — i znaleźli je na obu końcach ośmiu chromosomów oraz na jednym końcu większości pozostałych, co wskazuje, że złożenie sięga bardzo blisko prawdziwych końców chromosomów. Skatalogowali elementy powtarzalne, takie jak ruchome sekwencje DNA, które łącznie stanowiły około jednej piątej genomu, i zmapowali miejsca, gdzie geny mają tendencję do grupowania się w odniesieniu do tych powtórzeń.
Wykrywanie i walidacja genów
Następnie zespół przekształcił tę długą sekwencję DNA w funkcjonalną listę części. Predykcję genów przeprowadzono na kilka sposobów: rozpoznając typowe wzorce genów bezpośrednio w sekwencji, porównując je ze znanymi genami pokrewnych ryb oraz wykorzystując dane RNA pokazujące, które fragmenty DNA są aktywnie wykorzystywane w organizmie. Łącząc te źródła dowodów, zidentyfikowali niemal 24 000 genów kodujących białka, a testy względem standardowego zestawu konserwowanych genów ryb wykazały obecność ponad 97% z nich. Dodatkowe kontrole potwierdziły, że chromosomy dobrze pokrywają się z chromosomami pokrewnego gatunku ciernika, co wzmacnia wiarygodność nowego genomu.
Co otwiera przed nami ten nowy genom
Dla czytelnika niebędącego specjalistą końcowy efekt to podręcznik referencyjny dla Traccatichthys pulcher, tak kompletny, jak pozwala na to obecna technologia. Z tym prawie kompletnego genomem naukowcy mogą teraz wyszukiwać geny kształtujące barwy i wzory ciernika, śledzić pokrewieństwo rozproszonych populacji oraz badać, jak ryby żyjące w potokach radzą sobie ze zmieniającymi się warunkami górskimi. Planiści ochrony zyskują potężne narzędzie do monitorowania zdrowia genetycznego w naturze, a hodowcy mogą wykorzystać te informacje do opracowania zrównoważonych odmian ozdobnych. W istocie badanie przekształca ładną rybkę akwariową w dobrze poznany model do badań nad ewolucją, ekologią i odpowiedzialnym wykorzystaniem różnorodności biologicznej w środowiskach słodkowodnych.
Cytowanie: Du, LN., Wang, ZC., Chen, ZN. et al. Near telomere-to-telomere genome assembly of the stone loach (Traccatichthys pulcher). Sci Data 13, 492 (2026). https://doi.org/10.1038/s41597-026-06849-5
Słowa kluczowe: składanie genomu, ciernik, ryba słodkowodna, genetyka ochronna, hodowla ryb ozdobnych