Clear Sky Science · nl
Near telomeer-tot-telomeer genoomassemblage van de stone loach (Traccatichthys pulcher)
Een klein kleurrijk visje met een groot genetisch verhaal
De stone loach Traccatichthys pulcher is een kleine zoetwatervis die in thuisaquaria wordt gewaardeerd om zijn glinsterende groene strepen en scherpe zwarte vinrand. Onder die kleurrijke huid ligt echter een genetisch stappenplan dat kan onthullen hoe rivierbewonende vissen zich aanpassen aan snelstromende beken, hoe nieuwe soorten ontstaan en hoe we ze beter kunnen beschermen en fokken. Deze studie levert een vrijwel volledige kaart van dat stappenplan, en geeft wetenschappers een ongewoon gedetailleerd beeld van de loach‑DNA van het ene chromosoomuiteinde tot het andere.
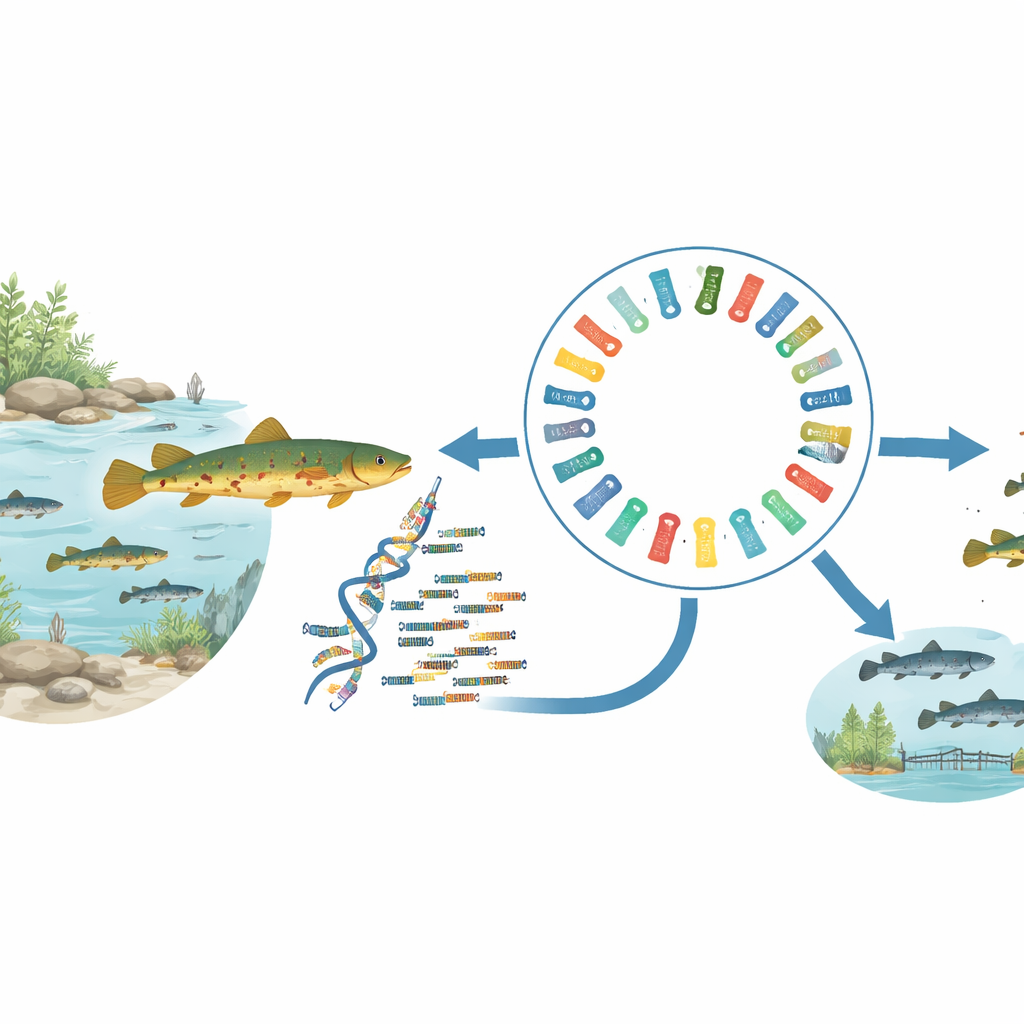
Waar deze beekvis leeft en waarom dat ertoe doet
Traccatichthys pulcher behoort tot een groep stone loaches die in rotsachtige beken leven in Zuid‑China en delen van Zuidoost‑Azië. De populaties zijn verspreid over eilanden, rivierbekkens en kustwateren, wat de soort tot een aantrekkelijk model maakt om te bestuderen hoe geografie en waterstroming evolutie vormen. Tegelijkertijd maken de levendige kleuren van de vis hem waardevol voor de sierhandel. Tot nu toe ontbrak het onderzoekers echter aan een hoogwaardige referentiegenoom — een hoofdkopie van de DNA‑volgorde — die nodig is om vragen over herkomst, natuurlijke variatie en het beheer van wilde en gekweekte populaties te beantwoorden.
Het bouwen van een bijna eind‑tot‑eind genoomkaart
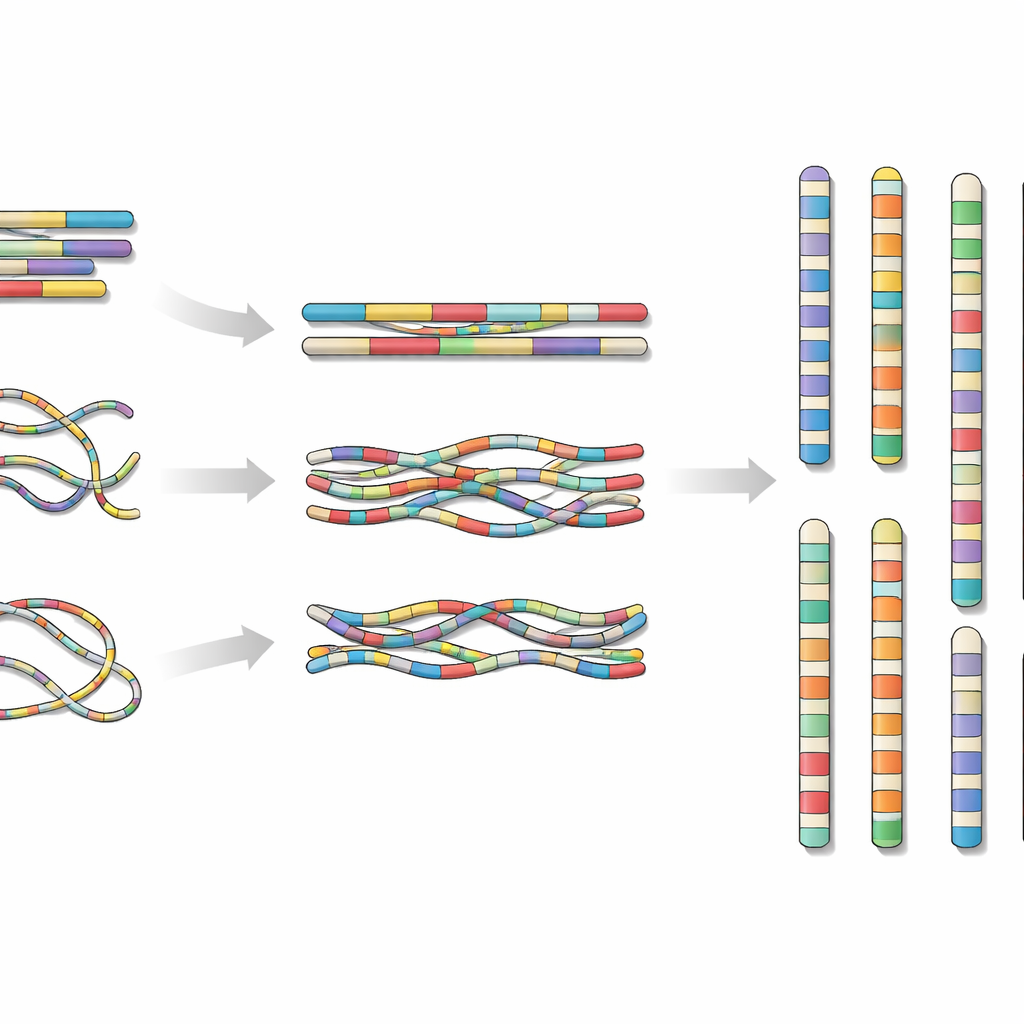
Om dit aan te pakken verzamelde het team één loach van Hainan‑eiland en extraheerde DNA en RNA uit zijn weefsels. Ze combineerden drie moderne sequentiebenaderingen: zeer nauwkeurige lange reads van het ene platform, ultralange reads van een ander en een techniek genaamd Hi‑C die laat zien hoe DNA‑fragmenten fysiek in de kern zijn geordend. Door deze verschillende gegevensstromen in gespecialiseerde assemblagesoftware te voeren en fouten zorgvuldig te controleren en te corrigeren, staken ze het DNA van de vis aan elkaar tot 24 chromosoomschaalstukken, die samen ongeveer 624 miljoen “letters” genetische code beslaan.
Controleren van gaten en verborgen herhalingen
Het resulterende genoom was vrijwel volledig continu. Drieëntwintig chromosomen hadden helemaal geen gaps, en het laatste chromosoom bevatte slechts één klein onopgelost gebied in een sterk repetitieve reeks niet‑coderend DNA. De onderzoekers zochten ook naar telomeren — de beschermende uiteinden van chromosomen — en vonden ze aan beide uiteinden van acht chromosomen en aan één uiteinde van de meeste van de overige chromosomen, een indicatie dat de assemblage zeer dicht bij de werkelijke chromosoomeinden kwam. Ze catalogueerden repetitieve elementen, zoals mobiele DNA‑sequenties, die gezamenlijk ongeveer een vijfde van het genoom uitmaakten, en brachten in kaart waar genen de neiging hebben te clusteren ten opzichte van deze herhalingen.
Het vinden en valideren van de genen
Vervolgens zette het team deze lange DNA‑reeks om in een functionele onderdelenlijst. Ze voorspelden genen op verschillende manieren: door veelvoorkomende genpatronen direct in de sequentie te herkennen, door vergelijking met bekende genen van verwante vissen en door gebruik te maken van RNA‑data die laten zien welke DNA‑secties actief in het lichaam worden gebruikt. Door deze bewijslijnen te combineren identificeerden ze bijna 24.000 eiwitcoderende genen, en tests tegen een standaardset van geconserveerde visgenen toonden aan dat meer dan 97% aanwezig was. Extra controles bevestigden dat de chromosomen goed overeenkwamen met die van een verwante loach‑soort, wat de nauwkeurigheid van het nieuwe genoom verder ondersteunt.
Wat dit nieuwe genoom mogelijk maakt
Voor de niet‑specialist is het eindresultaat een referentiehandleiding voor Traccatichthys pulcher die zo volledig is als de huidige technologie toelaat. Met dit bijna eind‑tot‑eind genoom kunnen wetenschappers nu zoeken naar de genen die de kleuren en patronen van de loach bepalen, nagaan hoe zijn verspreide populaties verwant zijn en onderzoeken hoe beekbewonende vissen omgaan met veranderende bergachtige omgevingen. Behoudsplanologen krijgen een krachtig instrument om de genetische gezondheid in het wild te monitoren, terwijl kwekers de informatie kunnen gebruiken om duurzame sierlijnen te ontwikkelen. In wezen verandert de studie een fraaie aquariumvis in een goed begrepen model voor evolutie, ecologie en zorgvuldig beheer van zoetwaterbiodiversiteit.
Bronvermelding: Du, LN., Wang, ZC., Chen, ZN. et al. Near telomere-to-telomere genome assembly of the stone loach (Traccatichthys pulcher). Sci Data 13, 492 (2026). https://doi.org/10.1038/s41597-026-06849-5
Trefwoorden: genoomassemblage, stone loach, zoetwatervis, conservatiegenetica, ornamentale viskweek