Clear Sky Science · de
Nahezu telomer-zu-telomer Genomassemblierung des Bachdorns (Traccatichthys pulcher)
Ein heller kleiner Fisch mit großer genetischer Geschichte
Der Bachdorn Traccatichthys pulcher ist ein kleiner Süßwasserfisch, der in Heim-Aquarien wegen seiner schimmernden grünen Streifen und der scharfen schwarzen Flossenbegrenzung geschätzt wird. Unter seiner farbenfrohen Haut verbirgt sich jedoch ein genetischer Bauplan, der aufzeigen kann, wie Flussfische sich an schnell fließende Gewässer anpassen, wie neue Arten entstehen und wie wir sie besser schützen und züchten können. Diese Studie liefert eine nahezu vollständige Karte dieses Bauplans und gibt Wissenschaftlern einen ungewöhnlich detaillierten Blick auf die DNA des Dorns von einem Ende der Chromosomen zum anderen.
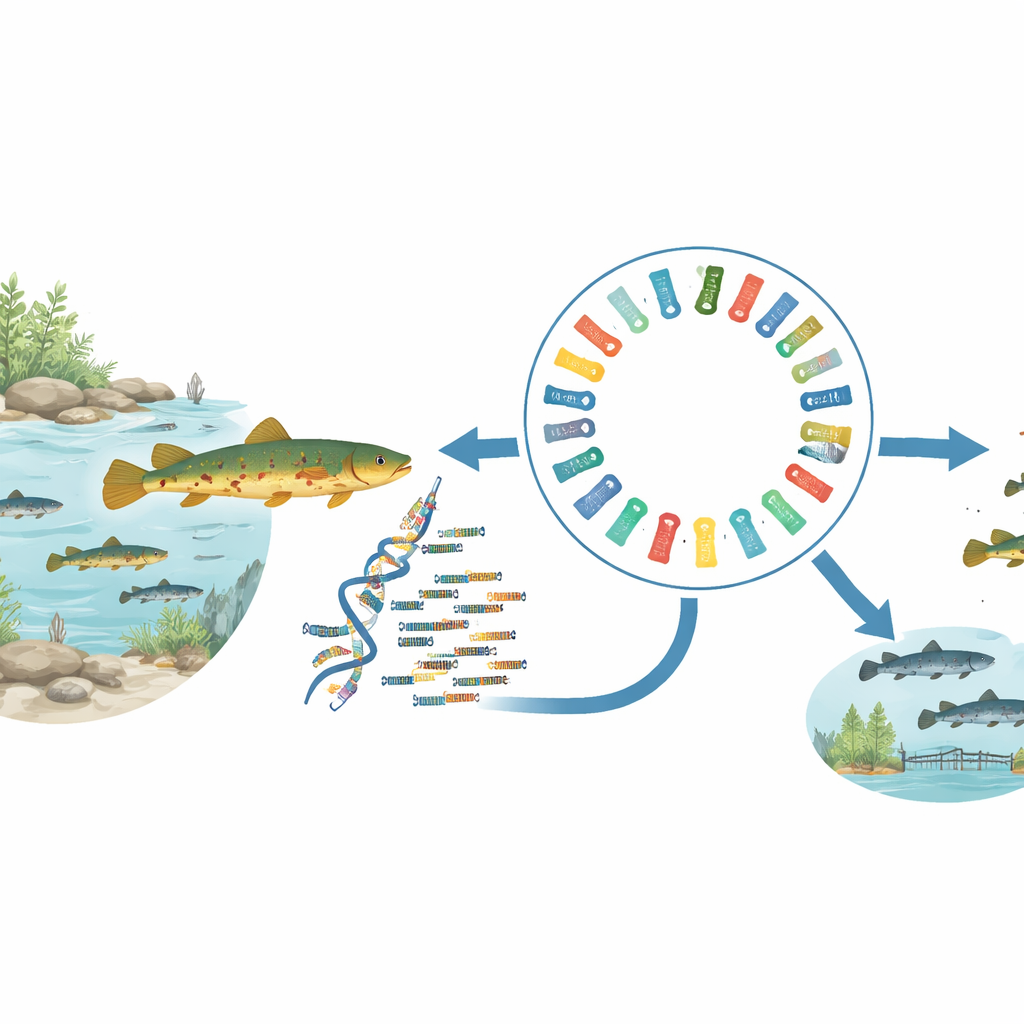
Wo dieser Bachfisch lebt und warum das wichtig ist
Traccatichthys pulcher gehört zu einer Gruppe von Bachdornen, die in felsigen Bächen im Süden Chinas und Teilen Südostasiens vorkommen. Seine Populationen sind über Inseln, Flussbecken und küstennahe Einzugsgebiete verstreut, was ihn zu einem attraktiven Modell macht, um zu untersuchen, wie Geographie und Wasserläufe die Evolution formen. Gleichzeitig machen die leuchtenden Farben den Fisch im Zierfischhandel wertvoll. Bisher fehlte den Forschern jedoch ein hochwertiges Referenzgenom — eine Masterkopie seiner DNA-Sequenz —, das nötig ist, um Fragen zu Herkunft, natürlicher Variation und zur bestmöglichen Bewirtschaftung wildlebender und gezüchteter Bestände zu beantworten.
Erstellung einer nahezu durchgehenden Genomkarte
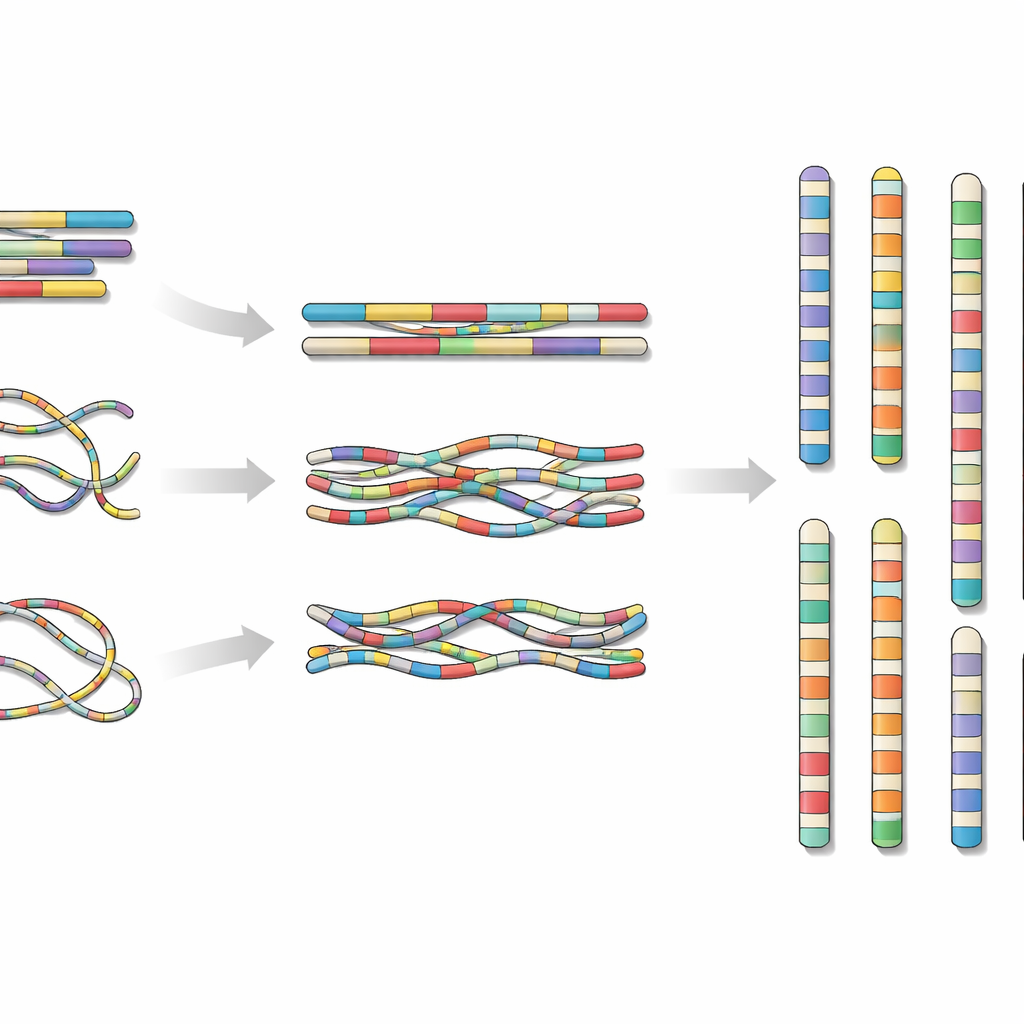
Um das anzugehen, sammelte das Team einen einzelnen Dorn von der Insel Hainan und isolierte DNA und RNA aus seinen Geweben. Sie kombinierten drei moderne Sequenzieransätze: hochpräzise Langreads von einer Plattform, ultra-lange Reads von einer anderen und eine Methode namens Hi-C, die zeigt, wie DNA-Stücke physisch im Zellkern angeordnet sind. Indem sie diese verschiedenen Datenströme in spezialisierte Assemblierungssoftware speisten und Fehler sorgfältig überprüften und korrigierten, setzten sie die DNA des Fisches zu 24 chromosomenähnlichen Einheiten zusammen, die etwa 624 Millionen „Buchstaben“ des genetischen Codes abdecken.
Überprüfung der Lücken und verborgenen Wiederholungen
Das resultierende Genom war nahezu vollständig kontinuierlich. Dreiundzwanzig Chromosomen wiesen überhaupt keine Lücken auf, und das letzte Chromosom enthielt nur einen winzigen, ungelösten Bereich in einer hoch repetitiven Region nichtkodierender DNA. Die Forscher suchten außerdem nach Telomeren — den schützenden Kappen an Chromosomenenden — und fanden sie an beiden Enden von acht Chromosomen und an einem Ende der meisten anderen, ein Hinweis darauf, dass die Assemblierung sehr nahe an die tatsächlichen Chromosomenenden gelangte. Sie katalogisierten repetitive Elemente, wie mobile DNA-Sequenzen, die zusammen etwa ein Fünftel des Genoms ausmachten, und kartierten, wo Gene sich in Relation zu diesen Wiederholungen häufen.
Entdeckung und Validierung der Gene
Als Nächstes wandelte das Team diese lange DNA-Sequenz in eine funktionale Teileliste um. Sie sagten Gene auf mehrere Weisen voraus: durch Erkennen typischer Genmuster direkt in der Sequenz, durch Vergleich mit bekannten Genen verwandter Fische und durch Nutzung von RNA-Daten, die zeigen, welche DNA-Abschnitte im Körper aktiv verwendet werden. Durch das Zusammenführen dieser Beweislinien identifizierten sie fast 24.000 protein-kodierende Gene, und Tests gegen einen Standardsatz konservierter Fischgene zeigten, dass mehr als 97 % vorhanden waren. Zusätzliche Kontrollen bestätigten, dass die Chromosomen gut mit denen einer verwandten Dornart übereinstimmen, was die Genauigkeit des neuen Genoms weiter stützt.
Was dieses neue Genom möglich macht
Für eine/n interessierte/n Leser/in ist das Endergebnis ein Referenzhandbuch für Traccatichthys pulcher, das so vollständig ist, wie es die derzeitige Technologie erlaubt. Mit diesem nahezu durchgehenden Genom in der Hand können Wissenschaftler nun nach den Genen suchen, die Farben und Muster des Dorns formen, verfolgen, wie seine verstreuten Populationen verwandt sind, und erforschen, wie in Bächen lebende Fische mit sich verändernden Gebirgslandschaften zurechtkommen. Schutzplaner erhalten ein leistungsfähiges Werkzeug zur Überwachung der genetischen Gesundheit in freier Wildbahn, während Züchter die Informationen nutzen können, um nachhaltige Zierfischlinien zu entwickeln. Im Wesentlichen verwandelt die Studie einen hübschen Aquarienfisch in ein gut verstandenes Modell für Evolution, Ökologie und den verantwortungsvollen Umgang mit Süßwasser-Biodiversität.
Zitation: Du, LN., Wang, ZC., Chen, ZN. et al. Near telomere-to-telomere genome assembly of the stone loach (Traccatichthys pulcher). Sci Data 13, 492 (2026). https://doi.org/10.1038/s41597-026-06849-5
Schlüsselwörter: Genomassemblierung, Bachdorn, Süßwasserfisch, Erhaltungsgenetik, Zierfischzüchtung