Clear Sky Science · sv
Alfakoronavirus från hjärtnästa fladdermöss använder mänskligt CEACAM6 för att ta sig in i celler
Varför fladdermusvirus berör oss alla
Efter COVID‑19 undrar många var nästa pandemi kan komma ifrån. Denna studie ser framåt genom att undersöka relativt okända coronavirus som lever i fladdermöss och ställer en enkel men avgörande fråga: kan någon av dem redan ta sig in i människoceller? Genom att hitta virus som är "för‑anpassade" på detta sätt hoppas forskare kunna upptäcka potentiella hot tillräckligt tidigt för att vaccin, läkemedel och övervakning ska kunna införas innan ett utbrott börjar.
Att söka i ett trångt virusuniversum
Alfakoronavirus är en stor grupp virus som mestadels infekterar fladdermöss, gnagare och tamdjur, men några orsakar redan vanliga förkylningar hos människor. Att testa varje känd stam i labbet vore omöjligt, så forskarna använde en datorbaserad genväg. Av mer än 2 700 spikeproteinsevenser—den del av viruset som fäster vid celler—valde de 40 som bäst fångade gruppens övergripande genetiska mångfald. De använde sedan dessa spikes för att skapa ofarliga "pseudovirus" som lyser när de framgångsrikt går in i celler, vilket möjliggör snabba tester av vilka receptorer, i vilka arter, varje virus kan använda.
De flesta fladdermusvirus kan inte använda våra vanliga dörrar
Människocoronavirus som vi redan känner till, såsom förkylningsvirus 229E och NL63 eller SARS‑CoV‑2, använder ett fåtal välstuderade molekyler på våra celler som inträdespunkter, inklusive proteiner kallade ACE2, APN och DPP4. När teamet testade sin 40‑viruspanel mot bibliotek av dessa receptorer från många däggdjur fann de att mycket få alfakoronavirus kunde använda dem alls, och nästan inga kunde använda de mänskliga varianterna. Detta tyder på att de klassiska coronavirus‑"dörrhandtagen" är undantaget snarare än regeln i denna gren av virusträdet. För de flesta fladdermusalfakoronavirus måste någon annan, okänd väg in i celler finnas.
Ett hjärtnästfladdermusvirus hittar ett nytt mänskligt handtag
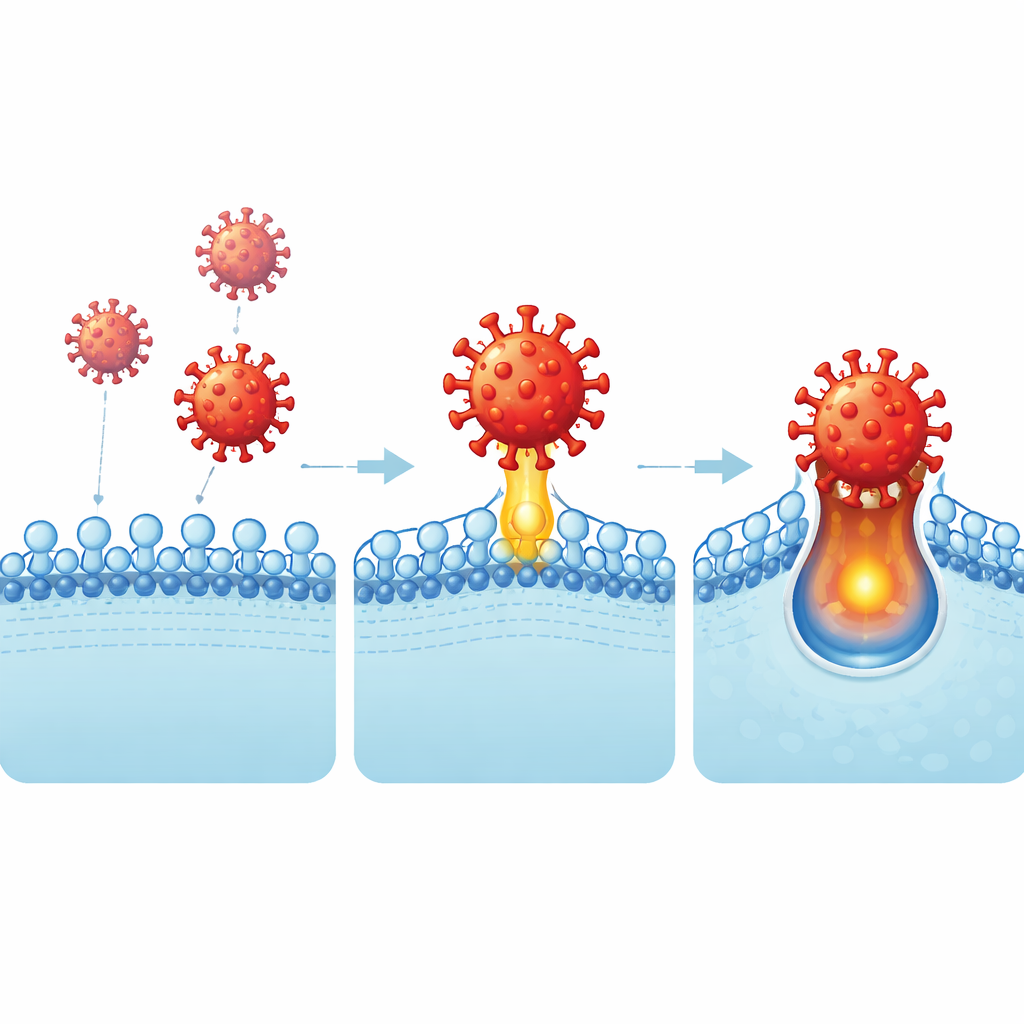
Men ett virus stack ut. En stam kallad CcCoV‑KY43, ursprungligen funnen i hjärtnästa fladdermöss i Kenya, kunde ta sig in i två humana cellinjer härledda från lung‑ respektive tarmvävnad. För att ta reda på hur använde forskarna virusets spikspets—the receptor‑binding domain—som bete mot ett stort panel med 759 mänskliga cellmembranproteiner. Tre nära besläktade kandidater dök upp, alla från CEACAM‑familjen, som normalt hjälper celler fästa vid varandra och är rikliga på slemhinneytor. Uppföljande experiment pekade ut en enda nyckelpartner: ett protein kallat CEACAM6. När mänskliga celler som vanligtvis är resistenta konstruerades att uttrycka CEACAM6 blev de plötsligt mottagliga för fladdermusviruspiken. Att blockera eller minska CEACAM6 kraftigt reducerade infektionen, vilket bekräftar att detta protein fungerar som virusets dörr.
Hur det molekylära omfamningen ser ut
För att se exakt hur denna interaktion fungerar kristalliserade teamet virusets bindningsdomän tillsammans med CEACAM6 och löste strukturen. De fann att tre små slingor på den virala spiken klämmer om spetsen av CEACAM6s yttersta domän och bildar ett tätt gränssnitt dominerat av hydrofoba (vattenavstötande) kontakter. Detta är samma region av CEACAM6 som normalt kontaktar dess partnerproteiner, vilket betyder att viruset har utvecklats för att efterlikna eller störa normala cell‑till‑cell‑interaktioner. Subtila förändringar i bara några aminosyror vid detta gränssnitt var tillräckligt för att stärka eller försvaga virusets inträde, vilket förklarar varför nära släktingar som CEACAM5 binder svagare och inte fungerar som effektiva receptorer.
Hur utbredd är denna riskfyllda egenskap?
Berättelsen slutar inte med ett enda virus. Två ytterligare coronavirus från samma fladdermusart i en annan del av Kenya, och flera besläktade virus från hästskofladdermöss i Kina och Ryssland, visade sig också använda CEACAM6‑lika proteiner som inträdesdörrar. Några kunde använda mänskligt CEACAM6, andra bara fladdermusvarianterna, beroende på finjusterade sekvensdetaljer i både virus och värd. Genom att granska evolutionsträd drar författarna slutsatsen att förmågan att använda CEACAM6 sannolikt uppstått minst två gånger, oberoende, i olika alfakoronavirus‑linjer. Viktigt är att när de screenade blodprover från hundratals personer som bor nära de kenyanska fladdermuskolonierna fann de endast spridda tecken på antikroppar som känner igen dessa fladdermusvirus, vilket talar emot en större, pågående överföring till människor, även om sällsynta eller kortvariga infektioner inte kan uteslutas.
Vad detta betyder för framtida utbrott
Enkelt uttryckt visar detta arbete att vissa fladdermuscoronavirus redan kan öppna en viss "dörr" på mänskliga lungceller, även om de ännu inte orsakat erkänd sjukdom. CEACAM6 är vanligt förekommande i de mänskliga luftvägarna och verkar användas av en geografiskt spridd grupp alfakoronavirus, särskilt i Östafrika och delar av Eurasien. Den kombinationen—färdig tillgång till våra celler och bred distribution i vilda djur—markerar dessa virus som sådana att hålla ögonen på. Genom att identifiera den exakta receptorn och kartlägga vilka virusstammar som kan använda den ger studien konkreta mål för övervakning, riskbedömning och i förlängningen vaccin eller antivirala medel, vilket förflyttar pandemiförberedelser från gissningar till en mer systematisk och evidensbaserad grund.
Citering: Gallo, G., Di Nardo, A., Lugano, D. et al. Heart-nosed bat alphacoronaviruses use human CEACAM6 to enter cells. Nature 653, 180–189 (2026). https://doi.org/10.1038/s41586-026-10394-x
Nyckelord: fladdermus‑coronavirus, CEACAM6, zoonotiskt spillover, virusreceptorer, pandemiförberedelser