Clear Sky Science · pt
Relaxamento 1H R1ρ identifica um intermediário oculto no pareamento de bases do DNA
Por que os movimentos ocultos do DNA importam
O DNA costuma ser desenhado como uma dupla hélice arrumada com pares de bases perfeitamente emparelhados, mas na vida real ele está constantemente respirando e alternando entre formas ligeiramente diferentes. Essas formas breves e raras podem influenciar como o DNA é reparado, lido ou alvo de fármacos. Este estudo desenvolve uma forma mais confiável de observar algumas dessas mudanças rápidas de forma em nível atômico e, usando esse método, revela um estado intermediário previamente oculto em um dos mais importantes comutadores de pareamento de bases do DNA — mostrando que até um fármaco clássico contra o câncer pode remodelar o movimento interno do DNA.
Um olhar mais próximo sobre as sutis mudanças de forma do DNA
Dentro de cada célula, os familiares pares A–T e G–C do DNA não permanecem congelados. Em escalas de tempo de microssegundos a milissegundos, eles podem visitar arranjos raros e de maior energia. Uma alternativa bem conhecida é o pareamento Hoogsteen, em que uma base do par vira temporariamente sua orientação. Embora esses estados costumem representar menos de 2% da população, eles estão ligados a processos como reparo de danos ao DNA, incorporação equivocada de bases e à forma como certas proteínas reconhecem seus alvos. Porque esses estados fugazes são curtos e escassos, são quase invisíveis para técnicas estruturais padrão como cristalografia de raios X ou criomicroscopia eletrônica, mas podem ser investigados por métodos de ressonância magnética nuclear (RMN) sensíveis ao movimento.
Afiando uma ferramenta de RMN para ver o invisível
Os autores concentram-se em uma abordagem especializada de RMN chamada dispersão de relaxamento R1ρ de prótons, que acompanha como os núcleos de hidrogênio no DNA relaxam sob um campo de “spinlock” de radiofrequência constante. Mudanças na taxa de relaxamento quando o campo é variado codificam quão rápido e com que frequência a molécula salta entre diferentes formas. Uma preocupação de longa data, no entanto, é que prótons próximos possam “conversar” entre si por meio de cross-relaxation, criando artefatos que imitam trocas conformacionais reais. Usando simulações detalhadas baseadas em equações de RMN estabelecidas, a equipe mostra que, para as separações típicas próton–próton encontradas entre bases empilhadas no DNA e RNA (em torno de 3,4–3,9 Å), esses efeitos indesejados são muito pequenos — na faixa de cerca de 5% do sinal. Somente quando os prótons estão mais próximos que cerca de 3 Å, como dentro de um único par de bases, os artefatos se tornam significativos, e o estudo estabelece regras práticas para escolher configurações experimentais que evitem essas armadilhas.
Um intermediário oculto no pareamento de bases do DNA
Munidos dessa imagem mais limpa do que seus sinais de RMN significam, os pesquisadores revisitam uma sequência modelo de DNA em que o par A–T padrão de Watson–Crick–Franklin é conhecido por converter-se transientemente para uma forma Hoogsteen. Trabalhos anteriores usando RMN de carbono e nitrogênio sugeriam um interruptor simples de dois estados. Medições de R1ρ de prótons agora revelam algo mais complexo: um terceiro estado excitado de baixa população (ES2) que se situa entre os arranjos usual e Hoogsteen. Ao monitorar os deslocamentos químicos e as taxas de troca de vários átomos de hidrogênio dentro e ao redor do par de bases-chave, a equipe constata que o ES2 é uma característica consistente de pares A–T vizinhos e conecta tanto o estado fundamental quanto o estado Hoogsteen, formando uma rede de três estados em vez de uma chave simples liga/desliga.
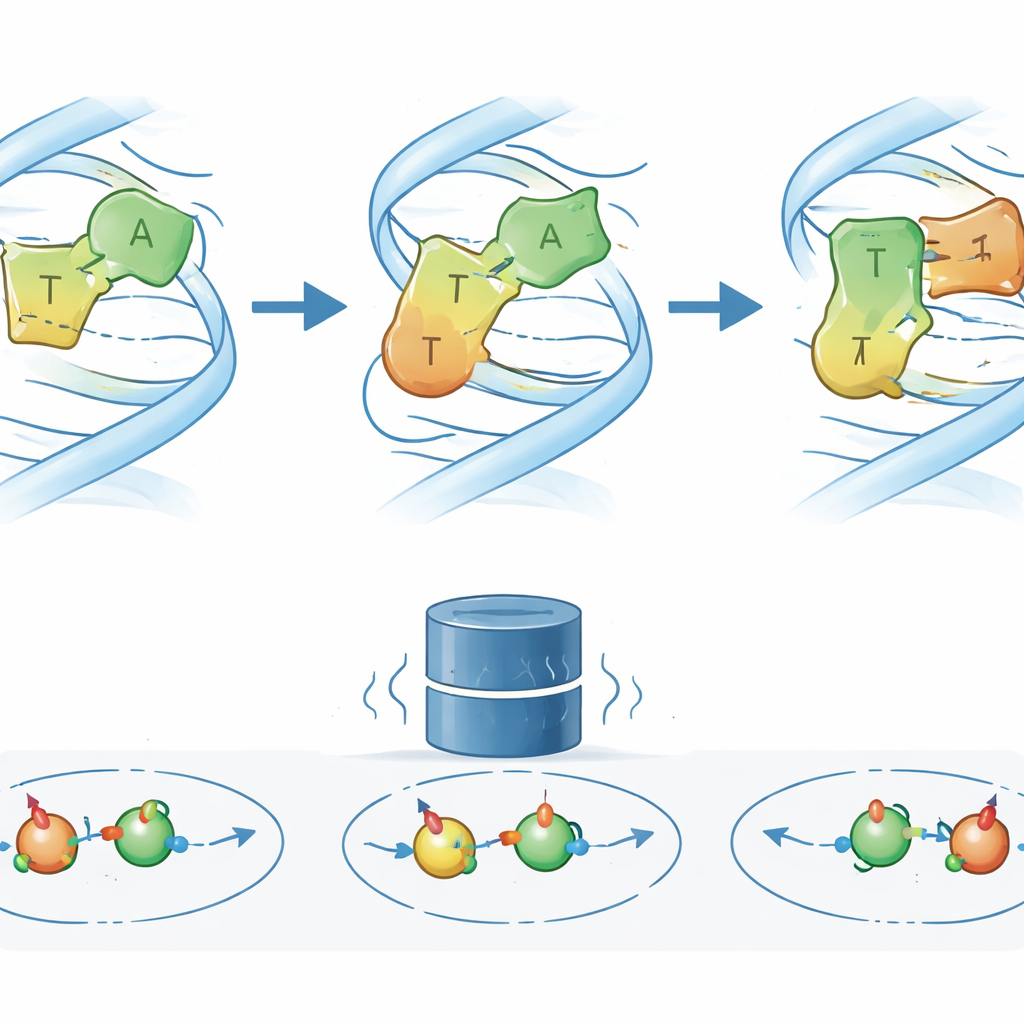
Sondando o novo estado com bases desenhadas e um fármaco contra o câncer
Para entender como o ES2 pode ser, os autores alteraram quimicamente uma das bases parceiras no par A–T chave, removendo ou modificando átomos específicos envolvidos nas ligações de hidrogênio. Essas bases “projetadas” enfraquecem seletivamente ou favorecem modos de pareamento diferentes. As mudanças resultantes nos sinais de RMN e nas taxas de troca mostram que, quando um grupo amino particular é removido, o DNA visita o ES2 com muito mais frequência, o que implica que esse grupo normalmente estabiliza o pareamento do estado fundamental e retarda o acesso ao intermediário. Simulações moleculares avançadas, combinadas com previsões quânticas de deslocamentos de RMN, então apontam para um modelo estrutural plausível: no ES2, a base adenina se reorienta parcialmente de modo que seu grupo amino forma uma ligação de hidrogênio temporária com um átomo de oxigênio alternativo na timina, afrouxando a rede de ligações original no caminho em direção a uma geometria semelhante à Hoogsteen. Notavelmente, quando o fármaco antineoplásico actinomicina D é adicionado, a “impressão digital” de RMN do ES2 torna-se mais proeminente, indicando que o fármaco estabiliza ou enriquece esse intermediário ao se ligar ao longo do DNA.
O que isso significa para a biologia do DNA e a ação de fármacos
Ao quantificar quando e como medidas de R1ρ baseadas em prótons podem ser confiáveis, este trabalho transforma um experimento de RMN especializado em uma ferramenta mais amplamente utilizável para observar movimentos rápidos e raros em DNA e RNA. Usando essa lente aprimorada, os autores descobrem um intermediário previamente oculto e estabilizado por um fármaco no comutador clássico A–T entre as formas normal e Hoogsteen. Para não especialistas, a mensagem principal é que o DNA não é apenas um código estático, mas uma paisagem mutável de estados, e alguns medicamentos podem agir em parte remodelando essa paisagem — favorecendo estruturas fugazes particulares que influenciam como o DNA é lido, danificado ou reparado.
Citação: Dasgupta, R., Steinmetzger, C., Ilgen, J. et al. 1H R1ρ relaxation identifies a hidden intermediate in DNA base-pairing. Nat Commun 17, 4114 (2026). https://doi.org/10.1038/s41467-026-72559-6
Palavras-chave: Dinâmica de pareamento de bases do DNA, Dispersão de relaxamento por RMN, pares de bases Hoogsteen, intermediários conformacionais, actinomicina D