Clear Sky Science · it
Rilassamento 1H R1ρ individua un intermedio nascosto nell’appaiamento delle basi del DNA
Perché contano i moti nascosti del DNA
Il DNA viene spesso rappresentato come una doppia elica ordinata con coppie di basi perfettamente abbinate, ma nella realtà è costantemente in respirazione, oscillando tra forme leggermente diverse. Quelle forme brevi e rare possono influenzare come il DNA viene riparato, letto o preso di mira dai farmaci. Questo studio sviluppa un modo più affidabile per osservare alcuni di questi rapidi cambiamenti conformazionali a livello atomico e, usando tale metodo, rivela uno stato intermedio precedentemente nascosto in uno degli switch di appaiamento delle basi più importanti del DNA—dimostrando che anche un classico farmaco antitumorale può rimodellare il moto interno del DNA.
Uno sguardo più ravvicinato ai cambiamenti silenziosi del DNA
All’interno di ogni cellula, le familiari coppie A–T e G–C nel DNA non restano immobilizzate. Su scale temporali da microsecondi a millisecondi possono visitare configurazioni rare e ad energia più elevata. Un’alternativa ben nota è l’appaiamento Hoogsteen, in cui una delle basi nella coppia ribalta brevemente la propria orientazione. Sebbene tali stati rappresentino tipicamente meno del 2% della popolazione, sono collegati a processi come la riparazione dei danni al DNA, l’incorporazione errata di basi e il modo in cui certe proteine riconoscono i loro bersagli. Poiché questi stati fugaci sono così brevi e scarsi, risultano quasi invisibili agli strumenti strutturali standard come la cristallografia a raggi X o la criomicroscopia elettronica, ma possono essere studiati con metodi di risonanza magnetica nucleare (NMR) sensibili al moto.
Affilare uno strumento NMR per vedere l’invisibile
Gli autori si concentrano su un approccio NMR specializzato chiamato dispersione di rilassamento protonico R1ρ, che monitora come i nuclei di idrogeno nel DNA rilassano sotto un campo di “spinlock” a radiofrequenza stabile. Le variazioni della velocità di rilassamento al variare del campo codificano la velocità e la frequenza con cui la molecola salta tra diverse conformazioni. Un problema noto, però, è che protoni vicini possono “comunicare” tra loro tramite cross‑rilassamento, creando artefatti che imitano un vero scambio conformazionale. Usando simulazioni dettagliate basate su equazioni NMR consolidate, il gruppo dimostra che per le usuali separazioni protoniche osservate tra basi impilate in DNA e RNA (circa 3,4–3,9 Å) questi effetti indesiderati sono molto piccoli—dell’ordine del 5% del segnale. Solo quando i protoni sono più vicini di circa 3 Å, come all’interno di una singola coppia di basi, gli artefatti diventano significativi, e lo studio propone regole pratiche per scegliere impostazioni sperimentali che evitino questi problemi.
Un intermedio nascosto nell’appaiamento delle basi del DNA
Con questa visione più chiara del significato dei segnali NMR, i ricercatori riesaminano una sequenza modello di DNA in cui la coppia A–T di tipo Watson–Crick–Franklin è nota per convertirsi transitoriamente in una forma Hoogsteen. Lavori precedenti basati su NMR su carbonio e azoto suggerivano un semplice interruttore a due stati. Le misure protoniche R1ρ rivelano ora qualcosa di più complesso: un terzo stato eccitato a bassa popolazione (ES2) che si colloca tra le disposizioni usuali e quelle Hoogsteen. Tracciando gli spostamenti chimici e i tassi di scambio di diversi atomi di idrogeno dentro e attorno alla coppia chiave, il gruppo trova che ES2 è una caratteristica coerente delle coppie A–T vicine e si connette sia allo stato fondamentale sia allo stato Hoogsteen, formando una rete a tre stati anziché un semplice interruttore acceso/spento.
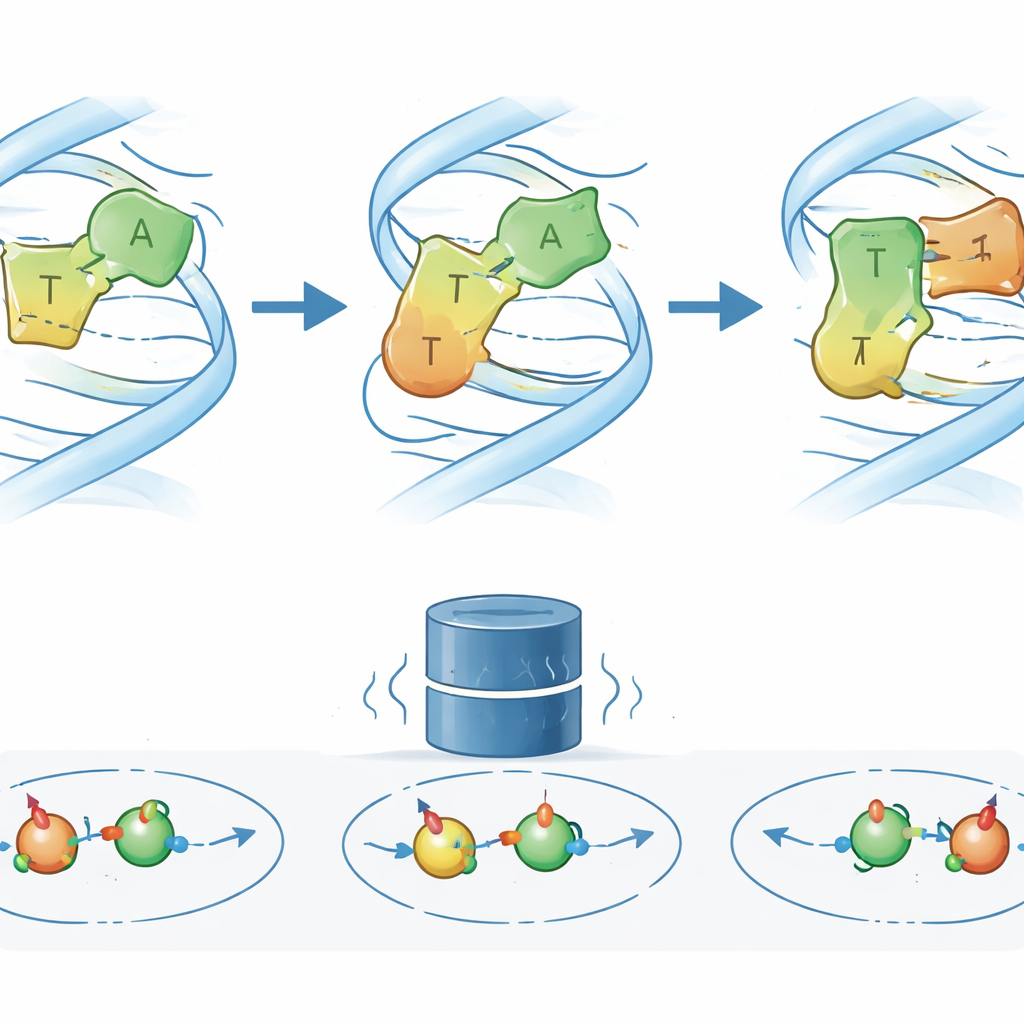
Indagare il nuovo stato con basi progettate e un farmaco antitumorale
Per capire l’aspetto di ES2, gli autori hanno modificato chimicamente una delle basi partner nella coppia A–T chiave, rimuovendo o cambiando atomi specifici coinvolti nei legami a idrogeno. Queste basi “su misura” indeboliscono o favoriscono selettivamente diversi modi di appaiamento. I cambiamenti risultanti nei segnali NMR e nei tassi di scambio mostrano che quando un particolare gruppo amminico è rimosso, il DNA visita ES2 molto più spesso, implicando che tale gruppo stabilizza normalmente l’appaiamento nello stato fondamentale e rallenta l’accesso all’intermedio. Simulazioni molecolari avanzate, combinate con previsioni quantistiche degli spostamenti NMR, indicano quindi un modello strutturale plausibile: in ES2, la base adenina si riorienta parzialmente in modo che il suo gruppo amminico formi un legame a idrogeno temporaneo con un ossigeno alternativo della timina, allentando la rete di legami originale nella transizione verso una geometria simile a Hoogsteen. È notevole che, quando viene aggiunta l’actinomicina D, il “impronta” NMR di ES2 diventi più pronunciata, indicando che il farmaco stabilizza o arricchisce questo intermedio mentre si lega lungo il DNA.
Cosa significa per la biologia del DNA e l’azione dei farmaci
Quantificando quando e come le misure protoniche R1ρ sono attendibili, questo lavoro trasforma un esperimento NMR specialistico in uno strumento più ampiamente utilizzabile per osservare moti rapidi e rari in DNA e RNA. Con quella lente migliorata, gli autori scoprono un intermedio precedentemente nascosto e stabilizzato da un farmaco nello switch classico della coppia A–T tra le forme normale e Hoogsteen. Per i non specialisti, il messaggio chiave è che il DNA non è solo un codice statico ma un paesaggio di stati in continuo cambiamento, e alcuni medicinali possono agire in parte rimodellando quel paesaggio—favorendo strutture fugaci particolari che influenzano come il DNA viene letto, danneggiato o riparato.
Citazione: Dasgupta, R., Steinmetzger, C., Ilgen, J. et al. 1H R1ρ relaxation identifies a hidden intermediate in DNA base-pairing. Nat Commun 17, 4114 (2026). https://doi.org/10.1038/s41467-026-72559-6
Parole chiave: dinamica degli appaiamenti del DNA, dispersione di rilassamento NMR, basi Hoogsteen, intermedi conformazionali, actinomicina D