Clear Sky Science · es
La relajación 1H R1ρ identifica un intermedio oculto en el apareamiento de bases del ADN
Por qué importan los movimientos ocultos del ADN
El ADN suele representarse como una hélice doble ordenada con parejas de bases perfectamente emparejadas, pero en la realidad está en constante respiración y cambia entre formas ligeramente distintas. Esas conformaciones breves y raras pueden influir en cómo se repara, se lee o se dirige el ADN por fármacos. Este estudio desarrolla una forma más fiable de observar algunos de estos cambios rápidos de forma a nivel atómico y, utilizando ese método, descubre un estado intermedio previamente oculto en uno de los intercambios de parejas de bases más importantes del ADN: muestra que incluso un fármaco anticancerígeno clásico puede remodelar el movimiento interno del ADN.
Una mirada más cercana a los cambios silenciosos de forma del ADN
Dentro de cada célula, las familiares parejas A–T y G–C del ADN no permanecen fijas. En escalas de tiempo de microsegundos a milisegundos pueden visitar conformaciones raras y de mayor energía. Una alternativa bien conocida es el apareamiento Hoogsteen, en el que una base del par cambia brevemente su orientación. Aunque esos estados representan típicamente menos del 2% de la población, están vinculados a procesos como la reparación de daños en el ADN, la incorporación errónea de bases y la manera en que ciertas proteínas reconocen sus dianas. Debido a que estos estados fugaces son tan efímeros y escasos, resultan casi invisibles para herramientas estructurales estándar como la cristalografía de rayos X o la criomicroscopía electrónica, pero pueden investigarse mediante métodos de resonancia magnética nuclear (RMN) sensibles al movimiento.
Perfeccionando una herramienta de RMN para ver lo invisible
Los autores se centran en un enfoque especializado de RMN llamado dispersión de relajación R1ρ de protones, que sigue cómo los núcleos de hidrógeno en el ADN se relajan bajo un campo de “bloqueo de espín” de radiofrecuencia constante. Los cambios en la tasa de relajación al variar el campo codifican la rapidez y la frecuencia con que la molécula salta entre distintas formas. Una preocupación de larga data, sin embargo, ha sido que protones cercanos pueden “comunicarse” entre sí mediante cross-relaxation, creando artefactos que imitan un intercambio conformacional real. Mediante simulaciones detalladas basadas en ecuaciones de RMN establecidas, el equipo demuestra que para las separaciones protón–protón típicas encontradas entre bases apiladas en ADN y ARN (alrededor de 3,4–3,9 Å), estos efectos no deseados son muy pequeños —del orden del 5% de la señal. Solo cuando los protones están a menos de unos ~3 Å, como dentro de una única pareja de bases, los artefactos se vuelven significativos, y el estudio establece reglas prácticas para elegir condiciones experimentales que eviten estas trampas.
Un intermedio oculto en el apareamiento de bases del ADN
Con esta imagen más limpia de lo que significan sus señales de RMN, los investigadores revisitan una secuencia modelo de ADN donde la pareja A–T de Watson–Crick–Franklin se sabe que se convierte transitoriamente en una forma Hoogsteen. Trabajos anteriores usando RMN de carbono y nitrógeno sugerían un intercambio simple de dos estados. Las medidas de R1ρ de protones revelan ahora algo más complejo: un tercer estado excitado de baja población (ES2) que se sitúa entre los arreglos habitual y Hoogsteen. Al seguir los desplazamientos químicos y las tasas de intercambio de varios átomos de hidrógeno dentro y alrededor de la pareja clave, el equipo encuentra que ES2 es una característica consistente de pares A–T vecinos y conecta tanto con el estado fundamental como con el estado Hoogsteen, formando una red de tres estados en lugar de un simple interruptor binario.
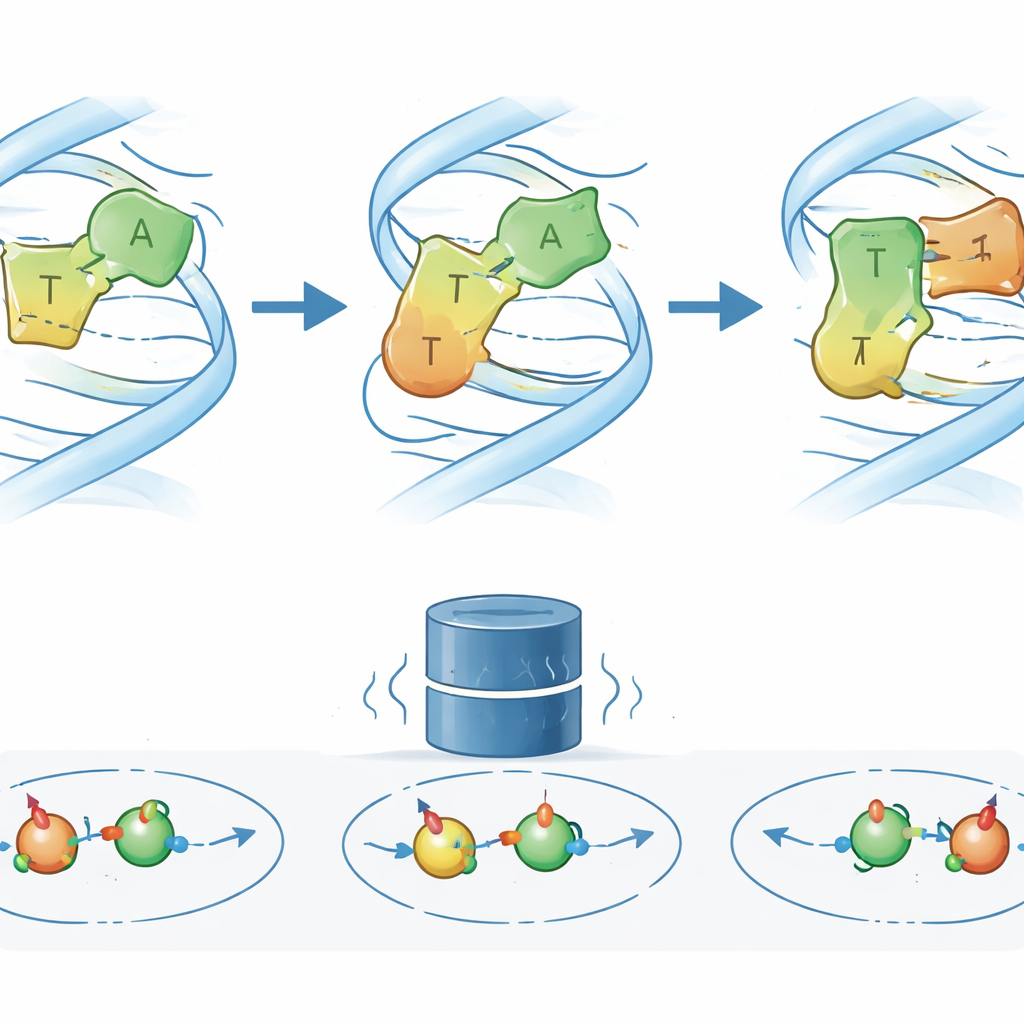
Sondeando el nuevo estado con bases diseñadas y un fármaco contra el cáncer
Para entender cómo podría ser ES2, los autores modificaron químicamente una de las bases de la pareja A–T clave, eliminando o cambiando átomos específicos implicados en el enlace de hidrógeno. Estas bases “diseñadas” debilitan selectivamente o favorecen distintos modos de apareamiento. Los cambios resultantes en las señales de RMN y en las tasas de intercambio muestran que cuando se elimina un grupo amino particular, el ADN visita ES2 con mucha más frecuencia, lo que sugiere que dicho grupo normalmente estabiliza el apareamiento en el estado fundamental y ralentiza el acceso al intermedio. Simulaciones moleculares avanzadas, combinadas con predicciones cuánticas de los desplazamientos de RMN, apuntan entonces a un modelo estructural plausible: en ES2, la adenina se reorienta parcialmente de modo que su grupo amino forma un enlace de hidrógeno temporal con un átomo de oxígeno alternativo en la timina, aflojando la red de enlaces original en el camino hacia una geometría similar a Hoogsteen. De forma llamativa, cuando se añade el fármaco anticancerígeno actinomicina D, la “huella” de RMN de ES2 se vuelve más prominente, lo que indica que el fármaco estabiliza o enriquece este intermedio al unirse a lo largo del ADN.
Qué significa esto para la biología del ADN y la acción de los fármacos
Al cuantificar cuándo y cómo pueden confiarse las medidas R1ρ basadas en protones, este trabajo convierte un experimento especializado de RMN en una herramienta más universal para observar movimientos rápidos y raros en ADN y ARN. Usando esa lente mejorada, los autores descubren un intermedio oculto y estabilizado por un fármaco en el clásico cambio de la pareja A–T entre las formas normal y Hoogsteen. Para los no especialistas, el mensaje clave es que el ADN no es solo un código estático sino un paisaje cambiante de estados, y algunos medicamentos pueden actuar en parte remodelando ese paisaje —favoreciendo estructuras fugaces particulares que influyen en cómo se lee, daña o repara el ADN.
Cita: Dasgupta, R., Steinmetzger, C., Ilgen, J. et al. 1H R1ρ relaxation identifies a hidden intermediate in DNA base-pairing. Nat Commun 17, 4114 (2026). https://doi.org/10.1038/s41467-026-72559-6
Palabras clave: Dinámica del apareamiento de bases del ADN, Dispersión de relajación por RMN, Parejas de bases Hoogsteen, intermedios conformacionales, actinomicina D