Clear Sky Science · pl
Relaksacja 1H R1ρ identyfikuje ukryty stan pośredni w parowaniu zasad DNA
Dlaczego ukryte ruchy DNA są ważne
DNA jest często przedstawiane jako uporządkowana podwójna helisa z idealnie dopasowanymi parami zasad, jednak w rzeczywistości nieustannie «oddycha» i przechodzi między nieco różnymi kształtami. Te krótkotrwałe, rzadkie konfiguracje mogą wpływać na to, jak DNA jest naprawiane, odczytywane lub ukierunkowywane przez leki. W pracy tej opracowano bardziej niezawodny sposób obserwacji niektórych z tych szybkich zmian kształtu na poziomie atomowym i, wykorzystując tę metodę, odkryto wcześniej niewidoczny stan pośredni w jednym z najważniejszych przełączeń par zasad DNA — pokazując, że nawet klasyczny lek przeciwnowotworowy może przekształcać wewnętrzne ruchy DNA.
Bliższe spojrzenie na subtelne zmiany kształtu DNA
W każdej komórce znane pary A–T i G–C w DNA nie pozostają nieruchome. W skalach czasowych od mikro- do milisekund mogą przechodzić do rzadkich, wyższej energii układów. Jedną z dobrze poznanych alternatyw jest parowanie Hoogsteena, w którym jedna zasada w parze krótkotrwale zmienia orientację. Chociaż takie stany zwykle stanowią poniżej 2% populacji, łączą się z procesami takimi jak naprawa uszkodzeń DNA, błędne włączenie zasad i sposobem, w jaki niektóre białka rozpoznają swoje cele. Ponieważ te ulotne stany są tak krótkotrwałe i nieliczne, są niemal niewidoczne dla standardowych narzędzi strukturalnych, takich jak krystalografia rentgenowska czy kriomikroskopia elektronowa, ale można je badać metodami rezonansu magnetycznego (NMR) wrażliwymi na ruch.
Wyostrzenie narzędzia NMR, aby zobaczyć to, co niewidoczne
Autorzy skupiają się na wyspecjalizowanym podejściu NMR zwanym relaksacją protonową R1ρ, które śledzi, jak jądra wodoru w DNA relaksują się pod stałym polem radiowym «spinlock». Zmiany w szybkości relaksacji przy różnych ustawieniach pola kodują, jak szybko i jak często cząsteczka przeskakuje między różnymi kształtami. Od dawna budziło to jednak obawy, że pobliskie protony mogą «komunikować się» ze sobą przez kros-relaksację, tworząc artefakty imitujące prawdziwą wymianę konformacyjną. Na podstawie szczegółowych symulacji opartych na ustalonych równaniach NMR zespół pokazuje, że dla typowych odległości proton–proton spotykanych między ułożonymi jedna nad drugą parami zasad w DNA i RNA (około 3,4–3,9 Å) te niepożądane efekty są bardzo małe — rzędu około 5% sygnału. Dopiero gdy protony znajdują się bliżej niż około 3 Å, na przykład w obrębie pojedynczej pary zasad, artefakty stają się istotne, a badanie przedstawia praktyczne zasady wyboru ustawień eksperymentalnych, które pozwalają uniknąć tych pułapek.
Ukryty stan pośredni w parowaniu zasad DNA
Uzbrojeni w jaśniejszy obraz tego, co oznaczają ich sygnały NMR, badacze odświeżają analizę modelowego odcinka DNA, w którym standardowa para A–T w układzie Watson–Crick–Franklin jest znana z przejściowego przełączania się do formy Hoogsteena. Wcześniejsze badania wykorzystujące NMR węgla i azotu sugerowały prosty przełącznik dwustanowy. Pomiary protonowego R1ρ ujawniają teraz coś bardziej złożonego: trzeci, niskoobszerny stan wzbudzony (ES2), który pośredniczy między stanem zwykłym a Hoogsteenem. Śledząc przesunięcia chemiczne i szybkości wymiany kilku atomów wodoru w i wokół kluczowej pary zasad, zespół stwierdza, że ES2 jest stałym elementem sąsiednich par A–T i łączy zarówno stan podstawowy, jak i stan Hoogsteena, tworząc sieć trzech stanów zamiast prostego przełącznika włącz/wyłącz.
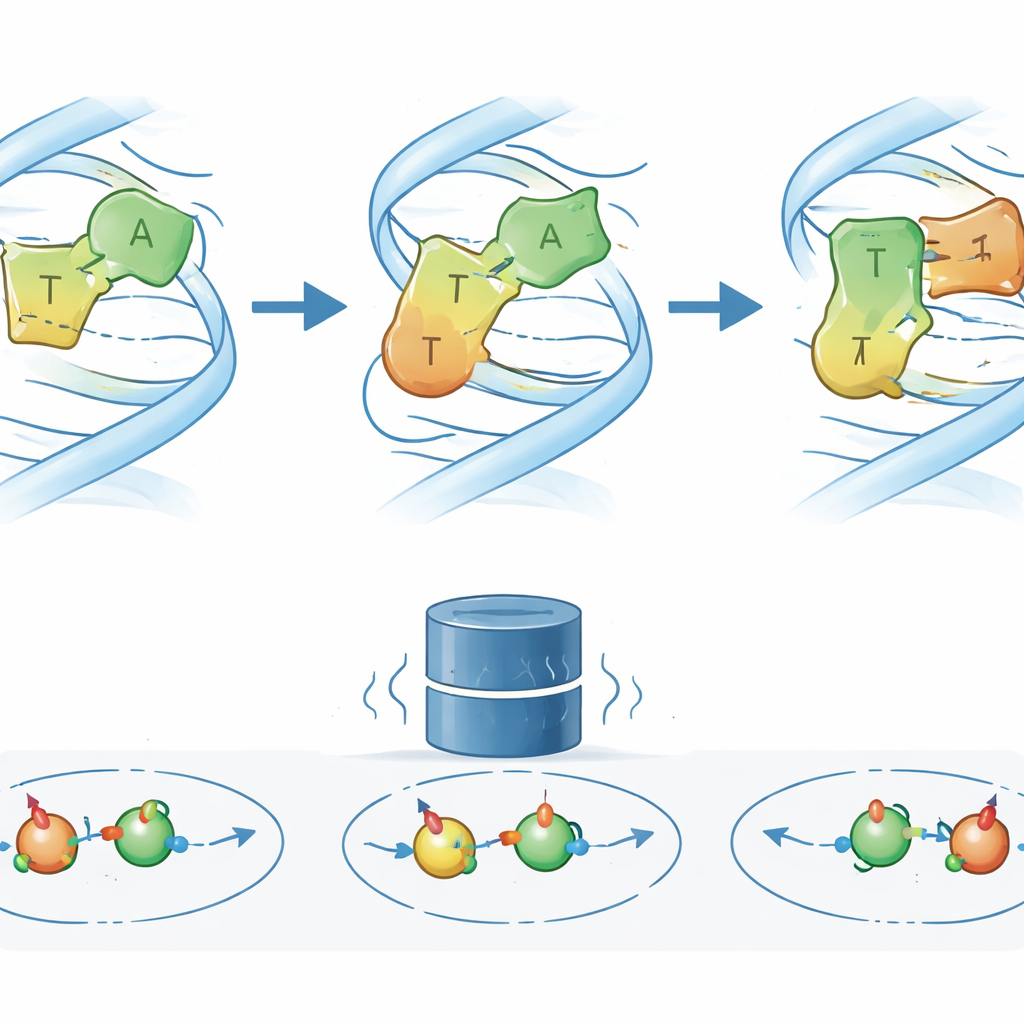
Badanie nowego stanu za pomocą zaprojektowanych zasad i leku przeciwnowotworowego
Aby zrozumieć, jak może wyglądać ES2, autorzy chemicznie zmodyfikowali jedną z zasad w kluczowej parze A–T, usuwając lub zmieniając konkretne atomy zaangażowane w wiązania wodorowe. Te «zaprojektowane» zasady selektywnie osłabiają lub sprzyjają różnym trybom parowania. Wynikające zmiany w sygnałach NMR i szybkościach wymiany pokazują, że po usunięciu określonej grupy aminowej DNA częściej odwiedza stan ES2, co sugeruje, że ta grupa zwykle stabilizuje parowanie w stanie podstawowym i spowalnia dostęp do stanu pośredniego. Zaawansowane symulacje molekularne, połączone z kwantowymi przewidywaniami przesunięć NMR, wskazują na prawdopodobny model strukturalny: w ES2 zasada adeniny częściowo zmienia orientację tak, że jej grupa aminowa tworzy tymczasowe wiązanie wodorowe z alternatywnym tlenem na tyminie, rozluźniając oryginalną sieć wiązań w drodze ku geometrii przypominającej Hoogsteena. Co znamienne, po dodaniu leku przeciwnowotworowego aktynomycyny D «odcisk palca» NMR dla ES2 staje się bardziej wyraźny, co wskazuje, że lek stabilizuje lub wzbogaca ten stan pośredni w czasie wiązania z DNA.
Co to znaczy dla biologii DNA i działania leków
Poprzez ilościowe określenie, kiedy i w jakim stopniu można ufać pomiarom protonowego R1ρ, praca ta przekształca wyspecjalizowany eksperyment NMR w narzędzie bardziej powszechnie użyteczne do obserwowania szybkich, rzadkich ruchów w DNA i RNA. Przy użyciu tej ulepszonej perspektywy autorzy odkrywają stabilizowany przez lek, wcześniej ukryty stan pośredni w klasycznym przełączniku pary A–T między formami zwykłą i Hoogsteena. Dla osób niebędących specjalistami kluczowy przekaz jest taki: DNA nie jest jedynie statycznym kodem, lecz przesuwającym się krajobrazem stanów, i niektóre leki mogą działać częściowo przez przekształcanie tego krajobrazu — faworyzując określone, ulotne struktury, które wpływają na to, jak DNA jest czytane, uszkadzane lub naprawiane.
Cytowanie: Dasgupta, R., Steinmetzger, C., Ilgen, J. et al. 1H R1ρ relaxation identifies a hidden intermediate in DNA base-pairing. Nat Commun 17, 4114 (2026). https://doi.org/10.1038/s41467-026-72559-6
Słowa kluczowe: dynamika par zasad DNA, dyspersja relaksacji NMR, pary Hoogsteena, konformacyjne stany pośrednie, aktynomycyna D