Clear Sky Science · fr
La relaxation 1H R1ρ révèle un intermédiaire caché dans l'appariement des bases de l'ADN
Pourquoi les mouvements discrets de l'ADN comptent
L'ADN est souvent représenté comme une double hélice bien ordonnée avec des paires de bases parfaitement appariées, mais en réalité il respire en permanence et oscille entre des conformations légèrement différentes. Ces formes brèves et rares peuvent influencer la façon dont l'ADN est réparé, lu ou ciblé par des médicaments. Cette étude met au point une méthode plus fiable pour observer certains de ces changements rapides de conformation au niveau atomique et, en l'appliquant, révèle un état intermédiaire auparavant caché dans l'un des commutateurs de paires de bases les plus importants de l'ADN — montrant que même un médicament anticancéreux classique peut remodeler le mouvement interne de l'ADN.
Un regard détaillé sur les faibles variations de conformation de l'ADN
À l'intérieur de chaque cellule, les paires A–T et G–C familières de l'ADN ne restent pas figées. Sur des échelles de temps allant de la microseconde à la milliseconde, elles peuvent visiter des arrangements rares et d'énergie plus élevée. Une alternative bien connue est l'appariement de type Hoogsteen, où l'une des bases du couple bascule brièvement d'orientation. Bien que ces états représentent typiquement moins de 2 % de la population, ils sont liés à des processus tels que la réparation des dommages de l'ADN, l'incorporation incorrecte de bases et la reconnaissance des cibles par certaines protéines. Parce que ces états fugitifs sont si éphémères et rares, ils échappent presque aux outils structuraux classiques comme la cristallographie aux rayons X ou la cryo‑microscopie électronique, mais peuvent être sondés par des méthodes de résonance magnétique nucléaire (RMN) sensibles au mouvement.
Aiguiser un outil de RMN pour voir l'invisible
Les auteurs se concentrent sur une approche RMN spécialisée appelée dispersion de relaxation protonique R1ρ, qui suit la façon dont les noyaux d'hydrogène de l'ADN se relâchent sous un champ de « spinlock » radiofréquence continu. Les variations du taux de relaxation en fonction du champ renseignent sur la vitesse et la fréquence des transitions entre conformations. Une inquiétude de longue date est toutefois que des protons proches puissent « communiquer » entre eux via la cross‑relaxation, créant des artefacts qui imitent un échange conformationnel réel. À l'aide de simulations détaillées basées sur des équations RMN établies, l'équipe montre que pour les séparations proton–proton typiques observées entre bases empilées dans l'ADN et l'ARN (environ 3,4–3,9 Å), ces effets indésirables sont très faibles — de l'ordre de 5 % du signal. Ce n'est que lorsque les protons sont plus proches d'environ 3 Å, comme à l'intérieur d'une même paire de bases, que les artefacts deviennent significatifs, et l'étude expose des règles pratiques pour choisir des paramètres expérimentaux évitant ces écueils.
Un intermédiaire caché dans l'appariement des bases de l'ADN
Fort d'une interprétation plus nette de leurs signaux RMN, les chercheurs revisitent une séquence d'ADN modèle où la paire A–T de Watson–Crick–Franklin est connue pour se convertir transitoirement en forme Hoogsteen. Des travaux antérieurs utilisant la RMN du carbone et de l'azote suggéraient un simple basculement à deux états. Les mesures protoniques R1ρ révèlent maintenant quelque chose de plus complexe : un troisième état excité à faible population (ES2) qui se situe entre les conformations usuelle et Hoogsteen. En suivant les déplacements chimiques et les taux d'échange de plusieurs atomes d'hydrogène dans et autour de la paire clé, l'équipe constate qu'ES2 est une caractéristique récurrente des paires A–T voisines et se connecte à la fois à l'état fondamental et à l'état Hoogsteen, formant un réseau à trois états plutôt qu'un simple interrupteur marche/arrêt.
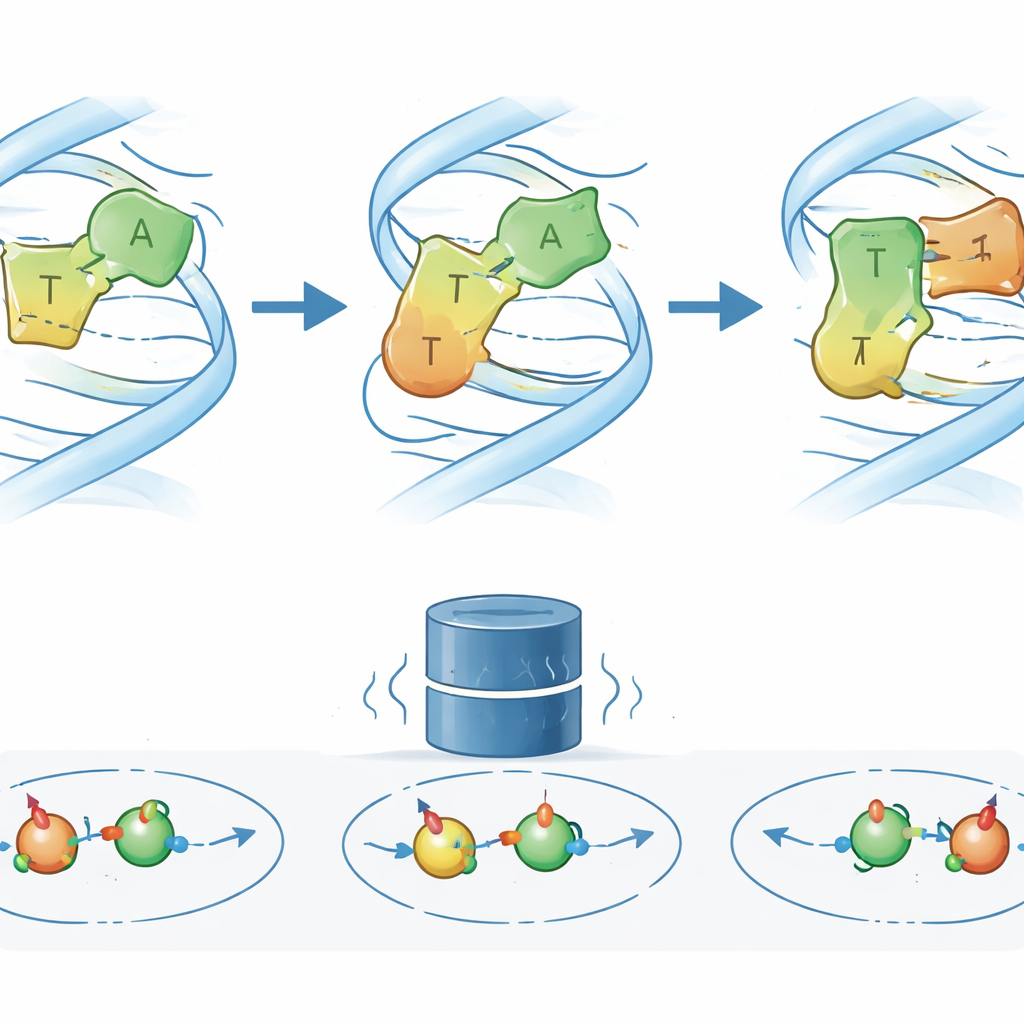
Explorer le nouvel état avec des bases conçues et un médicament anticancéreux
Pour cerner l'aspect possible d'ES2, les auteurs ont modifié chimiquement l'une des bases partenaires dans la paire A–T clé, en retirant ou en changeant des atomes spécifiques impliqués dans les liaisons hydrogène. Ces bases « sur mesure » affaiblissent ou favorisent sélectivement différents modes d'appariement. Les changements résultants dans les signaux RMN et les taux d'échange montrent que lorsque qu'un groupe amino particulier est supprimé, l'ADN échantillonne ES2 beaucoup plus souvent, ce qui implique que ce groupe stabilise normalement l'appariement en état fondamental et ralentit l'accès à l'intermédiaire. Des simulations moléculaires avancées, combinées à des prédictions quantiques des déplacements RMN, convergent vers un modèle structurel plausible : dans ES2, la base adénine se réoriente partiellement de sorte que son groupe amino forme une liaison hydrogène temporaire vers un atome d'oxygène alternatif de la thymine, relâchant le réseau de liaisons d'origine en direction d'une géométrie de type Hoogsteen. Fait frappant, lorsque l'antagoniste anticancéreux actinomycine D est ajouté, l'« empreinte » RMN d'ES2 devient plus marquée, indiquant que le médicament stabilise ou enrichit cet intermédiaire lorsqu'il se lie le long de l'ADN.
Ce que cela implique pour la biologie de l'ADN et l'action des médicaments
En quantifiant quand et comment les mesures protoniques R1ρ peuvent être considérées comme fiables, ce travail transforme une expérience RMN spécialisée en un outil plus largement utilisable pour observer des mouvements rapides et rares dans l'ADN et l'ARN. Grâce à cette loupe améliorée, les auteurs découvrent un intermédiaire précédemment caché et stabilisé par un médicament dans le commutateur classique A–T entre formes normale et Hoogsteen. Pour les non‑spécialistes, le message clé est que l'ADN n'est pas seulement un code statique mais un paysage changeant d'états, et que certains médicaments peuvent agir en partie en remodelant ce paysage — favorisant des structures fugitives particulières qui influencent la lecture, l'endommagement ou la réparation de l'ADN.
Citation: Dasgupta, R., Steinmetzger, C., Ilgen, J. et al. 1H R1ρ relaxation identifies a hidden intermediate in DNA base-pairing. Nat Commun 17, 4114 (2026). https://doi.org/10.1038/s41467-026-72559-6
Mots-clés: Dynamique des appariements de l'ADN, Dispersion de relaxation RMN, Paires de bases Hoogsteen, intermédiaires conformationnels, actinomycine D