Clear Sky Science · nl
Metagenomische analyse van antimicrobiële resistentie, virulentie en mobiele genetische elementen in het darmmicrobioom van Caprinae-soorten
Waarom de darmen van geiten en schapen belangrijk zijn voor onze gezondheid
De bacteriën in de darmen van landbouwdieren doen meer dan alleen helpen bij het verteren van gras. Ze kunnen ook fungeren als een verborgen voorraad van genen die bacteriën moeilijker te doden maken met antibiotica en die mogelijk schadelijker zijn voor mensen. Deze studie duikt diep in de darmmicroben van geiten, schapen en hun verwanten om te achterhalen hoeveel van zulke genen daar aanwezig zijn, hoe ze georganiseerd zijn en hoe gemakkelijk ze tussen soorten kunnen bewegen, inclusief naar mensen.
Inzicht in de darmgemeenschap
De onderzoekers combineerden DNA-gegevens van 779 darmsamples afkomstig van geiten, schapen en enkele wilde Caprinae-soorten. In plaats van microben te kweken in het laboratorium, gebruikten ze krachtige computers om meer dan 17.000 conceptgenomen rechtstreeks uit het gemengde DNA in de monsters samen te stellen. Deze genomen onthulden een enorme verscheidenheid aan microben, waarvan vele nog nooit formeel beschreven waren. Ondanks die diversiteit deelden geiten en schapen een gemeenschappelijke kern van darmbewoners, gedomineerd door bacteriën die floreren in herbivoren en helpen bij het afbreken van plantaardig voedsel.
Verborgen voorraden van resistentie en schadeveroorzakende factoren
Binnen deze microbiële genomen zocht het team naar twee verontrustende soorten genen: genen die bacteriën beschermen tegen antibiotica en genen die hen helpen gastheren te infecteren of schade toe te brengen. Ze vonden 2.440 antibioticaresistentiegenen verspreid over ongeveer één op de twaalf geassembleerde genomen, met bijzonder sterke verdedigingen tegen tetracycline en tegen meerdere antibioticaklassen tegelijk. Ze ontdekten ook meer dan 5.400 virulentiegerelateerde genen in ongeveer één op de zes genomen. Sommige stammen van Escherichia coli en Pseudomonas aeruginosa sprongen eruit als zware “genezamelaars”, waarbij elk tientallen resistentie- en virulentiteitskenmerken in één genoom droeg.
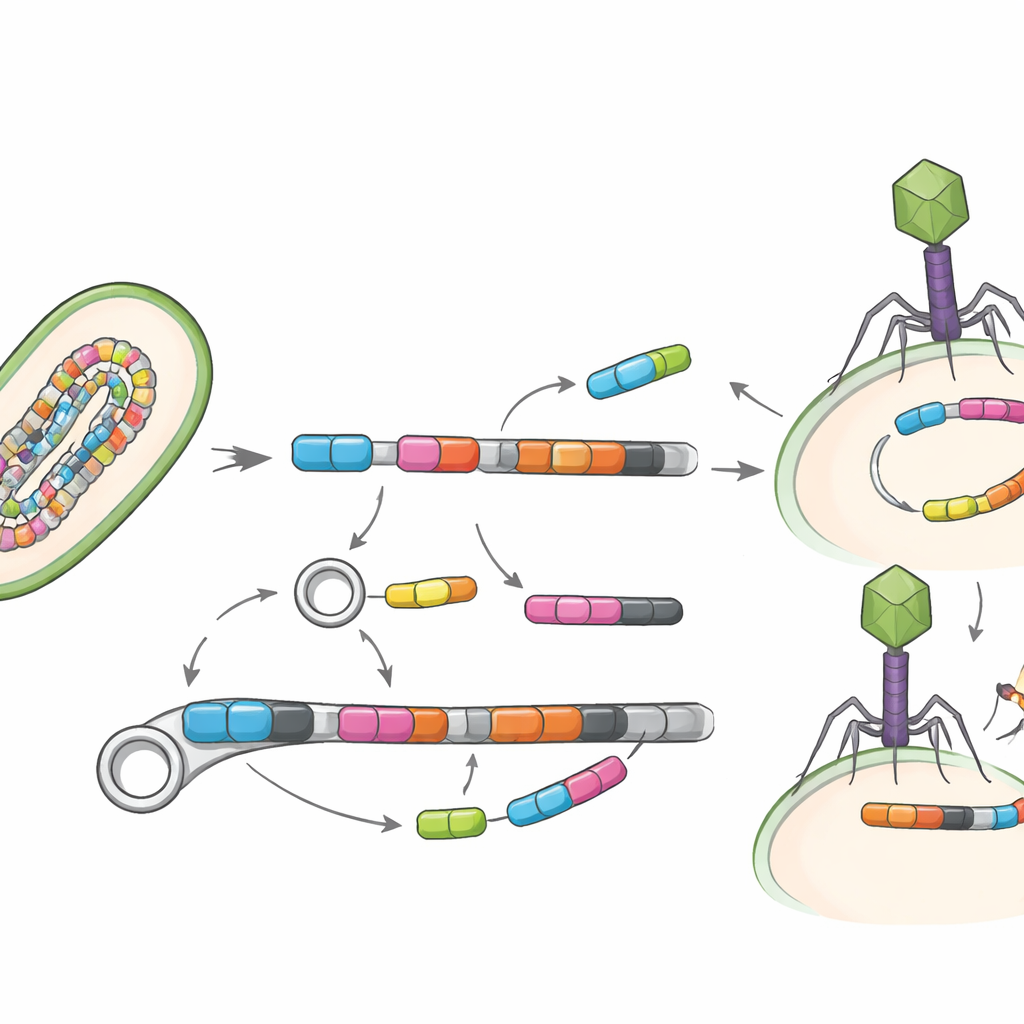
Genen in beweging
Een cruciale vraag is niet alleen welke genen aanwezig zijn, maar hoe gemakkelijk ze kunnen bewegen. De studie zocht daarom naar mobiele genetische elementen — DNA-segmenten zoals transposases en andere “springende” stukken die genen tussen bacteriën kunnen verplaatsen — en naar virussen die bacteriën infecteren, bekend als bacteriofagen. Slechts een klein deel van de genomen droeg duidelijk deze mobiele elementen, waarschijnlijk omdat zulke regio’s moeilijk samen te stellen zijn, maar waar ze wel opdoken stonden ze vaak direct naast resistentiegenen. Het team identificeerde 19 directe koppelingen van mobiele elementen met resistentiegenen, en vond zelfs drie resistentiegenen ingebed in virale genomen, wat suggereert dat zowel DNA-shuttles als darmvirussen kunnen bijdragen aan de verspreiding van deze eigenschappen.
Verbindingen tussen vee en mensen
Om te begrijpen wat dit buiten de stal betekent, vergeleken de onderzoekers resistentiegenen in Caprinae-darmmicroben met die gevonden in duizenden menselijke darmegenomen. Ze ontdekten 184 typen resistentiegenen die door dieren en mensen werden gedeeld, waaronder genen gekoppeld aan antibiotica die in ziekenhuizen als behandeling van laatste redmiddel worden beschouwd, zoals tigecycline en vancomycine. Hoewel deze studie niet bewijst dat genen rechtstreeks van geiten en schapen naar menselijke pathogenen bewegen, toont de overlap aan dat beide gastheren putten uit een gemeenschappelijke voorraad van resistentie. Aangezien mensen, vee en het milieu vaak nauw met elkaar vermengen — via mest, bodem, water en voedsel — vormen deze gedeelde genen mogelijke routes voor verspreiding tussen soorten.
Wat dit betekent voor het dagelijks leven
In zijn geheel schetst het werk het darmmicrobioom van Caprinae als een belangrijke, en tot nu toe ondergewaardeerde, reservoir van antibioticaresistentie en virulentiepotentieel. Het laat zien dat deze genen zich opstapelen in bepaalde bacteriestammen, vaak gekoppeld zijn aan mobiel DNA en zelfs door virussen kunnen worden gedragen, factoren die hun persistentie en beweging tussen gastheren kunnen vergemakkelijken. Voor de niet-specialist is de conclusie helder: hoe we omgaan met antibiotica en veehouderij beïnvloedt niet alleen boerderijdieren; het vormt een gedeeld genetisch landschap dat de toekomstige effectiviteit van levensreddende medicijnen kan beïnvloeden. De auteurs pleiten ervoor om geiten, schapen en verwante dieren op te nemen in geïntegreerde “One Health”-surveillance die gelijktijdig menselijke, dierlijke en omgevingsbronnen van antimicrobiële resistentie in beschouwing neemt.
Bronvermelding: Su, JW., Elsheikha, H.M., Guo, L. et al. Metagenomic analysis of antimicrobial resistance, virulence, and mobile genetic elements in the gut microbiota of Caprinae species. Commun Biol 9, 456 (2026). https://doi.org/10.1038/s42003-026-09726-4
Trefwoorden: antimicrobiële resistentie, darmmicrobioom, vee, mobiele genetische elementen, bacteriofagen