Clear Sky Science · it
Analisi metagenomica della resistenza antimicrobica, della virulenza e degli elementi genetici mobili nel microbiota intestinale delle specie Caprinae
Perché gli intestini di capre e pecore sono importanti per la nostra salute
I batteri che vivono nell’intestino degli animali da allevamento fanno più che aiutarli a digerire l’erba. Possono anche costituire un serbatoio nascosto di geni che rendono i batteri più difficili da eliminare con gli antibiotici e potenzialmente più dannosi per le persone. Questo studio esplora in profondità i microbi intestinali di capre, pecore e loro parenti per valutare quanti di questi geni sono presenti, come sono organizzati e quanto facilmente potrebbero trasferirsi tra specie, compresa quella umana.
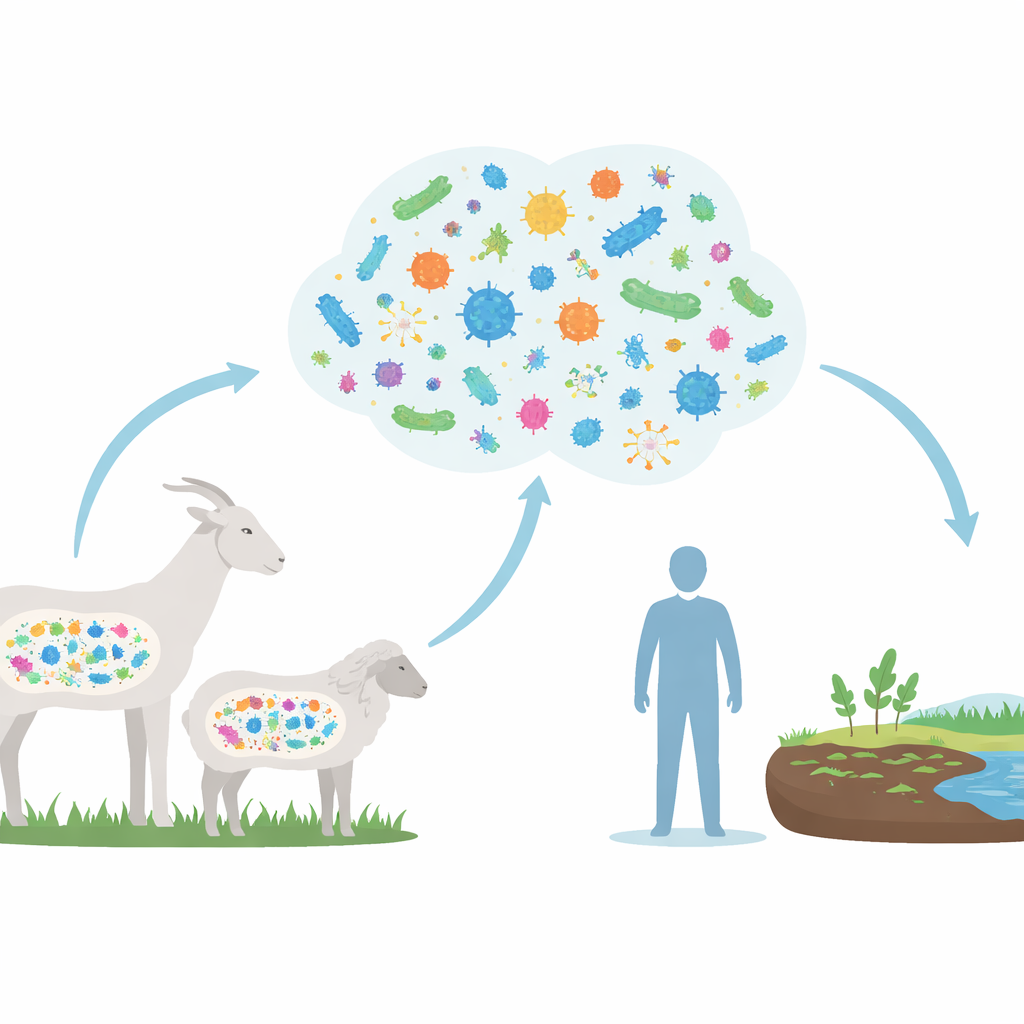
Uno sguardo alla comunità intestinale
I ricercatori hanno combinato dati di DNA provenienti da 779 campioni intestinali prelevati da capre, pecore e alcune specie selvatiche di Caprinae. Invece di coltivare i microbi in laboratorio, hanno usato potenti computer per ricostruire più di 17.000 genomi di bozze direttamente dal DNA misto dei campioni. Questi genomi hanno rivelato un’enorme varietà di microbi, molti dei quali non descritti formalmente prima d’ora. Nonostante questa diversità, capre e pecore condividono un nucleo comune di residenti intestinali, dominato da batteri tipici degli erbivori che li aiutano a degradare diete ricche di vegetali.
Riserve nascoste di resistenza e fattori di danno
All’interno di questi genomi microbici, il gruppo ha cercato due categorie di geni preoccupanti: quelli che proteggono i batteri dagli antibiotici e quelli che li aiutano a infettare o danneggiare gli ospiti. Hanno trovato 2.440 geni di resistenza agli antibiotici distribuiti in circa uno su dodici dei genomi assemblati, con difese particolarmente forti contro le tetracicline e contro più classi di antibiotici contemporaneamente. Hanno anche individuato oltre 5.400 geni correlati alla virulenza in circa uno su sei genomi. Alcuni ceppi di Escherichia coli e Pseudomonas aeruginosa si sono distinti come veri “accumulatori” di geni, ciascuno contenente dozzine di tratti di resistenza e virulenza concentrati in singoli genomi.
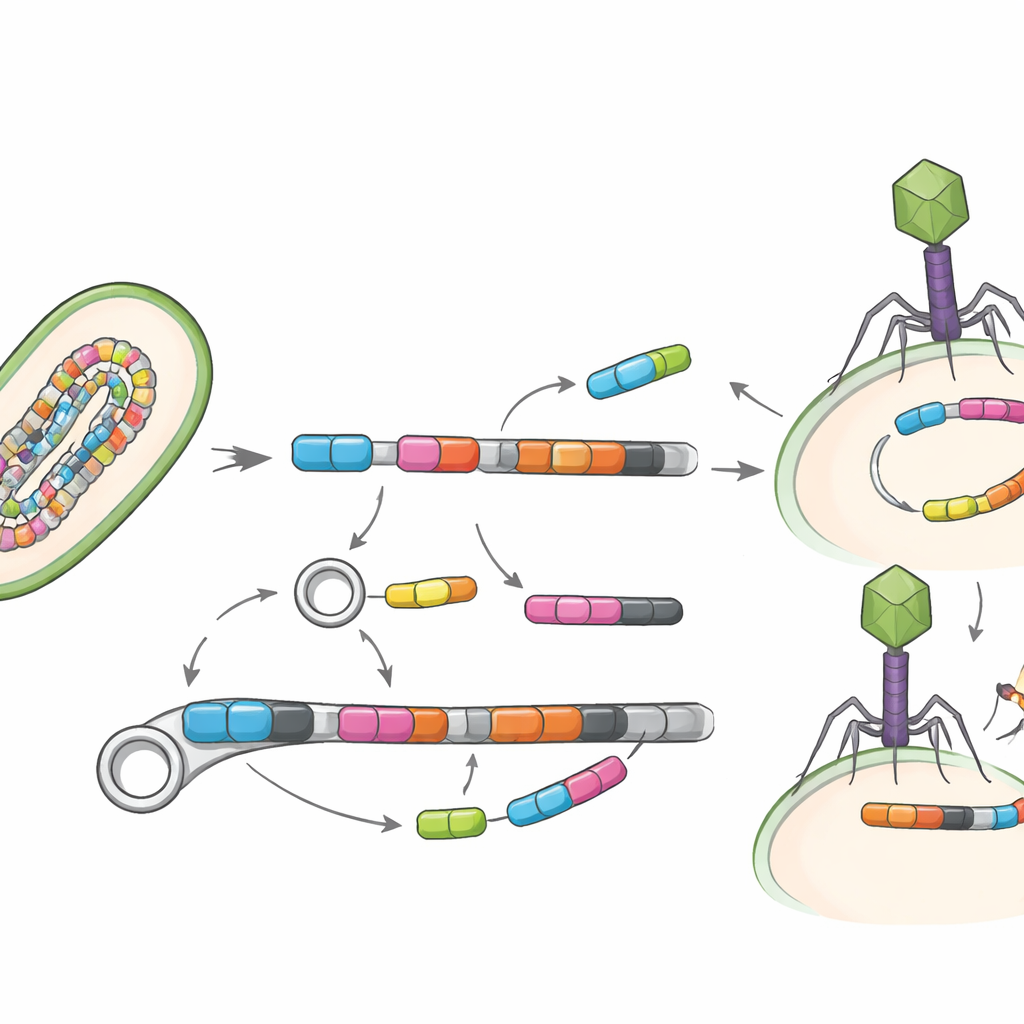
Geni in movimento
Una domanda chiave non è solo quali geni siano presenti, ma quanto facilmente possano spostarsi. Lo studio ha quindi cercato elementi genetici mobili—segmenti di DNA come trasposasi e altri pezzi “saltanti” che possono trasferire geni tra batteri—e virus che infettano i batteri, noti come batteriofagi. Solo una piccola frazione dei genomi mostrava chiaramente questi elementi mobili, probabilmente perché tali regioni sono difficili da ricostruire, ma dove comparivano spesso si trovavano proprio accanto ai geni di resistenza. Il gruppo ha identificato 19 accoppiamenti diretti di elementi mobili con geni di resistenza e ha persino trovato tre geni di resistenza integrati in genomi virali, suggerendo che sia i vettori di DNA sia i virus intestinali potrebbero contribuire alla diffusione di questi tratti.
Connessioni tra animali da allevamento e persone
Per comprendere le implicazioni oltre la stalla, i ricercatori hanno confrontato i geni di resistenza nei microbi intestinali delle Caprinae con quelli trovati in migliaia di genomi intestinali umani. Hanno scoperto 184 tipi di geni di resistenza condivisi tra animali e persone, inclusi quelli associati ad antibiotici considerati trattamenti di ultima istanza negli ospedali, come tigeciclina e vancomicina. Sebbene questo studio non dimostri che i geni si stiano trasferendo direttamente da capre e pecore ai patogeni umani, la sovrapposizione mostra che entrambi gli ospiti attingono da un pool comune di resistenza. Considerando che esseri umani, animali da allevamento e ambiente spesso interagiscono strettamente—tramite letame, suolo, acqua e alimenti—questi geni condivisi rappresentano potenziali vie di diffusione interspecie.
Cosa significa per la vita quotidiana
Nel complesso, il lavoro dipinge i microbi intestinali delle Caprinae come un serbatoio importante e finora sottovalutato di resistenza agli antibiotici e potenziale di virulenza. Mostra che questi geni si raggruppano in particolari ceppi batterici, sono spesso associati a DNA mobile e possono perfino essere trasportati da virus, fattori che ne facilitano la persistenza e la circolazione tra ospiti. Per il lettore non specialistico, il messaggio è chiaro: come gestiamo gli antibiotici e gli allevamenti non riguarda solo gli animali da fattoria; plasma un paesaggio genetico condiviso che può influenzare l’efficacia futura di farmaci salvavita. Gli autori sostengono che capre, pecore e animali correlati dovrebbero essere inclusi in sforzi di sorveglianza “One Health” integrati che considerino congiuntamente le fonti umane, animali e ambientali della resistenza antimicrobica.
Citazione: Su, JW., Elsheikha, H.M., Guo, L. et al. Metagenomic analysis of antimicrobial resistance, virulence, and mobile genetic elements in the gut microbiota of Caprinae species. Commun Biol 9, 456 (2026). https://doi.org/10.1038/s42003-026-09726-4
Parole chiave: resistenza agli antimicrobici, microbioma intestinale, animali da allevamento, elementi genetici mobili, batteriofagi