Clear Sky Science · es
Análisis metagenómico de la resistencia a los antimicrobianos, la virulencia y los elementos genéticos móviles en la microbiota intestinal de especies de Caprinae
Por qué importan los intestinos de cabras y ovejas para nuestra salud
Las bacterias que habitan los intestinos de los animales de granja hacen más que ayudarles a digerir el pasto. También pueden actuar como un almacén oculto de genes que dificultan la eliminación de bacterias con antibióticos y que, potencialmente, las hacen más dañinas para las personas. Este estudio se adentra en los microbios intestinales de cabras, ovejas y sus parientes para ver cuántos de esos genes existen allí, cómo están organizados y qué facilidad tendrían para moverse entre especies, incluso hacia los humanos.
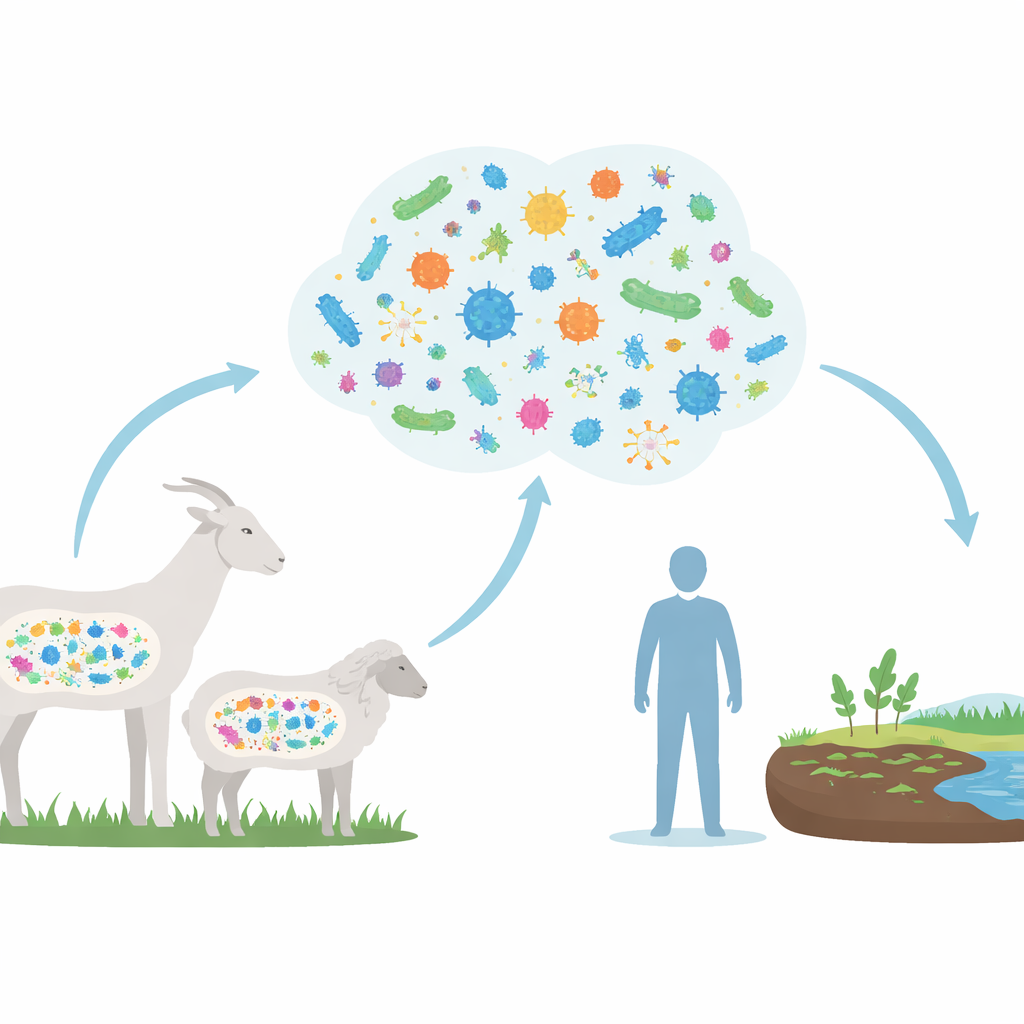
Explorando la comunidad intestinal
Los investigadores combinaron datos de ADN de 779 muestras intestinales tomadas de cabras, ovejas y algunas especies silvestres de Caprinae. En lugar de cultivar microbios en el laboratorio, emplearon potentes ordenadores para ensamblar más de 17 000 genomas provisionales directamente a partir del ADN mixto de las muestras. Esos genomas revelaron una enorme variedad de microbios, muchos de los cuales no han sido descritos formalmente hasta ahora. A pesar de esa diversidad, cabras y ovejas compartían un núcleo común de habitantes intestinales, dominado por bacterias que prosperan en herbívoros y les ayudan a descomponer dietas ricas en plantas.
Reservorios ocultos de resistencia y daño
Dentro de estos genomas microbianos, el equipo buscó dos tipos de genes preocupantes: los que protegen a las bacterias frente a los antibióticos y los que las ayudan a infectar o dañar a los hospedadores. Encontraron 2 440 genes de resistencia a antibióticos repartidos en aproximadamente uno de cada doce de los genomas ensamblados, con defensas especialmente fuertes contra la tetraciclina y contra múltiples tipos de antibióticos a la vez. También detectaron más de 5 400 genes relacionados con la virulencia en cerca de uno de cada seis genomas. Algunas cepas de Escherichia coli y Pseudomonas aeruginosa destacaron como importantes “acumuladores de genes”, cada una portando docenas de rasgos de resistencia y virulencia agrupados en genomas únicos.
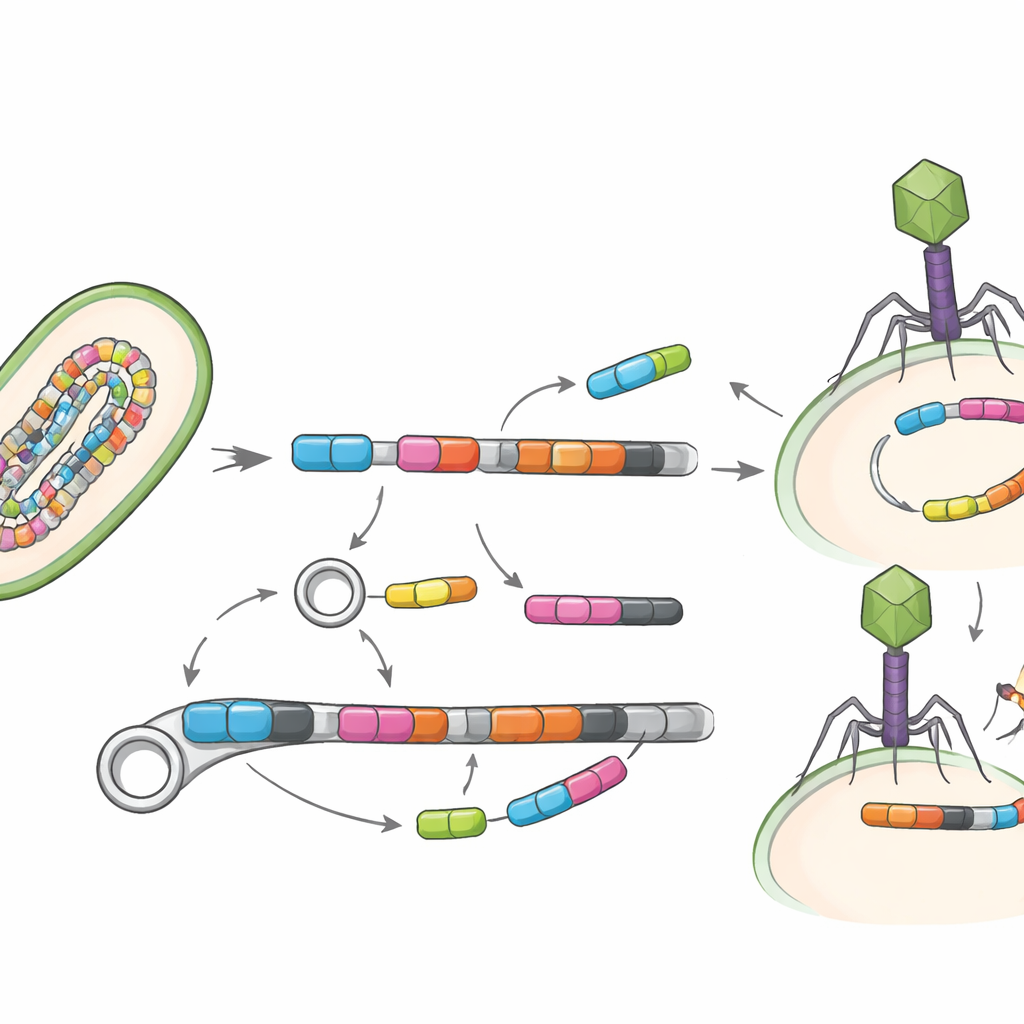
Genes en movimiento
Una cuestión clave no es solo qué genes están presentes, sino con qué facilidad pueden moverse. Por eso el estudio buscó elementos genéticos móviles —segmentos de ADN como transposasas y otras piezas “saltantes” que pueden transportar genes entre bacterias— y virus que infectan bacterias, conocidos como bacteriófagos. Solo una pequeña fracción de los genomas claramente llevaba estos elementos móviles, probablemente porque esas regiones son difíciles de reconstruir, pero donde sí aparecían, a menudo se ubicaban justo al lado de genes de resistencia. El equipo identificó 19 emparejamientos directos de elementos móviles con genes de resistencia e incluso halló tres genes de resistencia integrados en genomas virales, lo que sugiere que tanto los transportadores de ADN como los virus intestinales podrían ayudar a difundir estos rasgos.
Vínculos entre la ganadería y las personas
Para entender lo que esto significa más allá del establo, los investigadores compararon los genes de resistencia en los microbios intestinales de Caprinae con los hallados en miles de genomas intestinales humanos. Descubrieron 184 tipos de genes de resistencia compartidos entre animales y personas, incluidos algunos asociados a antibióticos considerados de último recurso en hospitales, como la tigeciclina y la vancomicina. Aunque este estudio no prueba que los genes se estén moviendo directamente de cabras y ovejas a patógenos humanos, la superposición muestra que ambos hospedadores extraen de un reservorio común de resistencia. Dado que humanos, ganado y el medio ambiente suelen mezclarse estrechamente —a través del estiércol, el suelo, el agua y los alimentos—, estos genes compartidos representan posibles vías de diseminación entre especies.
Qué implica esto para la vida cotidiana
En conjunto, el trabajo sitúa a los microbios intestinales de las Caprinae como un reservorio importante y, hasta ahora, poco valorado de resistencia a antibióticos y potencial de virulencia. Muestra que estos genes se agrupan en ciertas cepas bacterianas, que con frecuencia están vinculados a ADN móvil y que incluso pueden ser transportados por virus, factores que favorecen su persistencia y su transferencia entre hospedadores. Para el lector general, la conclusión es clara: la gestión de antibióticos y del ganado no solo afecta a los animales de granja; configura un panorama genético compartido que puede influir en la eficacia futura de fármacos vitales. Los autores sostienen que cabras, ovejas y animales relacionados deberían incluirse en los esfuerzos integrados de vigilancia “One Health” que consideren de forma conjunta las fuentes humanas, animales y ambientales de resistencia a los antimicrobianos.
Cita: Su, JW., Elsheikha, H.M., Guo, L. et al. Metagenomic analysis of antimicrobial resistance, virulence, and mobile genetic elements in the gut microbiota of Caprinae species. Commun Biol 9, 456 (2026). https://doi.org/10.1038/s42003-026-09726-4
Palabras clave: resistencia a los antimicrobianos, microbioma intestinal, ganadería, elementos genéticos móviles, bacteriófagos