Clear Sky Science · de
Metagenomische Analyse von antimikrobieller Resistenz, Virulenz und mobilen genetischen Elementen im Darmmikrobiom von Caprinae-Arten
Warum Ziegen- und Schafdärme für unsere Gesundheit wichtig sind
Die Bakterien im Darm von Nutztieren tun mehr, als ihnen nur beim Verdauen von Gras zu helfen. Sie können auch als verborgener Vorrat für Gene dienen, die Bakterien gegen Antibiotika widerstandsfähiger und potenziell für Menschen schädlicher machen. Diese Studie geht den Darmmikroben von Ziegen, Schafen und nahen Verwandten tiefgehend nach, um zu ermitteln, wie viele solcher Gene dort lauern, wie sie organisiert sind und wie leicht sie zwischen Arten — einschließlich des Menschen — übertragen werden könnten.
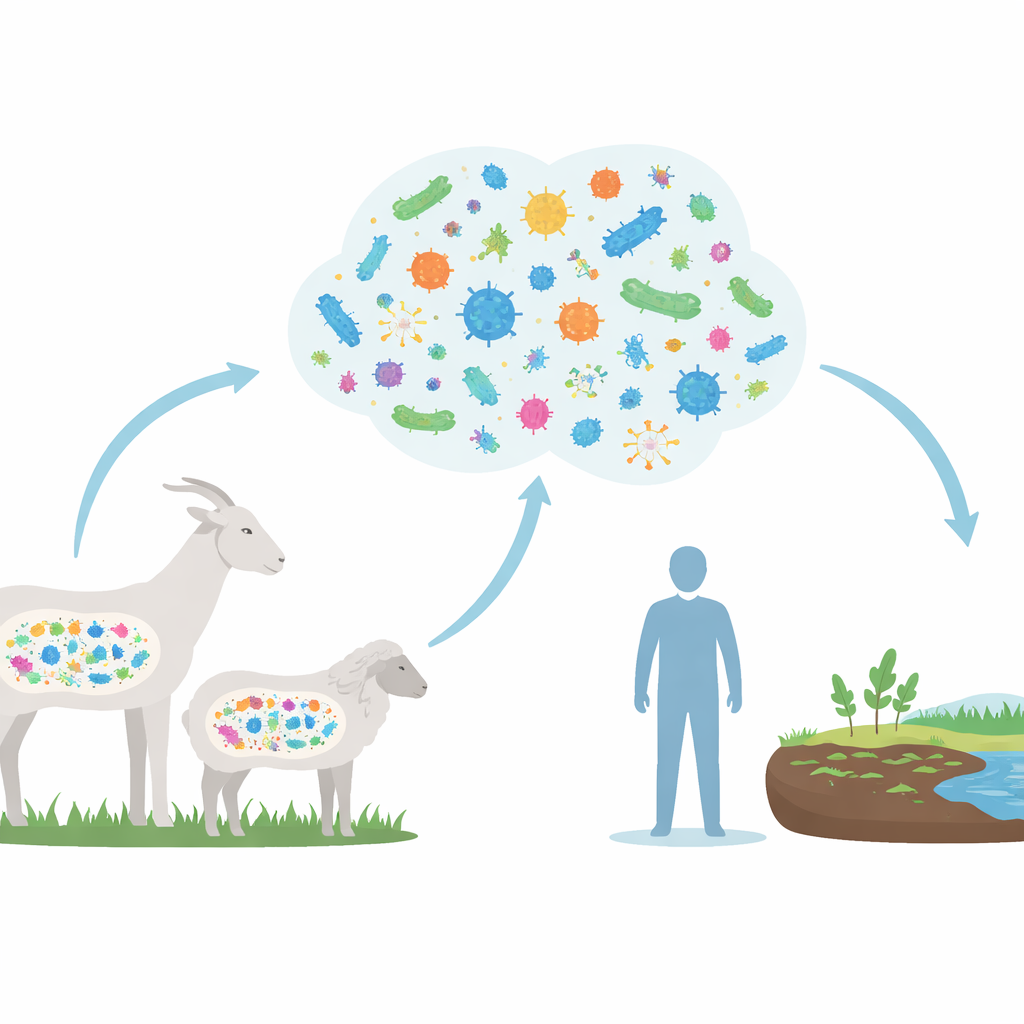
Blick in die Darmgemeinschaft
Die Forschenden kombinierten DNA-Daten aus 779 Darmproben von Ziegen, Schafen und einigen wilden Caprinae-Arten. Anstatt Mikroben im Labor anzuzüchten, nutzten sie leistungsstarke Rechner, um aus den gemischten DNA-Proben direkt mehr als 17.000 Entwurfsgenome zusammenzusetzen. Diese Genome enthüllten eine enorme Vielfalt an Mikroben, von denen viele bislang nicht formal beschrieben wurden. Trotz dieser Diversität teilten Ziegen und Schafe einen gemeinsamen Kern von Darmbewohnern, dominiert von Bakterien, die bei Pflanzenfressern gedeihen und ihnen helfen, pflanzenreiche Kost zu zersetzen.
Verborgene Vorräte an Resistenz und Gefährlichkeit
In diesen mikrobiellen Genomen suchte das Team nach zwei besorgniserregenden Genklassen: solchen, die Bakterien vor Antibiotika schützen, und solchen, die ihnen helfen, Wirte zu infizieren oder zu schädigen. Sie fanden 2.440 Antibiotikaresistenzgene, verteilt auf etwa eines von zwölf der zusammengebauten Genome, mit besonders starken Abwehrmechanismen gegen Tetracycline und gegen mehrere Antibiotikaklassen gleichzeitig. Außerdem entdeckten sie mehr als 5.400 virulenzbezogene Gene in etwa einem von sechs Genomen. Einige Stämme von Escherichia coli und Pseudomonas aeruginosa fielen als starke „Genanhäufer“ auf, die jeweils Dutzende von Resistenz- und Virulenzmerkmalen in einzelnen Genomen trugen.
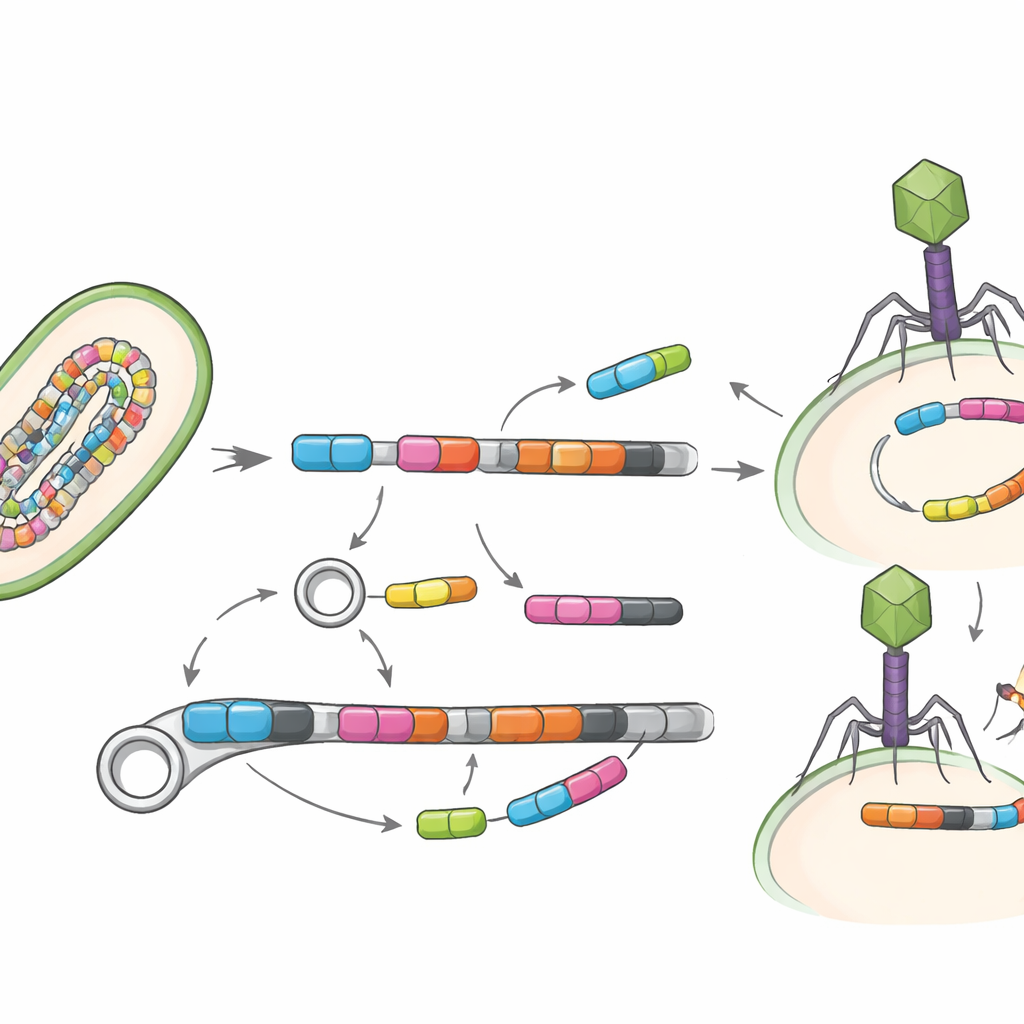
Gene in Bewegung
Eine zentrale Frage ist nicht nur, welche Gene vorhanden sind, sondern wie leicht sie sich bewegen können. Die Studie suchte daher nach mobilen genetischen Elementen — DNA-Segmenten wie Transposasen und anderen „springenden“ Stücken, die Gene zwischen Bakterien verschieben können — sowie nach Viren, die Bakterien infizieren, sogenannten Bakteriophagen. Nur ein kleiner Bruchteil der Genome trug diese mobilen Elemente deutlich, vermutlich weil solche Regionen schwer zu rekonstruieren sind; dort, wo sie jedoch auftauchten, lagen sie oft direkt neben Resistenzgenen. Das Team identifizierte 19 direkte Paarungen mobiler Elemente mit Resistenzgenen und fand sogar drei Resistenzgene, die in viralen Genomen eingebettet waren, was darauf hindeutet, dass sowohl DNA-Shuttles als auch Darmviren zur Verbreitung dieser Merkmale beitragen könnten.
Verbindungen zwischen Nutztieren und Menschen
Um die Bedeutung über den Stall hinaus zu verstehen, verglichen die Forschenden Resistenzgene in Caprinae-Darmmikroben mit denen in Tausenden menschlicher Darmgenomen. Sie entdeckten 184 Resistenzgen-Typen, die zwischen Tieren und Menschen geteilt werden, einschließlich solcher, die mit in Krankenhäusern als letzte Rettung eingesetzten Antibiotika in Verbindung stehen, etwa Tigecyclin und Vancomycin. Zwar beweist die Studie nicht, dass Gene direkt von Ziegen und Schafen auf menschliche Krankheitserreger springen, doch die Überlappung zeigt, dass beide Wirte aus einem gemeinsamen Genpool schöpfen. Da Menschen, Nutztiere und Umwelt oft eng miteinander in Kontakt stehen — über Mist, Boden, Wasser und Lebensmittel — stellen diese gemeinsamen Gene potenzielle Wege für eine artsprungübergreifende Ausbreitung dar.
Was das für den Alltag bedeutet
Insgesamt zeichnet die Arbeit ein Bild von Caprinae-Darmmikroben als einem wichtigen und bislang unterschätzten Reservoir für Antibiotikaresistenz und Virulenzpotenzial. Sie zeigt, dass diese Gene in bestimmten bakteriellen Stämmen gehäuft vorkommen, oft mit mobiler DNA verknüpft sind und sogar von Viren getragen werden können — all das erleichtert ihr Fortbestehen und die Übertragung zwischen Wirten. Für die interessierte Öffentlichkeit ist die Schlussfolgerung klar: Wie wir Antibiotika und Nutztierhaltung handhaben, betrifft nicht nur die Tiere auf dem Hof; es formt eine gemeinsame genetische Landschaft, die die künftige Wirksamkeit lebensrettender Medikamente beeinflussen kann. Die Autorinnen und Autoren plädieren dafür, Ziegen, Schafe und verwandte Tiere in integrierte "One Health"-Überwachungsmaßnahmen einzubeziehen, die menschliche, tierische und umweltbedingte Quellen antimikrobieller Resistenz gemeinsam betrachten.
Zitation: Su, JW., Elsheikha, H.M., Guo, L. et al. Metagenomic analysis of antimicrobial resistance, virulence, and mobile genetic elements in the gut microbiota of Caprinae species. Commun Biol 9, 456 (2026). https://doi.org/10.1038/s42003-026-09726-4
Schlüsselwörter: antimikrobielle Resistenz, Darmmikrobiom, Viehbestand, mobile genetische Elemente, Bakteriophagen