Clear Sky Science · fr
Analyse métagénomique de la résistance aux antimicrobiens, de la virulence et des éléments génétiques mobiles dans le microbiote intestinal des espèces de Caprinae
Pourquoi les intestins des chèvres et des moutons comptent pour notre santé
Les bactéries vivant dans les intestins des animaux d’élevage font bien plus qu’aider à digérer l’herbe. Elles peuvent aussi constituer une réserve cachée de gènes qui rendent les bactéries plus difficiles à éliminer avec des antibiotiques et potentiellement plus nocives pour les humains. Cette étude explore en profondeur les microbes intestinaux des chèvres, des moutons et de leurs proches parents pour évaluer combien de ces gènes s’y cachent, comment ils sont organisés et à quel point ils peuvent se déplacer entre espèces, y compris vers l’homme.
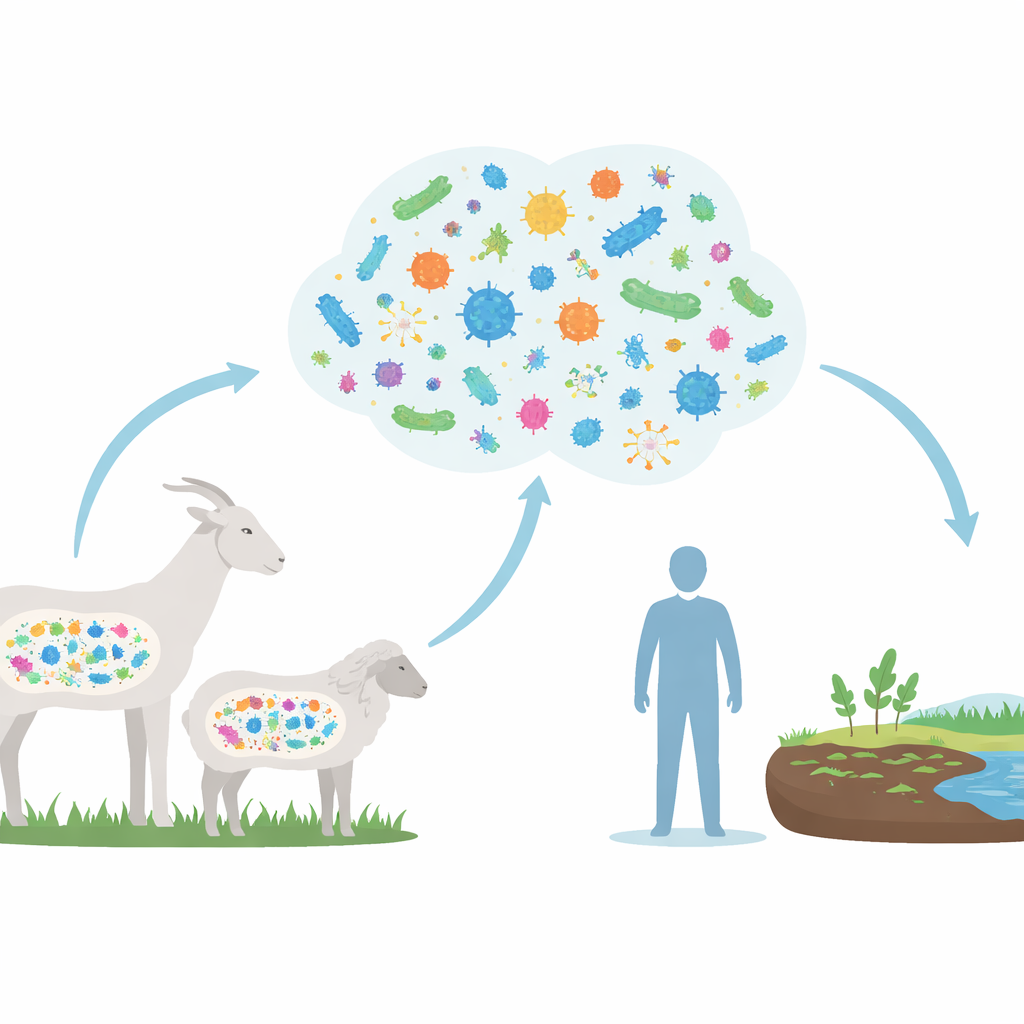
Observation de la communauté intestinale
Les chercheurs ont combiné des données d’ADN provenant de 779 échantillons intestinaux prélevés sur des chèvres, des moutons et quelques espèces sauvages de Caprinae. Plutôt que de cultiver les microbes en laboratoire, ils ont utilisé des calculateurs puissants pour reconstituer directement plus de 17 000 génomes provisoires à partir de l’ADN mélangé des échantillons. Ces génomes ont révélé une énorme diversité microbienne, dont beaucoup n’avaient jamais été décrites formellement. Malgré cette diversité, chèvres et moutons partagent un noyau commun de résidents intestinaux, dominé par des bactéries qui prospèrent chez les herbivores et les aident à dégrader des régimes riches en plantes.
Réserves cachées de résistance et de virulence
Au sein de ces génomes microbiens, l’équipe a recherché deux types de gènes préoccupants : ceux qui protègent les bactéries des antibiotiques et ceux qui facilitent l’infection ou les dommages aux hôtes. Ils ont trouvé 2 440 gènes de résistance aux antibiotiques répartis dans environ un génome assemblé sur douze, avec des défenses particulièrement marquées contre la tétracycline et contre plusieurs classes d’antibiotiques simultanément. Ils ont aussi mis au jour plus de 5 400 gènes liés à la virulence dans environ un génome sur six. Certaines souches d’Escherichia coli et de Pseudomonas aeruginosa se distinguaient comme de « gros thésauriseurs » de gènes, chacune portant des dizaines de facteurs de résistance et de virulence rassemblés dans des génomes individuels.
Les gènes en mouvement
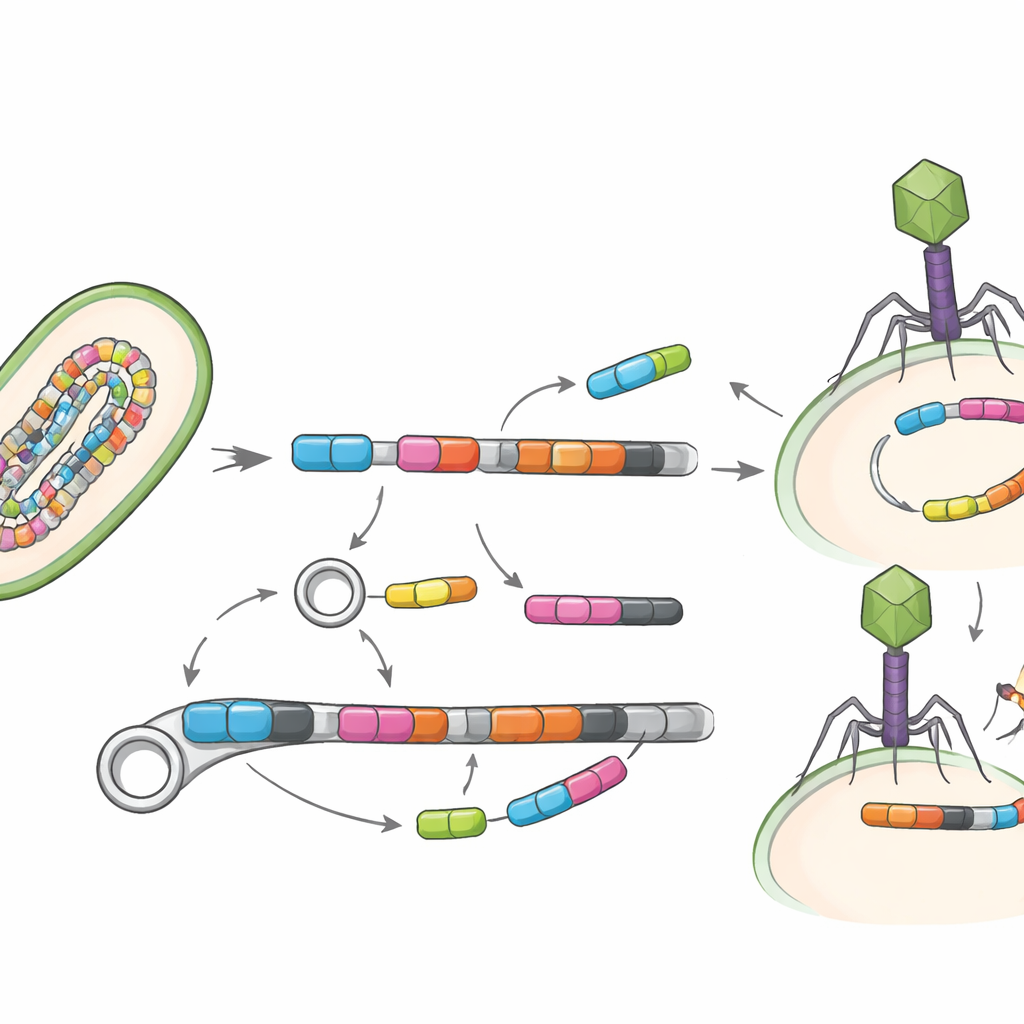
La question clé n’est pas seulement quels gènes sont présents, mais à quelle facilité ils peuvent se déplacer. L’étude a donc recherché des éléments génétiques mobiles — segments d’ADN tels que des transposases et d’autres éléments « sauteurs » pouvant transférer des gènes entre bactéries — ainsi que des virus qui infectent les bactéries, dits bactériophages. Seule une petite fraction des génomes portait clairement ces éléments mobiles, vraisemblablement parce que ces régions sont difficiles à reconstituer, mais lorsqu’ils étaient présents ils se trouvaient souvent juste à côté de gènes de résistance. L’équipe a identifié 19 associations directes d’éléments mobiles avec des gènes de résistance, et a même trouvé trois gènes de résistance intégrés dans des génomes viraux, ce qui suggère que tant les navettes d’ADN que les virus intestinaux pourraient contribuer à la propagation de ces traits.
Liens entre l’élevage et l’homme
Pour comprendre ce que cela signifie au‑delà de la ferme, les chercheurs ont comparé les gènes de résistance des microbes intestinaux de Caprinae à ceux trouvés dans des milliers de génomes intestinaux humains. Ils ont découvert 184 types de gènes de résistance partagés entre animaux et humains, y compris des gènes associés à des antibiotiques considérés comme des traitements de dernier recours en milieu hospitalier, tels que la tigécycline et la vancomycine. Bien que cette étude ne prouve pas que les gènes passent directement des chèvres et des moutons aux agents pathogènes humains, le chevauchement montre que les deux hôtes prélèvent dans un même réservoir de résistance. Étant donné que les humains, le bétail et l’environnement se mélangent souvent — via le fumier, le sol, l’eau et les aliments — ces gènes partagés constituent des voies potentielles de propagation inter‑espèces.
Ce que cela signifie pour la vie de tous les jours
Dans l’ensemble, ce travail dresse le portrait des microbes intestinaux de Caprinae comme d’un réservoir important, et jusqu’ici sous‑estimé, de résistance aux antibiotiques et de potentiel de virulence. Il montre que ces gènes se concentrent dans certaines souches bactériennes, sont souvent liés à de l’ADN mobile et peuvent même être véhiculés par des virus, autant de mécanismes favorisant leur persistance et leur transmission entre hôtes. Pour le lecteur non spécialiste, la conclusion est claire : la façon dont nous gérons les antibiotiques et l’élevage n’affecte pas seulement les animaux de ferme ; elle façonne un paysage génétique partagé qui peut influencer l’efficacité future de médicaments vitaux. Les auteurs soutiennent que les chèvres, les moutons et les animaux apparentés devraient être inclus dans des dispositifs intégrés de surveillance « Une Santé » qui prennent en compte conjointement les sources humaines, animales et environnementales de la résistance aux antimicrobiens.
Citation: Su, JW., Elsheikha, H.M., Guo, L. et al. Metagenomic analysis of antimicrobial resistance, virulence, and mobile genetic elements in the gut microbiota of Caprinae species. Commun Biol 9, 456 (2026). https://doi.org/10.1038/s42003-026-09726-4
Mots-clés: résistance aux antimicrobiens, microbiome intestinal, bétail, éléments génétiques mobiles, bactériophages