Clear Sky Science · ja
コントラスト学習で解き明かすDELポケットのパターン
タンパク質の「ポケット」を見ることが新薬発見を加速する理由
現代の薬物探索では、DNAエンコードライブラリ(DEL)を使って一度に何兆もの小分子をスクリーニングできるようになりました。しかし、DEL由来の化合物が実際の薬になる例はまだ少数です。その大きな要因の一つは、どの体内タンパク質がDEL分子を結合させるのに適した“窪み”や“ポケット”を持っているかが十分に分かっていないことです。本研究は、成功したDEL結合ポケットの特徴を体系的にマッピングし、ErePOCと呼ばれるAIモデルを構築してヒト全体で類似のポケットを見つけることに取り組んでいます。
DEL技術が新規薬分子を探索する仕組み
DELはバーコード付きのルアーのように働きます。化学者は候補小分子を短いDNA断片(IDタグ)に結合させ、目的のタンパク質に対して大量のタグ付き分子混合物を曝露します。結合した分子はDNA配列をシーケンスすることで読み出されます。この手法は高速で低コストですが、DELヒットを実際の薬にするには依然として困難があります。その一因は、DEL分子が持つ化学的制約(例えば水中で合成されることやDNAタグの結合方法など)です。これらの制約によりDEL分子は特定タイプのポケットを好む傾向があるものの、その嗜好性が体系的にマップされたことはこれまでありませんでした。
DEL分子が魅力を感じるポケットの特徴
著者らはまず、様々な種類のリガンドを結合する何千ものポケットを比較しました:普通の生体小分子、FDA承認薬、そしてDELヒットです。すると、DELや薬が結合するポケットは、自然由来のリガンド用ポケットよりも大きく化学的に複雑である傾向が見られました。具体的には、DELポケットはより開放的で疎水性(油のような水を避ける相互作用を好む)である一方、結合を微調整する小さいが重要な極性接点も保持していました。チロシンやフェニルアラニンのような、芳香族で疎水的表面を提供するかさ高いアミノ酸が、典型的なタンパク質表面よりもDELや薬結合ポケットに多く現れます。総じて、DELポケットは通常の代謝部位よりも古典的な薬標的ポケットに似ていますが、大きく疎水的な空洞への偏りがさらに強いことが特徴です。
ポケットの「性格」を認識するAIモデルの教育
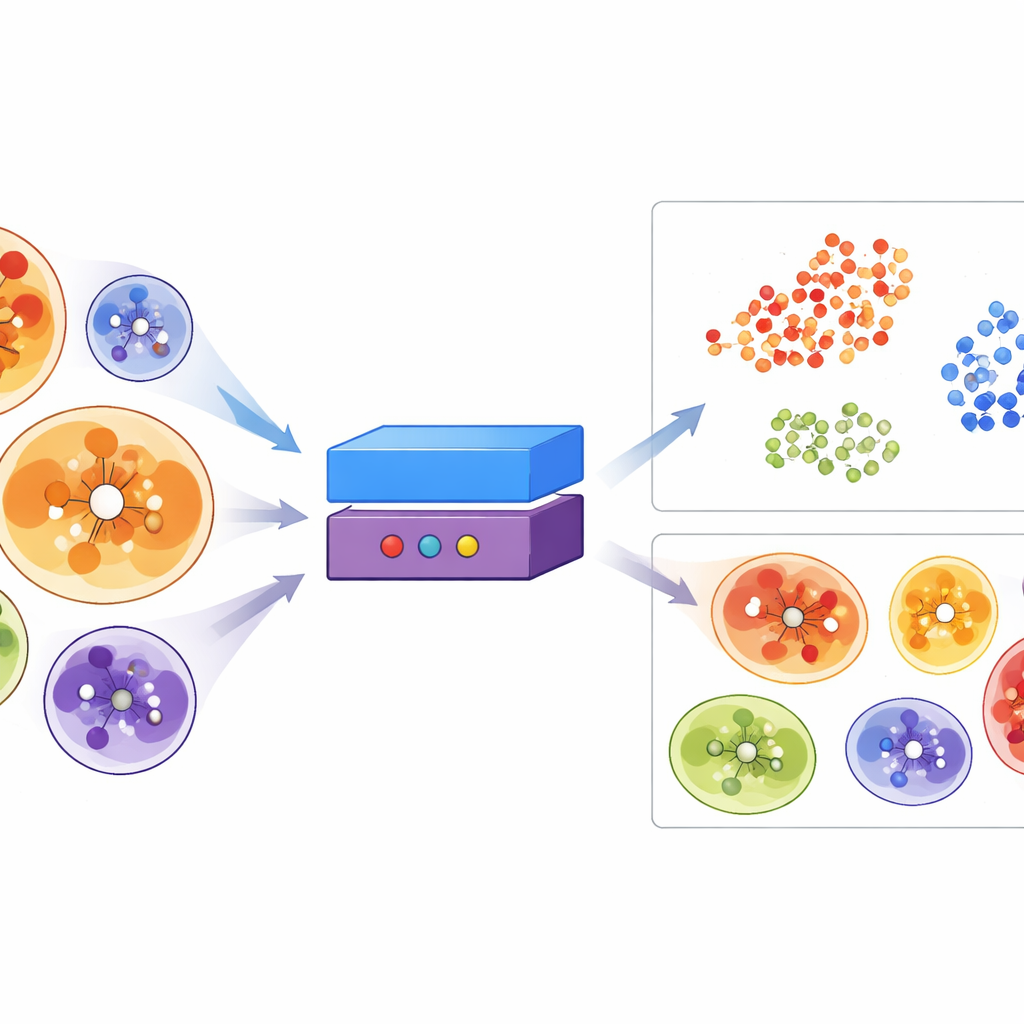
単なるサイズや化学的指標を超えるために、チームは各結合ポケットを指紋のように表現するErePOCという表現モデルを構築しました。これはまずタンパク質言語モデルの埋め込み(数百万の配列から学んだパターンを捉える)を出発点とし、ポケットを形成する残基に関する情報をコンパクトな数値ベクトルに圧縮します。コントラスト学習を用いて、化学的に類似したリガンドを結合するポケットが抽象空間で近くに来るように、逆に非常に異なる分子を結合するポケットは離れるようにErePOCを訓練しました。空間を可視化すると、ATPやヘムなど同じ補因子を結合するポケットが明確に分かれたクラスターを形成し、モデルが単なるタンパク質形状ではなく機能的振る舞いでポケットを群化することを学んでいることが示されました。
ヒトプロテオーム全体でのDEL適合ターゲットの探索
ErePOCを訓練した後、研究者らは既知のDELポケット、薬結合ポケット、そして実験的・予測構造から得られた数十万のポケットを同じランドスケープに投影しました。DELポケットは広く散らばっており、理論上DELスクリーニングは従来の「ドラッガブル」空間の多くに到達し得ることを示していますが、それでも大きく疎水的なポケットに関連する特定領域への明確な嗜好を示しました。次にチームは、よく定義されたポケットをフィルタリングして23,000超のAlphaFold予測ヒトタンパク質をスキャンし、ErePOC空間で既知のDELポケットに最も近いものを探しました。その結果、成功したDEL部位に非常に類似したポケットを持つヒトタンパク質が約2,800種同定され、トランスフェラーゼ、ヒドロラーゼ、酸化還元酵素、クロマチン調節因子、および一部のRNA結合タンパク質などのファミリーに強い濃縮が見られました。大型の仮想DELを用いた追試ドッキングでも、ErePOCでフラグされたポケットは実際にDEL様分子をより好んで結合する傾向が示されました。
将来の創薬にとっての意義
非専門家向けに言うと、超巨大化学ライブラリの成功は分子そのものと同じくらい、正しいタンパク質ポケットを選ぶことに依存するという点が重要です。本研究は、DELヒットが大きく柔軟で疎水性の高いポケットから生じやすいことを示し、配列や構造だけからそのようなポケットを認識する強力なAIツールを紹介します。ErePOCを用いて既にDELに適した見た目のポケットを持つタンパク質にスクリーニングを絞れば、より有望なターゲットを優先し、無駄なスクリーニング労力を削減し、クロマチンやRNA結合タンパク質などこれまであまり探られてこなかったクラスに進出する可能性が高まります。要するに、本研究は「DEL対応」ポケットの姿を明確に描き出すとともに、ヒトプロテオーム中でそれらを見つけ出すための実用的な地図とコンパスを提供しています。
引用: Zhang, W., Wang, Y., Zhan, R. et al. Deciphering DEL pocket patterns through contrastive learning. Nat Commun 17, 2810 (2026). https://doi.org/10.1038/s41467-026-69663-y
キーワード: DNAエンコードライブラリ, タンパク質結合ポケット, コントラスト学習, ドラッグディスカバリーAI, ErePOC