Clear Sky Science · it
Epidemiologia molecolare di OXA-1054, una nuova β-lattamasi di Classe D che idrolizza i carbapenemi, in Enterobacteriaceae isolate dalle acque reflue
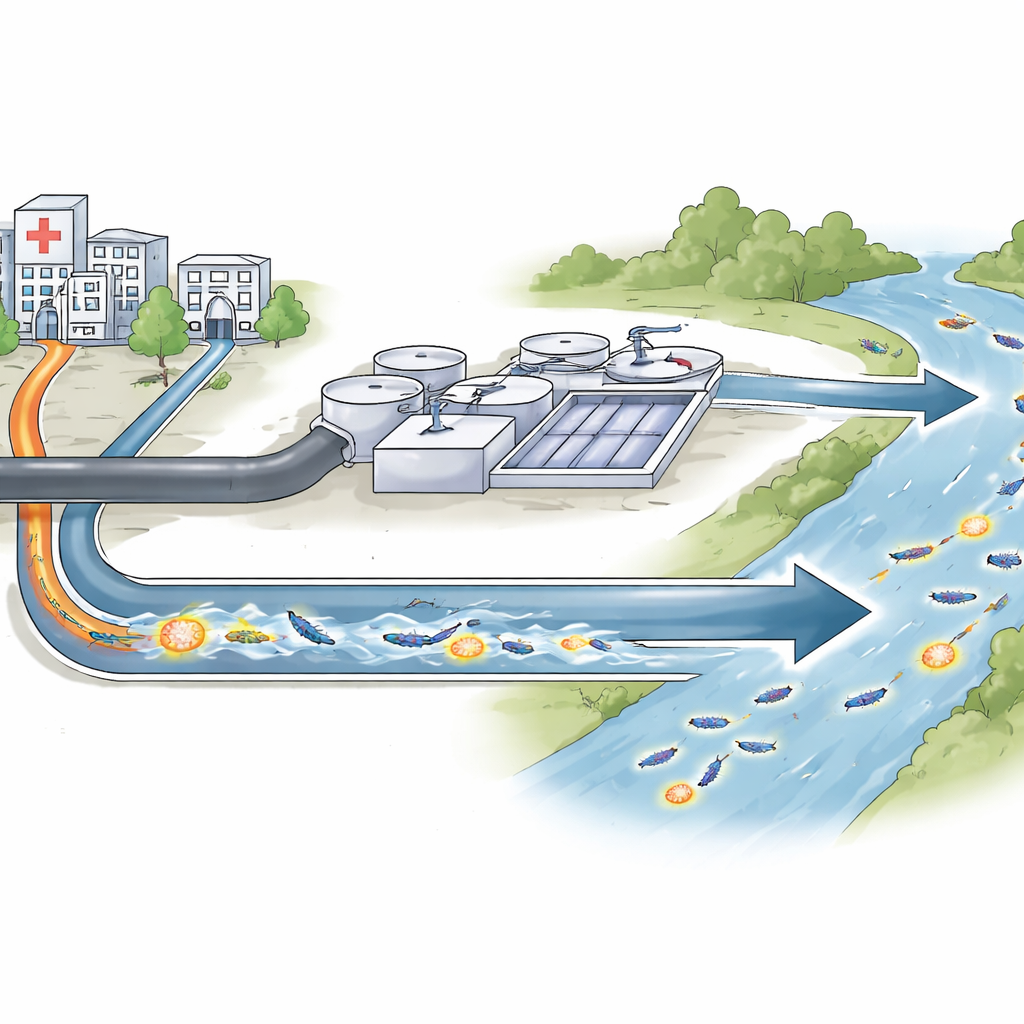
Perché i germi nelle acque sporche contano
La maggior parte di noi associa la resistenza agli antibiotici a quanto avviene negli ospedali. Però i farmaci che usiamo e i microrganismi su cui agiscono non restano confinati lì. Fuoriescono con le acque reflue verso gli impianti di trattamento e i fiumi, dove batteri provenienti da molte sorgenti si mescolano e si scambiano espedienti genetici per sopravvivere ai nostri farmaci più efficaci. Questo studio segue uno di questi espedienti — un gene di resistenza appena scoperto — nel sistema delle acque reflue di Siviglia, in Spagna, per capire dove risiede, come si muove e perché ciò è importante per le future infezioni.
Un nuovo stratagemma di resistenza in batteri intestinali comuni
I ricercatori si sono concentrati su un gruppo di batteri chiamato Enterobacteriaceae, che include molti microrganismi intestinali in grado di provocare infezioni gravi. Alcuni membri di questo gruppo hanno imparato a degradare i carbapenemi, una famiglia di antibiotici considerata ultima risorsa. Il team ha trovato una versione precedentemente sconosciuta di un enzima di resistenza, denominata OXA-1054, in batteri raccolti da scarichi ospedalieri, impianti di trattamento delle acque cittadine e dall’immediato fiume Guadalquivir. Questo enzima appartiene a una filiera chiamata OXA-372, correlata ma distinta dalla più nota famiglia OXA-48, diffusa negli ospedali. Clonando il nuovo gene in ceppi di laboratorio innocui di Escherichia coli, gli scienziati hanno dimostrato che OXA-1054 può effettivamente aumentare la resistenza verso diversi farmaci importanti, inclusi i carbapenemi.
Le acque reflue come crogiolo della resistenza
La maggior parte dei batteri portatori di OXA-1054 è stata trovata nelle acque reflue grezze in ingresso agli impianti di trattamento, soprattutto in un grande impianto, con alcuni isolati presenti negli scarichi ospedalieri e nell’acqua del fiume a valle. Il gene è comparso in diverse specie, come Citrobacter, Enterobacter e Raoultella, e in molti cloni non correlati all’interno di quelle specie. Questo schema suggerisce che il gene di resistenza non è confinato a un unico ceppo di successo, ma si sta diffondendo tra batteri diversi che condividono lo stesso ambiente acquatico. Sebbene il trattamento abbia ridotto la carica batterica rilevabile nell’effluente trattato, il gene è ricomparso nel fiume in momenti diversi, suggerendo che le acque ambientali possono funzionare come serbatoio a lungo termine.
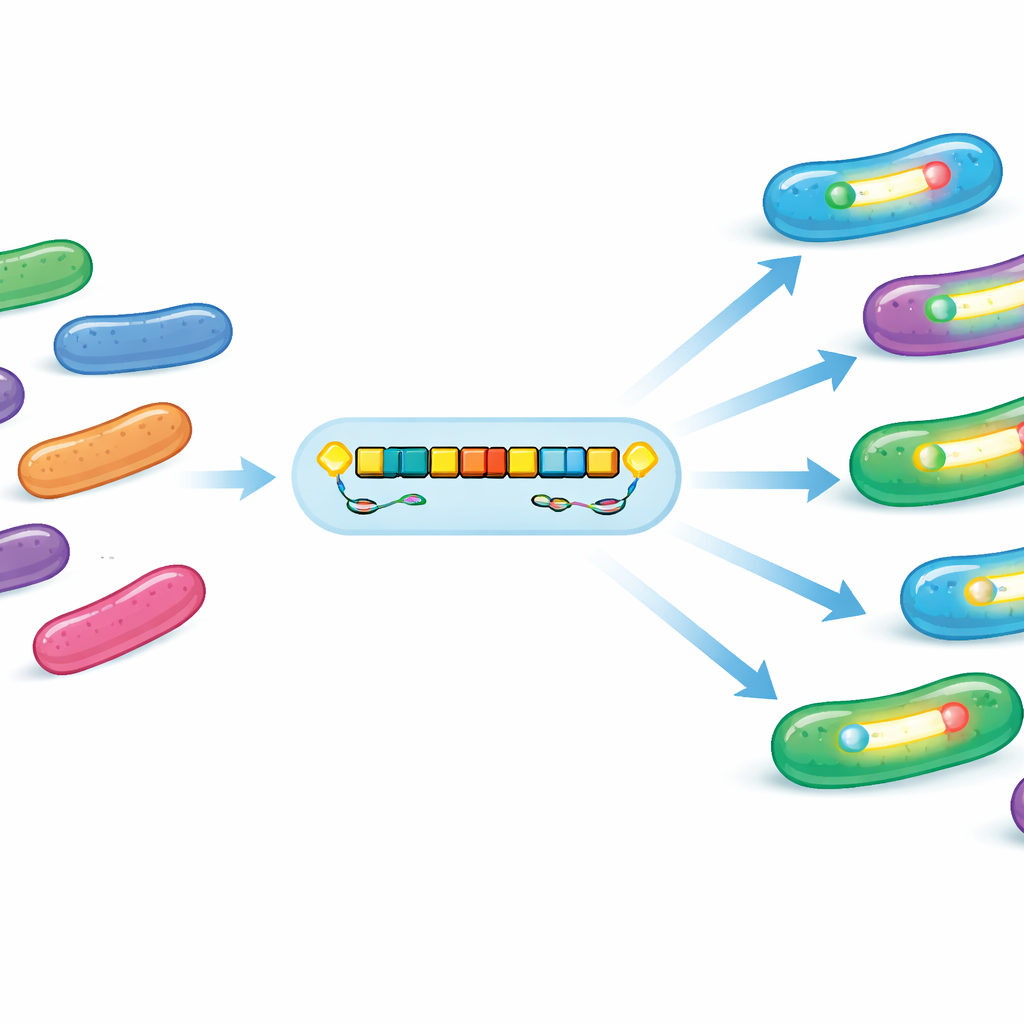
Un pacchetto mobile costruito per persistere
Analizzando da vicino il DNA intorno al gene blaOXA-1054, il team ha trovato che era inserito in un modulo mobile ricorrente — essenzialmente un piccolo pacchetto genetico portatile. Questo pacchetto conteneva quasi sempre due geni di trasposizione, istA e istB, della famiglia IS21, oltre a diverse copie di un altro tipo di elemento mobile. In molti casi si trovava nelle vicinanze un secondo gene di resistenza (ampC) e cluster per la resistenza a metalli pesanti come arsenico e mercurio. Questi componenti aggiuntivi significano che l’inquinamento da metalli o da altri farmaci potrebbe favorire indirettamente batteri che portano anche OXA-1054. I plasmidi (piccoli anelli di DNA) che ospitavano questo modulo spesso contenevano molteplici sistemi “tossina–antitossina”, trappole genetiche che aiutano a mantenere il plasmide nelle cellule durante la divisione batterica, conservando il tratto di resistenza nella popolazione anche in assenza di antibiotici.
Come si diffonde senza il trasferimento classico
Con sorpresa, la maggior parte dei plasmidi portatori di OXA-1054 mancava del macchinario tipico per il trasferimento tra batteri mediante coniugazione, e esperimenti di accoppiamento in laboratorio non hanno trasferito il gene in un ceppo ricevente. Questo indica una modalità di diffusione differente: anziché un singolo plasmide altamente mobile che si propaga tra le comunità batteriche, una piattaforma mobile conservata contenente blaOXA-1054 sembra saltare in vari plasmidi e talvolta direttamente nei cromosomi batterici. Geni accessori extra — come elicasi del DNA, metiltransferasi del DNA e proteine di mantenimento strutturale — possono contribuire a stabilizzare queste piattaforme e a supportarne il movimento e la sopravvivenza in acque inquinate e soggette a stress.
Cosa significa per le persone e i fiumi
In termini semplici, lo studio mostra che un potente nuovo gene di resistenza circola già nelle acque reflue cittadine e nel fiume vicino, anche se non è ancora diventato comune tra i pazienti ospedalieri. È localizzato su un robusto pacchetto di DNA mobile che gli consente di persistere e di viaggiare insieme ad altri tratti di resistenza, comprese difese contro i metalli pesanti. Questa combinazione aumenta la probabilità che il gene persista nell’ambiente e rimanga pronto a entrare in batteri associati agli esseri umani. Il lavoro sottolinea che proteggere i nostri antibiotici più preziosi richiede di sorvegliare non solo le cliniche, ma anche i mondi microbici nascosti nelle tubature, negli impianti di trattamento e nei fiumi che collegano l’attività umana all’ambiente più ampio.
Citazione: Monge-Olivares, L., González-Pinto, L., Pulido, M.R. et al. Molecular epidemiology of OXA-1054, a novel carbapenem-hydrolysing Class D β-lactamase, in Enterobacteriaceae isolated from wastewaters. npj Antimicrob Resist 4, 36 (2026). https://doi.org/10.1038/s44259-026-00209-4
Parole chiave: resistenza agli antibiotici, acque reflue, carbapenemasi, elementi genetici mobili, microbiologia ambientale