Clear Sky Science · it
Identità di sequenze nucleotidiche a pezzi tra genomi di specie diverse facilitano la ricombinazione illegittima
Modelli nascosti nel codice genetico della vita
Ogni essere vivente, dai virus e batteri al grano e alle balene, conserva le sue istruzioni genetiche in lunghe stringhe di quattro “lettere” chimiche. Questo studio pone una domanda apparentemente semplice: cosa succede se si confronta il codice genetico di due organismi molto diversi e si cercano tratti corrispondenti? La risposta si rivela sorprendentemente universale — e potrebbe aiutare a spiegare come i genomi si rimodellano continuamente, alimentando l’evoluzione e la comparsa di nuovi agenti patogeni.
Brevi tratti corrispondenti ovunque
I ricercatori hanno iniziato confrontando la sequenza genetica completa del virus SARS-CoV-2 con vari altri genomi, incluse le cromosomi umani, altri virus, batteri, piante e animali. Invece di cercare segmenti lunghi e ovviamente correlati, hanno prestato attenzione a “pezzi” — brevi serie di lettere identiche interrotte da non corrispondenze e gap. In oltre 90 confronti tra specie, hanno riscontrato una regolarità sorprendente: circa il 40–50% delle posizioni allineate risultava una corrispondenza esatta, quasi sempre organizzata in questi tratti sparsi e a macchia. Ciò valeva anche per organismi che non condividono un recente antenato comune e svolgono ruoli biologici completamente diversi.
Casualità con lo stesso aspetto
Per capire se queste identità a macchia riflettessero relazioni biologiche profonde o qualcosa di più fondamentale, il gruppo ha creato sequenze di controllo artificiali. Hanno mescolato genomi reali per mantenere la stessa composizione complessiva di lettere ma rimescolare l’ordine, e hanno anche generato stringhe di DNA completamente casuali con frequenze di basi simili o fissate. Quando hanno allineato queste sequenze sintetiche tra loro o con genomi reali, hanno osservato sostanzialmente lo stesso schema: molte brevi corrispondenze esatte distribuite in modo irregolare, con l’identità complessiva di nuovo intorno alla fascia del 40% medio. Hanno ripetuto i test con diversi programmi di allineamento e impostazioni di punteggio, e il risultato è rimasto sostanzialmente invariato. La conclusione è che l’alfabeto a quattro lettere in sé, combinato con le dimensioni tipiche dei genomi e le frequenze delle lettere, quasi garantisce questo pattern a macchia.
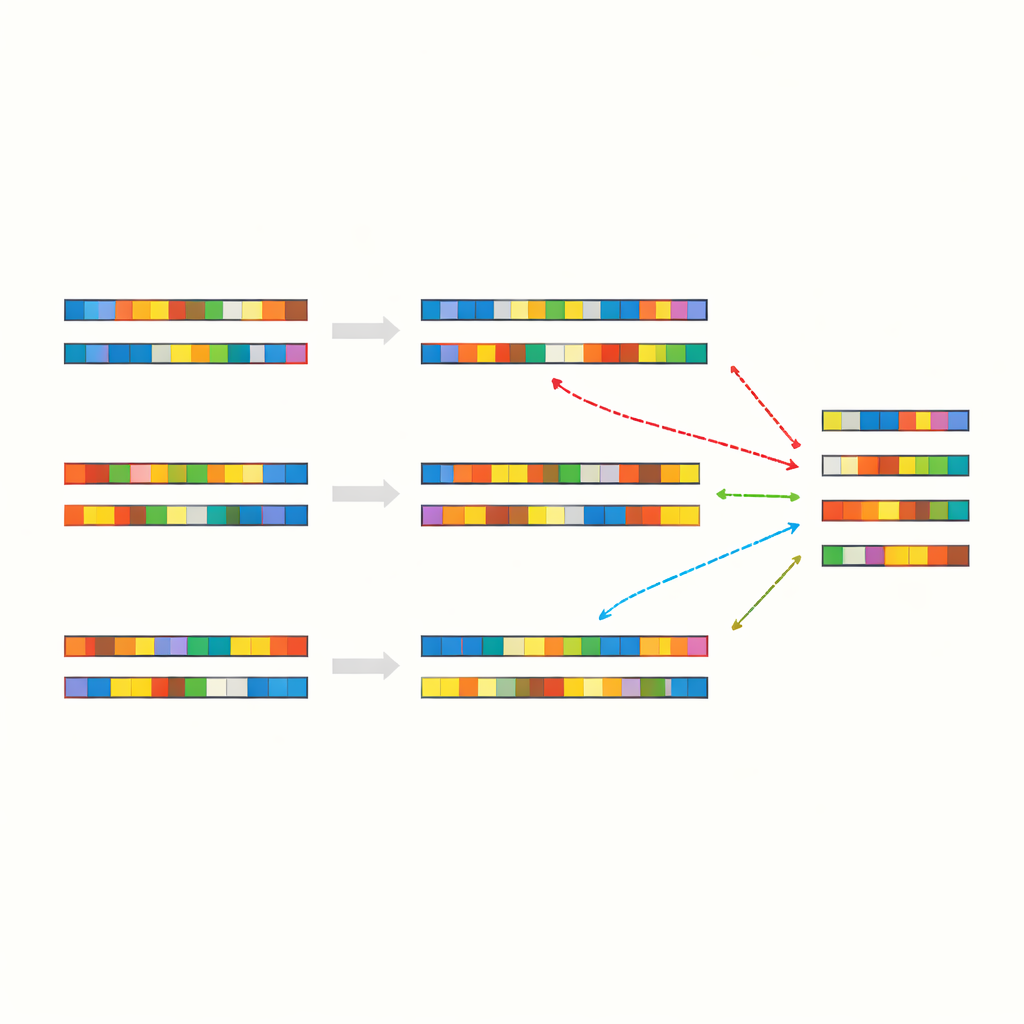
Quando la casualità diventa un segnale utile
Le corrispondenze a macchia nel DNA non sono solo una curiosità. Studi precedenti, compreso il lavoro dello stesso gruppo, hanno mostrato che schemi simili spesso appaiono proprio nei punti in cui materiale genetico estraneo si inserisce permanentemente in un genoma ospite — per esempio quando certi virus o elementi mobili del DNA si integrano nelle cellule animali. Questi eventi si basano sulla “ricombinazione illegittima”, un termine ombrello per eventi di taglia-e-incolla o copia-e-incolla che non richiedono lunghe regioni perfettamente corrispondenti. Lo studio attuale rafforza l’idea che le identità a macchia, sempre presenti per ragioni statistiche, possano fungere da appigli comodi per la macchina cellulare che unisce frammenti di materiale genetico. Gli autori identificano persino rare regioni locali in cui l’identità supera di gran lunga le aspettative casuali, segnalandole come potenziali hotspot dove tale ricombinazione è particolarmente probabile.
Modellare i genomi nel corso dell’evoluzione
Poiché questi schemi a macchia compaiono sia in regioni codificanti sia non codificanti, in elementi ripetitivi e attraverso specie estremamente diverse, gli autori sostengono che siano una caratteristica intrinseca del DNA piuttosto che un effetto collaterale di geni particolari. Nel corso dell’evoluzione, questo sfondo costante di brevi tratti corrispondenti potrebbe aver facilitato gli scambi, i riarrangiamenti o le inserzioni di nuovi pezzi nei genomi primitivi, molto prima che evolvessero enzimi altamente specializzati e meccanismi di copia rigorosi. Negli organismi moderni, compresi virus a RNA in rapido cambiamento come SARS-CoV-2, lo stesso impalcatura statistica può ancora favorire scambi rari ma consequenziali di materiale genetico con altri virus o persino con cellule ospiti, potenzialmente dando origine a varianti con comportamento modificato.
Cosa significa questo per il quadro generale
Per un non specialista, il messaggio chiave è che il codice a quattro lettere del DNA porta con sé due tipi di informazione allo stesso tempo. Uno strato spiega geni e istruzioni regolatorie. L’altro, più sottile, è statistico: semplicemente usando quattro lettere con frequenze sbilanciate su lunghe porzioni, i genomi condividono inevitabilmente molte corrispondenze brevi e sparse. Questo studio suggerisce che l’evoluzione ha sfruttato quel secondo strato, trasformando schemi dall’aspetto casuale in punti di ancoraggio pratici per il rimescolamento genetico. In altre parole, le stesse regole semplici che fanno sembrare le sequenze simili a macchia attraverso l’albero della vita possono anche aiutare i sistemi viventi a riscrivere e adattare continuamente i propri progetti.»
Citazione: Weber, S., Ramirez, C.M. & Doerfler, W. Patch type nucleotide sequence identities between genomes from many different species facilitate illegitimate recombination. Sci Rep 16, 10524 (2026). https://doi.org/10.1038/s41598-026-44124-0
Parole chiave: ricombinazione del genoma, schemi di sequenza del DNA, evoluzione genetica, genetica di SARS-CoV-2, plasticità del genoma