Clear Sky Science · de
Patch-ähnliche Nukleotidsequenz-Identitäten zwischen Genomen vieler verschiedener Arten fördern illegitime Rekombination
Verborgene Muster im genetischen Code des Lebens
Jeder Lebewesen — von Viren und Bakterien bis hin zu Weizen und Walen — speichert seine genetischen Anweisungen in langen Reihen von vier chemischen „Buchstaben“. Diese Studie stellt eine scheinbar einfache Frage: Was passiert, wenn man die genetischen Codes zweier sehr unterschiedlicher Organismen nebeneinanderlegt und nach übereinstimmenden Abschnitten sucht? Die Antwort erweist sich als überraschend allgemein gültig — und könnte dazu beitragen zu erklären, wie Genome sich beständig umgestalten, Evolution antreiben und neue Krankheitserreger entstehen lassen.
Kurz übereinstimmende Abschnitte überall
Die Forschenden begannen damit, die vollständige genetische Sequenz des SARS-CoV-2-Virus mit einer Vielzahl anderer Genome zu vergleichen, darunter menschliche Chromosomen, andere Viren, Bakterien, Pflanzen und Tiere. Statt nach langen, offensichtlich verwandten Segmenten zu suchen, richteten sie ihr Augenmerk auf „Patches“ — kurze Sequenzabschnitte identischer Buchstaben, unterbrochen von Fehlpaarungen und Lücken. In mehr als 90 solcher artübergreifender Vergleiche fanden sie eine auffällige Regelmäßigkeit: Etwa 40–50 % der Positionen stimmten genau überein, fast immer in Form dieser verstreuten, patchartigen Abschnitte. Dies traf selbst für Organismen zu, die keine jüngere gemeinsame Abstammung teilen und völlig unterschiedliche biologische Rollen erfüllen.
Zufälligkeit, die gleich aussieht
Um zu prüfen, ob diese patchigen Identitäten tiefe biologische Beziehungen widerspiegeln oder etwas Grundlegenderes, erzeugte das Team künstliche Kontrollsequenzen. Sie mischten reale Genome so um, dass zwar die gleiche Gesamtbuchstabenverteilung erhalten blieb, die Reihenfolge aber verwirbelt wurde, und sie erzeugten außerdem vollständig zufällige DNA-Stränge mit ähnlichen oder festen Basenhäufigkeiten. Wenn sie diese synthetischen Sequenzen miteinander oder mit realen Genomen ausrichteten, zeigte sich im Grunde dasselbe Muster: viele kurze exakte Übereinstimmungen, unregelmäßig verteilt, mit einer Gesamtidentität, die erneut im mittleren 40-Prozent-Bereich lag. Die Tests wurden mit verschiedenen Alignierungsprogrammen und Bewertungseinstellungen wiederholt — das Ergebnis änderte sich kaum. Die Schlussfolgerung lautet, dass das Vierbuchstaben-Alphabet selbst, kombiniert mit typischen Genomgrößen und Buchstabenhäufigkeiten, dieses patchartige Muster nahezu garantiert.
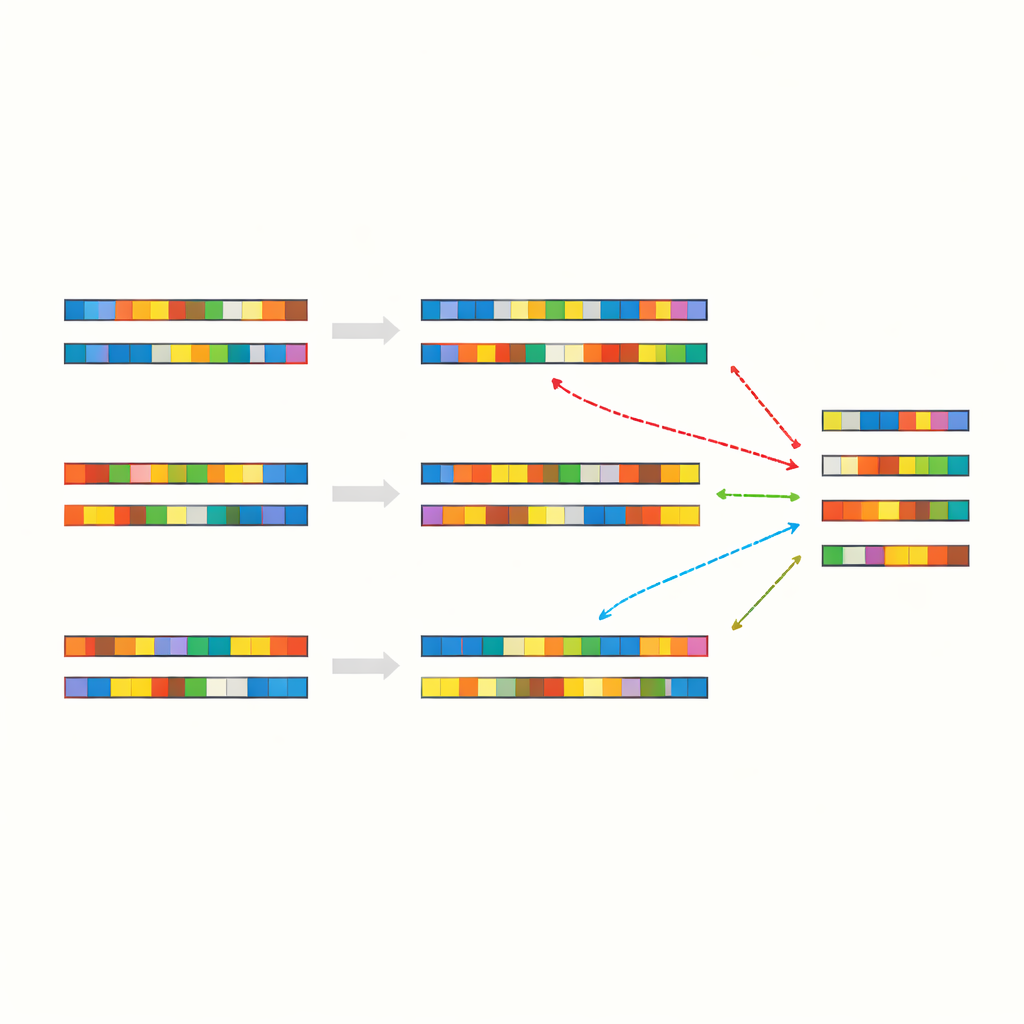
Wenn Zufall zu einem nützlichen Signal wird
Patchartige Übereinstimmungen in der DNA sind nicht nur eine Kuriosität. Frühere Studien, einschließlich Arbeiten derselben Gruppe, haben gezeigt, dass ähnliche Muster häufig genau dort auftreten, wo fremdes genetisches Material dauerhaft in ein Wirtsgenom eingefügt wird — zum Beispiel wenn bestimmte Viren oder mobile DNA-Elemente in tierische Zellen integrieren. Solche Ereignisse beruhen auf „illegitimer Rekombination“, einem Sammelbegriff für Ausschneide‑/Einfüge- oder Kopier‑/Einfüge-Vorgänge, die keine langen, perfekt übereinstimmenden Abschnitte erfordern. Die aktuelle Studie stützt die Auffassung, dass die allgegenwärtigen, statistisch erzeugten patchigen Identitäten als bequeme Ansatzpunkte für die zellulären Mechanismen dienen können, die Genmaterialstücke zusammenführen. Die Autorinnen und Autoren identifizieren sogar seltene lokale Regionen, in denen die Identität weit über den Zufallserwartungen liegt, und markieren diese als potenzielle Hotspots, an denen solche Rekombination besonders wahrscheinlich ist.
Genome im Wandel der Evolution formen
Da diese Patch-Muster sowohl in codierenden als auch in nicht-codierenden Regionen, in repetitiven Elementen und bei sehr verschiedenen Arten auftreten, argumentieren die Autorinnen und Autoren, dass sie ein eingebautes Merkmal der DNA sind und nicht bloß eine Nebenwirkung bestimmter Gene. Im Verlauf der Evolution könnte dieser konstante Hintergrund kurz übereinstimmender Abschnitte frühen Genomen das Austauschen, Umordnen oder Einfügen neuer Stücke erleichtert haben — lange bevor hochspezialisierte Enzyme und strenge Kopiermechanismen entstanden. In modernen Organismen, einschließlich schnell veränderlicher RNA‑Viren wie SARS-CoV-2, kann dasselbe statistische Gerüst weiterhin seltene, aber folgenschwere Austauschvorgänge von genetischem Material mit anderen Viren oder sogar Wirtszellen begünstigen und so möglicherweise zur Entstehung neuer Varianten mit veränderter Eigenschaft beitragen.
Was das für das große Ganze bedeutet
Für Nicht-Fachleute ist die Kernbotschaft, dass der vierbuchstabige Code der DNA gleichzeitig zwei Arten von Information trägt. Eine Ebene kodiert Gene und regulatorische Anweisungen. Die andere, subtilere Ebene ist statistisch: Allein durch die Verwendung von vier Buchstaben mit verzerrten Häufigkeiten über lange Strecken teilen Genome zwangsläufig viele verstreute kurze Übereinstimmungen. Diese Studie legt nahe, dass die Evolution diese zweite Ebene genutzt hat — und zufällig wirkende Muster in praktische Andockpunkte für genetische Umgestaltungen verwandelt hat. Anders ausgedrückt: Dieselben einfachen Regeln, die Sequenzen über den Baum des Lebens hinweg patchartig ähnlich erscheinen lassen, können lebenden Systemen helfen, ihre eigenen Baupläne beständig neu zu schreiben und anzupassen.
Zitation: Weber, S., Ramirez, C.M. & Doerfler, W. Patch type nucleotide sequence identities between genomes from many different species facilitate illegitimate recombination. Sci Rep 16, 10524 (2026). https://doi.org/10.1038/s41598-026-44124-0
Schlüsselwörter: Genomrekombination, DNA-Sequenzmuster, genetische Evolution, SARS-CoV-2-Genetik, Genomplastizität