Clear Sky Science · it
Progetto in silico di un vaccino multiepitope contro Acinetobacter baumannii resistente agli antibiotici
Perché questo è importante per la salute di tutti i giorni
Gli ospedali dovrebbero curarci, ma alcune delle infezioni più pericolose oggi nascono proprio al loro interno. Un colpevole, un batterio resistente chiamato Acinetobacter baumannii, ha imparato a resistere a molti dei nostri antibiotici più potenti, trasformando cure di routine in un rischio per la vita per i pazienti più vulnerabili. Questo studio esplora un nuovo modo per restare davanti a questi super‑batteri: usare i computer per progettare un vaccino di nuova generazione composto da frammenti proteici accuratamente scelti, con l’obiettivo di prevenire le infezioni prima che si manifestino.
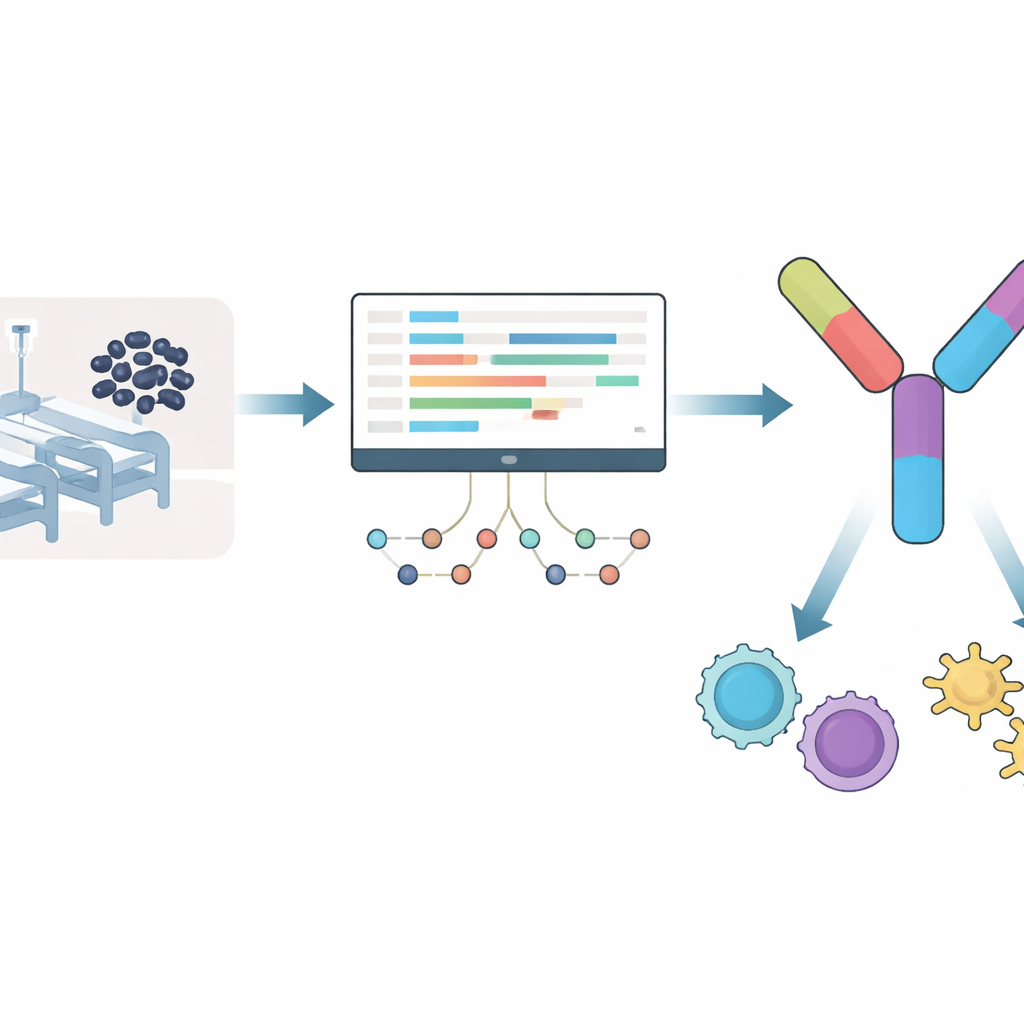
Un germe ospedaliero che non se ne va
Acinetobacter baumannii prospera su superfici e attrezzature ospedaliere, dove può infettare persone con sistema immunitario indebolito, malattie polmonari croniche o ricoveri prolungati in terapia intensiva. Appartiene a un gruppo noto di microrganismi ospedalieri famosi per la loro resistenza a più farmaci. Quando questo germe diventa resistente ai carbapenemi, una classe di antibiotici di ultima risorsa, i medici si trovano con poche opzioni sicure. Poiché non esiste un vaccino approvato, l’Organizzazione Mondiale della Sanità ha etichettato questo batterio come una priorità assoluta per lo sviluppo di vaccini, spingendo i ricercatori a cercare modi più intelligenti per colpirlo.
Lasciare che il batterio riveli i suoi punti deboli
Invece di partire da congetture su quali parti del batterio potrebbero essere buoni bersagli per un vaccino, il team ha osservato come Acinetobacter baumannii risponde quando viene attaccato da un antibiotico chiave, il meropenem. Hanno analizzato dati di sequenziamento dell’RNA, che mostrano quali geni vengono attivati o disattivati, dopo nove ore di esposizione al farmaco. Oltre un migliaio di geni è risultato sovraespresso e un numero simile è risultato sottoregolato, in particolare nelle vie legate al metabolismo, ai sistemi di secrezione e ai meccanismi di pompaggio dei farmaci che il batterio può usare per sfuggire al trattamento. Dalle proteine codificate da questi geni attivati, i ricercatori hanno eliminato qualunque proteina somigliante a quelle umane o a quelle di batteri intestinali comuni, per ridurre il rischio di effetti collaterali. Questo filtraggio ha lasciato una lista ristretta di proteine batteriche che sono sia importanti durante l’attacco farmacologico sia improbabili a confondere il sistema immunitario.
Costruire un vaccino a molti pezzi partendo da piccoli frammenti
Da questo insieme raffinato, gli scienziati hanno cercato brevi tratti di proteina, chiamati epitopi, che le cellule immunitarie umane riconoscono particolarmente bene. Si sono concentrati su due tipi: frammenti che stimolano le cellule T “uccisori”, che distruggono le cellule infette, e quelli che attivano le cellule T “helpers”, che coordinano difese immunitarie più ampie. Usando strumenti di predizione consolidati, hanno selezionato 12 epitopi per le cellule uccisori e 7 epitopi per le cellule helper che risultavano non tossici, poco probabili a scatenare allergie e con forte sicurezza di legarsi ai marcatori immunitari umani comuni. In modo cruciale, questi epitopi provenivano da proteine completamente conservate in diverse ceppi altamente virulenti di Acinetobacter, aumentando la probabilità che un singolo vaccino possa proteggere contro molte varianti del germe.
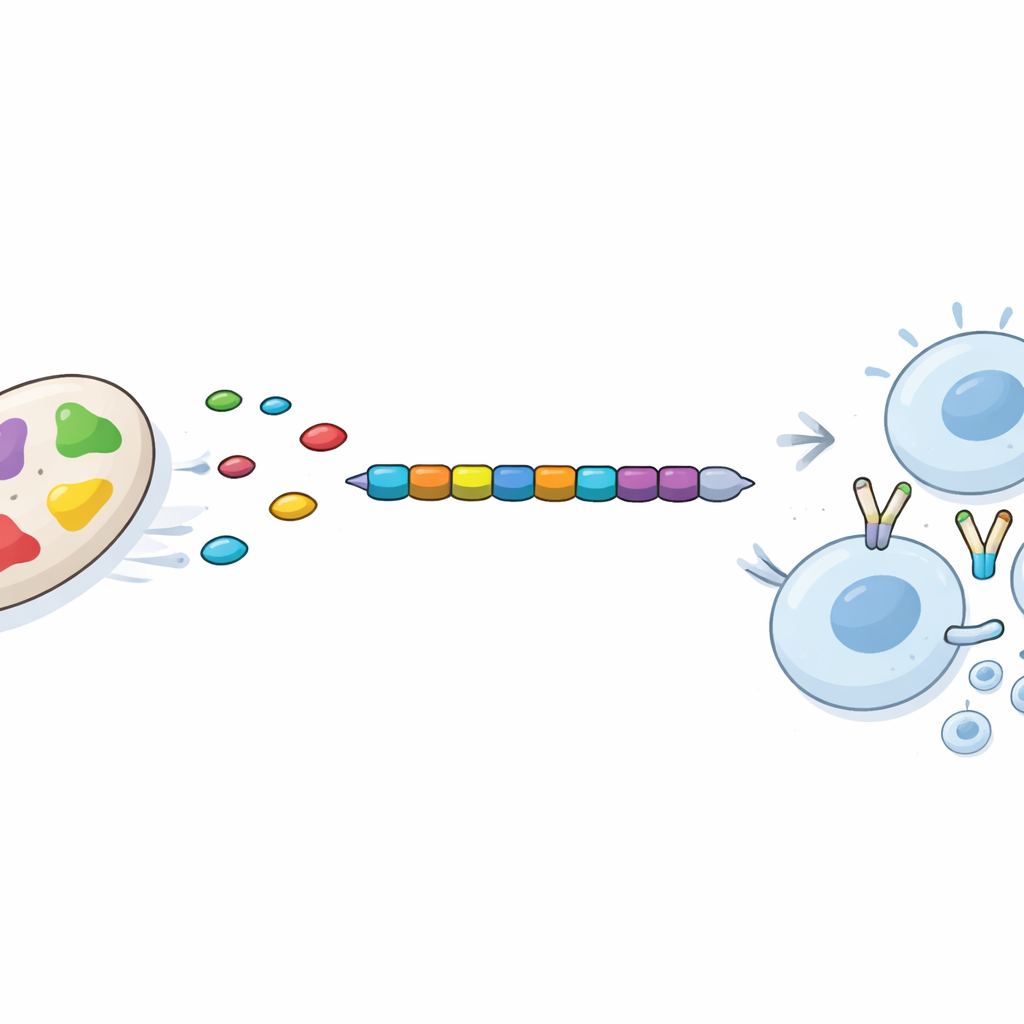
Testare il vaccino virtuale per stabilità e risposta
Gli epitopi scelti sono stati cuciti insieme in un ordine definito per creare un’unica proteina vaccinale di 335 amminoacidi, con un componente immunostimolante di origine umana aggiunto a un’estremità. Il team ha quindi usato modellazione computazionale all’avanguardia per prevedere come questa proteina multipezzo si ripiegherebbe in tre dimensioni e quanto sarebbe stabile in un ambiente acquoso come il corpo. Simulazioni dettagliate hanno suggerito che la struttura si stabilizza rapidamente in una forma compatta e stabile e la mantiene nel tempo. Studi separati di docking hanno indicato che ciascun epitope potrebbe adattarsi saldamente ai recettori immunitari umani. Infine, un simulatore in silico del sistema immunitario ha previsto che una dose di questo vaccino eliminerebbe rapidamente l’antigene introdotto, stimolerebbe la produzione precoce di anticorpi, attiverebbe fortemente le cellule T uccisori e helper e costruirebbe una memoria immunitaria duratura, tutto senza segnali di una risposta esagerata o sbilanciata.
Cosa significa e quali sono i prossimi passi
Questo lavoro non produce ancora un’iniezione pronta per i pazienti, ma dimostra quanto possano essere potenti i metodi basati sui computer per progettare vaccini che prendano di mira le caratteristiche che rendono un germe ospedaliero resistente ai farmaci. Concentrandosi su componenti batterici attivati durante lo stress da antibiotico e condivisi tra molti ceppi pericolosi, e assemblando più di questi frammenti in un unico costrutto, lo studio delinea un progetto promettente per un vaccino a copertura ampia contro Acinetobacter baumannii. I prossimi passi cruciali saranno studi di laboratorio e su animali per confermare che questo vaccino virtuale sia sicuro, stabile e protettivo nel mondo reale—un ponte essenziale dal progetto intelligente su uno schermo alla protezione salvavita al letto del paziente.
Citazione: Khadka, S., Khan, M.A., Iqbal, S. et al. In silico design of a multiepitope vaccine against antibiotic drug-resistant Acinetobacter baumannii. Sci Rep 16, 14151 (2026). https://doi.org/10.1038/s41598-025-30795-8
Parole chiave: resistenza agli antibiotici, infezioni ospedaliere, Acinetobacter baumannii, progettazione di vaccini, immunologia computazionale