Clear Sky Science · es
Diseño in silico de una vacuna multiepítopo contra Acinetobacter baumannii resistente a antibióticos
Por qué esto importa para la salud cotidiana
Los hospitales están pensados para curarnos, pero algunas de las infecciones más peligrosas surgen ahora dentro de ellos. Un culpable, una bacteria resistente llamada Acinetobacter baumannii, ha aprendido a hacerse la vista gorda ante muchos de nuestros antibióticos más potentes, convirtiendo una atención rutinaria en un riesgo potencialmente mortal para pacientes vulnerables. Este estudio explora una forma nueva de adelantarse a esos superbichos: usar ordenadores para diseñar una vacuna de nueva generación compuesta por fragmentos protéicos cuidadosamente seleccionados, con el objetivo de prevenir las infecciones antes de que empiecen.
Un germen hospitalario que no se va
Acinetobacter baumannii prospera en las superficies y el material hospitalario, donde puede infectar a personas con sistemas inmunitarios debilitados, enfermedad pulmonar crónica o estancias prolongadas en cuidados intensivos. Pertenece a un grupo notorio de microbios hospitalarios conocidos por su resistencia a múltiples fármacos. Una vez que este germen se vuelve resistente a los carbapenémicos, una clase de antibióticos de último recurso, los médicos se quedan con pocas opciones seguras. Como no existe una vacuna aprobada, la Organización Mundial de la Salud ha catalogado a esta bacteria como una prioridad máxima para el desarrollo de vacunas, lo que ha impulsado a los investigadores a buscar formas más inteligentes de atacarla.
Dejar que la bacteria revele sus puntos débiles
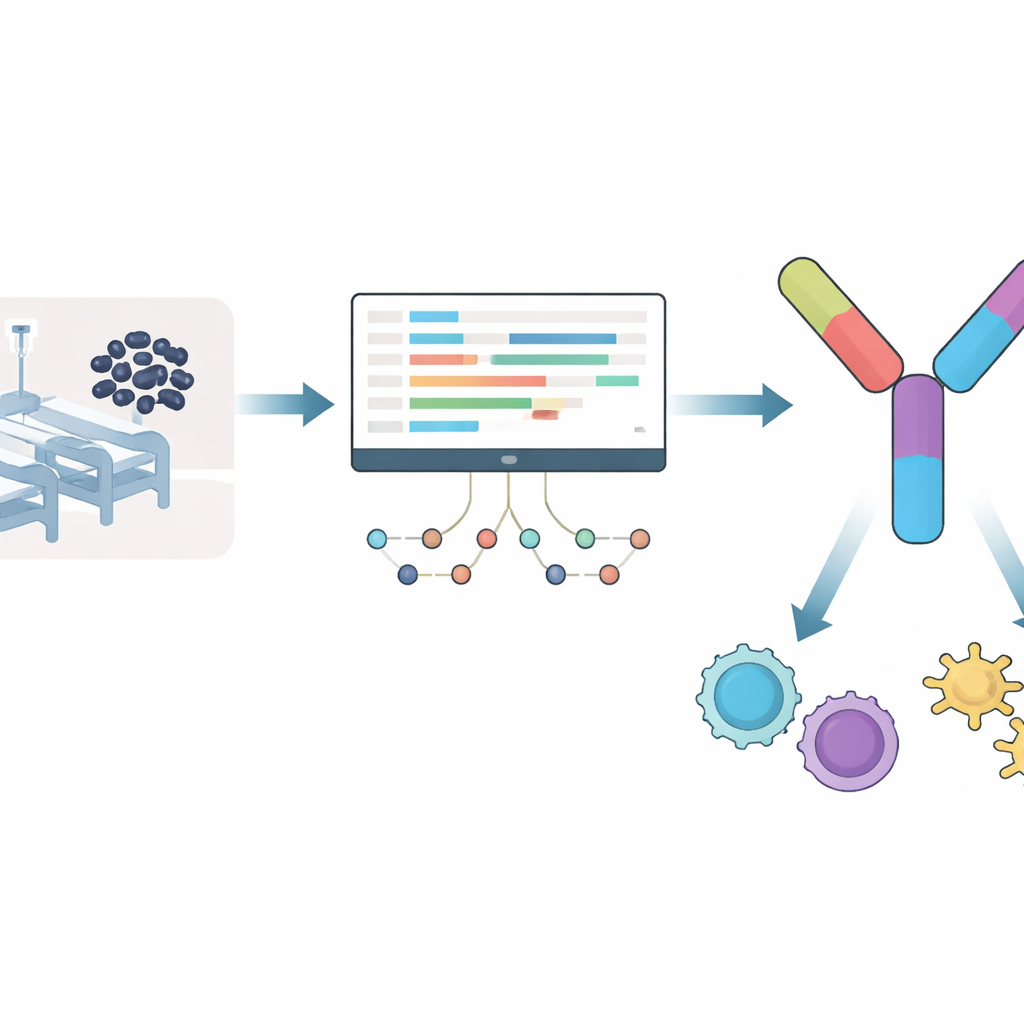
En lugar de partir de conjeturas sobre qué partes bacterianas podrían ser buenos blancos para una vacuna, el equipo observó cómo responde Acinetobacter baumannii cuando es atacada por un antibiótico clave, el meropenem. Analizaron datos de secuenciación de ARN, que muestran qué genes se activan o se silencian, después de nueve horas de exposición al fármaco. Más de mil genes se activaron y un número similar se reprimió, sobre todo en vías relacionadas con el metabolismo, sistemas de secreción y maquinaria de bombeo de fármacos que la bacteria puede usar para escapar del tratamiento. De las proteínas codificadas por esos genes activados, los investigadores eliminaron cualquier proteína que se pareciera a proteínas humanas o a las de las bacterias intestinales comunes, para reducir el riesgo de efectos secundarios. Este filtrado dejó una lista corta de proteínas bacterianas que son importantes bajo el ataque de antibióticos y que, probablemente, no confundirán al sistema inmunitario.
Construir una vacuna de muchas piezas a partir de fragmentos diminutos
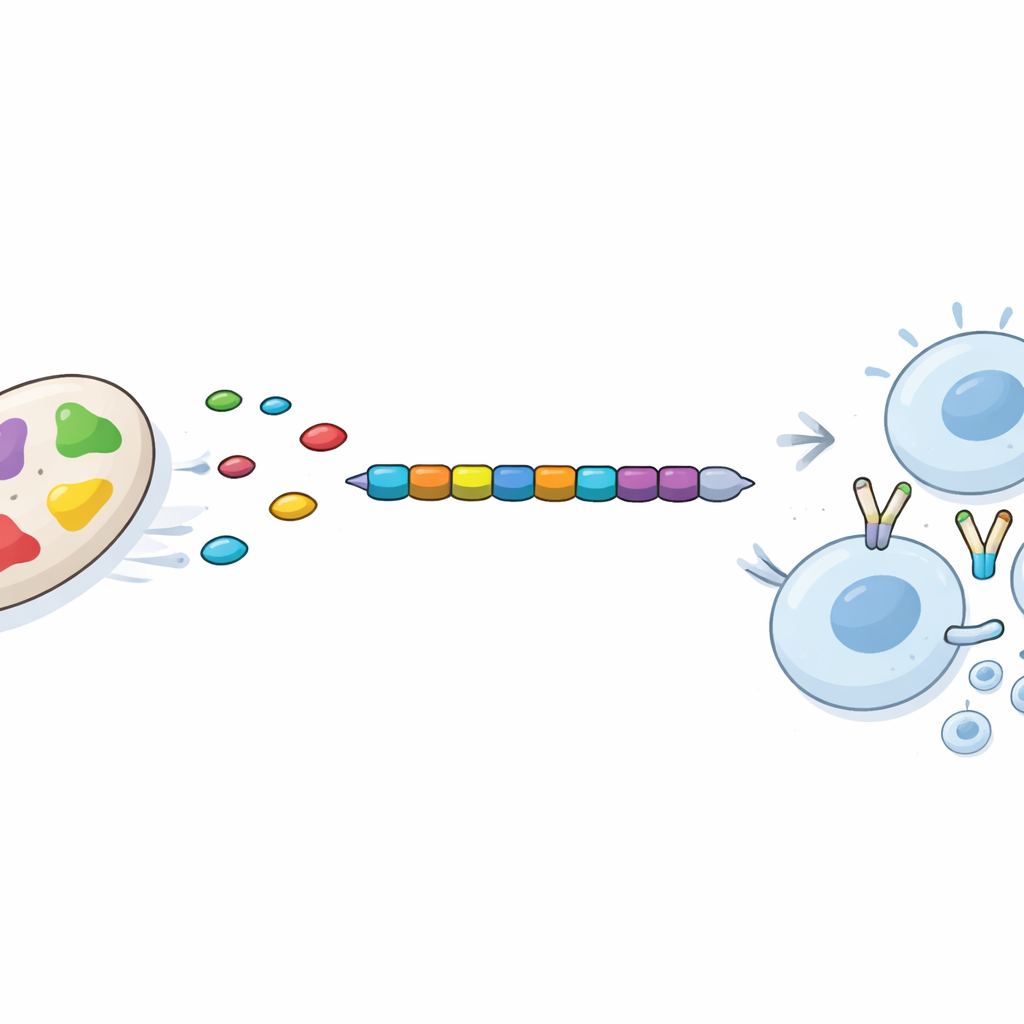
Del conjunto refinado, los científicos buscaron fragmentos cortos de proteína, llamados epítopos, que las células inmunitarias humanas reconocen especialmente bien. Se centraron en dos tipos: piezas que estimulan a los linfocitos T “asesinos”, que destruyen células infectadas, y otras que activan a los linfocitos T “cooperadores”, que coordinan defensas inmunitarias más amplias. Usando herramientas de predicción consolidadas, seleccionaron 12 epítopos para células asesinas y 7 para células cooperadoras que eran no tóxicos, poco probables de provocar alergias y con alta predicción de unión a marcadores inmunitarios humanos comunes. De forma crucial, estos epítopos provenían de proteínas totalmente conservadas entre varias cepas altamente virulentas de Acinetobacter, lo que aumenta la probabilidad de que una sola vacuna pueda proteger frente a muchas variantes del germen.
Probar la vacuna virtual en cuanto a estabilidad y respuesta
Los epítopos elegidos se cosieron en un orden definido para crear una única proteína vacuna de 335 aminoácidos, con un componente inmunoestimulador derivado del humano añadido en un extremo. El equipo utilizó entonces modelado computacional de última generación para predecir cómo se plegaría en tres dimensiones esta proteína multipieza y qué tan estable sería en un entorno acuoso como el del cuerpo. Simulaciones detalladas sugirieron que la estructura se asentaba rápidamente en una forma compacta y estable y la mantenía a lo largo del tiempo. Estudios de acoplamiento por separado indicaron que cada epítopo podía encajar con precisión en receptores inmunitarios humanos. Por último, un simulador in silico del sistema inmune predijo que una dosis de esta vacuna eliminaría rápidamente el antígeno introducido, estimularía la producción temprana de anticuerpos, activaría con fuerza a los linfocitos T asesinos y cooperadores, y construiría memoria inmunitaria duradera, todo ello sin señales de una respuesta exagerada o descompensada.
Qué significa esto y qué sigue
Este trabajo aún no produce una inyección lista para pacientes, pero muestra lo poderosos que pueden ser los métodos basados en ordenador para diseñar vacunas que apunten a las mismas características que hacen a un germen hospitalario resistente a los fármacos. Al centrarse en componentes bacterianos que se activan durante el estrés por antibióticos y que están compartidos entre muchas cepas peligrosas, y al ensamblar múltiples de esas piezas en un solo constructo, el estudio traza un plan prometedor para una vacuna de amplia cobertura contra Acinetobacter baumannii. Los siguientes pasos cruciales serán estudios de laboratorio y en animales para confirmar que esta vacuna virtual es segura, estable y protectora en el mundo real —un puente esencial desde un diseño ingenioso en pantalla hasta la protección que salva vidas en la cama del hospital.
Cita: Khadka, S., Khan, M.A., Iqbal, S. et al. In silico design of a multiepitope vaccine against antibiotic drug-resistant Acinetobacter baumannii. Sci Rep 16, 14151 (2026). https://doi.org/10.1038/s41598-025-30795-8
Palabras clave: resistencia a los antibióticos, infecciones hospitalarias, Acinetobacter baumannii, diseño de vacunas, inmunología computacional