Clear Sky Science · de
In silico-Entwurf eines multiepitope Impfstoffs gegen antibiotikaresistentes Acinetobacter baumannii
Warum das für die Gesundheit im Alltag wichtig ist
Krankenhäuser sollen uns heilen, doch einige der gefährlichsten Infektionen entstehen heute gerade dort. Ein Übeltäter, das widerstandsfähige Bakterium Acinetobacter baumannii, hat gelernt, vielen unserer stärksten Antibiotika zu trotzen und verwandelt so routinemäßige Pflege für gefährdete Patientinnen und Patienten in ein lebensbedrohliches Risiko. Diese Studie untersucht einen neuen Weg, um solchen Superkeimen voraus zu sein: Computerbasiertes Design eines Impfstoffs der nächsten Generation aus gezielt ausgewählten kleinen Proteinfragmenten, mit dem Ziel, Infektionen zu verhindern, bevor sie beginnen.
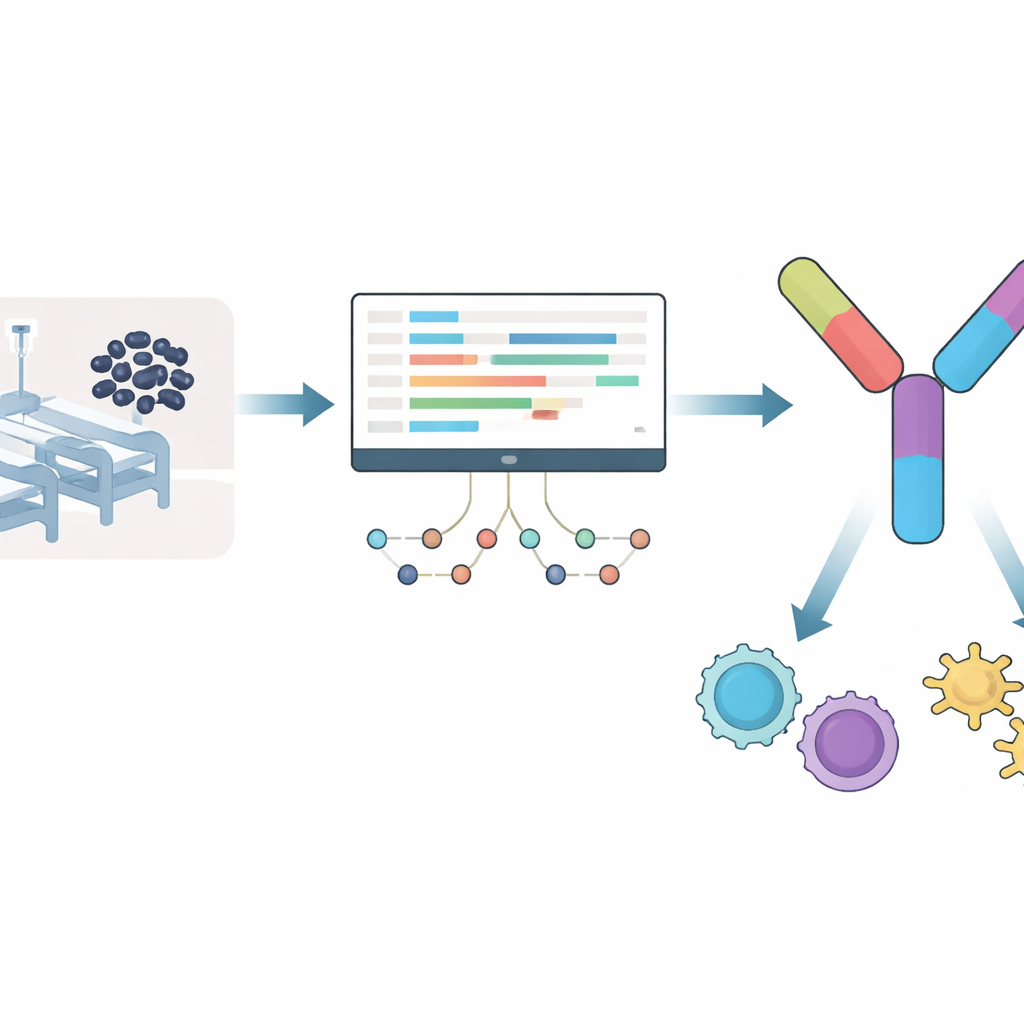
Ein Krankenhauskeim, der nicht verschwindet
Acinetobacter baumannii gedeiht auf Krankenhausoberflächen und -geräten und kann Menschen mit geschwächtem Immunsystem, chronischen Lungenerkrankungen oder langen Aufenthalten auf Intensivstationen infizieren. Er gehört zu einer berüchtigten Gruppe nosokomialer Keime, die für ihre Multiresistenz bekannt sind. Sobald dieser Erreger gegenüber Carbapenemen resistent wird — einer Klasse von Reserveantibiotika — stehen Ärztinnen und Ärzten nur noch wenige sichere Optionen zur Verfügung. Da kein zugelassener Impfstoff existiert, hat die Weltgesundheitsorganisation dieses Bakterium als vorrangig für die Impfstoffentwicklung eingestuft, was Forschende dazu anspornt, intelligentere Zielstrategien zu suchen.
Dem Bakterium seine Schwachstellen entlocken
Anstatt aus der Ferne zu raten, welche bakteriellen Komponenten geeignete Impfstoffziele sein könnten, beobachtete das Team, wie Acinetobacter baumannii reagiert, wenn es von einem wichtigen Antibiotikum, Meropenem, angegriffen wird. Sie analysierten RNA-Sequenzierungsdaten, die zeigen, welche Gene nach neun Stunden Medikamentenexposition an- oder ausgeschaltet sind. Mehr als tausend Gene wurden hochreguliert und eine ähnliche Anzahl runterreguliert, insbesondere in Signalwegen, die mit Stoffwechsel, Sekretionssystemen und dem Wirkstoffpumpen zusammenhängen — Mechanismen, die das Bakterium zur Behandlungsevasion nutzen könnte. Aus den Proteinen dieser aktivierten Gene schlossen die Forschenden alle aus, die menschlichen Proteinen oder solchen häufiger Darmbakterien ähnelten, um das Risiko von Nebenwirkungen zu verringern. Diese Filterung ergab eine Kurzliste bakterieller Proteine, die sowohl unter Antibiotikadruck wichtig sind als auch das Immunsystem vermutlich nicht verwirren.
Aufbau eines Impfstoffs aus vielen kleinen Stücken
Aus diesem bereinigten Satz suchten die Wissenschaftler nach kurzen Proteinabschnitten, sogenannten Epitopen, die vom menschlichen Immunsystem besonders gut erkannt werden. Sie konzentrierten sich auf zwei Typen: Abschnitte, die „Killer“-T-Zellen stimulieren, welche infizierte Zellen zerstören, und solche, die „Helfer“-T-Zellen aktivieren, die breitere Immunantworten koordinieren. Mithilfe etablierter Vorhersagewerkzeuge wählten sie 12 Killer-Zell-Epitope und 7 Helfer-Zell-Epitope aus, die nicht toxisch, vermutlich nicht allergen und voraussichtlich stark an gängige menschliche Immunmarker binden. Entscheidend war, dass diese Epitope aus Proteinen stammten, die über mehrere hochvirulente Stämme von Acinetobacter vollständig konserviert waren, was die Chance erhöht, dass ein einziger Impfstoff gegen viele Varianten des Erregers schützt.
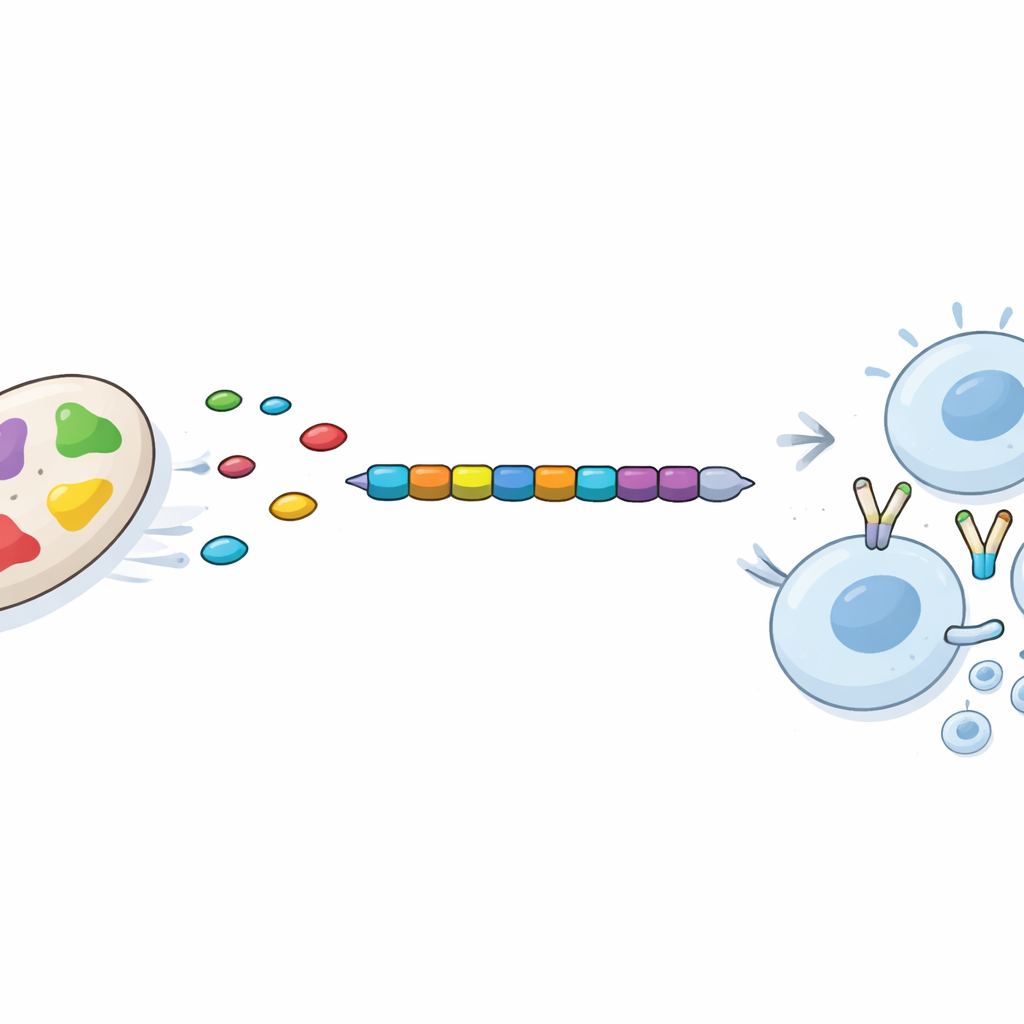
Prüfung des virtuellen Impfstoffs auf Stabilität und Reaktion
Die ausgewählten Epitope wurden in einer definierten Reihenfolge zusammengefügt, um ein einzelnes Impfstoffprotein von 335 Aminosäuren zu erzeugen, dem ein menschlich abgeleiteter immunverstärkender Bestandteil an einem Ende hinzugefügt wurde. Das Team nutzte anschließend moderne Computermodellierung, um vorherzusagen, wie dieses mehrteilige Protein sich dreidimensional faltet und wie stabil es in einer wässrigen Umgebung wie dem Körper wäre. Detaillierte Simulationen deuteten darauf hin, dass die Struktur sich schnell in eine kompakte, stabile Form einstellte und diese über die Zeit beibehielt. Separate Docking-Studien zeigten, dass jedes Epitop passgenau in menschliche Immunrezeptoren einzufügen sein könnte. Schließlich sagte ein in silico Simulator des Immunsystems voraus, dass eine Dosis dieses Impfstoffs das eingeführte Antigen rasch beseitigen, eine frühe Antikörperproduktion anregen, Killer- und Helfer-T-Zellen stark aktivieren und eine dauerhafte Immunerinnerung aufbauen würde — und das ohne Anzeichen einer übertriebenen oder unausgewogenen Reaktion.
Was das bedeutet und wie es weitergeht
Diese Arbeit liefert noch keinen sofort einsatzbereiten Impfstoff für Patientinnen und Patienten, zeigt aber, wie kraftvoll computerbasierte Methoden beim Design von Impfstoffen sein können, die gerade die Eigenschaften ins Visier nehmen, die einen Krankenhauskeim resistent gegen Medikamente machen. Indem sie sich auf bakterielle Komponenten konzentrieren, die unter Antibiotikastress aktiv sind und über viele gefährliche Stämme geteilt werden, und indem sie mehrere dieser Teile in einem Konstrukt vereinen, skizziert die Studie einen vielversprechenden Bauplan für einen breit wirksamen Impfstoff gegen Acinetobacter baumannii. Die nächsten entscheidenden Schritte werden Labor- und Tierstudien sein, um zu bestätigen, dass dieser virtuelle Impfstoff in der realen Welt sicher, stabil und schützend ist — eine notwendige Brücke vom cleveren Design auf dem Bildschirm zum lebensrettenden Schutz am Krankenbett.
Zitation: Khadka, S., Khan, M.A., Iqbal, S. et al. In silico design of a multiepitope vaccine against antibiotic drug-resistant Acinetobacter baumannii. Sci Rep 16, 14151 (2026). https://doi.org/10.1038/s41598-025-30795-8
Schlüsselwörter: Antibiotikaresistenz, Krankenhausinfektionen, Acinetobacter baumannii, Impfstoffdesign, computationale Immunologie