Clear Sky Science · fr
Conception in silico d’un vaccin multi-épitopes contre Acinetobacter baumannii résistant aux antibiotiques
Pourquoi cela compte pour la santé quotidienne
Les hôpitaux sont faits pour nous soigner, et pourtant certaines des infections les plus dangereuses y prennent naissance. Un coupable, une bactérie résistante nommée Acinetobacter baumannii, a appris à esquiver nombre de nos antibiotiques les plus puissants, transformant des soins de routine en risque mortel pour les patients vulnérables. Cette étude explore une nouvelle façon de prendre de l’avance sur ces super‑microbes : utiliser des ordinateurs pour concevoir un vaccin de nouvelle génération constitué de fragments protéiques soigneusement choisis, dans le but de prévenir les infections avant qu’elles ne commencent.
Un germe hospitalier qui ne disparaît pas
Acinetobacter baumannii prospère sur les surfaces et le matériel hospitaliers, où il peut infecter des personnes à système immunitaire affaibli, atteintes de maladies pulmonaires chroniques ou à séjour prolongé en soins intensifs. Il appartient à un groupe notoire de microbes hospitaliers connus pour leur résistance à de multiples médicaments. Une fois que ce germe devient résistant aux carbapénèmes, une classe d’antibiotiques de dernier recours, les médecins disposent de peu d’options sûres. En l’absence de vaccin approuvé, l’Organisation mondiale de la Santé a classé cette bactérie comme une priorité majeure pour le développement de vaccins, poussant les chercheurs à chercher des moyens plus intelligents pour la cibler.
Lettre au germe pour révéler ses points faibles
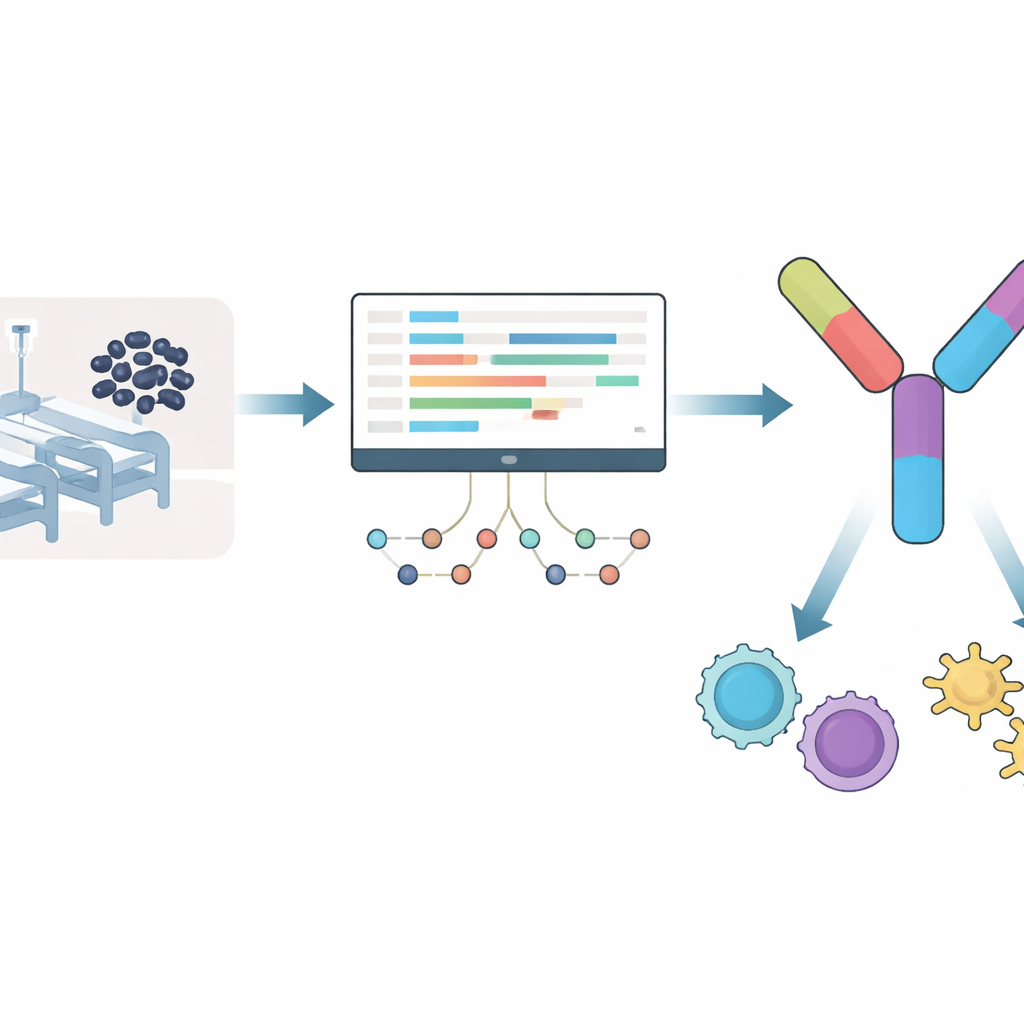
Plutôt que de partir d’hypothèses sur les parties bactériennes qui pourraient constituer de bons cibles vaccinales, l’équipe a observé comment Acinetobacter baumannii réagit lorsqu’il est attaqué par un antibiotique clé, la méropénem. Ils ont analysé des données de séquençage ARN, qui montrent quels gènes sont activés ou désactivés, après neuf heures d’exposition au médicament. Plus d’un millier de gènes ont été surexprimés et un nombre similaire réprimés, en particulier dans des voies liées au métabolisme, aux systèmes de sécrétion et aux machines d’expulsion de médicaments que la bactérie peut utiliser pour échapper au traitement. Parmi les protéines codées par ces gènes activés, les chercheurs ont éliminé celles qui ressemblaient à des protéines humaines ou à celles de bactéries intestinales communes, afin de réduire le risque d’effets indésirables. Ce filtrage a laissé une liste restreinte de protéines bactériennes qui sont à la fois importantes sous stress antibiotique et peu susceptibles de perturber le système immunitaire.
Assembler un vaccin à pièces multiples à partir de petits fragments
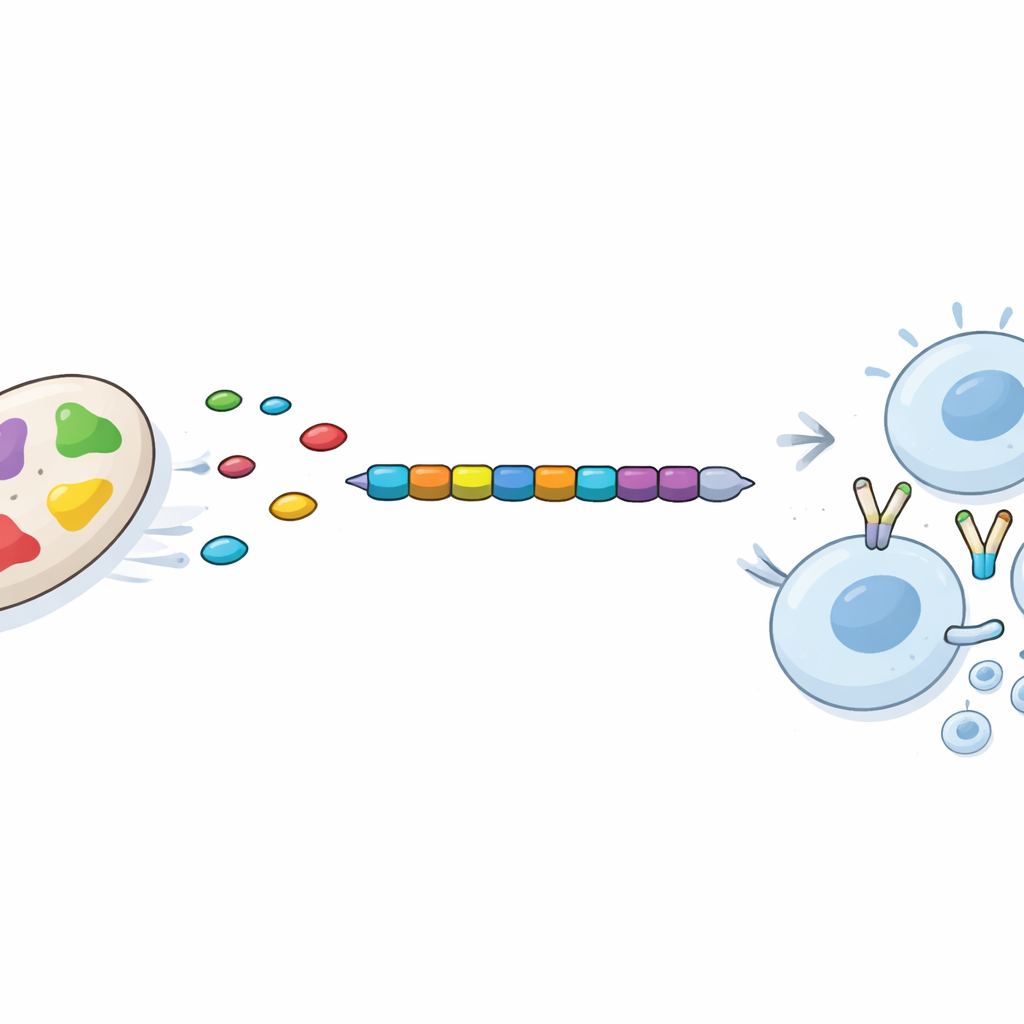
À partir de cet ensemble affiné, les scientifiques ont recherché de courtes séquences protéiques, appelées épitopes, que les cellules immunitaires humaines reconnaissent particulièrement bien. Ils se sont concentrés sur deux types : des morceaux qui stimulent les cellules T « tueuses », qui détruisent les cellules infectées, et ceux qui activent les cellules T « auxiliaires », qui coordonnent des défenses immunitaires plus larges. En utilisant des outils de prédiction établis, ils ont sélectionné 12 épitopes pour les cellules tueuses et 7 pour les cellules auxiliaires, non toxiques, peu susceptibles de déclencher des allergies et fortement prédits pour se lier aux marqueurs immunitaires humains courants. De façon cruciale, ces épitopes provenaient de protéines entièrement conservées entre plusieurs souches hautement virulentes d’Acinetobacter, augmentant la probabilité qu’un seul vaccin puisse protéger contre de nombreuses variantes du germe.
Tester le vaccin virtuel pour la stabilité et la réponse
Les épitopes choisis ont été enchaînés dans un ordre défini pour créer une seule protéine vaccinale de 335 acides aminés, avec un composant immunostimulant d’origine humaine ajouté à une extrémité. L’équipe a ensuite utilisé la modélisation informatique de pointe pour prédire la manière dont cette protéine multi‑éléments se replierait en trois dimensions et sa stabilité dans un milieu aqueux similaire à l’organisme. Des simulations détaillées ont suggéré que la structure se stabilisait rapidement en une forme compacte et stable et la conservait au fil du temps. Des études d’amarrage séparées ont indiqué que chaque épitope pouvait s’emboîter étroitement dans les récepteurs immunitaires humains. Enfin, un simulateur in silico du système immunitaire a prédit qu’une dose de ce vaccin éliminerait rapidement l’antigène introduit, déclencherait une production précoce d’anticorps, activerait fortement les cellules T tueuses et auxiliaires et établirait une mémoire immunitaire durable, le tout sans signes d’une réponse exagérée ou déséquilibrée.
Ce que cela signifie et les étapes suivantes
Ce travail ne fournit pas encore une injection prête pour les patients, mais il montre la puissance des méthodes informatiques pour concevoir des vaccins qui ciblent précisément les caractéristiques rendant un germe hospitalier résistant aux médicaments. En se concentrant sur des composants bactériens activés pendant le stress antibiotique et partagés par de nombreuses souches dangereuses, et en assemblant plusieurs de ces éléments en un seul construct, l’étude décrit un plan prometteur pour un vaccin à large couverture contre Acinetobacter baumannii. Les prochaines étapes cruciales seront des études en laboratoire et chez l’animal pour confirmer que ce vaccin virtuel est sûr, stable et protecteur dans le monde réel — un pont essentiel entre la conception astucieuse sur écran et une protection salvatrice au chevet.
Citation: Khadka, S., Khan, M.A., Iqbal, S. et al. In silico design of a multiepitope vaccine against antibiotic drug-resistant Acinetobacter baumannii. Sci Rep 16, 14151 (2026). https://doi.org/10.1038/s41598-025-30795-8
Mots-clés: résistance aux antibiotiques, infections nosocomiales, Acinetobacter baumannii, conception de vaccin, immunologie computationnelle