Clear Sky Science · it
Varianti molecolari, evoluzione clonale e rilevanza clinica nelle neoplasie linfoblastiche T pediatriche e adulte
Perché questi tumori del sangue sono importanti per le famiglie
Le leucemie e i linfomi a cellule T sono neoplasie aggressive che colpiscono prevalentemente bambini, adolescenti e giovani adulti. Nonostante le terapie moderne, molti pazienti che vanno incontro a recidiva continuano ad avere scarse probabilità di sopravvivenza. Questo studio pone una domanda apparentemente semplice ma con grandi implicazioni pratiche: la leucemia a cellule T riscontrata in sangue e midollo osseo e il linfoma linfoblastico T, che si trova nei linfonodi, sono davvero la stessa malattia o si comportano in modo diverso a livello genetico — e questa conoscenza può aiutare i medici a prevedere meglio chi avrà una recidiva?
Due tumori correlati sotto la lente
I ricercatori hanno analizzato campioni tumorali di 211 bambini e adulti con leucemia linfoblastica acuta a cellule T (T-ALL) o linfoma linfoblastico a cellule T (T-LBL). Entrambe le neoplasie originano da precursori T molto primitivi nel timo ma sono solitamente classificate in base alla sede predominante delle cellule tumorali: prevalentemente midollo osseo e sangue per la leucemia, e principalmente linfonodi o altri tessuti per il linfoma. Attraverso il sequenziamento del DNA moderno e scansioni genomiche estese, il team ha catalogato diversi tipi di danno genetico — piccole variazioni del DNA e più ampie acquisizioni o perdite di porzioni cromosomiche — e ha confrontato i modelli tra fasce d’età e tra le due malattie.
Radici condivise con sfumature legate all’età
Nel complesso, T-ALL e T-LBL si sono rivelate condividere un set molto simile di geni “driver” — geni che, quando alterati, favoriscono l’avvio o il mantenimento del cancro. Un gene in particolare, NOTCH1, era alterato nella maggioranza dei pazienti in tutti i gruppi e tendeva a essere più comune nei pazienti più giovani. Un altro gene, PHF6, aumentava di frequenza con l’età. Pur avendo un numero totale di mutazioni per paziente simile tra i gruppi, le alterazioni cromosomiche di grande entità si accumulavano con l’età in T-ALL ma non in T-LBL. Alcune acquisizioni e perdite cromosomiche erano associate alla recidiva nei bambini con linfoma, suggerendo che anche tumori strettamente correlati possono invecchiare ed evolvere in modi diversi.
Colpi iniziali che plasmano l’albero genealogico del cancro
Analizzando più in profondità, il team ha ricostruito come ogni tumore si è sviluppato nel tempo, costruendo gli “alberi genealogici” dei cloni tumorali. Hanno osservato che le alterazioni su larga scala del cromosoma 9, in particolare delezioni o perdita di una delle copie parentali, erano spesso tra i primissimi eventi genetici sia nella leucemia sia nel linfoma. Questi eventi iniziali interessavano frequentemente un tratto del cromosoma 9 che include importanti geni di controllo del ciclo cellulare, rimuovendo di fatto freni chiave alla crescita cellulare. In molti bambini, le cellule portanti questo danno al cromosoma 9 acquisivano successivamente mutazioni di NOTCH1, dando origine a nuovi rami del tumore che potevano espandersi o estinguersi durante il trattamento.
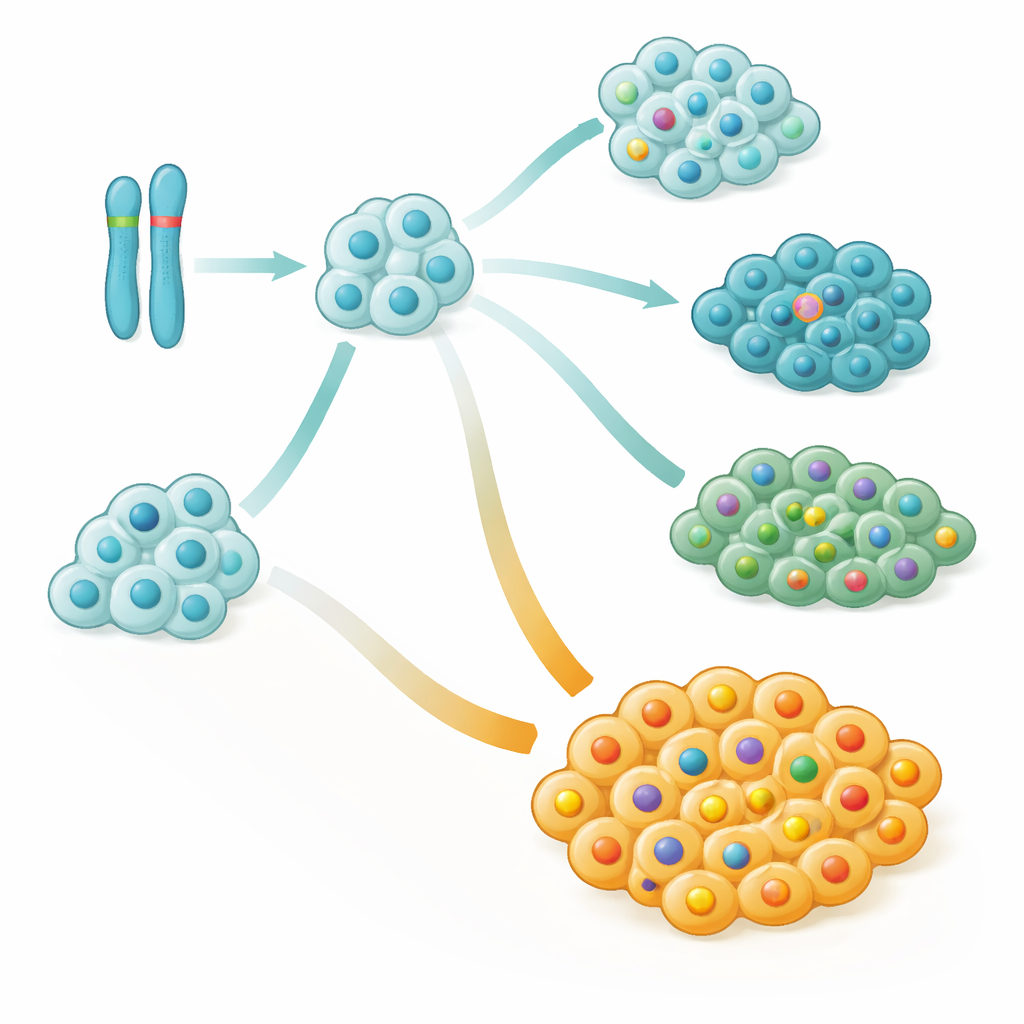
Rami favorevoli e sfavorevoli all’interno dello stesso tumore
Un’intuizione sorprendente è stata che le alterazioni di NOTCH1, a lungo considerate semplicemente promotrici di cancro, erano in realtà associate a esiti migliori quando comparivano precocemente e dominavano il tumore. I pazienti tendevano ad avere prognosi peggiore quando una larga frazione delle loro cellule tumorali era priva di mutazioni di NOTCH1, anche se alcune cellule le presentavano. In termini statistici, ogni piccolo incremento nella proporzione di cellule tumorali con NOTCH1 intatto si traduceva in un aumento significativo del rischio di recidiva. Studi di casi dettagliati hanno mostrato che recidive aggressive spesso derivavano da rami minori dell’albero genealogico del tumore che non avevano mai acquisito mutazioni in NOTCH1 ma avevano invece accumulato altre alterazioni dannose.
Cosa significa per pazienti e medici
Lo studio suggerisce che in questi tumori a cellule T il quando e il dove una mutazione compare nell’albero genealogico del tumore conta tanto quanto quale gene sia mutato. Il danno cromosomico precoce al cromosoma 9 sembra predisporre la scena, mentre rami diversi — con o senza alterazioni di NOTCH1 — competono e rispondono in modo differente alla terapia. Per i pazienti, questo apre la possibilità di stime di rischio più precise: non solo chiedersi “NOTCH1 è mutato?” ma piuttosto “quanta parte del tumore è guidata da cellule NOTCH1-mutanti rispetto a cellule NOTCH1-intatte?” Gli autori sostengono che queste informazioni clonali, già promettenti nei linfomi, potrebbero essere impiegate per affinare i gruppi di rischio e l’intensità terapeutica anche nella leucemia a cellule T, aiutando a calibrare meglio le terapie sul reale rischio di recidiva di ciascun paziente.
Citazione: Sandmann, S., te Vrugt, M., Randau, G. et al. Molecular variants, clonal evolution and clinical relevance in pediatric and adult T-cell lymphoblastic neoplasia. Blood Cancer J. 16, 57 (2026). https://doi.org/10.1038/s41408-026-01488-w
Parole chiave: Leucemia a cellule T, Linfoma a cellule T, evoluzione clonale, alterazioni del cromosoma 9, mutazione NOTCH1