Clear Sky Science · es
Generación de fármacos covalentes de novo con mayor asequibilidad como medicamento y seguridad
Por qué importan los fármacos covalentes más inteligentes
Las terapias contra el cáncer y los antivirales a menudo actúan uniéndose a proteínas dentro de nuestras células. Una clase potente de medicamentos, denominados fármacos covalentes, va un paso más allá: forman enlaces firmes y duraderos con sus dianas, lo que puede aumentar considerablemente su eficacia. Pero esa misma «adherencia» puede provocar efectos secundarios graves si los compuestos se unen a proteínas equivocadas. Este estudio presenta CovaGEN, un nuevo sistema de inteligencia artificial diseñado para generar candidatos a fármacos covalentes desde cero teniendo en cuenta tanto la eficacia como la seguridad.
Del ensayo y error al diseño inteligente
El descubrimiento tradicional de fármacos covalentes es lento y costoso. Los químicos suelen partir de un fármaco existente y añadirle un «mango» reactivo, o bien comienzan con un fragmento reactivo y afinan laboriosamente el resto de la molécula. Los métodos asistidos por ordenador ayudan al cribar grandes bibliotecas de compuestos conocidos, pero se limitan a lo que ya existe. Los avances recientes en aprendizaje profundo pueden generar moléculas enteramente nuevas, sin embargo, estas herramientas suelen centrarse en fármacos convencionales no covalentes y a menudo ignoran rasgos cruciales como la facilidad de síntesis, si un compuesto se comporta como un medicamento real o su posible toxicidad. CovaGEN pretende afrontar todos estos problemas de forma simultánea.
Un mapa oculto de la química con carácter farmacéutico
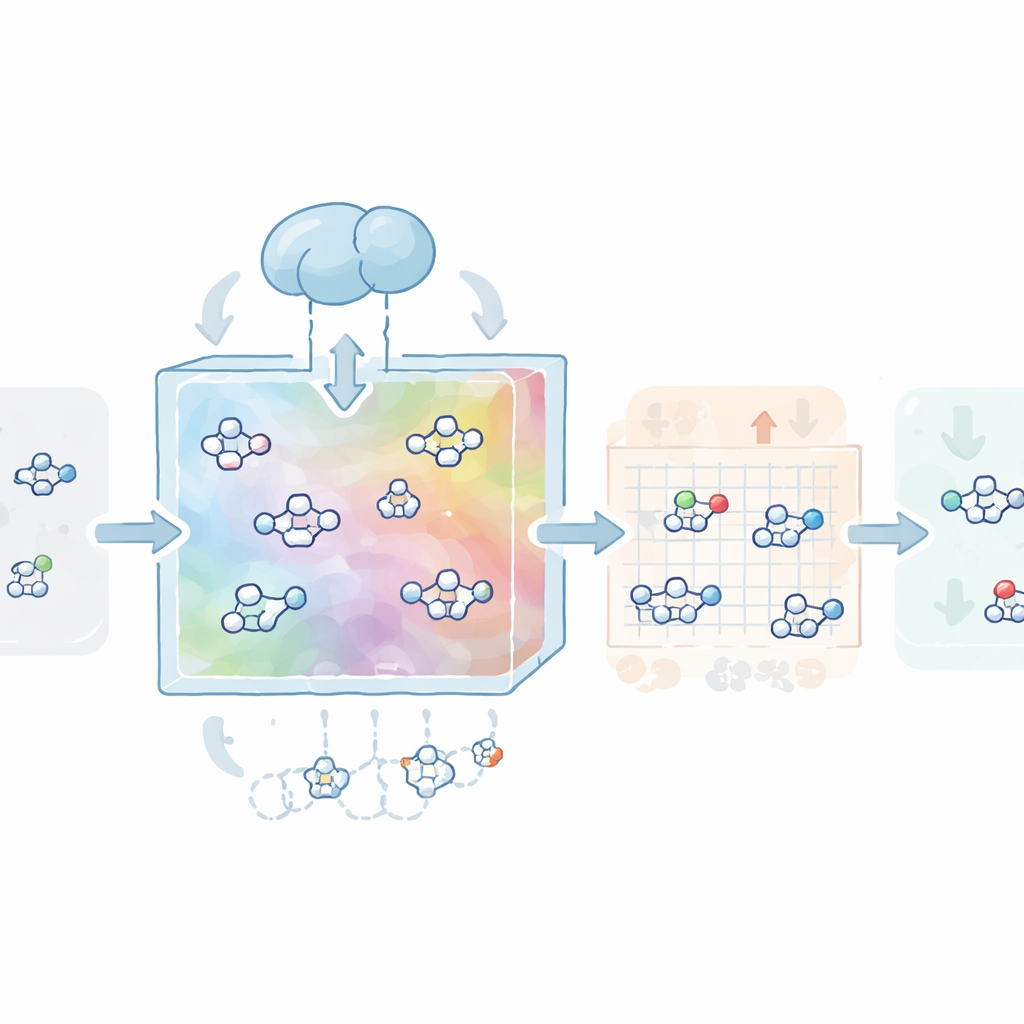
Los autores construyeron primero un «mapa» del espacio químico usando más de un millón de moléculas con aspecto de fármaco procedentes de la base de datos pública ZINC. Entrenaron un tipo de red neuronal llamada autoencoder variacional para comprimir cada molécula en un código numérico compacto, o vector latente, y luego reconstruirla. Este paso enseña al modelo la gramática básica de la química medicinal: qué resulta realista, qué respeta las reglas comunes para fármacos orales y qué tiende a ser sintéticamente factible. Sobre este mapa aprendido, se entrenó un segundo modelo basado en difusión —un proceso que convierte gradualmente la estructura en ruido y aprende después a invertir ese proceso— para explorar y generar nuevos vectores latentes que decodifican en moléculas válidas, diversas y realistas.
Ajustar moléculas a proteínas y ganchos reactivos
A continuación, CovaGEN aprende a diseñar moléculas para dianas proteicas específicas. El sistema toma la secuencia de aminoácidos de una proteína y la codifica con un potente modelo de lenguaje para proteínas, que captura patrones relacionados con estructura y función. Durante la difusión, el modelo atiende mediante cross‑attention a esta representación de la proteína para que las moléculas que genera estén predispuestas a encajar en el sitio de unión de la diana. En pruebas con un amplio conjunto de referencia, estas moléculas a medida no solo obtuvieron buenos puntajes en afinidad de unión predicha, sino que también mostraron mayor carácter farmacológico y accesibilidad sintética que las generadas por varias herramientas 3D de última generación. Para convertir estos ligandos no covalentes en candidatos covalentes, el equipo añadió un clasificador que orienta el proceso de difusión hacia moléculas que portan ciertos grupos reactivos, conocidos como warheads covalentes, sin sacrificar la calidad global.
Incorporar la seguridad desde el inicio
Dado que los fármacos covalentes pueden causar daños duraderos si atacan dianas equivocadas, la seguridad es una preocupación central. Por eso los investigadores trataron la toxicidad como una magnitud a optimizar, no como una ocurrencia posterior. Entrenaron modelos predictivos de toxicidad aguda y de riesgos orgánicos específicos, y luego aplicaron aprendizaje por refuerzo para afinar el modelo de difusión de modo que prefiera moléculas con menor toxicidad predicha. Tras este entrenamiento, CovaGEN generó compuestos que mantenían buena afinidad y rasgos farmacológicos, pero eran menos propensos a contener «señales rojas» estructurales asociadas con efectos dañinos. Es importante destacar que el método consiguió esto sin colapsar hacia un conjunto estrecho de moléculas similares, preservando la diversidad química.
Poner el método a prueba
Para demostrar el potencial en el mundo real, el equipo pidió a CovaGEN que diseñara inhibidores covalentes para dos dianas de alto interés: una forma mutante de la proteína EGFR implicada en cáncer de pulmón resistente a fármacos, y la proteasa principal del SARS‑CoV‑2, el virus responsable de la COVID‑19. Para cada proteína, el sistema generó numerosos candidatos equipados con los warheads apropiados. Estudios de acoplamiento por ordenador sugirieron que los diseños de CovaGEN tenían más probabilidades de adoptar posturas capaces de formar enlaces covalentes que compuestos en los que los warheads se habían añadido simplemente a diseños no covalentes. Varios de los mejores candidatos también igualaron o superaron a fármacos de referencia en medidas combinadas de afinidad predicha, carácter farmacéutico y facilidad sintética.
Qué significa esto para los medicamentos del futuro
CovaGEN demuestra que la IA generativa moderna puede hacer más que imaginar moléculas que se adhieran con fuerza a proteínas. Al trabajar en un espacio de estructuras intrínsecamente con carácter farmacéutico, guiar la adición de grupos reactivos y alejarse explícitamente de la toxicidad, el sistema avanza el descubrimiento de fármacos covalentes hacia un proceso más holístico y automatizado. Aunque serán necesarias más pruebas de laboratorio para confirmar cómo se comportan estas moléculas virtuales en sistemas biológicos, el enfoque abre una vía para una exploración más rápida y amplia de fármacos covalentes que no solo sean potentes, sino también más seguros para los pacientes.
Cita: Zhang, W., Liu, T., Dong, X. et al. De novo covalent drug generation with enhanced drug-likeness and safety. Commun Biol 9, 446 (2026). https://doi.org/10.1038/s42003-026-09725-5
Palabras clave: fármacos covalentes, IA generativa, descubrimiento de fármacos, modelos de difusión, predicción de toxicidad