Clear Sky Science · de
Cut-Instance-Mixing: Eine domänenspezifische Datenaugmentationsmethode angewendet auf die Erkennung gastrointestinaler Läsionen
Warum intelligentere Trainingsdaten für die Darmgesundheit wichtig sind
Ärztinnen und Ärzte nutzen winzige Kameras, um in unseren Verdauungstrakt zu schauen und frühe Krankheitszeichen zu erkennen, etwa kleine auffällige Stellen, die sich eines Tages zu Krebs entwickeln können. Diese Warnzeichen sind jedoch oft extrem subtil, und Computer, die Ärztinnen und Ärzten bei der Entdeckung helfen könnten, benötigen Tausende gut annotierter Bilder, um zu lernen, worauf sie achten müssen. Dieser Beitrag stellt eine neue Methode vor, um realistische Trainingsbilder rechnerisch zu „erzeugen“, wodurch es einfacher wird, KI-Systeme darin zu schulen, diese schwer sichtbaren Läsionen frühzeitig zu erkennen.
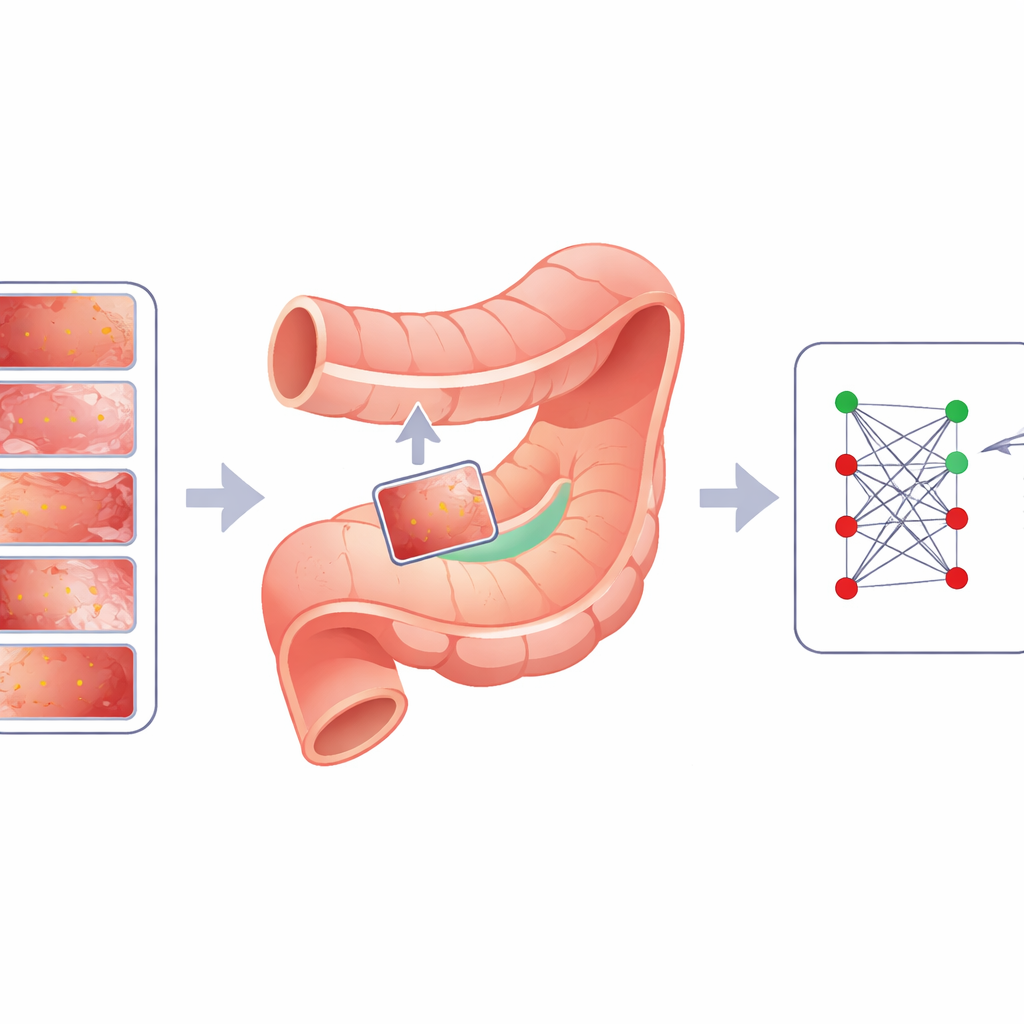
Die Herausforderung der versteckten Warnpunkte
Läsionen im Magen und Darm – wie intestinale Metaplasie, frühe Dysplasien und kleine Polypen – sind wichtige frühe Warnsignale für Krebs, sehen aber häufig nur geringfügig anders aus als gesundes Gewebe. Auch menschliche Expertinnen und Experten übersehen sie mitunter, und Computermodelle haben ähnliche Schwierigkeiten, vor allem weil es nicht genügend qualitativ hochwertige, sorgfältig beschriftete Bilder zum Lernen gibt. Das Sammeln und Annotieren von Endoskopiebildern ist teuer, zeitaufwendig und ethisch sensibel, insbesondere bei seltenen Läsionstypen. Traditionelle Tricks zur Erweiterung der Trainingsdaten – wie Spiegeln, Rotieren oder das Vermischen ganzer Bilder – helfen bei alltäglicher Fotografie, neigen jedoch dazu, gerade die feinen Details und Kanten zu verwischen oder fehlzuplatzieren, die in gastrointestinalen Untersuchungen am wichtigsten sind.
Von grobem Ausschneiden-und-Einfügen zu anatomiebewusstem Mischen
Forscherinnen und Forscher haben bereits fortgeschrittenere „Ausschneiden-und-Einfügen“-Methoden getestet, die sichtbare Läsionen aus einem Bild kopieren und in ein anderes einsetzen, oder generative Modelle verwenden, um völlig neue Bilder zu erzeugen. Obwohl diese Strategien die Vielfalt erhöhen, ignorieren sie häufig die umgebende Anatomie. Eine eingefügte Läsion kann an einer unrealistischen Stelle landen oder in Farbe und Textur mit dem angrenzenden Gewebe nicht übereinstimmen, wodurch die Trainingsbilder weniger glaubwürdig werden. Generative Modelle wie GANs und Diffusionsnetzwerke können beeindruckende Bilder erzeugen, brauchen aber sehr große Datensätze, sind schwer zu steuern und laufen Gefahr, erfundene Strukturen zu produzieren, die bei realen Patientinnen und Patienten nicht vorkommen. Für Aufgaben, die auf subtile Farbunterschiede und feine Oberflächenmuster angewiesen sind – wie bei frühen Erkrankungen von Magen und Kolon – begrenzen diese Schwächen den Nutzen gängiger Augmentationsmethoden.
Eine neue Art, Läsionen in realistische Szenen einzubetten
Die Autorinnen und Autoren stellen Cut Instance Mixing (CIM) vor, einen domänenspezifischen Ansatz, der speziell für gastrointestinale Bilder entwickelt wurde. Anstatt Läsionen zufällig zu platzieren, analysiert CIM zuerst ein gesundes Bild, um sinnvolle Bereiche zu finden, die realen Schleimhautmustern ähneln. Dazu werden Pixel in glatte, biologisch plausible Patches geclustert und anschließend in kleinere, ordentliche Unterregionen unterteilt. Anschließend wählt CIM eine reale Läsion aus einem anderen Bild und sucht die Unterregion aus, deren Farbe und Textur der Umgebung der Läsion am ähnlichsten ist. Die Läsion wird dort positioniert und mit Techniken eingefügt, die Kanten und Beleuchtung erhalten; ein Stellrad (genannt α) steuert, wie deutlich oder dezent die Läsion erscheint. Das Ergebnis ist ein synthetisches Bild, in dem die Läsion so wirkt, als habe sie sich natürlich an dieser Stelle gebildet, und weil das ursprüngliche Läsionslabel bekannt ist, ist das neue Bild automatisch für das Training annotiert.
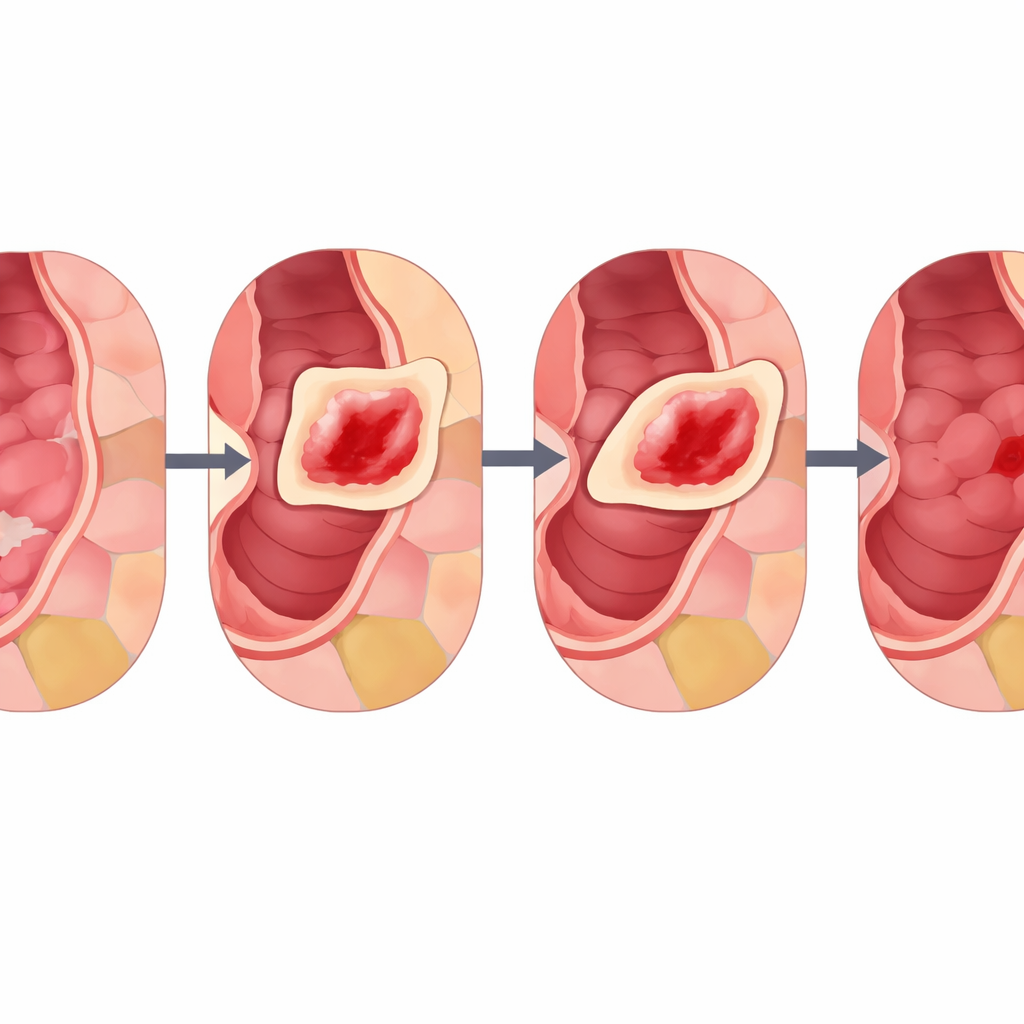
Die Methode auf die Probe gestellt
Um zu prüfen, ob CIM tatsächlich hilft, trainierte das Team dasselbe Deep-Learning-Modell mit drei unterschiedlichen Endoskopie-Sammlungen: intestinale Metaplasie, Dysplasie und Kolonpolypen. Für jeden Datensatz verglichen sie CIM mit Standardtechniken wie MixUp, CutMix und einfachem zufälligem Kopieren–Einfügen, wobei sie strenge Kreuzvalidierung und für den Polypenfall einen externen Testdatensatz aus anderen Krankenhäusern verwendeten. In nahezu allen Leistungsmaßen – etwa Gesamtgenauigkeit, Fähigkeit, krankes von gesundem Gewebe zu trennen, und Stabilität über wiederholte Tests – lag CIM, insbesondere bei stärkerer Mischung (α um 0,8), vorn. Die Forschenden betrachteten außerdem Heatmaps, die zeigen, wo das Modell „hinblickt“, wenn es Entscheidungen trifft. Modelle, die mit CIM trainiert wurden, fokussierten präziser auf echte Läsionsregionen, stimmten besser mit medizinischen Annotationen überein als die Konkurrenz und deuten darauf hin, dass CIM dem Netzwerk hilft, klinisch sinnvollere Merkmale zu lernen statt Abkürzungen oder Rauschen.
Was das für die künftige Darmkrebsvorsorge bedeutet
Einfach gesagt verschafft CIM den Computerprogrammen der Ärztinnen und Ärzte mehr und bessere Übungsbilder, indem reale Läsionen an glaubwürdigen neuen Orten eingefügt werden, wobei die Anatomie respektiert wird. Dieser Ansatz verringert die Ungleichheit zwischen häufigen und seltenen Erkrankungen, verbessert die Erkennung früher und subtiler Erkrankungen und funktioniert ohne große, schwer steuerbare generative Modelle oder zusätzliche Hilfsnetzwerke. Während die vorliegende Arbeit auf binäre Entscheidungen – Läsion oder keine Läsion – fokussiert ist, könnte dieselbe Strategie auf mehrere Läsionstypen ausgeweitet und an anderen Organsystemen getestet werden. Bei breiter Anwendung könnten CIM und ähnliche anatomiebewusste Daten‑“Mischwerkzeuge” die computerassistierte Endoskopie zuverlässiger machen und Spezialistinnen und Spezialisten helfen, gefährliche Veränderungen im Verdauungstrakt früher und konstanter zu finden.
Zitation: Neto, A., Almeida, E., Libânio, D. et al. Cut instance mixing: A domain-specific data augmentation method applied to gastrointestinal lesion detection. Sci Rep 16, 11941 (2026). https://doi.org/10.1038/s41598-026-42138-2
Schlüsselwörter: gastrointestinale Läsionen, Endoskopie-Bildgebung, Datenaugmentation, Tiefes Lernen, Krebsfrüherkennung