Clear Sky Science · sv
MAMMAL - Molekylärt anpassad multimodal arkitektur och språk för biomedicinska upptäckter
Varför smartare läkemedelsupptäckt spelar roll
Att hitta nya läkemedel är långsamt, riskabelt och extremt kostsamt. De flesta läkemedelskandidater misslyckas fortfarande i kliniska prövningar, ofta efter år av arbete. Samtidigt producerar biologilabb nu enorma mängder data om gener, proteiner, celler och kemikalier. Denna artikel introducerar MAMMAL, en ny typ av artificiellt intelligenssystem som lär sig från alla dessa datatyper samtidigt. Genom att koppla mönster mellan molekyler, celler och läkemedel syftar det till att hjälpa forskare välja bättre mål, designa bättre läkemedel och undvika kostsamma återvändsgränder tidigare i processen.
En hjärna för många slags biologiska data
Dagens AI-verktyg inom biomedicin är ofta specialister: en modell hanterar proteinsekvenser, en annan små molekyler och ytterligare en tittar bara på genaktivitet. MAMMAL går en annan väg. Den behandlar proteiner, antikroppar, småmolekylära läkemedel och genuttrycksprofiler som olika slags "meningar" som alla kan läsas av samma modell. För att göra detta byggde forskarna ett flexibelt sätt att omvandla varje datatyp till ett gemensamt sekvensformat, och de tränade ett stort transformerbaserat nätverk—liknande i anda moderna språkmodeller—på ungefär två miljarder exempel hämtade från offentliga dataset för proteiner, antikroppar, kemikalier och cellnivådata.
Att lära sig läkemedels- och cellers språk
MAMMAL är utformat både för att förstå och generera biologisk information. Det kan klassificera, ranka eller förutsäga siffror såsom bindningsstyrka eller läkemedelspotens, och det kan också hitta på nya sekvenser, till exempel föreslå nya antikroppsfragment. En nyckelfunktion är att det inte bara ser symboler; det kan också ta emot och producera numeriska värden direkt, såsom mätningar från labbtester. Detta hjälper det att resonera kring hur starkt ett läkemedel binder till ett protein eller hur en cancercell svarar på behandling. Alla dessa uppgifter är formulerade som variationer av en kärnaktivitet: att omvandla en sekvens till en annan, ungefär som att översätta mellan språk.
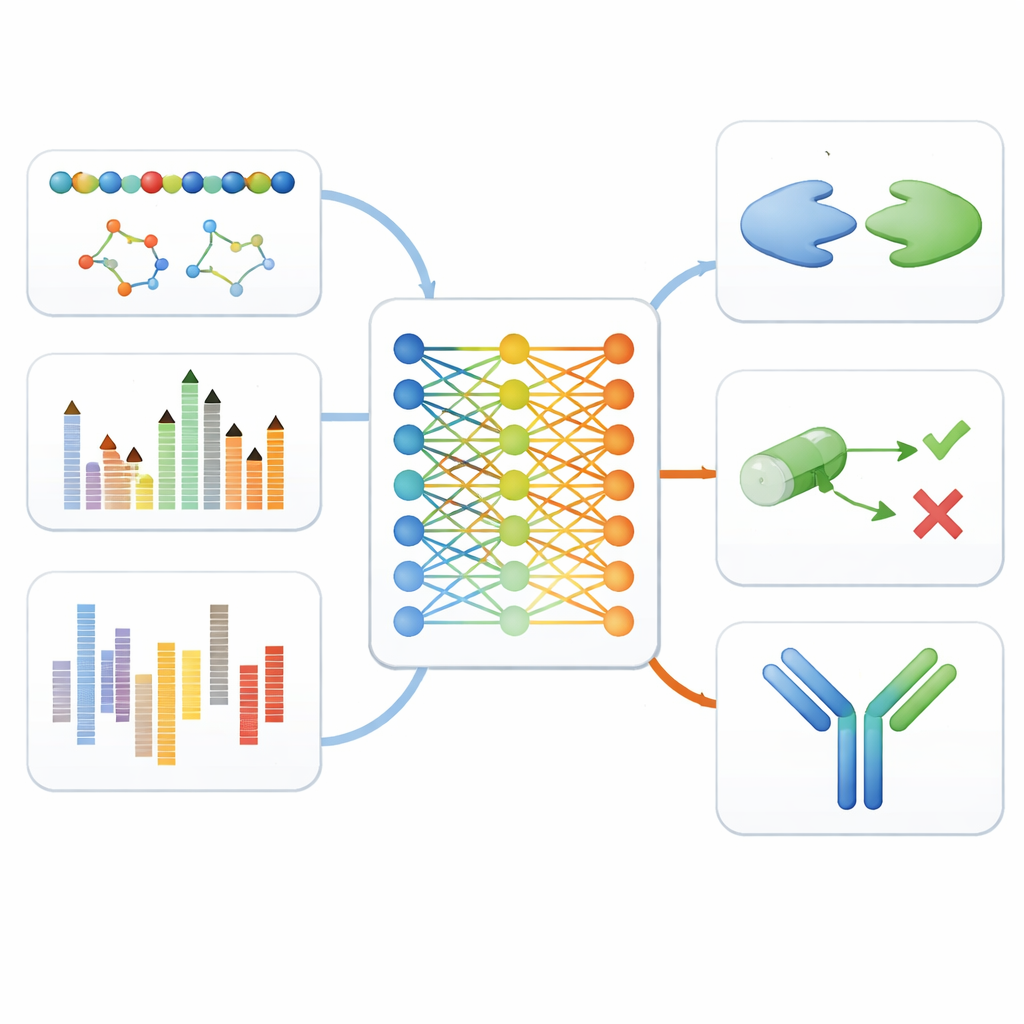
Testning av modellen längs läkemedelsprocessen
För att se om detta enhetliga angreppssätt verkligen hjälper testade författarna finjusterade versioner av MAMMAL på elva olika riktmärken som efterliknar verkliga steg i läkemedelsupptäckt. Dessa inkluderade att känna igen celltyper från single-cell genuttrycksdata, förutsäga om små molekyler kan passera blod–hjärnbarriären eller orsaka toxisk biverkan, uppskatta hur cancerceller svarar på olika läkemedel och förutsäga hur starkt proteiner binder till varandra eller till småmolekylära läkemedel. MAMMAL nådde eller överträffade den bästa rapporterade prestandan i nio av elva tester, ofta genom att slå högt specialiserade modeller som var anpassade för bara en datatyp.
Designa antikroppar och slå strukturella modeller på deras egen mark
Några av de mest anmärkningsvärda resultaten kom från proteinbaserade uppgifter. I en utmaning för antikropps"infilling"—där målet är att fylla i de mest varierande segmenten som faktiskt kontaktar ett mål—återfann MAMMAL de korrekta aminosyrorna mycket oftare än tidigare metoder, särskilt i den ökända svåra centrala regionen av antikroppens bindningsställe. Teamet undersökte också om MAMMAL kunde skilja bindande från icke-bindande antikroppar och jämförde det med AlphaFold 3, ett verktyg för strukturprediktion vars konfidenspoäng kan användas som en indirekt uppskattning av bindning. För fem av sju testmål, inklusive stora och flexibla proteiner relevanta för cancer, var MAMMALs bindningsförutsägelser tydligt mer exakta, trots att den bara såg sekvenser och inte 3D-strukturer.
Tecken på verklig påverkan
Utöver riktmärken kontrollerade forskarna om modellens förutsägelser stämmer med laboratorieverkligheten. De undersökte fyra cancerläkemedel, däribland Carfilzomib, som främst är godkänt för blodcancer. MAMMAL förutsade korrekt den relativa styrkan hos dessa läkemedel över hundratals cellinjer, och denna rangordning bekräftades i riktade experiment. Resultatet antyder att läkemedlet kan ha bredare användning vid solida tumörer än vad som hittills uppskattats, en möjlighet som nu förtjänar vidare testning. Modellen har också visat löfte i samarbeten som syftar till att förutsäga antikroppsaktivitet mot influensavirus och andra mål.
Vad detta betyder för framtida läkemedel
Förenklat fungerar MAMMAL som en flerspråkig läsare och skribent för biologi, kapabel att koppla samman vad som händer på nivåerna gener, proteiner och kemikalier inom ett enda ramverk. Dess starka prestanda över många uppgifter tyder på att sådana enhetliga modeller kan bli kärnkomponenter i AI-assisterade "virtuella celler" som hjälper forskare att utforska behandlingar in silico innan de går in i labbet. Även om den inte ersätter experiment—och fortfarande kräver noggrann validering—kan den begränsa sökutrymmet, lyfta fram överraskande möjligheter och göra den långa vägen från idé till godkänt läkemedel något snabbare och mer effektiv.
Citering: Shoshan, Y., Raboh, M., Ozery-Flato, M. et al. MAMMAL - Molecular Aligned Multi-Modal Architecture and Language for biomedical discovery. npj Drug Discov. 3, 14 (2026). https://doi.org/10.1038/s44386-026-00047-4
Nyckelord: AI-driven läkemedelsupptäckt, multimodala biomedicinska modeller, antikroppsdesign, protein–läkemedelsinteraktioner, genuttrycksprofilering