Clear Sky Science · nl
MAMMAL - Molecular Aligned Multi-Modal Architecture and Language for biomedical discovery
Waarom slimmer medicijnonderzoek ertoe doet
Nieuwe geneesmiddelen vinden is traag, risicovol en extreem duur. De meeste geneesmiddelkandidaten falen nog steeds in klinische proeven, vaak na jaren werk. Tegelijkertijd produceren biologische laboratoria tegenwoordig enorme hoeveelheden gegevens over genen, eiwitten, cellen en chemicaliën. Dit artikel introduceert MAMMAL, een nieuw soort kunstmatig intelligentiesysteem dat tegelijk leert van al deze datatypes. Door patronen te verbinden tussen moleculen, cellen en geneesmiddelen, wil het onderzoekers helpen betere doelen te kiezen, betere medicijnen te ontwerpen en kostbare doodlopende wegen eerder in het proces te vermijden.
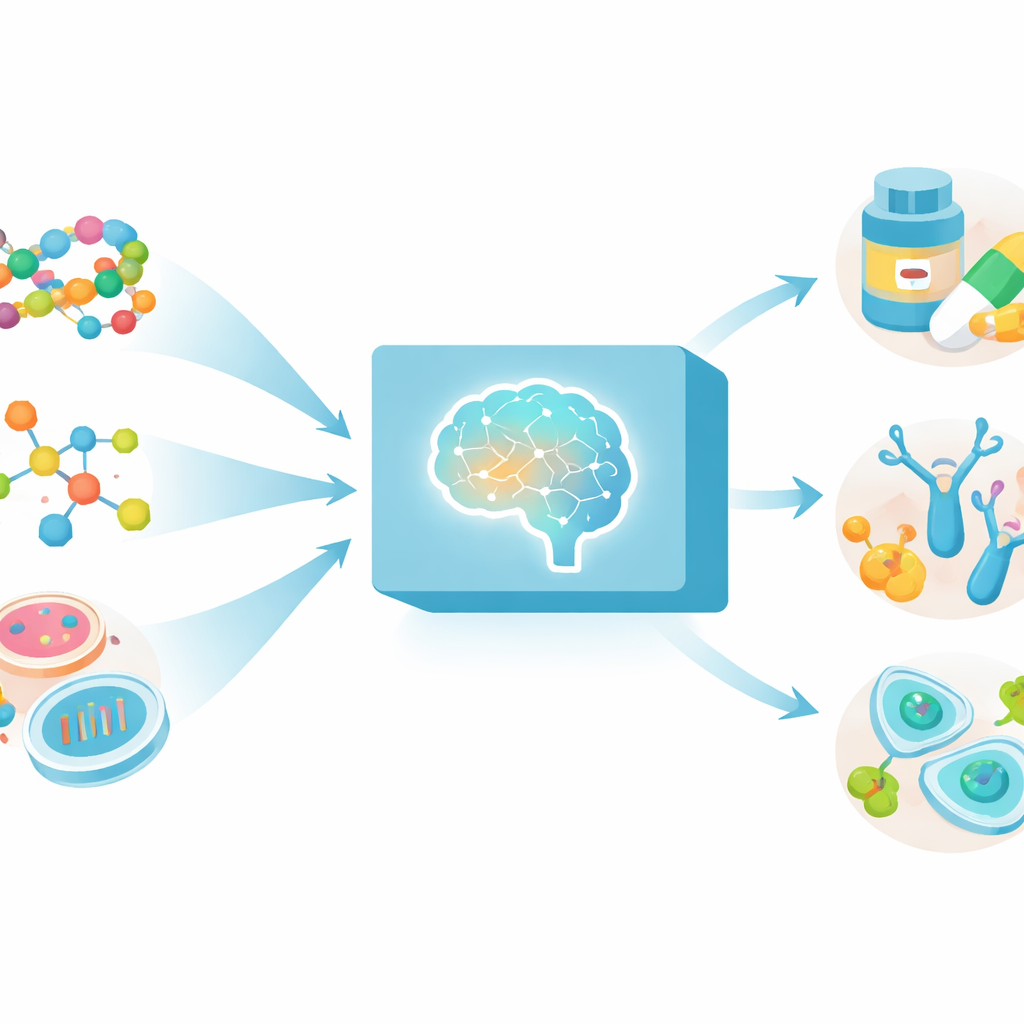
Eén brein voor vele soorten biologische data
De huidige AI-hulpmiddelen in de biomedische wereld zijn vaak specialisten: één model verwerkt eiwitsequenties, een ander behandelt kleine moleculen, en weer een ander kijkt alleen naar genactiviteit. MAMMAL volgt een andere route. Het behandelt eiwitten, antilichamen, small-molecule geneesmiddelen en genexpressieprofielen als verschillende soorten "zinnen" die allemaal door hetzelfde model gelezen kunnen worden. Om dit te bereiken bouwden de onderzoekers een flexibele manier om elk datatype om te zetten naar een gedeeld sequentieformaat, en trainden ze een groot transformer-gebaseerd netwerk—vergelijkbaar in geest met moderne taalmodellen—op ongeveer twee miljard voorbeelden afkomstig van openbare eiwit-, antilichaam-, chemische- en celniveau-datasets.
De taal van geneesmiddelen en cellen leren
MAMMAL is ontworpen om biologische informatie zowel te begrijpen als te genereren. Het kan classificeren, rangschikken of getallen voorspellen zoals bindingssterkte of medicijnpotentie, en het kan ook nieuwe sequenties verzinnen, bijvoorbeeld door nieuwe antilichaamfragmenten voor te stellen. Een belangrijk kenmerk is dat het niet alleen symbolen ziet; het kan ook numerieke waarden rechtstreeks opnemen en produceren, zoals metingen uit laboratoriumassays. Dat helpt het redeneren over hoe sterk een geneesmiddel aan een eiwit bindt of hoe een kankercel op een behandeling reageert. Al deze taken zijn geformuleerd als variaties op één kernactiviteit: het omzetten van de ene sequentie in een andere, vergelijkbaar met vertalen tussen talen.
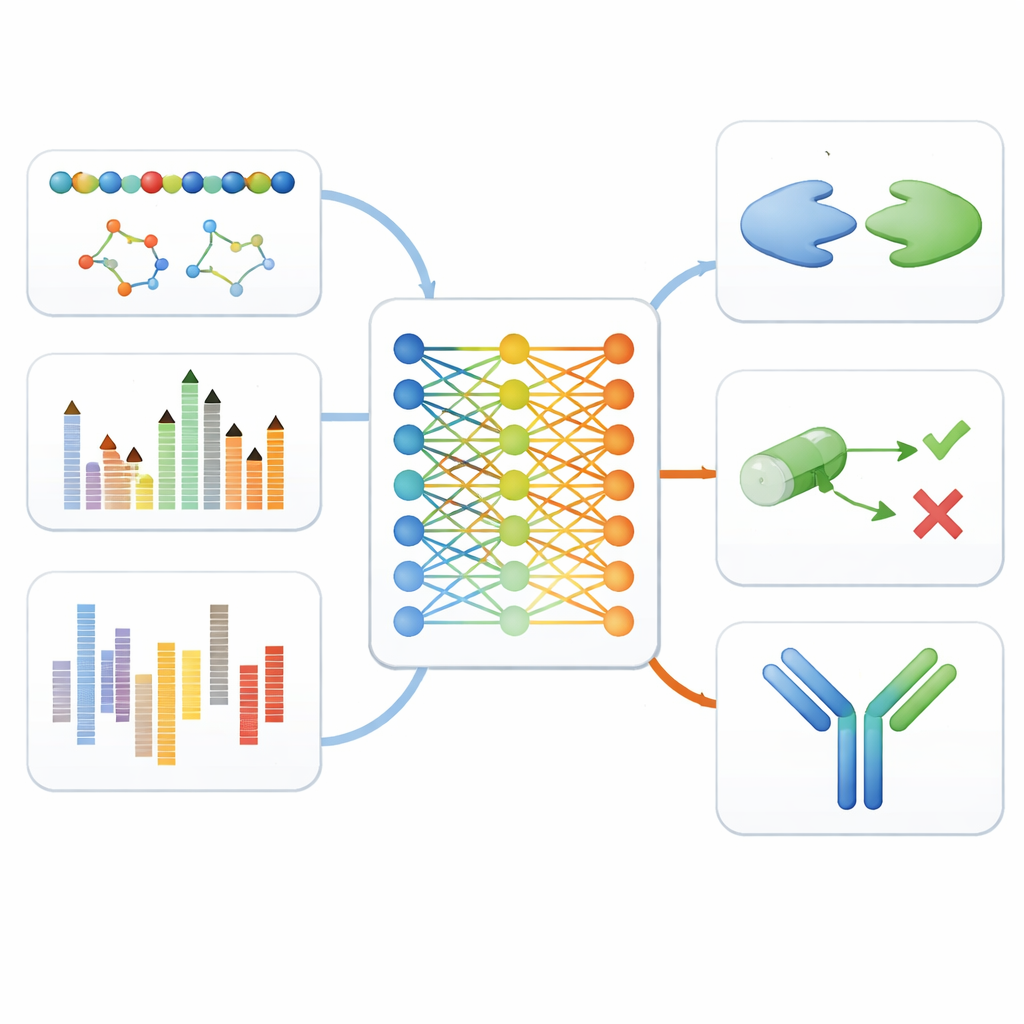
Het model testen over de hele geneesmiddelpijplijn
Om te onderzoeken of deze uniforme aanpak echt helpt, testten de auteurs fijn afgestelde versies van MAMMAL op elf verschillende benchmarks die echte stappen in de medicijnontwikkeling nabootsen. Deze omvatten het herkennen van celtypen uit single-cell genexpressiegegevens, het voorspellen of kleine moleculen de bloed-hersenbarrière kunnen passeren of toxische bijwerkingen kunnen veroorzaken, het inschatten hoe kankercellen op verschillende geneesmiddelen reageren, en het voorspellen hoe sterk eiwitten aan elkaar of aan small-molecule geneesmiddelen zullen binden. MAMMAL bereikte of overtrof de beste gerapporteerde prestaties in negen van de elf tests, en versloeg vaak zeer gespecialiseerde modellen die alleen voor één datatype waren afgestemd.
Antilichamen ontwerpen en structuurmodellen verslaan in hun eigen spel
Sommige van de meest opvallende resultaten kwamen uit eiwit-gebaseerde taken. In een antilichaam "infilling"-uitdaging—waar het doel is de meest variabele segmenten in te vullen die daadwerkelijk contact maken met een doelwit—herwon MAMMAL de correcte aminozuren veel vaker dan eerdere methoden, vooral in de berucht moeilijke centrale regio van het bindingsgebied van het antilichaam. Het team vroeg ook of MAMMAL bindende en niet-bindende antilichamen van elkaar kon onderscheiden en vergeleek het met AlphaFold 3, een structuur-voorspellingshulpmiddel waarvan de vertrouwensscores als indirecte schatting van binding kunnen dienen. Voor vijf van de zeven testdoelen, waaronder grote en flexibele eiwitten relevant voor kanker, waren MAMMAL’s bindingsvoorspellingen duidelijk nauwkeuriger, ondanks dat het alleen sequenties zag en geen 3D-structuren.
Sporen van impact in de praktijk
Voorbij benchmarks controleerden de onderzoekers of de voorspellingen van het model overeenkomen met laboratoriumrealiteit. Ze onderzochten vier kankergeneesmiddelen, waaronder Carfilzomib, dat voornamelijk is goedgekeurd voor bloedkankers. MAMMAL voorspelde correct de relatieve sterkte van deze geneesmiddelen over honderden cellijnen, en deze rangorde werd bevestigd in gerichte experimenten. De vondst suggereert dat het geneesmiddel mogelijk breder inzetbaar is bij solide tumoren dan momenteel wordt aangenomen, een mogelijkheid die nu verder testen rechtvaardigt. Het model heeft ook veelbelovend gepresteerd in samenwerkingen die gericht waren op het voorspellen van antilichaamactiviteit tegen griepvirussen en andere doelwitten.
Wat dit betekent voor toekomstige geneesmiddelen
In eenvoudige bewoordingen functioneert MAMMAL als een meertalig lees- en schrijfgereedschap voor biologie, in staat om te verbinden wat er gebeurt op het niveau van genen, eiwitten en chemicaliën binnen één enkel kader. De sterke prestaties over veel taken suggereren dat dergelijke eengemaakte modellen kerncomponenten kunnen worden van AI-ondersteunde "virtuele cellen" die onderzoekers helpen behandelingen in silico te verkennen voordat ze het laboratorium ingaan. Hoewel het experimenten niet vervangt—en nog steeds zorgvuldige validatie nodig heeft—kan het de zoekruimte verkleinen, verrassende mogelijkheden benadrukken en de lange weg van idee naar goedgekeurd geneesmiddel iets sneller en efficiënter maken.
Bronvermelding: Shoshan, Y., Raboh, M., Ozery-Flato, M. et al. MAMMAL - Molecular Aligned Multi-Modal Architecture and Language for biomedical discovery. npj Drug Discov. 3, 14 (2026). https://doi.org/10.1038/s44386-026-00047-4
Trefwoorden: AI-gestuurde medicijnontdekking, multimodale biomedische modellen, antilichaamontwerp, eiwit–geneesmiddelinteracties, genexpressieprofilering