Clear Sky Science · it
MAMMAL - Architettura Multi-Modalità Allineata Molecolare e Linguaggio per la scoperta biomedica
Perché una scoperta di farmaci più intelligente è importante
Trovare nuovi medicinali è un processo lento, rischioso e estremamente costoso. La maggior parte dei candidati farmaci fallisce ancora nelle prove cliniche, spesso dopo anni di lavoro. Allo stesso tempo, i laboratori di biologia producono oggi una quantità enorme di dati su geni, proteine, cellule e composti chimici. Questo articolo presenta MAMMAL, un nuovo tipo di sistema di intelligenza artificiale che apprende simultaneamente da tutti questi tipi di dati. Collegando pattern tra molecole, cellule e farmaci, mira ad aiutare gli scienziati a scegliere bersagli migliori, progettare medicinali più efficaci e evitare costosi vicoli ciechi nelle fasi iniziali del processo.
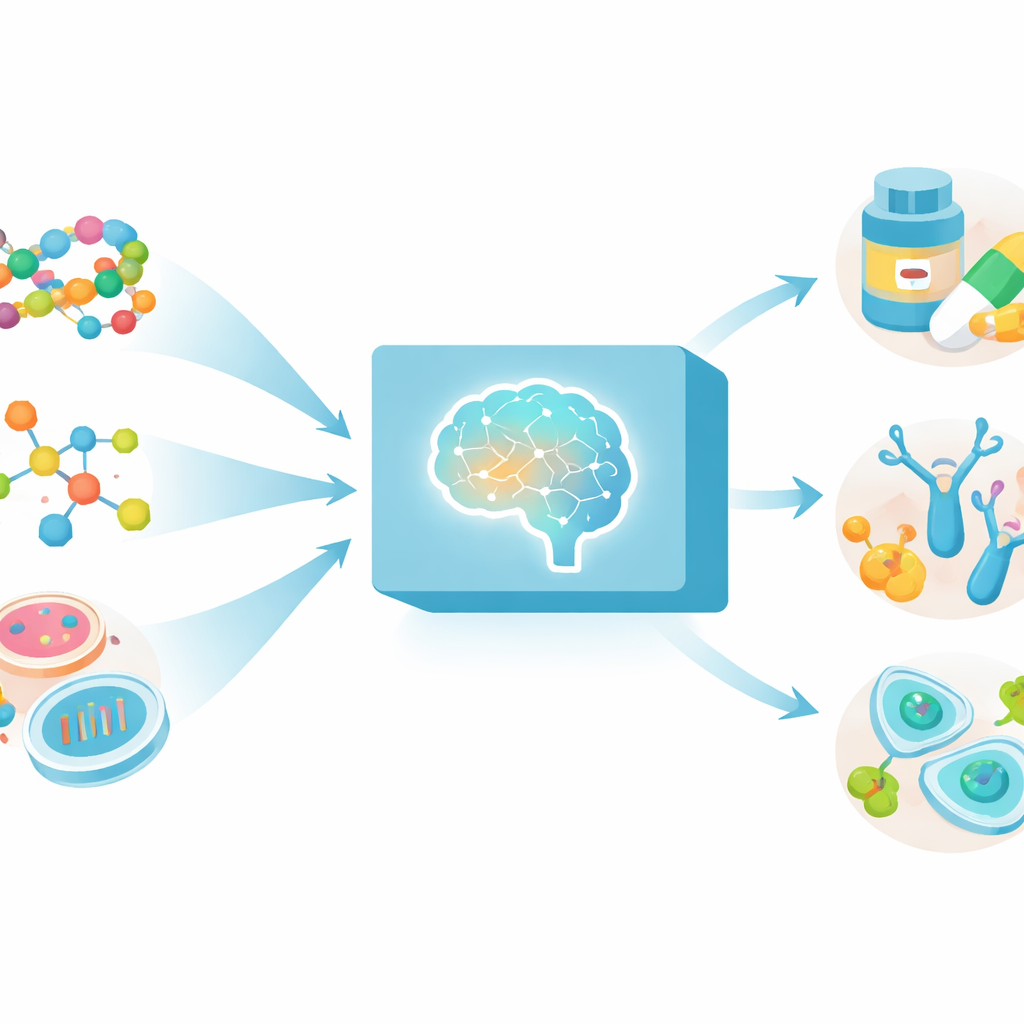
Un cervello per molti tipi di dati biologici
Gli strumenti di IA attuali in biomedicina sono spesso specialisti: un modello gestisce sequenze proteiche, un altro si occupa di piccole molecole e un altro ancora guarda solo l'attività genica. MAMMAL segue una strada diversa. Tratta proteine, anticorpi, farmaci a piccola molecola e profili di espressione genica come diversi tipi di “frasi” che possono essere lette dallo stesso modello. Per farlo, i ricercatori hanno costruito un metodo flessibile per convertire ogni tipo di dato in un formato di sequenza condiviso e hanno addestrato una grande rete basata su transformer—simile nello spirito ai moderni modelli linguistici—su circa due miliardi di esempi estratti da dataset pubblici su proteine, anticorpi, composti chimici e dati a livello cellulare.
Apprendere il linguaggio di farmaci e cellule
MAMMAL è progettato sia per comprendere sia per generare informazioni biologiche. Può classificare, ordinare o prevedere valori numerici come la forza di legame o la potenza di un farmaco, e può anche inventare nuove sequenze, per esempio suggerendo nuovi frammenti di anticorpi. Una caratteristica chiave è che non vede solo simboli; può anche ricevere e produrre valori numerici direttamente, come misure provenienti da saggi di laboratorio. Questo lo aiuta a ragionare su quanto fortemente un farmaco si leghi a una proteina o su come una cellula tumorale risponda a un trattamento. Tutti questi compiti sono inquadrati come variazioni di un'attività centrale: trasformare una sequenza in un'altra, molto simile al tradurre tra lingue.
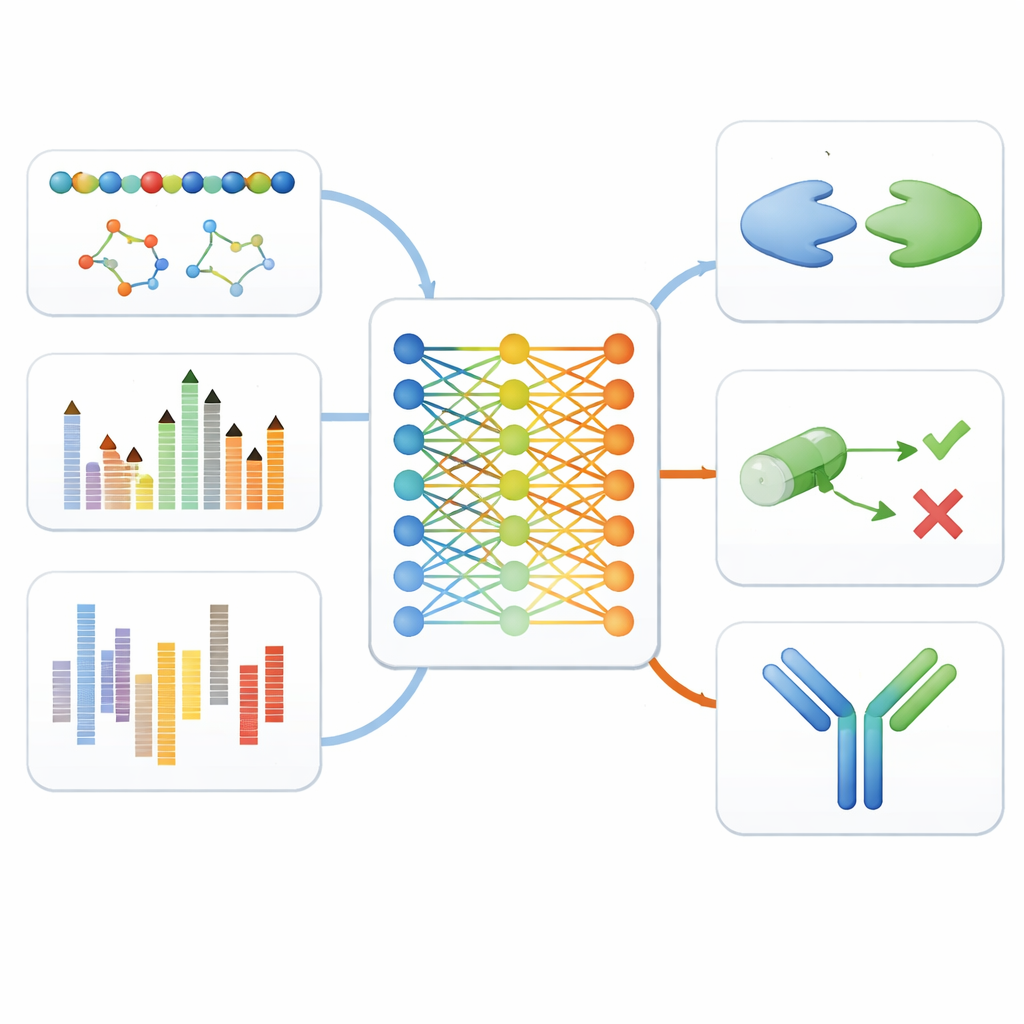
Testare il modello lungo la pipeline di scoperta di farmaci
Per verificare se questo approccio unificato è veramente utile, gli autori hanno testato versioni fine-tuned di MAMMAL su undici diversi benchmark che simulano passaggi reali nella scoperta di farmaci. Questi includevano il riconoscimento dei tipi cellulari da dati di espressione genica a singola cellula, la previsione se piccole molecole possono attraversare la barriera emato-encefalica o causare effetti tossici, la stima di come le cellule tumorali rispondono a vari farmaci e la previsione di quanto fortemente le proteine si legheranno tra loro o a piccole molecole. MAMMAL ha raggiunto o superato le migliori prestazioni riportate in nove su undici test, spesso battendo modelli altamente specializzati tarati su un solo tipo di dato.
Progettare anticorpi e battere i modelli strutturali sul loro terreno
Alcuni dei risultati più sorprendenti sono venuti dai compiti basati sulle proteine. In una sfida di “infilling” di anticorpi—dove l'obiettivo è riempire i segmenti più variabili che effettivamente entrano in contatto con un bersaglio—MAMMAL ha recuperato gli amminoacidi corretti molto più spesso rispetto ai metodi precedenti, specialmente nella regione centrale notoriamente difficile del sito di legame dell'anticorpo. Il team ha inoltre verificato se MAMMAL potesse distinguere tra anticorpi leganti e non leganti e lo ha confrontato con AlphaFold 3, uno strumento di predizione strutturale i cui punteggi di confidenza possono essere usati come stima indiretta del legame. In cinque dei sette bersagli di test, inclusi grandi proteine flessibili rilevanti per il cancro, le previsioni di legame di MAMMAL sono risultate chiaramente più accurate, nonostante il modello avesse visto solo sequenze e non strutture 3D.
Segni di impatto nel mondo reale
Oltre ai benchmark, i ricercatori hanno verificato se le previsioni del modello corrispondessero alla realtà sperimentale. Hanno esaminato quattro farmaci oncologici, incluso il Carfilzomib, approvato principalmente per i tumori del sangue. MAMMAL ha previsto correttamente la forza relativa di questi farmaci su centinaia di linee cellulari, e questa classifica è stata confermata in esperimenti mirati. Il risultato suggerisce che il farmaco potrebbe avere un uso più ampio nei tumori solidi rispetto a quanto attualmente riconosciuto, una possibilità che merita ulteriori studi. Il modello ha anche mostrato potenziale in collaborazioni volte a prevedere l'attività di anticorpi contro i virus influenzali e altri bersagli.
Cosa significa per i medicinali del futuro
In termini semplici, MAMMAL funziona come un lettore e uno scrittore multilingue per la biologia, capace di collegare ciò che accade a livello di geni, proteine e composti chimici all'interno di un unico quadro. La sua solida performance su molti compiti suggerisce che modelli unificati di questo tipo possano diventare componenti centrali di “cellule virtuali” assistite dall'IA che aiutino gli scienziati a esplorare i trattamenti in silico prima di passare al laboratorio. Pur non sostituendo gli esperimenti—e richiedendo ancora una convalida accurata—può restringere lo spazio di ricerca, mettere in evidenza possibilità sorprendenti e rendere il lungo percorso dall'idea al farmaco approvato un po' più veloce ed efficiente.
Citazione: Shoshan, Y., Raboh, M., Ozery-Flato, M. et al. MAMMAL - Molecular Aligned Multi-Modal Architecture and Language for biomedical discovery. npj Drug Discov. 3, 14 (2026). https://doi.org/10.1038/s44386-026-00047-4
Parole chiave: scoperta di farmaci guidata dall'IA, modelli biomedici multimodali, progettazione di anticorpi, interazioni proteina–farmaco, profilazione dell'espressione genica