Clear Sky Science · es
MAMMAL - Arquitectura Multimodal y Alineada Molecular y Lenguaje para el descubrimiento biomédico
Por qué importa un descubrimiento de fármacos más inteligente
Encontrar nuevos medicamentos es lento, arriesgado y extremadamente caro. La mayoría de los candidatos a fármacos siguen fracasando en ensayos clínicos, a menudo después de años de trabajo. Al mismo tiempo, los laboratorios de biología generan hoy océanos de datos sobre genes, proteínas, células y compuestos químicos. Este artículo presenta MAMMAL, un nuevo tipo de sistema de inteligencia artificial que aprende de todos esos tipos de datos a la vez. Al conectar patrones entre moléculas, células y fármacos, pretende ayudar a los científicos a elegir mejores dianas, diseñar medicamentos más eficaces y evitar callejones sin salida costosos antes en el proceso.
Un solo cerebro para muchos tipos de datos biológicos
Las herramientas de IA actuales en biomedicina suelen ser especialistas: un modelo procesa secuencias de proteínas, otro se ocupa de pequeñas moléculas y otro más analiza solo la actividad génica. MAMMAL toma una ruta diferente. Trata proteínas, anticuerpos, fármacos de pequeña molécula y perfiles de expresión génica como distintos tipos de “frases” que puede leer el mismo modelo. Para ello, los investigadores construyeron una forma flexible de convertir cada tipo de dato en un formato de secuencia compartido y entrenaron una gran red basada en transformadores—similar en espíritu a los modelos de lenguaje modernos—con unos dos mil millones de ejemplos extraídos de conjuntos de datos públicos de proteínas, anticuerpos, compuestos químicos y datos a nivel celular.
Aprendiendo el lenguaje de fármacos y células
MAMMAL está diseñado tanto para entender como para generar información biológica. Puede clasificar, ordenar o predecir valores numéricos como la fuerza de unión o la potencia de un fármaco, y también puede inventar nuevas secuencias, por ejemplo sugiriendo fragmentos de anticuerpos. Una característica clave es que no solo procesa símbolos; también puede incorporar y producir valores numéricos directamente, como medidas de ensayos de laboratorio. Esto le ayuda a razonar sobre cuán fuertemente se une un fármaco a una proteína o cómo responde una célula cancerosa a un tratamiento. Todas estas tareas se enmarcan como variaciones de una actividad central: convertir una secuencia en otra, de manera similar a traducir entre idiomas.
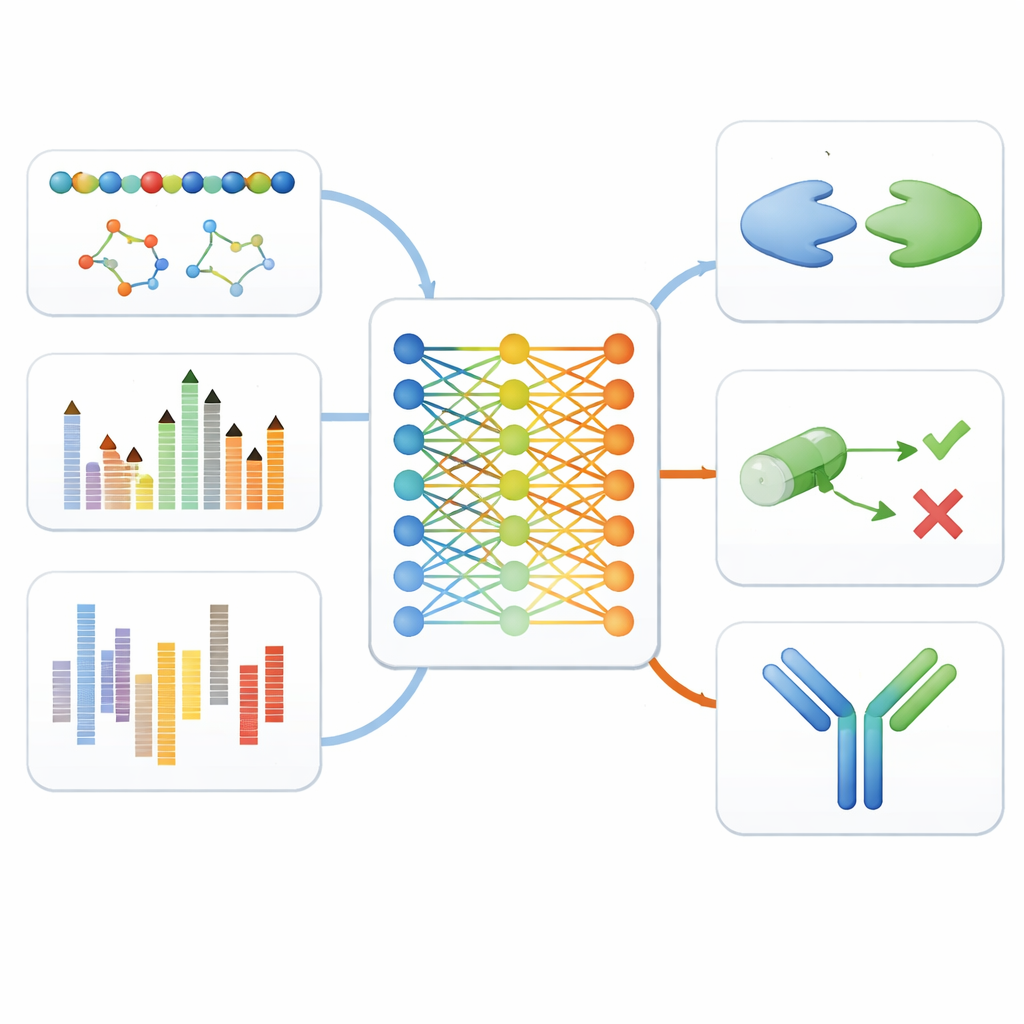
Evaluando el modelo a lo largo de la cadena de desarrollo de fármacos
Para comprobar si este enfoque unificado realmente ayuda, los autores evaluaron versiones afinadas de MAMMAL en once benchmarks distintos que imitan pasos reales en el descubrimiento de fármacos. Estos incluyeron reconocer tipos celulares a partir de datos de expresión génica unicelular, predecir si pequeñas moléculas pueden cruzar la barrera hematoencefálica o causar efectos tóxicos, estimar cómo responden las células cancerosas a diversos fármacos y pronosticar la fuerza de unión entre proteínas o entre proteínas y fármacos de pequeña molécula. MAMMAL alcanzó o superó el mejor rendimiento reportado en nueve de las once pruebas, a menudo superando a modelos altamente especializados ajustados para un solo tipo de dato.
Diseñar anticuerpos y superar a los modelos de estructura en su propio terreno
Algunos de los resultados más llamativos provinieron de tareas basadas en proteínas. En un reto de “relleno” de anticuerpos—donde el objetivo es completar los segmentos más variables que realmente contactan con una diana—MAMMAL recuperó los aminoácidos correctos con mucha más frecuencia que métodos anteriores, especialmente en la región central, notoriamente difícil, del sitio de unión del anticuerpo. El equipo también evaluó si MAMMAL podía distinguir entre anticuerpos que se unen y los que no, y lo comparó con AlphaFold 3, una herramienta de predicción de estructuras cuyos puntajes de confianza pueden usarse como una estimación indirecta de unión. En cinco de siete dianas de prueba, incluidas proteínas grandes y flexibles relevantes para el cáncer, las predicciones de unión de MAMMAL fueron claramente más precisas, a pesar de que solo vio secuencias y no estructuras 3D.
Indicios de impacto en el mundo real
Más allá de los benchmarks, los investigadores comprobaron si las predicciones del modelo coincidían con la realidad experimental. Examinaron cuatro fármacos contra el cáncer, incluido Carfilzomib, aprobado principalmente para cánceres de la sangre. MAMMAL predijo correctamente la fuerza relativa de estos fármacos en cientos de líneas celulares, y esta clasificación se confirmó en experimentos focalizados. El hallazgo sugiere que el fármaco podría tener un uso más amplio en tumores sólidos del que se reconoce actualmente, una posibilidad que ahora merece más pruebas. El modelo también ha mostrado potencial en colaboraciones para predecir la actividad de anticuerpos frente a virus de la gripe y otras dianas.
Qué implica esto para los medicamentos del futuro
En términos sencillos, MAMMAL actúa como un lector y escritor multilingüe para la biología, capaz de conectar lo que ocurre a nivel de genes, proteínas y compuestos químicos dentro de un único marco. Su sólido desempeño en múltiples tareas sugiere que modelos unificados así pueden convertirse en componentes centrales de “células virtuales” asistidas por IA que ayuden a los científicos a explorar tratamientos in silico antes de entrar al laboratorio. Aunque no reemplaza los experimentos—y todavía necesita una validación cuidadosa—puede reducir el espacio de búsqueda, destacar posibilidades sorprendentes y hacer que el largo camino desde la idea hasta un fármaco aprobado sea un poco más rápido y eficiente.
Cita: Shoshan, Y., Raboh, M., Ozery-Flato, M. et al. MAMMAL - Molecular Aligned Multi-Modal Architecture and Language for biomedical discovery. npj Drug Discov. 3, 14 (2026). https://doi.org/10.1038/s44386-026-00047-4
Palabras clave: descubrimiento de fármacos impulsado por IA, modelos biomédicos multimodales, diseño de anticuerpos, interacciones proteína‑fármaco, perfilado de expresión génica