Clear Sky Science · pl
MAMMAL - Molekularna Zharmonizowana Wielomodalna Architektura i Język dla odkryć biomedycznych
Dlaczego inteligentniejsze odkrywanie leków ma znaczenie
Odnalezienie nowych leków jest powolne, ryzykowne i niezwykle kosztowne. Większość kandydatów na leki nadal nie przechodzi prób klinicznych, często po latach pracy. Jednocześnie laboratoria biologiczne generują dziś ogromne ilości danych o genach, białkach, komórkach i związkach chemicznych. Ten artykuł przedstawia MAMMAL — nowy rodzaj systemu sztucznej inteligencji, który uczy się na wszystkich tych typach danych jednocześnie. Poprzez łączenie wzorców między cząsteczkami, komórkami i lekami ma pomóc naukowcom w wyborze lepszych celów, projektowaniu skuteczniejszych leków i wcześniejszym unikaniu kosztownych ślepych ulic.
Jeden mózg dla wielu rodzajów danych biologicznych
Obecne narzędzia AI w biomedycynie często są wyspecjalizowane: jeden model przetwarza sekwencje białek, inny zajmuje się małymi cząsteczkami, a jeszcze inny analizuje tylko aktywność genów. MAMMAL idzie inną drogą. Traktuje białka, przeciwciała, leki małocząsteczkowe i profile ekspresji genów jako różne rodzaje „zdania”, które ten sam model potrafi czytać. Aby to osiągnąć, badacze opracowali elastyczny sposób przekształcania każdego typu danych do wspólnego formatu sekwencyjnego i wyszkolili dużą sieć opartą na transformatorach — w duchu nowoczesnych modeli językowych — na około dwóch miliardach przykładów pochodzących z publicznych baz danych białek, przeciwciał, związków chemicznych i danych komórkowych.
Nauka języka leków i komórek
MAMMAL został zaprojektowany tak, by zarówno rozumieć, jak i generować informacje biologiczne. Potrafi klasyfikować, punktować lub przewidywać wartości liczbowe, takie jak siła wiązania czy aktywność leku, a także tworzyć nowe sekwencje, na przykład proponować fragmenty przeciwciał. Kluczową cechą jest to, że nie operuje tylko na symbolach — może przyjmować i generować bezpośrednio wartości numeryczne, takie jak pomiary z testów laboratoryjnych. Ułatwia to rozumowanie o tym, jak mocno lek wiąże się z białkiem albo jak komórka nowotworowa reaguje na terapię. Wszystkie te zadania zostały sformułowane jako warianty jednej podstawowej czynności: przekształcania jednej sekwencji w inną, podobnie jak tłumaczenie między językami.
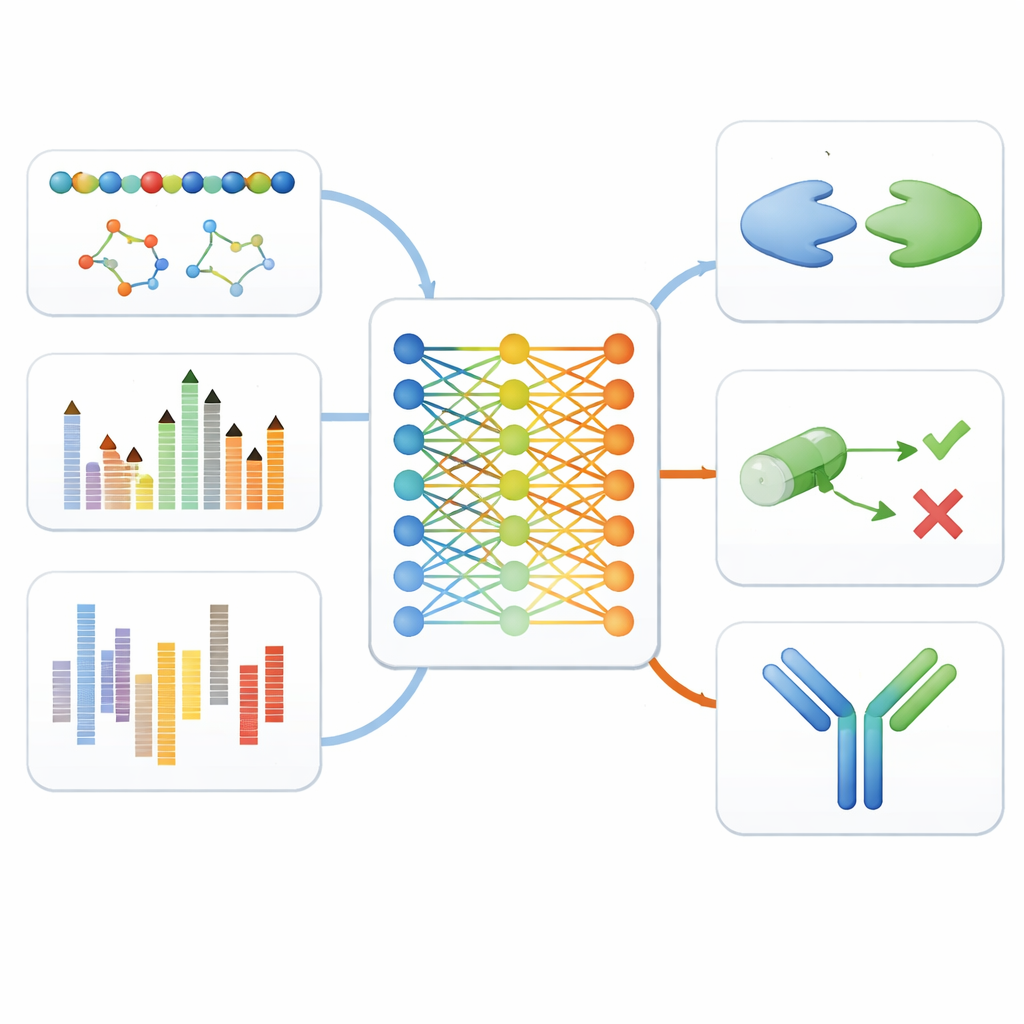
Testowanie modelu wzdłuż ścieżki odkrywania leków
Aby sprawdzić, czy to zunifikowane podejście rzeczywiście pomaga, autorzy przetestowali wersje MAMMAL po dostrojeniu na jedenaście różnych benchmarków naśladujących rzeczywiste etapy odkrywania leków. Obejmowały one rozpoznawanie typów komórek z danych pojedynczokomórkowej ekspresji genów, przewidywanie, czy małe cząsteczki mogą przenikać barierę krew–mózg lub wywoływać toksyczne skutki uboczne, szacowanie, jak komórki nowotworowe reagują na różne leki, oraz prognozowanie, jak silnie białka będą się ze sobą lub z małymi cząsteczkami wiązać. MAMMAL osiągnął lub przekroczył najlepsze zgłoszone wyniki w dziewięciu z jedenastu testów, często pokonując wysoko wyspecjalizowane modele dostrojone tylko do jednego typu danych.
Projektowanie przeciwciał i pokonywanie modeli strukturalnych ich własną bronią
Niektóre z najbardziej uderzających wyników pochodziły z zadań opartych na białkach. W wyzwaniu „uzupełniania” przeciwciał — gdzie celem jest wypełnienie najbardziej zmiennych segmentów, które faktycznie kontaktują się z celem — MAMMAL poprawnie odtworzył właściwe aminokwasy znacznie częściej niż wcześniejsze metody, szczególnie w notorycznie trudnym centralnym regionie miejsca wiązania przeciwciała. Zespół zapytał także, czy MAMMAL potrafi rozróżnić przeciwciała wiążące od niewiążących i porównał go z AlphaFold 3, narzędziem do przewidywania struktur, którego wskaźniki pewności można użyć jako pośredniego oszacowania wiązania. W pięciu z siedmiu testowanych celów, w tym dużych i elastycznych białek związanych z rakiem, przewidywania wiązania MAMMAL-a były wyraźnie dokładniejsze, mimo że widział on jedynie sekwencje, a nie struktury 3D.
Przejawy realnego wpływu
Ponad samymi benchmarkami, badacze sprawdzili, czy przewidywania modelu zgadzają się z wynikami laboratoryjnymi. Zbadali cztery leki przeciwnowotworowe, w tym karfilzomib, który jest zatwierdzony głównie do leczenia nowotworów krwi. MAMMAL poprawnie przewidział względną siłę tych leków w setkach linii komórkowych, a to porządkowanie zostało potwierdzone w ukierunkowanych eksperymentach. Odkrycie sugeruje, że lek ten może mieć szersze zastosowanie w guzach litech niż dotychczas sądzono, co teraz zasługuje na dalsze badania. Model wykazał także obiecujące wyniki we współpracach mających na celu przewidywanie aktywności przeciwciał przeciwko wirusom grypy i innym celom.
Co to znaczy dla przyszłych leków
Mówiąc prosto, MAMMAL działa jak wielojęzyczny czytelnik i twórca w biologii, potrafiący łączyć to, co dzieje się na poziomie genów, białek i związków chemicznych w ramach jednego systemu. Jego silna wydajność w wielu zadaniach sugeruje, że takie zunifikowane modele mogą stać się kluczowymi komponentami wspomaganych AI „wirtualnych komórek”, które pomagają naukowcom eksplorować terapie in silico przed wejściem do laboratorium. Choć nie zastępuje eksperymentów — i nadal wymaga starannej walidacji — potrafi zawęzić przestrzeń poszukiwań, uwydatnić zaskakujące możliwości i sprawić, że długa droga od pomysłu do zatwierdzonego leku będzie nieco szybsza i bardziej efektywna.
Cytowanie: Shoshan, Y., Raboh, M., Ozery-Flato, M. et al. MAMMAL - Molecular Aligned Multi-Modal Architecture and Language for biomedical discovery. npj Drug Discov. 3, 14 (2026). https://doi.org/10.1038/s44386-026-00047-4
Słowa kluczowe: Odkrywanie leków napędzane przez AI, wielomodalne modele biomedyczne, projektowanie przeciwciał, interakcje białko–lek, profilowanie ekspresji genów