Clear Sky Science · sv
Stereologiska rekonstruktioner av 3D-cellulära mikrostukturer genom att kombinera adversarial inlärning och Voronoi-tessellationer
Varför materialens dolda inre struktur spelar roll
Vardagliga material, från cykelramar i metall till växters blad och skumkuddar, är uppbyggda av små tredimensionella ”celler” packade tätt tillsammans. Cellernas former, storlekar och förbindelser styr i det tysta hur ett material böjer sig, går sönder, isolerar värme eller leder elektricitet. Att visualisera dessa 3D-cellnät kräver ofta dyra eller destruktiva avbildningsmetoder. Denna artikel presenterar ett nytt sätt att återskapa realistiska 3D-cellstrukturer från mycket enklare tvådimensionella bilder, vilket hjälper forskare att utforska och designa material utan att skära upp dem.
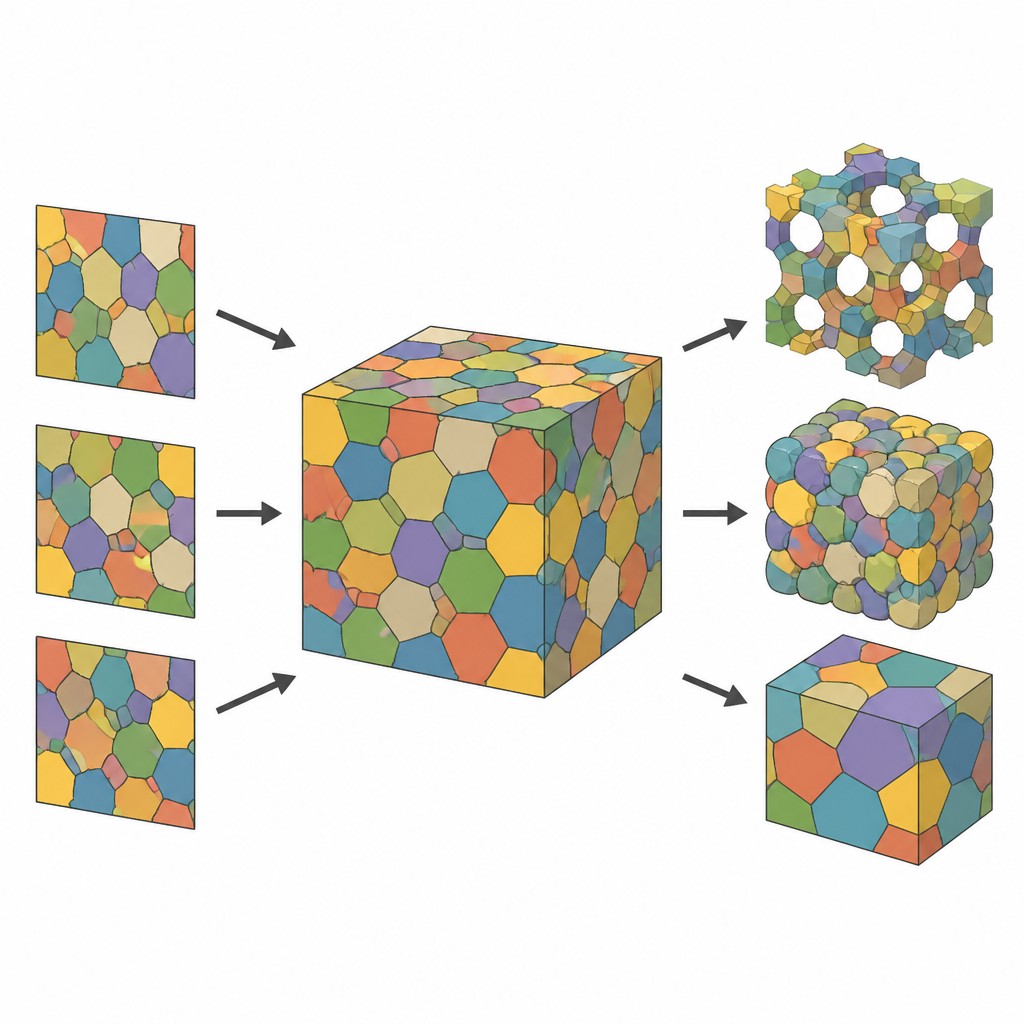
Från plana snitt till fullständiga 3D-kartor
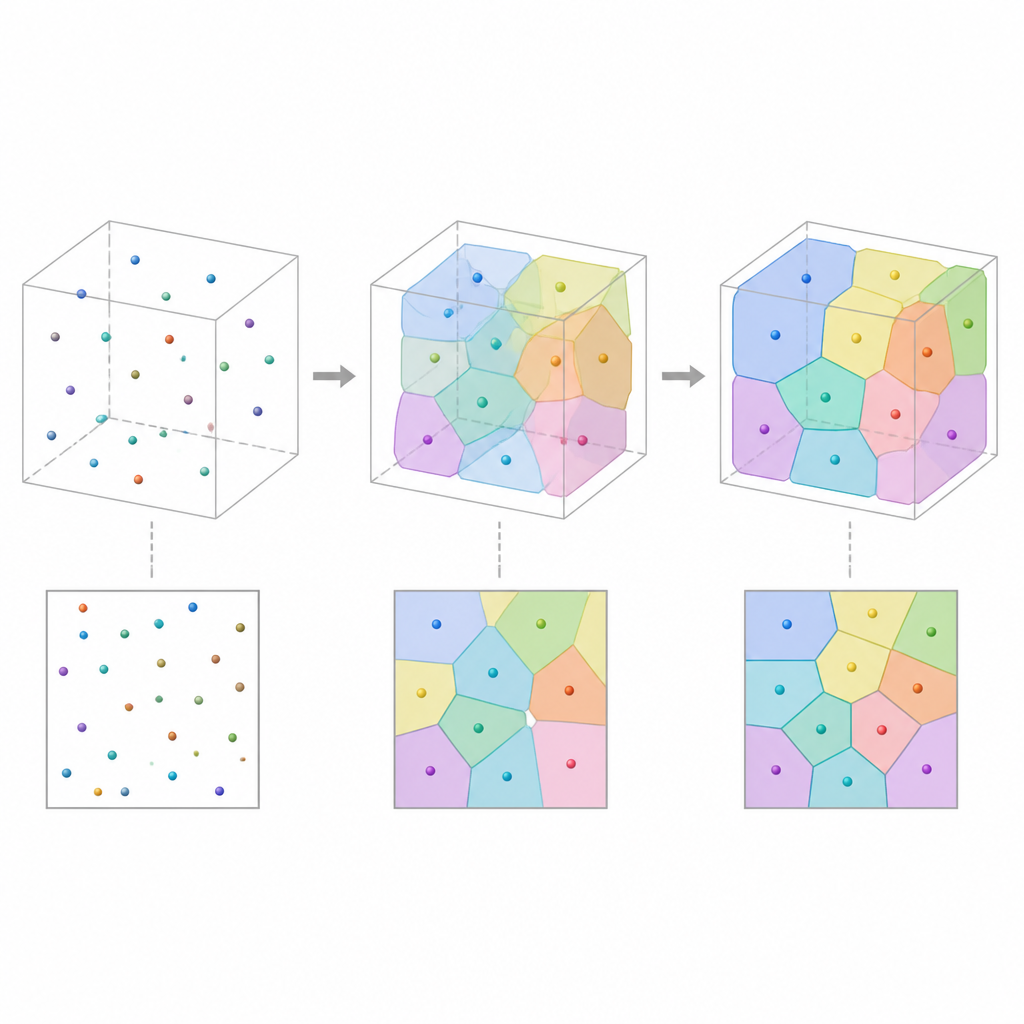
De flesta experiment fångar bara tunna snitt av ett material: mikroskopbilder som visar hur cellerna ser ut i ett plant tvärsnitt. Sådana 2D-vyer missar hur cellerna sträcker sig och är sammanbundna i djupet. Författarna angriper detta genom att betrakta den osedda 3D-strukturen som en samling celler som partitionerar rummet, ungefär som ett mosaik av sammanhängande polyedriska ”bubblor”. Genom att börja från ett moln av punkter i rummet och tilldela varje punkt den region som ligger närmast den får man en Voronoi-tessellation, ett geometriskt ramverk som naturligt efterliknar många cellulära material. Varje cell färgläggs och representeras som en slät, datorvänlig bild så att modellen kan justeras och jämföras med uppmätta snitt.
Att lära ett neuralt nätverk bedöma realism
För att få den syntetiska 3D-strukturen att likna verkliga material tränar författarna ett diskriminatornätverk, liknande de som används i bildgenererande artificiell intelligens. Detta nätverk lär sig skilja 2D-bilder skurna från den aktuella 3D-modellen från verkliga 2D-snitts-bilder från experiment. I början ser modellens snitt orealistiska ut, så diskriminatorn upptäcker dem lätt som falska. Algoritmen flyttar då något på de fröpunkter som definierar cellerna, med gradientbaserad optimering, för att göra modellens snitt svårare att skilja från verkliga. Över många omgångar utvecklas den 3D-cellulära mönstret tills diskriminatorn bedömer att simulerade och uppmätta snitt är statistiskt lika.
Att balansera detalj, effektivitet och tolkbarhet
Metoden är utformad för att använda mycket få parametrar per cell samtidigt som den behåller en tydlig fysisk betydelse. Varje cell definieras huvudsakligen av positionen för en enda punkt, istället för tusentals bildpixlar. Denna kompakta beskrivning minskar minnesanvändningen med ungefär hundratals gånger jämfört med fullständiga 3D-bilder, samtidigt som den ger direkt kontroll över viktiga egenskaper som cellstorlek, form och grannskapsrelationer. Periodiska randvillkor undviker artificiella kanteffekter i små prov, och en ”mjuk” version av tessellationen, baserad på släta avståndsvikter, håller optimeringen stabil och differentiell samtidigt som möjligheten att återfå skarpa cellgränser senare bevaras.
Testning på syntetiska och verkliga material
Teamet kontrollerar först sitt ramverk på artificiella mikrostrukturer som redan är väl beskrivna av Voronoi-celler. Genom att rekonstruera 3D-mönster från många 2D-snitt och jämföra statistiska mått som cellvolym, yta, förlängning och antal grannar finner de att de genererade strukturerna nära matchar originalen. De tillämpar sedan metoden på verkliga uppmätta data: polymerskum, nästan sfäriska biologiska celler och polykrystallina metaller med mer långsträckta och tvillingkorn. I alla tre fallen återger de rekonstruerade 3D-tessellationerna viktiga geometriska trender som observerats i experimenten, och ofta gör de det mer noggrant vad gäller cellstorlekar och ytor än en ren voxelbaserad konkurrerande metod.
Vad detta betyder för framtida materialdesign
Studien visar att det är möjligt att härleda rika 3D-cellulära arkitekturer från 2D-bilder genom en blandning av geometriska tessellationer och adversarial inlärning. Medan den nuvarande versionen är begränsad till celler med raka, plana ytor och isotropa statistiker, erbjuder den redan en snabb, lågparameter och fysikaliskt tolkbar väg för att bygga virtuella 3D-prov som kan matas direkt in i simuleringsverktyg. För icke-experter är huvudbudskapet att forskare nu kan ”återuppblåsa” platta materialsnitt till realistiska 3D-modeller, vilket minskar beroendet av kostsam 3D-avbildning samtidigt som den väsentliga inre strukturen som styr materialets beteende fångas upp.
Citering: Fuchs, L., Wilhelm, T., Furat, O. et al. Stereological reconstructions of 3D cellular microstructures by combining adversarial learning and Voronoi tessellations. Sci Rep 16, 15058 (2026). https://doi.org/10.1038/s41598-026-52851-7
Nyckelord: 3D-mikrostruktur, cellulära material, Voronoi-modell, adversarial inlärning, stereologi