Clear Sky Science · pt
Reconstruções esterológicas de microestruturas celulares 3D combinando aprendizado adversarial e tesselações de Voronoi
Por que a estrutura interna oculta dos materiais importa
Materiais do cotidiano, de quadros de bicicleta metálicos a folhas de plantas e espumas de almofadas, são constituídos por pequenas “células” tridimensionais encaixadas. As formas, tamanhos e conexões dessas células controlam silenciosamente como um material dobra, quebra, isola calor ou conduz eletricidade. Contudo, visualizar essas redes celulares 3D normalmente exige técnicas de imagem caras ou destrutivas. Este artigo apresenta um novo modo de reconstruir estruturas celulares 3D realistas a partir de imagens bidimensionais muito mais simples, ajudando cientistas a explorar e projetar materiais sem a necessidade de cortá‑los.
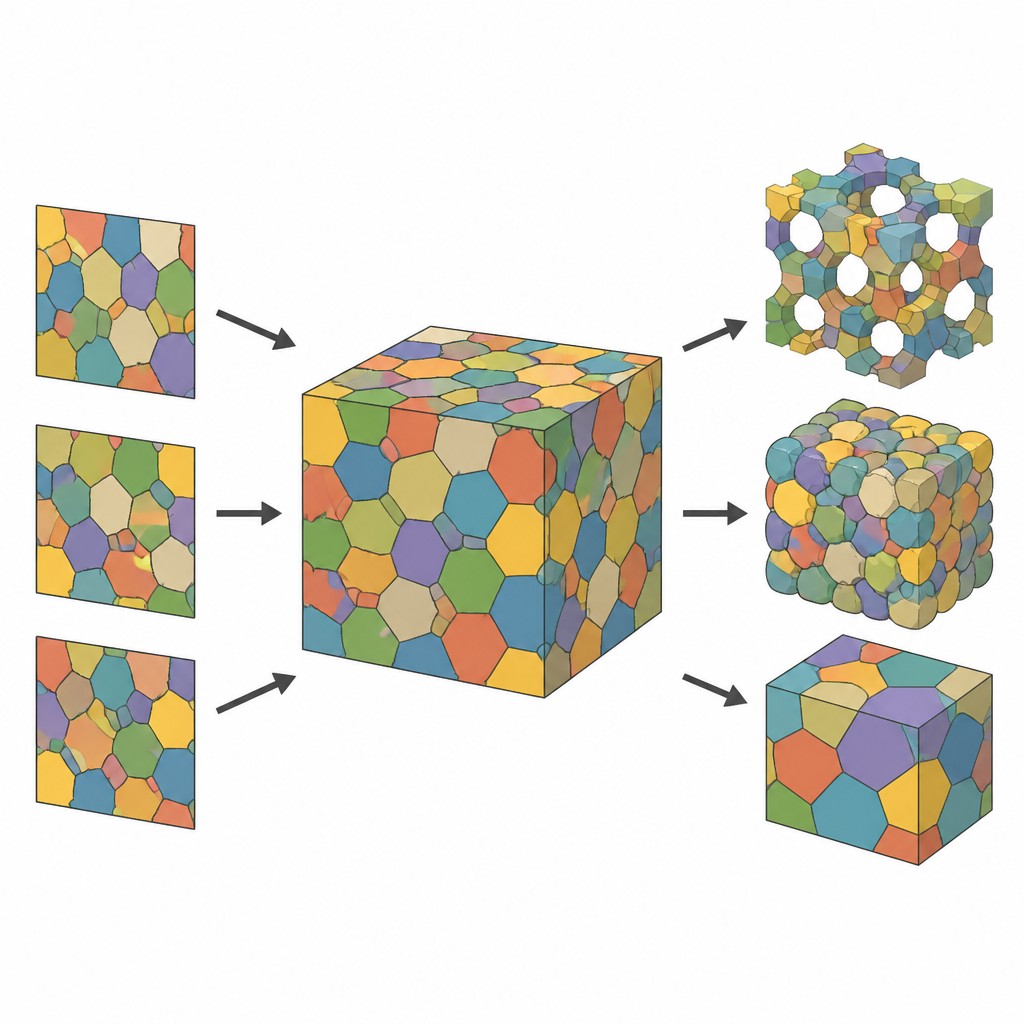
De fatias planas a mapas celulares 3D completos
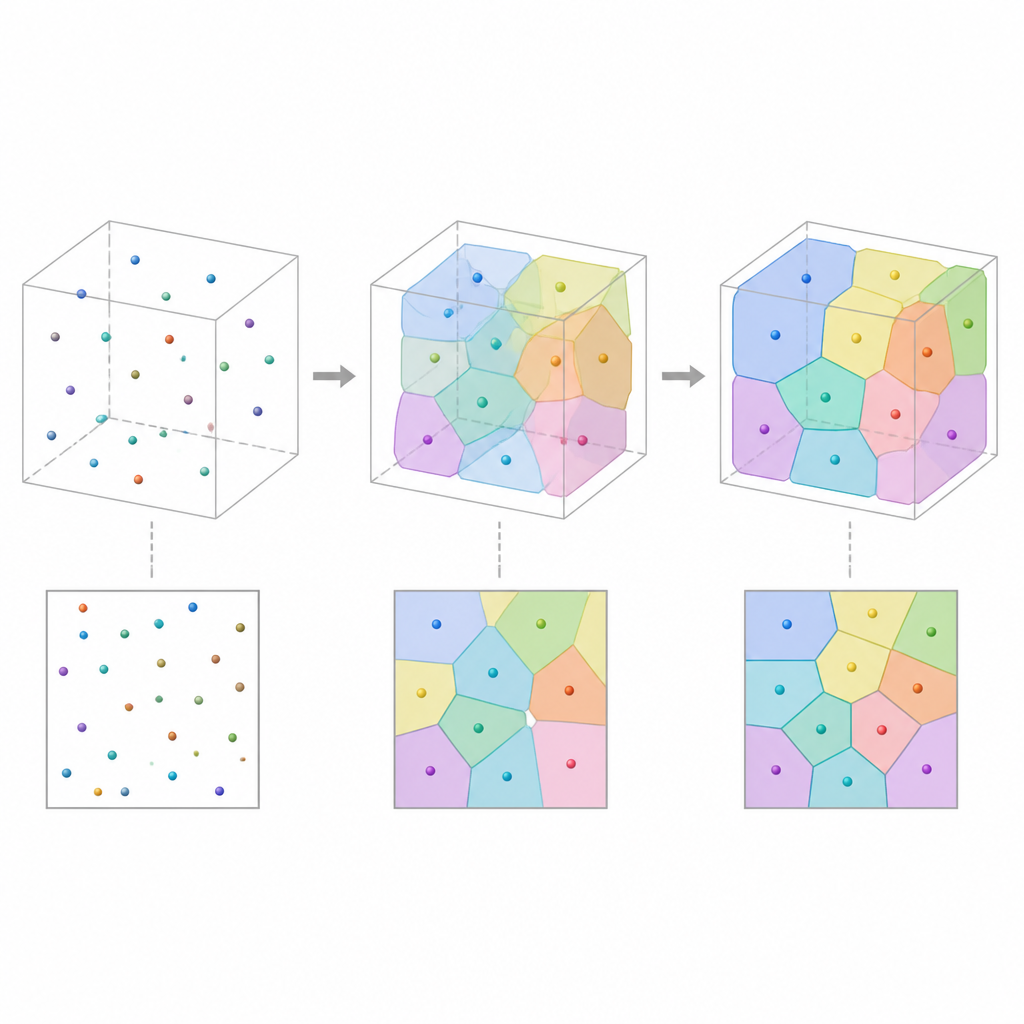
A maioria dos experimentos captura apenas fatias finas de um material: imagens de microscópio que mostram como as células aparecem em uma seção plana. Apesar de úteis, essas vistas 2D deixam de revelar como as células se estendem e se conectam em profundidade. Os autores enfrentam isso tratando a estrutura 3D invisível como uma coleção de células que particionam o espaço, como um mosaico de poliedros “borbulhantes” em contato. Ao partir de uma nuvem de pontos no espaço e atribuir a cada ponto a região mais próxima, obtém‑se uma tesselação de Voronoi, um arcabouço geométrico que mimetiza naturalmente muitos materiais celulares. Cada célula é então colorida e representada como uma imagem suavizada, amigável ao computador, para que o modelo possa ser ajustado e comparado com fatias medidas.
Treinando uma rede neural para avaliar o realismo
Para fazer a estrutura 3D sintética se assemelhar a materiais reais, os autores treinam uma rede discriminadora, semelhante às usadas em inteligências artificiais geradoras de imagens. Essa rede aprende a distinguir imagens 2D cortadas do modelo 3D corrente e fatias 2D reais medidas experimentalmente. A princípio, as fatias do modelo parecem irreais, de modo que o discriminador as identifica facilmente como falsas. O algoritmo então desloca ligeiramente os pontos‑semente que definem as células, usando otimização baseada em gradiente, para tornar as fatias do modelo mais difíceis de distinguir das reais. Ao longo de muitas iterações, o padrão celular 3D evolui até que o discriminador considere as fatias simuladas e medidas estatisticamente semelhantes.
Equilibrando detalhe, eficiência e interpretabilidade
A abordagem foi projetada para usar pouquíssimos parâmetros por célula, mantendo um significado físico claro. Cada célula é definida principalmente pela posição de um único ponto, em vez de milhares de pixels de imagem. Essa descrição compacta reduz o uso de memória em aproximadamente centenas de vezes em comparação com imagens 3D completas, sem perder o controle direto sobre características importantes como tamanho, forma e relações de vizinhança das células. Condições de contorno periódicas evitam efeitos artificiais de borda em amostras pequenas, e uma versão “suave” da tesselação, baseada em pesos contínuos de distância, mantém a otimização estável e diferenciável, preservando a capacidade de recuperar contornos nítidos das células posteriormente.
Testes em materiais sintéticos e reais
A equipe primeiro verifica seu quadro em microestruturas artificiais já conhecidas por serem bem descritas por células de Voronoi. Ao reconstruir padrões 3D a partir de várias fatias 2D e comparar estatísticas como volume celular, área de superfície, alongamento e número de vizinhos, eles constataram que as estruturas geradas correspondem de perto aos originais. Em seguida aplicam o método a dados medidos reais: espumas poliméricas, células biológicas quase esféricas e metais policristalinos com grãos mais alongados e comemorações (twinned). Nos três casos, as tesselações 3D reconstruídas reproduzem tendências geométricas-chave observadas nos experimentos, e frequentemente o fazem com maior precisão em termos de tamanhos e superfícies celulares do que um método concorrente puramente baseado em voxels.
O que isso significa para o desenho futuro de materiais
O estudo demonstra que é possível inferir arquiteturas celulares 3D ricas a partir de imagens 2D usando uma combinação de tesselações geométricas e aprendizado adversarial. Embora a versão atual seja limitada a células com faces retas e planas e estatísticas isotrópicas, ela já oferece uma via rápida, de poucos parâmetros e fisicamente interpretável para construir amostras 3D virtuais que podem ser integradas diretamente a ferramentas de simulação. Para não especialistas, a mensagem principal é que os cientistas agora podem “reinflar” fatias planas de materiais em modelos 3D realistas, reduzindo a dependência de técnicas de imagem 3D caras, ao mesmo tempo em que capturam a estrutura interna essencial que governa o comportamento do material.
Citação: Fuchs, L., Wilhelm, T., Furat, O. et al. Stereological reconstructions of 3D cellular microstructures by combining adversarial learning and Voronoi tessellations. Sci Rep 16, 15058 (2026). https://doi.org/10.1038/s41598-026-52851-7
Palavras-chave: microestrutura 3D, materiais celulares, modelo de Voronoi, aprendizado adversarial, esterologia