Clear Sky Science · fr
Reconstructions stéréologiques de microstructures cellulaires 3D en combinant apprentissage adversarial et tessellations de Voronoi
Pourquoi la structure interne cachée des matériaux importe
Les matériaux du quotidien, des cadres de vélo en métal aux feuilles de plante en passant par les coussins en mousse, sont constitués de minuscules « cellules » tridimensionnelles assemblées. La forme, la taille et les connexions de ces cellules gouvernent silencieusement la manière dont un matériau fléchit, se rompt, isole la chaleur ou conduit l’électricité. Pourtant, voir ces réseaux cellulaires 3D exige souvent des imageries coûteuses ou destructrices. Cet article présente une nouvelle méthode pour reconstruire des structures cellulaires 3D réalistes à partir d’images bidimensionnelles beaucoup plus simples, aidant les chercheurs à explorer et concevoir des matériaux sans les découper.
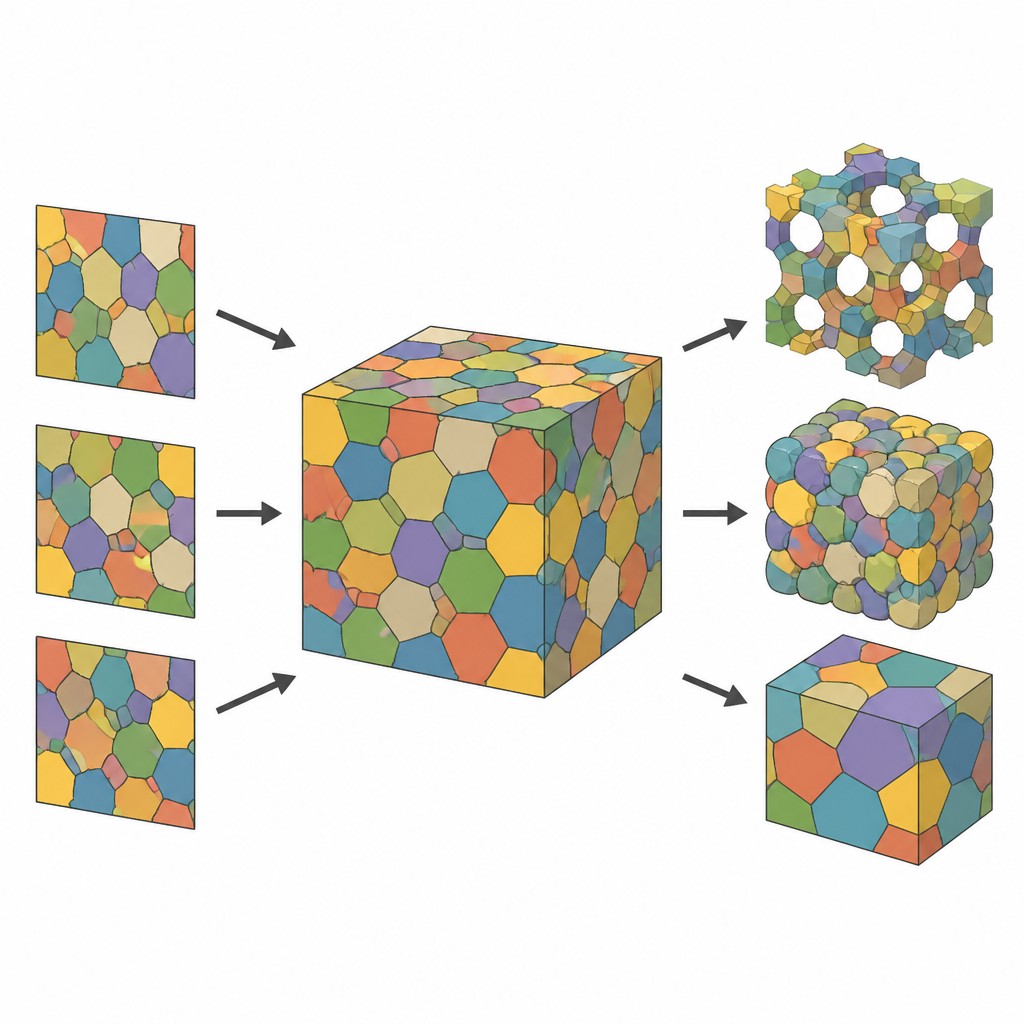
Des tranches planes aux cartes cellulaires 3D complètes
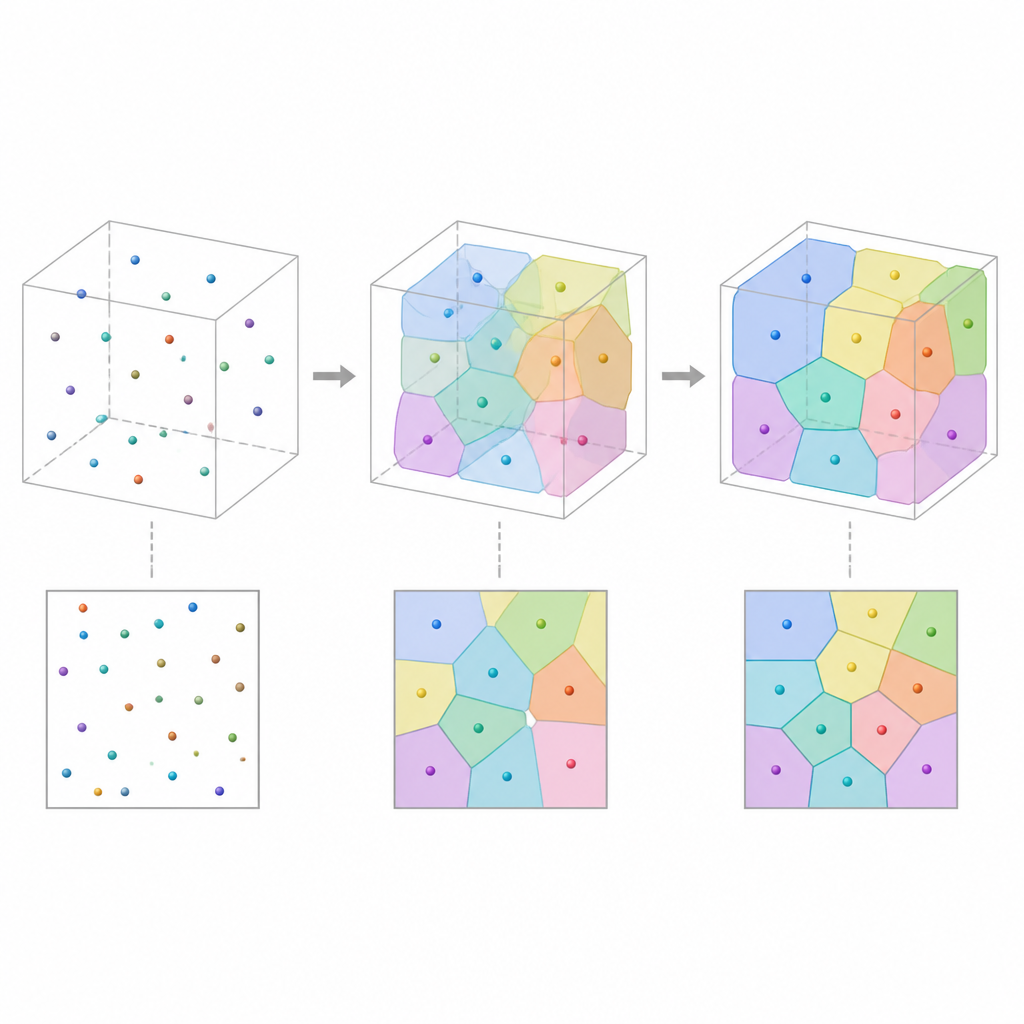
La plupart des expériences ne capturent que des fines tranches d’un matériau : des images au microscope montrant l’apparence des cellules en coupe. Bien que utiles, ces vues 2D ne révèlent pas comment les cellules s’étendent et se connectent en profondeur. Les auteurs abordent ce problème en considérant la structure 3D invisible comme un ensemble de cellules qui partitionnent l’espace, à la manière d’une mosaïque de polyèdres « bulles » en contact. En partant d’un nuage de points dans l’espace et en assignant à chaque point la région la plus proche, ils obtiennent une tessellation de Voronoi, un cadre géométrique qui imite naturellement de nombreux matériaux cellulaires. Chaque cellule est ensuite colorée et représentée comme une image lisse, adaptée au calcul, de sorte que le modèle puisse être ajusté et comparé aux tranches mesurées.
Apprendre à un réseau de juger le réalisme
Pour que la structure 3D synthétique ressemble aux matériaux réels, les auteurs entraînent un réseau discriminant, similaire à ceux utilisés dans les intelligences artificielles génératrices d’images. Ce réseau apprend à distinguer les images 2D extraites du modèle 3D courant des tranches 2D réelles mesurées expérimentalement. Au début, les tranches du modèle paraissent irréalistes, si bien que le discriminateur les repère facilement comme factices. L’algorithme déplace alors légèrement les points graines qui définissent les cellules, en utilisant une optimisation basée sur le gradient, pour rendre les tranches du modèle plus difficiles à distinguer des vraies. Au fil de nombreuses itérations, le motif cellulaire 3D évolue jusqu’à ce que le discriminateur considère les tranches simulées et mesurées comme statistiquement similaires.
Concilier détail, efficacité et interprétabilité
L’approche est conçue pour utiliser très peu de paramètres par cellule tout en conservant une signification physique claire. Chaque cellule est principalement définie par la position d’un seul point, plutôt que par des milliers de pixels d’image. Cette description compacte réduit l’utilisation de mémoire d’un facteur de l’ordre de centaines par rapport à des images 3D complètes, tout en permettant un contrôle direct sur des caractéristiques importantes comme la taille, la forme et les relations de voisinage des cellules. Des conditions périodiques aux frontières évitent des effets de bord artificiels sur de petits échantillons, et une version « douce » de la tessellation, basée sur des poids lissés proportionnels aux distances, maintient la stabilité et la différentiabilité de l’optimisation tout en préservant la possibilité de récupérer ensuite des frontières cellulaires nettes.
Tests sur matériaux synthétiques et réels
L’équipe vérifie d’abord son cadre sur des microstructures artificielles déjà bien décrites par des cellules de Voronoi. En reconstruisant des motifs 3D à partir de nombreuses tranches 2D et en comparant des statistiques telles que le volume cellulaire, la surface, l’allongement et le nombre de voisins, ils montrent que les structures générées correspondent étroitement aux originales. Ils appliquent ensuite la méthode à des données mesurées réelles : mousses de polymère, cellules biologiques presque sphériques et métaux polycristallins aux grains plus allongés et twins. Dans ces trois cas, les tessellations 3D reconstruites reproduisent les tendances géométriques clés observées en expérience, et le font souvent avec une meilleure précision sur les tailles et surfaces des cellules qu’une méthode concurrente purement basée sur des voxels.
Ce que cela signifie pour la conception future des matériaux
L’étude montre qu’il est possible d’inférer des architectures cellulaires 3D riches à partir d’images 2D en combinant tessellations géométriques et apprentissage adversarial. Bien que la version actuelle soit limitée aux cellules aux faces droites et planes et à des statistiques isotropes, elle offre déjà une voie rapide, peu paramétrique et physiquement interprétable pour construire des échantillons 3D virtuels utilisables directement par des outils de simulation. Pour les non-experts, le message clé est que les scientifiques peuvent désormais « regonfler » des tranches planes de matériau en modèles 3D réalistes, réduisant la dépendance à l’imagerie 3D coûteuse tout en capturant la structure interne essentielle qui gouverne le comportement du matériau.
Citation: Fuchs, L., Wilhelm, T., Furat, O. et al. Stereological reconstructions of 3D cellular microstructures by combining adversarial learning and Voronoi tessellations. Sci Rep 16, 15058 (2026). https://doi.org/10.1038/s41598-026-52851-7
Mots-clés: microstructure 3D, matériaux cellulaires, modèle de Voronoi, apprentissage adversarial, stéréologie