Clear Sky Science · pt
O dipolo de torque hidrodinâmico das flagelas bacterianas rotativas movimenta discos simétricos
Pequenos nadadores que podem girar pequenas engrenagens
À primeira vista, uma nuvem de bactérias nadando parece um caos sem rumo. Este estudo revela que, sob as condições certas, esses microrganismos podem fazer algo surpreendentemente ordenado: podem fazer discos perfeitamente redondos e simétricos girarem na direção escolhida sem jamais empurrar diretamente suas bordas. O trabalho mostra como o movimento de torção das caudas bacterianas pode ser aproveitado como um novo tipo de fonte de energia microscópica, com possíveis implicações para materiais inteligentes, máquinas minúsculas e para entender como bactérias se movem por espaços estreitos na natureza.
Como bactérias se deslocam e agitam o entorno
Bactérias móveis como Escherichia coli se impulsionam com motores rotativos que giram longas caudas flexíveis chamadas flagelas. Na escala de alguns micrômetros, a água se comporta como um xarope espesso: nada desliza, e para continuar se movendo a célula precisa constantemente empurrar o fluido. Durante anos, físicos descreveram microrganismos nadadores principalmente por como eles puxam ou empurram o fluido ao longo de sua direção de movimento, um quadro que explica efeitos como a difusão aumentada de partículas próximas e até comportamento semelhante a “superfluidos” em sopas microbianas densas. Mas essa visão padrão ignora em grande parte outra característica do movimento: como o feixe de flagelas gira de um lado e o corpo celular gira do outro para equilibrar o torque total, cada bactéria também atua como um pequeno par de agitadores que giram em sentidos opostos.
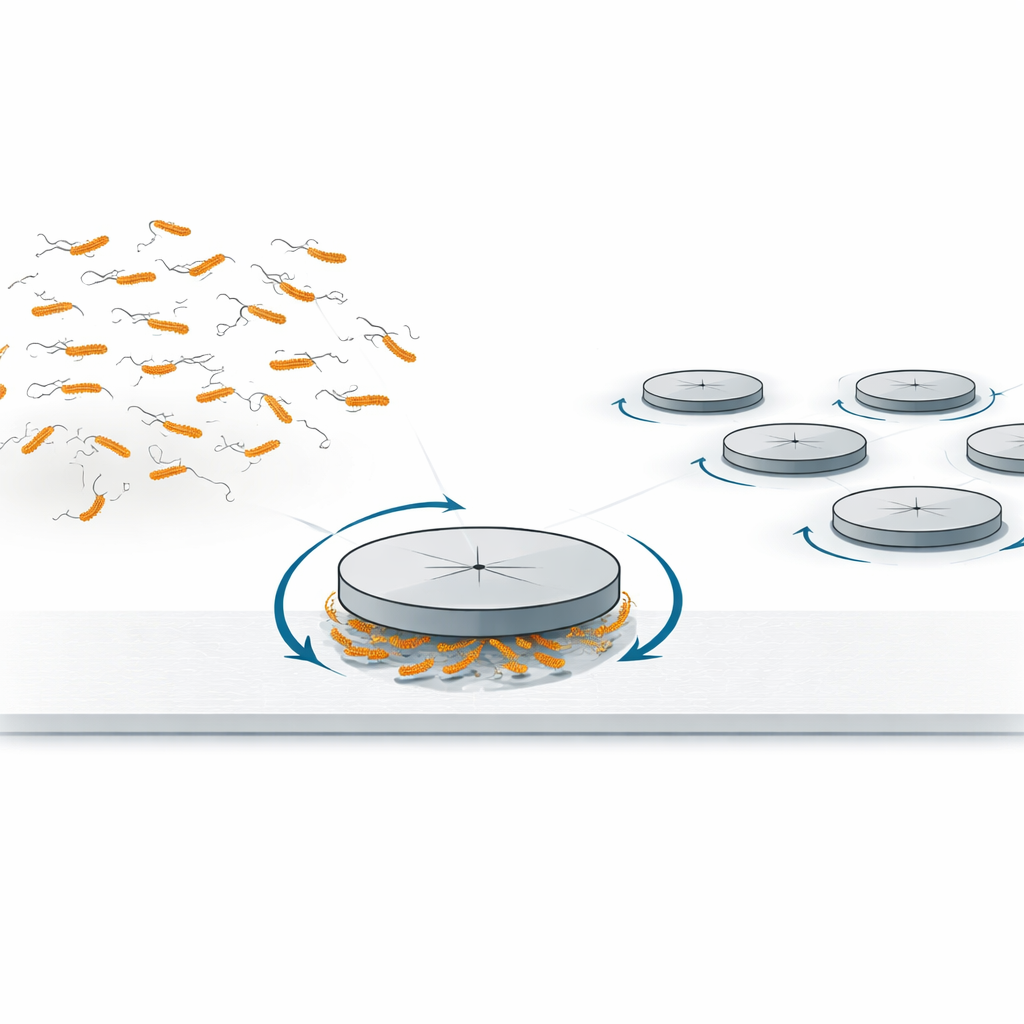
De colisões aleatórias a giro controlado
Os autores primeiro revisitaram um efeito mais familiar: quando discos lisos, ou “pucks”, eram colocados na parede inferior de uma câmara de vidro estreita cheia de uma suspensão densa de bactérias nadadoras, as colisões das bactérias com as bordas dos discos faziam os pucks girarem lentamente no sentido horário. Esse comportamento já havia sido observado antes com agregados de forma irregular, e pode ser explicado pelo fato de que, perto de uma superfície sólida, E. coli naturalmente nadam ao longo de trajetórias curvas, no sentido horário. Essas trajetórias curvas levam a leves impactos com predomínio em um sentido de rotação sobre o outro, produzindo um torque líquido suave no perímetro do disco. A equipe mediu como a taxa de rotação dependia do tamanho do disco e mostrou que ela escalava como esperado para esse mecanismo de colisões nas bordas, confirmando que impactos simples com bactérias nadadoras podem pôr objetos simétricos em rotação.
Confinando uma única bactéria sob um disco
Para sondar uma fonte de movimento mais sutil, os pesquisadores usaram impressão 3D de alta resolução para esculpir discos com passagens subterrâneas estreitas de apenas alguns micrômetros de altura e largura. Em um projeto, quatro câmaras radiais curtas terminavam pouco antes do centro do disco; em outro, um canal retilíneo atravessava o disco, aberto em ambas as extremidades. Essas estruturas foram orientadas voltadas para baixo, de modo que bactérias nadando ao longo da superfície inferior pudessem ocasionalmente entrar e ficar fortemente confinadas sob um puck. Como os canais eram tão estreitos, as bactérias não podiam facilmente se virar ou deslizar ao longo das paredes de uma maneira que simplesmente as fizesse empurrar contra um beco sem saída. Ainda assim, uma vez que uma única célula entrava numa câmara radial, a taxa de rotação do disco saltava em uma ordem de magnitude, sempre no mesmo sentido (horário), e aumentava ainda mais à medida que mais câmaras eram preenchidas. Mesmo quando os canais estavam abertos em ambas as extremidades — de modo que não havia parede contra a qual empurrar — a passagem de uma única bactéria através do disco produzia uma mudança característica “para baixo–para cima” no ângulo do disco: ele primeiro girava para um lado e depois para o outro quando a célula saía. Crucialmente, esse padrão não dependia de a bactéria nadar da esquerda para a direita ou da direita para a esquerda, afastando a hipótese de que empurrões simples fossem a causa.
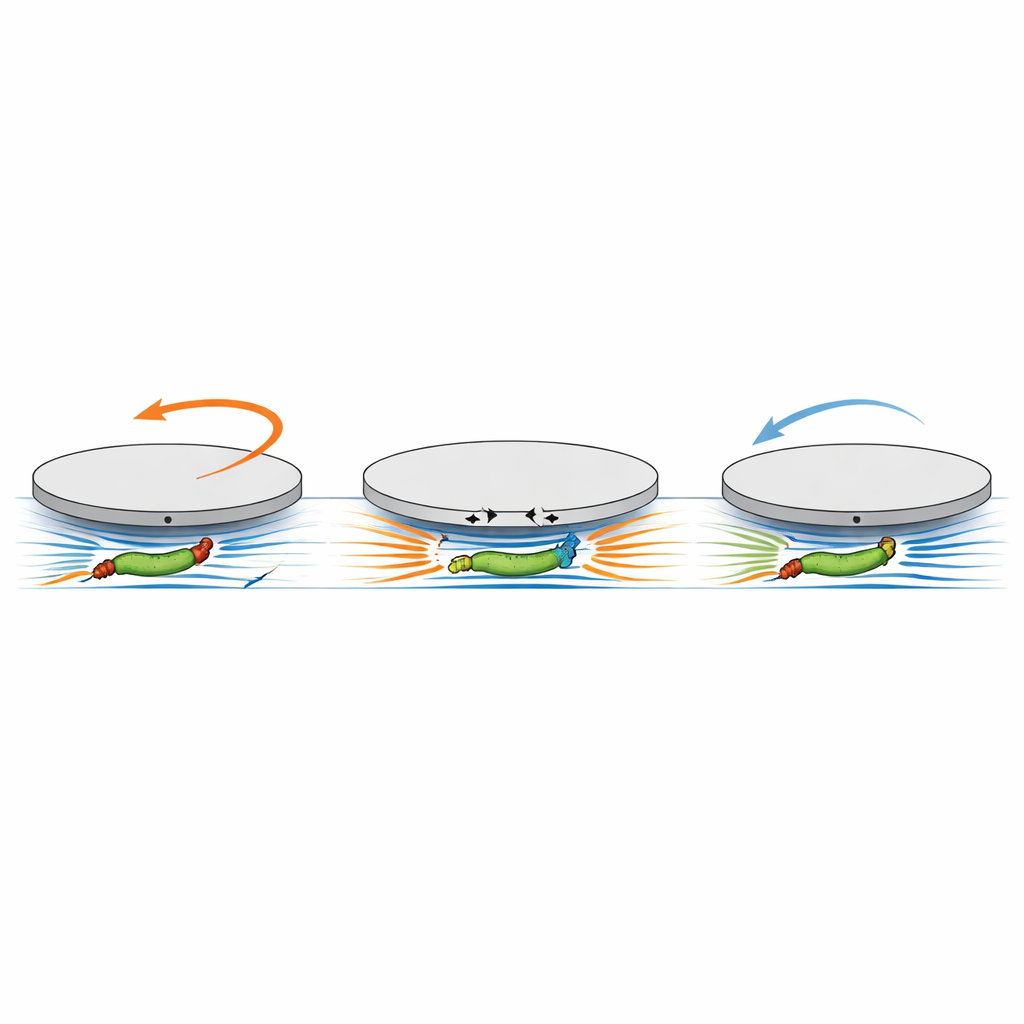
Um torque oculto que agarra o disco
Para explicar essas observações intrigantes, a equipe construiu um modelo hidrodinâmico que se concentrou na ação de torção, em vez da ação em linha reta, do motor bacteriano. No modelo, o corpo celular giratório e o feixe de flagelas que gira em sentido contrário são tratados como duas pequenas fontes de movimento rotacional no fluido, separadas por uma distância comparável ao comprimento da célula. Quando esse par está dentro de um canal estreito logo abaixo do disco, os fluxos rotacionais que geram arrastam a parede superior do canal — a face inferior do disco — em direções opostas em posições ligeiramente diferentes. Como esses dois padrões de tração estão deslocados ao longo do canal, eles não se cancelam perfeitamente. Em vez disso, combinam-se para exercer um torque líquido que tende a girar o disco inteiro. Os cálculos mostram que esse torque é independente da direção de natação da célula e escala com a separação efetiva entre corpo e flagelas, que por sua vez cresce com o comprimento da célula. O modelo reproduz tanto a rotação inicial no sentido horário quando corpo e flagelas estão sob o disco juntos, quanto a inversão posterior quando apenas um deles permanece no canal enquanto a célula sai.
Rumo a fluidos quirais e máquinas microbianas
Ao comparar as medições com seu modelo, os autores concluem que os motores rotativos de E. coli atuam como “dipolos de torque” que podem transmitir movimento de torção através de um fluido para objetos próximos sem contato direto ou assimetria de forma. O confinamento — aqui, os canais estreitos sob os discos — é o que converte essa torção local em um giro persistente e direcional. Quando muitos desses pucks são colocados em um banho bacteriano, podem formar uma coleção de rotores idênticos todos girando no mesmo sentido, um passo rumo a fluidos “quirais” cujo comportamento em escala macroscópica depende de um sentido geral de torção. Além de oferecer uma nova forma de projetar máquinas microscópicas movidas por células vivas, esse mecanismo pode ser relevante sempre que bactérias com flagelas rotativas se deslocam por ambientes lotados ou porosos, como solos, biofilmes ou filtros projetados, acoplando sutilmente sua própria navegação ao movimento de seu entorno.
Citação: Grober, D., Dhar, T., Saintillan, D. et al. The hydrodynamic torque dipole from rotary bacterial flagella powers symmetric discs. Nat. Phys. 22, 620–627 (2026). https://doi.org/10.1038/s41567-026-03189-4
Palavras-chave: motilidade bacteriana, microfluídica, matéria ativa, micronadadores, micro-robôs