Clear Sky Science · es
El dipolo de par hidrodinámico de los flagelos bacterianos rotatorios impulsa discos simétricos
Pequeños nadadores que pueden girar pequeños engranajes
A primera vista, una nube de bacterias nadando parece un caos sin rumbo. Este estudio revela que, bajo las condiciones adecuadas, esos microbios pueden hacer algo sorprendentemente ordenado: pueden hacer girar discos perfectamente redondos y simétricos en una dirección elegida sin empujar directamente sus bordes. El trabajo muestra cómo el movimiento de torsión de las colas bacterianas puede aprovecharse como una nueva fuente microscópica de energía, con posibles implicaciones para materiales inteligentes, micromáquinas y la locomoción bacteriana en espacios estrechos en la naturaleza.
Cómo se mueven las bacterias y agitan su entorno
Bacterias móviles como Escherichia coli se impulsan con motores rotatorios que hacen girar largas colas flexibles llamadas flagelos. A escala de unos pocos micrómetros, el agua se comporta como un jarabe espeso: nada se desliza y, para seguir moviéndose, una célula debe empujar constantemente sobre el fluido. Durante años, los físicos han descrito a los microbios nadadores principalmente por cómo tiran o empujan el fluido a lo largo de su dirección de movimiento, una imagen que explica efectos como la difusión mejorada de partículas cercanas e incluso un comportamiento parecido a “superfluido” en caldos microbianos densos. Pero esa visión estándar ignora en gran medida otra característica del movimiento: dado que el haz de flagelos gira en un sentido y el cuerpo celular gira en el otro para equilibrar el par total, cada bacteria también actúa como una diminuta pareja de agitadores que rotan en sentidos opuestos.
De colisiones aleatorias a giro controlado
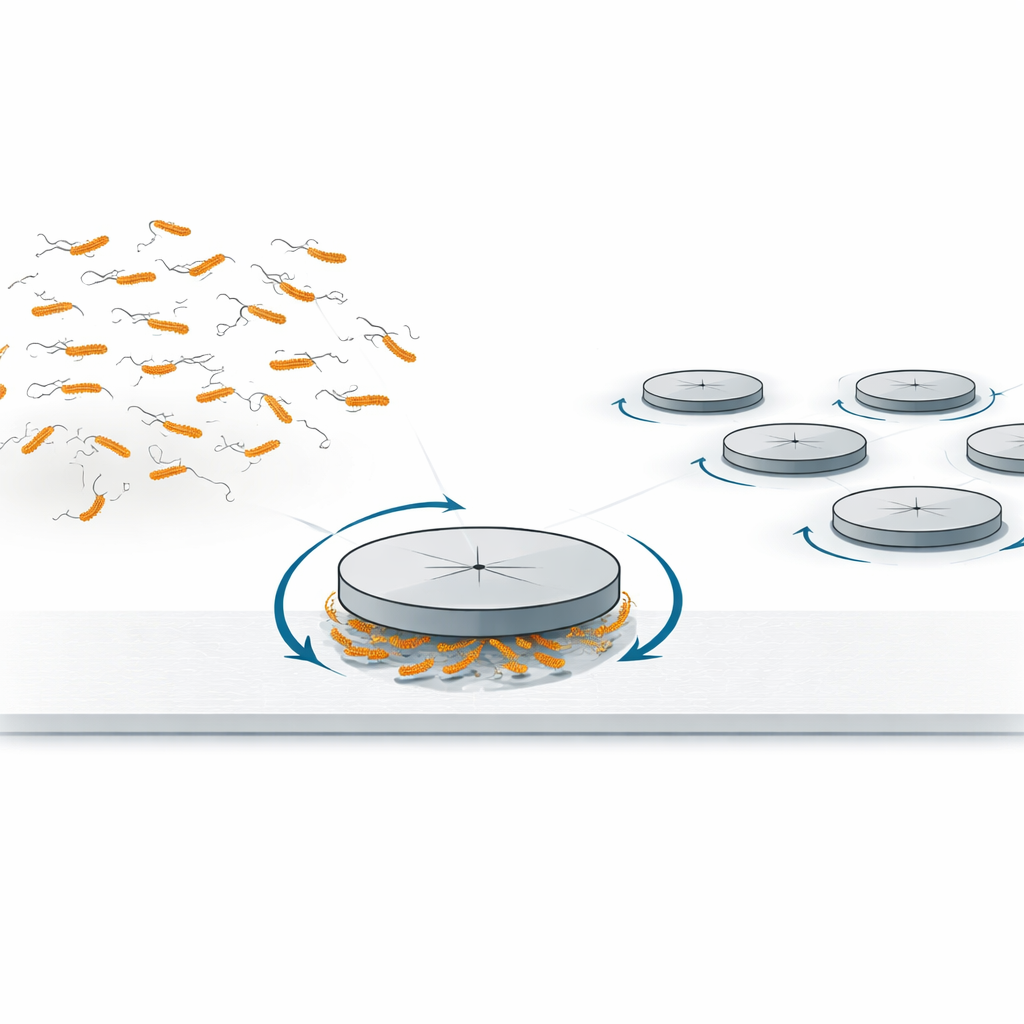
Los autores primero revisitaron un efecto más familiar: cuando discos lisos, o “pucks”, se colocaban en la pared inferior de una cámara de vidrio estrecha llena de una suspensión densa de bacterias nadadoras, las colisiones de las bacterias con los bordes del disco hacían que los pucks giraran lentamente en sentido horario. Este comportamiento ya se había observado antes con agregados de formas irregulares, y puede explicarse por el hecho de que cerca de una superficie sólida E. coli nada naturalmente siguiendo trayectorias curvadas en sentido horario. Esas trayectorias curvas producen ligeramente más impactos en una dirección de rotación que en la otra, generando un par neto suave en el perímetro del disco. El equipo midió cómo dependía la velocidad de rotación del tamaño del disco y mostró que escalaba como se espera para este mecanismo de colisión en el borde, confirmando que impactos simples con bacterias nadadoras pueden poner a girar objetos simétricos.
Confinando bacterias individuales bajo un disco
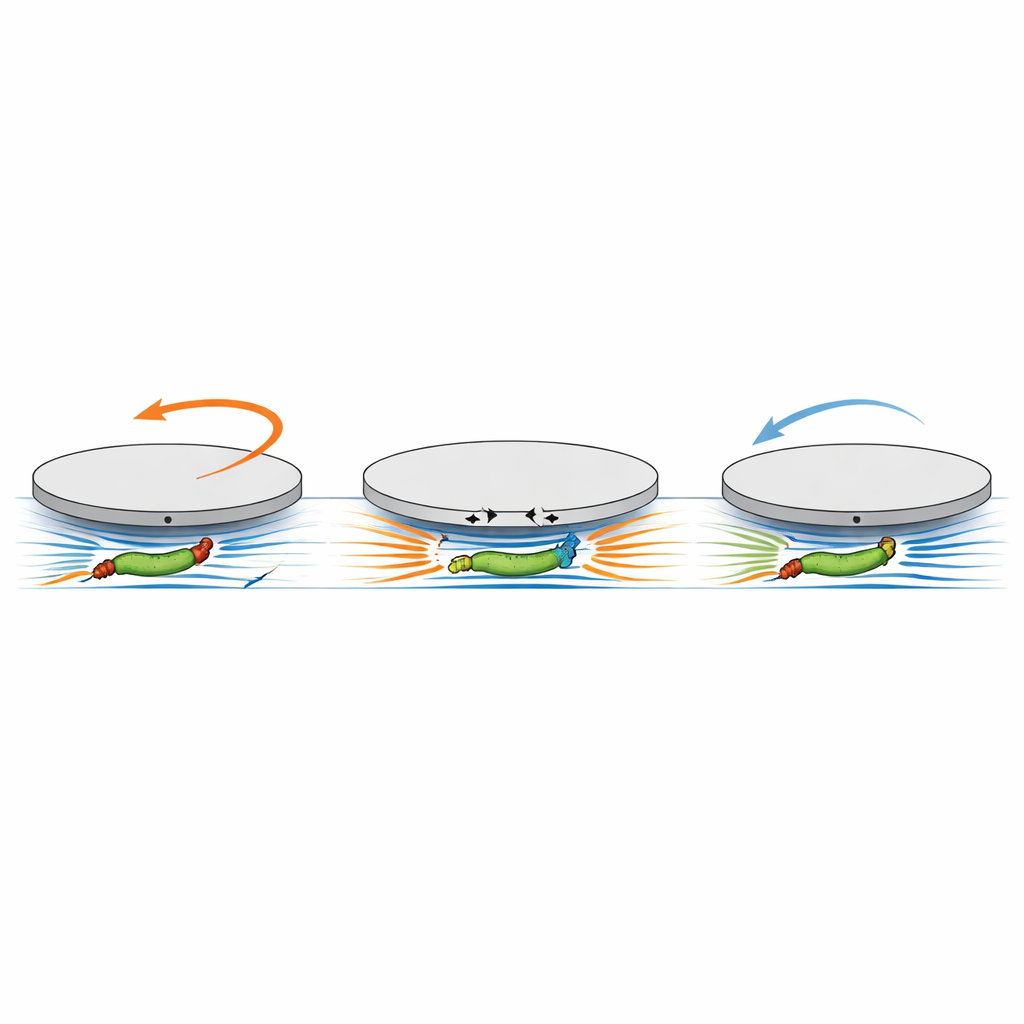
Para indagar en una fuente de movimiento más sutil, los investigadores usaron impresión 3D de alta resolución para esculpir discos con pasadizos subterráneos estrechos de apenas unos micrómetros de alto y ancho. En un diseño, cuatro cámaras radiales cortas terminaban a poca distancia del centro del disco; en otro, un canal recto atravesaba el disco abierto en ambos extremos. Estas cavidades estaban orientadas hacia abajo, de modo que las bacterias que nadaban a lo largo de la superficie inferior podían entrar ocasionalmente y quedar fuertemente confinadas bajo un puck. Debido a que los canales eran tan estrechos, las bacterias no podían girar fácilmente ni deslizarse junto a las paredes de manera que simplemente empujaran contra un callejón sin salida. Aun así, una vez que una sola célula entraba en una cámara radial, la velocidad de rotación del disco aumentaba en un orden de magnitud, siempre en la misma dirección (horaria), y crecía aún más a medida que se llenaban más cámaras. Incluso cuando los canales estaban abiertos por ambos extremos—de modo que no había pared contra la que empujar—el paso de una sola bacteria a través del disco producía un cambio característico “baja–sube” en el ángulo del disco: primero giraba en un sentido y luego en el otro al salir la célula. Crucialmente, este patrón no dependía de si la bacteria nadaba de izquierda a derecha o de derecha a izquierda, lo que descarta el empuje simple como la causa.
Un par de par oculto que atrapa el disco
Para explicar estas observaciones desconcertantes, el equipo construyó un modelo hidrodinámico que se centró en la acción de torsión del motor bacteriano, más que en el movimiento en línea recta. En el modelo, el cuerpo celular giratorio y el haz de flagelos que gira en sentido contrario se tratan como dos diminutas fuentes de movimiento rotatorio en el fluido, separadas por una distancia comparable a la longitud celular. Cuando este par se sitúa dentro de un canal estrecho justo bajo el disco, los flujos rotatorios que generan arrastran la pared superior del canal—la parte inferior del disco—en direcciones opuestas y en posiciones ligeramente distintas. Porque esos dos patrones de tracción están desplazados a lo largo del canal, no se anulan perfectamente. En su lugar, se combinan para ejercer un par neto que tiende a hacer girar todo el disco. Los cálculos muestran que este par es independiente de la dirección de nado de la célula y escala con la separación efectiva entre cuerpo y flagelos, que a su vez aumenta con la longitud celular. El modelo reproduce tanto el giro horario inicial cuando cuerpo y flagelos están bajo el disco juntos, como la inversión posterior cuando solo uno de ellos permanece en el canal mientras la célula sale.
Hacia fluidos chirales y máquinas microbianas
Al comparar las medidas con su modelo, los autores concluyen que los motores rotatorios de E. coli actúan como “dipolos de par” que pueden transmitir movimiento de torsión a través de un fluido a objetos cercanos sin contacto directo ni asimetría de forma. El confinamiento—aquí, los canales estrechos bajo los discos—es lo que convierte esa torsión local en un giro persistente y direccional. Cuando muchos de estos pucks se colocan en un baño bacteriano, pueden formar una colección de rotores idénticos que giran todos en el mismo sentido, un paso hacia fluidos “chirales” cuyo comportamiento a gran escala depende de un sentido global de torsión. Más allá de ofrecer una nueva forma de diseñar micromáquinas impulsadas por células vivas, este mecanismo puede ser relevante dondequiera que bacterias con flagelos rotatorios se muevan a través de entornos concurridos o porosos, como suelos, biopelículas o filtros diseñados, acoplando sutilmente su propia navegación al movimiento de su entorno.
Cita: Grober, D., Dhar, T., Saintillan, D. et al. The hydrodynamic torque dipole from rotary bacterial flagella powers symmetric discs. Nat. Phys. 22, 620–627 (2026). https://doi.org/10.1038/s41567-026-03189-4
Palabras clave: motilidad bacteriana, microfluídica, materia activa, micronadadores, micro-robots