Clear Sky Science · nl
Populatiegenetische variatie gekarakteriseerd via seriële onafhankelijke pool‑seq: het Cyprus Genoom Project
Waarom het DNA van een klein eiland ertoe doet
Stel je voor dat je ziekten wilt diagnosticeren en behandelen met kaarten die vooral andere mensen uit andere plekken beschrijven. Dat is de situatie waarin veel landen zich bevinden binnen de moderne genetica. Deze studie verkleint die kloof voor Cyprus door de eerste grootschalige genetische referentiekaart samen te stellen die specifiek is gemaakt van mensen die op het eiland wonen. Door op slimme wijze DNA van 10.000 vrijwilligers te poolen, creëerden de onderzoekers een kosten‑efficiënte, privacy‑vriendelijke manier om in kaart te brengen welke genetische veranderingen veelvoorkomend of zeldzaam zijn bij Cyprioten — en hoe die patronen afwijken van de wereldwijde gemiddelden waarop artsen doorgaans vertrouwen.
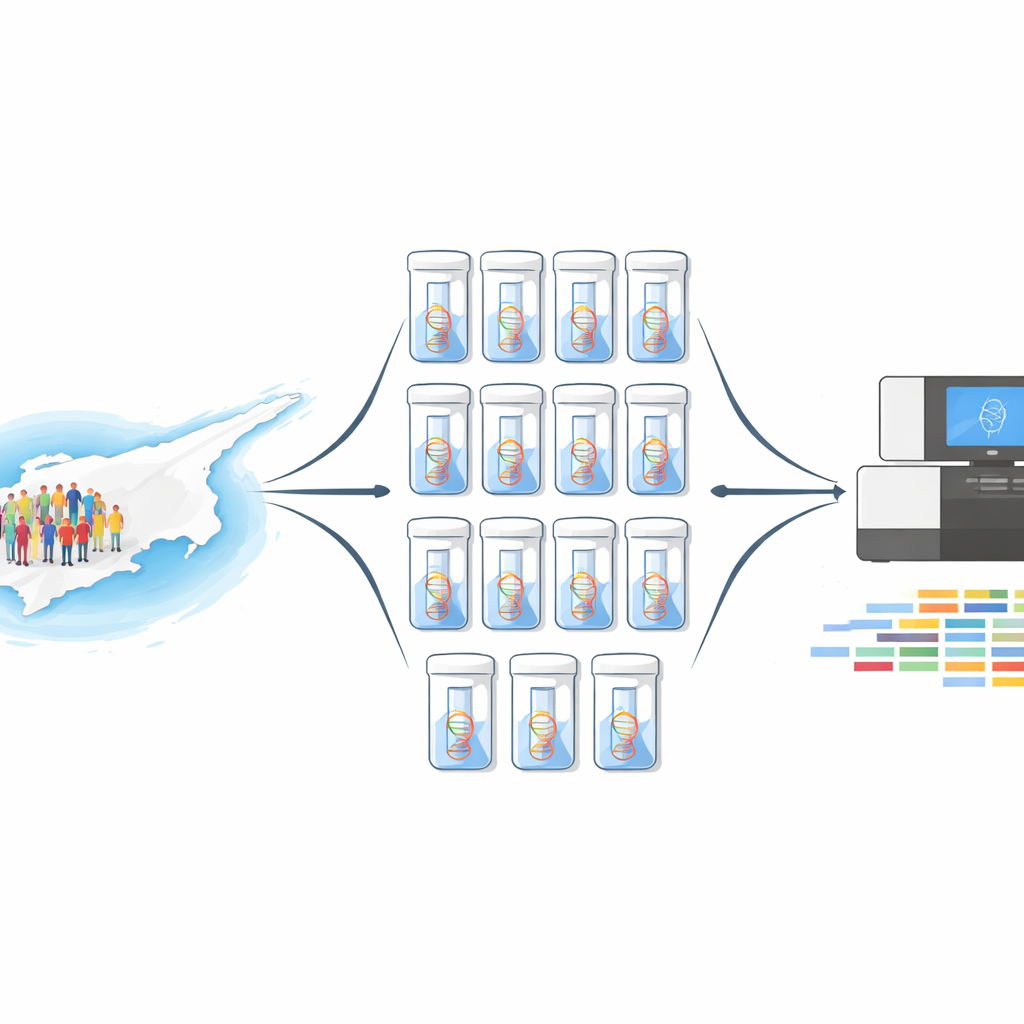
Een nieuwe manier om duizenden mensen tegelijk te bekijken
Het volledig sequentiëren van het genoom van 10.000 individuen één voor één zou enorm duur en tijdrovend zijn. In plaats daarvan gebruikte het team een methode die DNA‑pooling heet. Ze combineerden gelijke hoeveelheden DNA van 1.000 vrijwillige beenmergdonoren in één mengsel en herhaalden dit tien keer, waardoor er tien onafhankelijke pools ontstonden. Elke pool werd vervolgens twee keer gesequenced: eenmaal met whole‑exome sequencing, die alle eiwitcoderende regio’s van het genoom doorzoekt, en eenmaal met een gericht paneel van 813 medisch belangrijke genen. Dit ontwerp leverde zowel breedte over het genoom als zeer diepe dekking in genen die klinisch het belangrijkst zijn.
Reële signalen scheiden van ruis
DNA poolen kent afwegingen. Hoewel het de identiteit van individuele personen verbergt en kosten verlaagt, maakt het het ook lastiger om zeer zeldzame veranderingen te detecteren en om zeker te zijn dat een zwak signaal geen machinefout is. Om dit aan te pakken bouwden de auteurs stevige waarborgen in hun studie. Ze eisten dat elk gerapporteerd genetisch variant ondersteund werd door minstens 20 sequencingreads en in ten minste drie van de tien onafhankelijke pools voorkwam. Voor een subset met hoge betrouwbaarheid vroegen ze om duizenden totale reads over de pools heen. Ze controleerden ook of het patroon van variantfrequenties in elke pool overeenkwam met de andere en vergeleken hun resultaten met internationale databases en kleinere Cypriotische studies. Sterke statistische overeenstemming liet zien dat de pooled‑benadering de frequentie van elke variant met hoge precisie kon meten.
Wat het Cypriotische DNA onderscheidt
Uit de gepoolde gegevens heeft het project meer dan vier miljoen genetische varianten gecatalogiseerd, inclusief meer dan 100.000 die niet voorkomen in grote internationale bronnen zoals gnomAD en ClinVar. Veel van deze verschillen zijn klinisch relevant. Sommige genveranderingen die in verband worden gebracht met bloedziekten of neiging tot bloedingen, bijvoorbeeld, zijn tientallen keren vaker voorkomend in Cyprus dan in wereldwijde datasets, wat suggereert dat ze mogelijk een plek verdienen in nationale screeningsprogramma’s. Omgekeerd vond het team ook varianten die wereldwijd extreem zeldzaam lijken maar relatief vaak voorkomen bij gezonde Cypriotische donoren. Zonder lokale gegevens zouden zulke veranderingen ten onrechte verdacht kunnen worden van ziekte omdat ze elders zo ongewoon zijn.
Het heroverwegen van risicoscores en genetische tests
De nieuwe kaart toont ook dat sommige risicoverhogende varianten die wereldwijd veel voorkomen in Cyprus veel zeldzamer zijn, en omgekeerd. Die mismatch heeft praktische consequenties. Veel moderne instrumenten, zoals polygenische risicoscores die iemands kans op aandoeningen als kanker of hartziekten schatten, gaan ervan uit dat de onderliggende variantfrequenties in de doelpopulatie lijken op die in de referentiepopulatie waarmee het instrument is gebouwd. De Cyprus‑gegevens laten zien dat die veronderstelling vaak niet opgaat. Daardoor kunnen risicoscores en diagnostische panelen die op buitenlandse data zijn gebouwd het risico voor Cypriotische patiënten overschatten of onderschatten, tenzij ze worden gekalibreerd met deze nieuwe lokale referentie.
Hoe deze bron toekomstige gezondheidszorg kan vormen
Voor niet‑specialisten is de kernboodschap dat dit project de genetische achtergrond van Cyprus van een blinde vlek verandert in een gedetailleerde kaart. De database op cyprusgenome.org stelt clinici en onderzoekers in staat om te zien of een genetische variant lokaal echt zeldzaam en verdacht is, of eenvoudigweg een onschuldige eigenschap van Cypriotische afkomst die wereldwijde studies gemist hebben. Die helderheid kan verkeerde diagnoses voorkomen, slimmer nationale screeningsstrategieën sturen en het fundament leggen voor nauwkeurigere risicovoorspellingsinstrumenten op maat van de eilandbevolking. Naarmate er meer sequencing en aanvullende datalagen, zoals profielen van immuungerelateerde genen en metingen van genactiviteit, worden toegevoegd, staat deze bron op het punt een hoeksteen te worden voor precisiegeneeskunde en volksgezondheidsplanning in Cyprus.
Bronvermelding: Antoniades, A., Chi, J., Brown, C. et al. Population genetic variation characterised through serial independent pool-seq: the Cyprus Genome Project. Sci Rep 16, 14215 (2026). https://doi.org/10.1038/s41598-026-44707-x
Trefwoorden: Cyprus-genoom, populatiegenetica, gepoolde DNA‑sequencing, zeldzame varianten, precisiemedicine