Clear Sky Science · es
Variación genética poblacional caracterizada mediante pool-seq independiente en serie: el Proyecto Genoma de Chipre
Por qué importa el ADN de una isla pequeña
Imagínese intentar diagnosticar y tratar enfermedades usando mapas que describen principalmente a otras personas, de otros lugares. Esa es la situación a la que se enfrentan muchos países en la genética moderna. Este estudio aborda esa carencia para Chipre construyendo el primer mapa de referencia genética a gran escala hecho específicamente con personas que viven en la isla. Al agrupar de forma astuta el ADN de 10.000 voluntarios, los investigadores crearon una forma rentable y respetuosa con la privacidad de cartografiar qué cambios genéticos son comunes o raros en los chipriotas —y cómo esos patrones difieren de los promedios globales en los que los médicos suelen confiar.
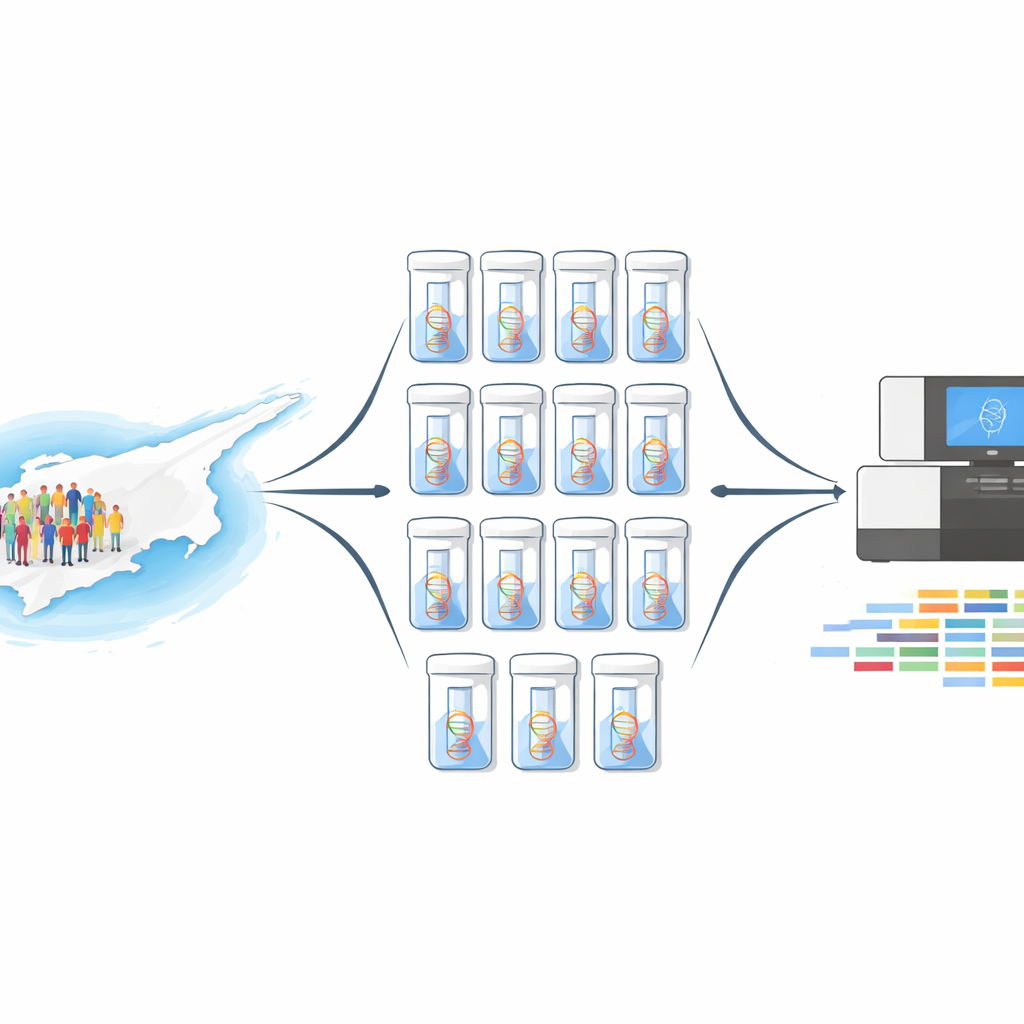
Una nueva manera de observar a miles de personas a la vez
Secuenciar el código genético completo de 10.000 individuos uno por uno sería enormemente caro y llevaría mucho tiempo. En su lugar, el equipo utilizó un método llamado agrupación de ADN (DNA pooling). Combinaron cantidades iguales de ADN de 1.000 donantes voluntarios de médula ósea en una única mezcla, y repitieron esto diez veces, creando diez grupos independientes. Cada grupo se secuenció dos veces: una vez mediante secuenciación del exoma completo, que explora todas las regiones codificantes de proteínas del genoma, y otra vez usando un panel focalizado de 813 genes con importancia médica. Este diseño proporcionó tanto amplitud a lo largo del genoma como una cobertura muy profunda en los genes que importan más para la enfermedad.
Separar señales reales del ruido
El agrupamiento de ADN tiene compensaciones. Si bien oculta la identidad de cualquier persona individual y reduce costes, también dificulta la detección de cambios muy raros y asegura que una señal débil no sea un error de la máquina. Para abordar esto, los autores integraron salvaguardas sólidas en su estudio. Requirieron que cualquier variante genética reportada estuviera respaldada por al menos 20 lecturas de secuenciación y apareciera en al menos tres de los diez grupos independientes. Para un subconjunto de alta confianza, exigieron miles de lecturas totales a través de los grupos. También comprobaron que el patrón de frecuencias de variantes en cada grupo coincidiera con los demás y compararon sus resultados con bases de datos globales y estudios chipriotas más pequeños. El fuerte acuerdo estadístico mostró que el enfoque agrupado podía medir con alta precisión la frecuencia de cada variante.
Qué hace que el ADN chipriota destaque
A partir de los datos agrupados, el proyecto catalogó más de cuatro millones de variantes genéticas, incluidas más de 100.000 que no aparecen en recursos internacionales importantes como gnomAD y ClinVar. Muchas de estas diferencias tienen importancia clínica. Algunos cambios genéticos vinculados a trastornos sanguíneos o problemas de coagulación, por ejemplo, son varias decenas de veces más comunes en Chipre que en los conjuntos de datos globales, lo que sugiere que podrían merecer un lugar en los programas nacionales de cribado. Por el contrario, el equipo también encontró variantes que parecen extremadamente raras a nivel mundial, pero que resultan relativamente frecuentes entre donantes chipriotas sanos. Sin datos locales, tales cambios podrían ser erróneamente sospechados de causar enfermedad simplemente porque son poco comunes en otros lugares.
Replantear las puntuaciones de riesgo y las pruebas genéticas
El nuevo mapa también muestra que algunas variantes que aumentan el riesgo y son comunes a nivel mundial son mucho más raras en Chipre, y viceversa. Ese desfase tiene consecuencias prácticas. Muchas herramientas modernas, como las puntuaciones de riesgo poligénico que estiman la probabilidad de desarrollar condiciones como cáncer o enfermedades cardíacas, asumen que las frecuencias de variantes subyacentes en la población objetivo se parecen a las de la población de referencia utilizada para construir la herramienta. Los datos chipriotas revelan que esa suposición a menudo falla. Como resultado, las puntuaciones de riesgo y los paneles diagnósticos basados en datos extranjeros pueden sobrestimar o subestimar el riesgo para pacientes chipriotas a menos que se recalibren usando esta nueva referencia local.
Cómo este recurso puede moldear la atención sanitaria futura
Para el público general, la conclusión es que este proyecto convierte el contexto genético de Chipre de un punto ciego en un mapa detallado. La base de datos en cyprusgenome.org permite a clínicos e investigadores ver si una variante genética es realmente rara y sospechosa a nivel local, o simplemente una característica inofensiva de la ascendencia chipriota que los estudios globales han pasado por alto. Esa claridad puede prevenir diagnósticos erróneos, orientar estrategias nacionales de cribado más inteligentes y sentar las bases para herramientas de predicción de riesgo más precisas, adaptadas a la población de la isla. A medida que se añadan más secuenciaciones y futuras capas de datos, como perfiles de genes inmunitarios y mediciones de actividad génica, este recurso está listo para convertirse en una piedra angular de la medicina de precisión y la planificación de la salud pública en Chipre.
Cita: Antoniades, A., Chi, J., Brown, C. et al. Population genetic variation characterised through serial independent pool-seq: the Cyprus Genome Project. Sci Rep 16, 14215 (2026). https://doi.org/10.1038/s41598-026-44707-x
Palabras clave: genoma de Chipre, genética poblacional, secuenciación de ADN agrupado, variantes raras, medicina de precisión