Clear Sky Science · de
Die genetische Variation der Bevölkerung durch serielle, unabhängige Pool‑Seq charakterisiert: Das Cyprus Genome Project
Warum die DNA einer kleinen Insel zählt
Stellen Sie sich vor, Krankheiten zu diagnostizieren und zu behandeln auf der Grundlage von Karten, die überwiegend andere Menschen aus anderen Regionen beschreiben. So ist die Lage, der viele Länder in der modernen Genetik gegenüberstehen. Diese Studie schließt diese Lücke für Zypern, indem sie die erste groß angelegte genetische Referenzkarte erstellt, die speziell aus Menschen stammt, die auf der Insel leben. Durch das clevere Poolen von DNA von 10.000 Freiwilligen entwickelten die Forscher eine kosteneffiziente, datenschutzfreundliche Methode, um zu kartieren, welche genetischen Veränderungen bei Zyprern häufig oder selten sind — und wie diese Muster von den globalen Durchschnitten abweichen, auf die Ärztinnen und Ärzte normalerweise zurückgreifen.
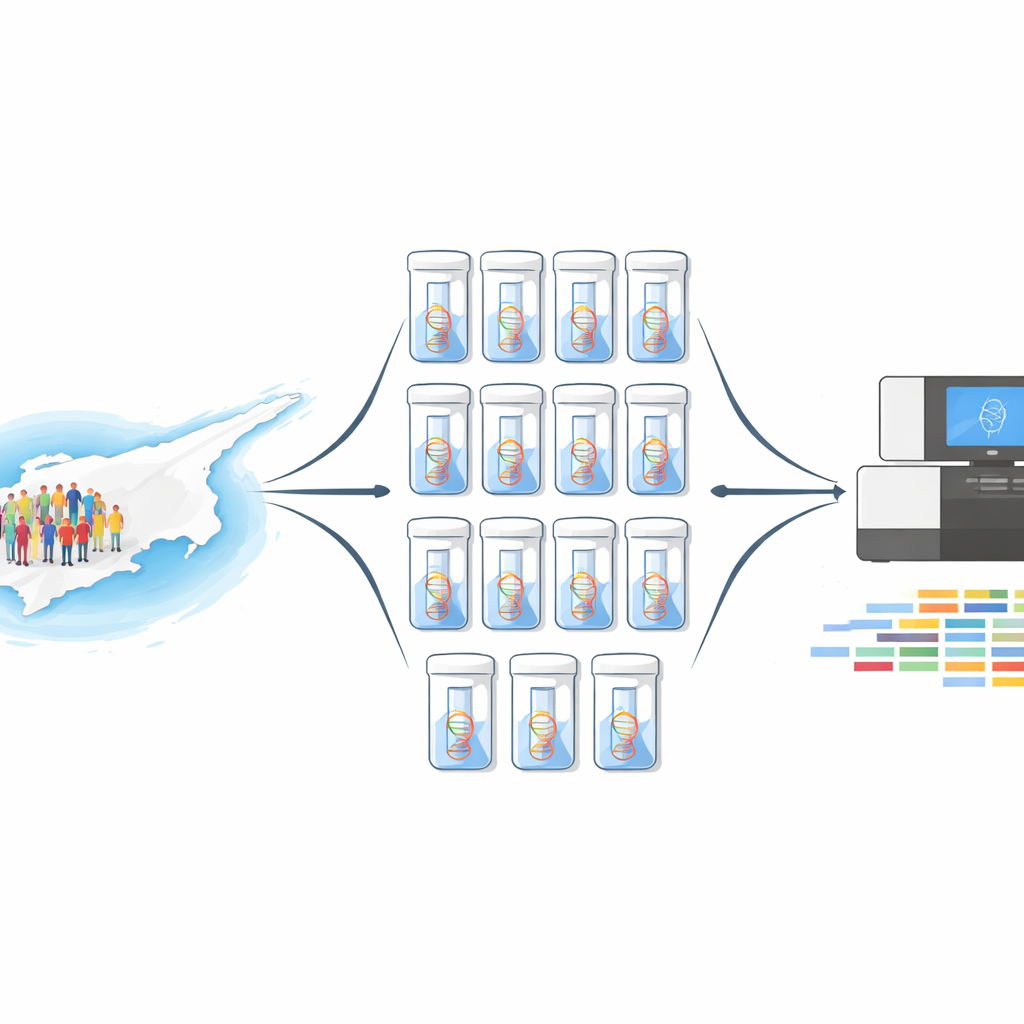
Eine neue Art, Tausende Menschen zugleich zu betrachten
Das komplette Sequenzieren des Erbguts von 10.000 Individuen einzeln wäre enorm teuer und zeitaufwendig. Stattdessen nutzte das Team eine Methode namens DNA-Pooling. Sie kombinierten gleiche Mengen an DNA von 1.000 freiwilligen Knochenmarkspendern zu einer einzigen Mischung und wiederholten das zehnmal, wodurch zehn unabhängige Pools entstanden. Jeder Pool wurde dann zweimal sequenziert: einmal mittels Whole‑Exome‑Sequencing, das alle protein-kodierenden Regionen des Genoms abtastet, und einmal mit einem fokussierten Panel von 813 medizinisch relevanten Genen. Dieses Design lieferte sowohl Breite über das gesamte Genom als auch sehr tiefe Abdeckung in den Genen, die für Krankheiten besonders wichtig sind.
Echte Signale von Rauschen trennen
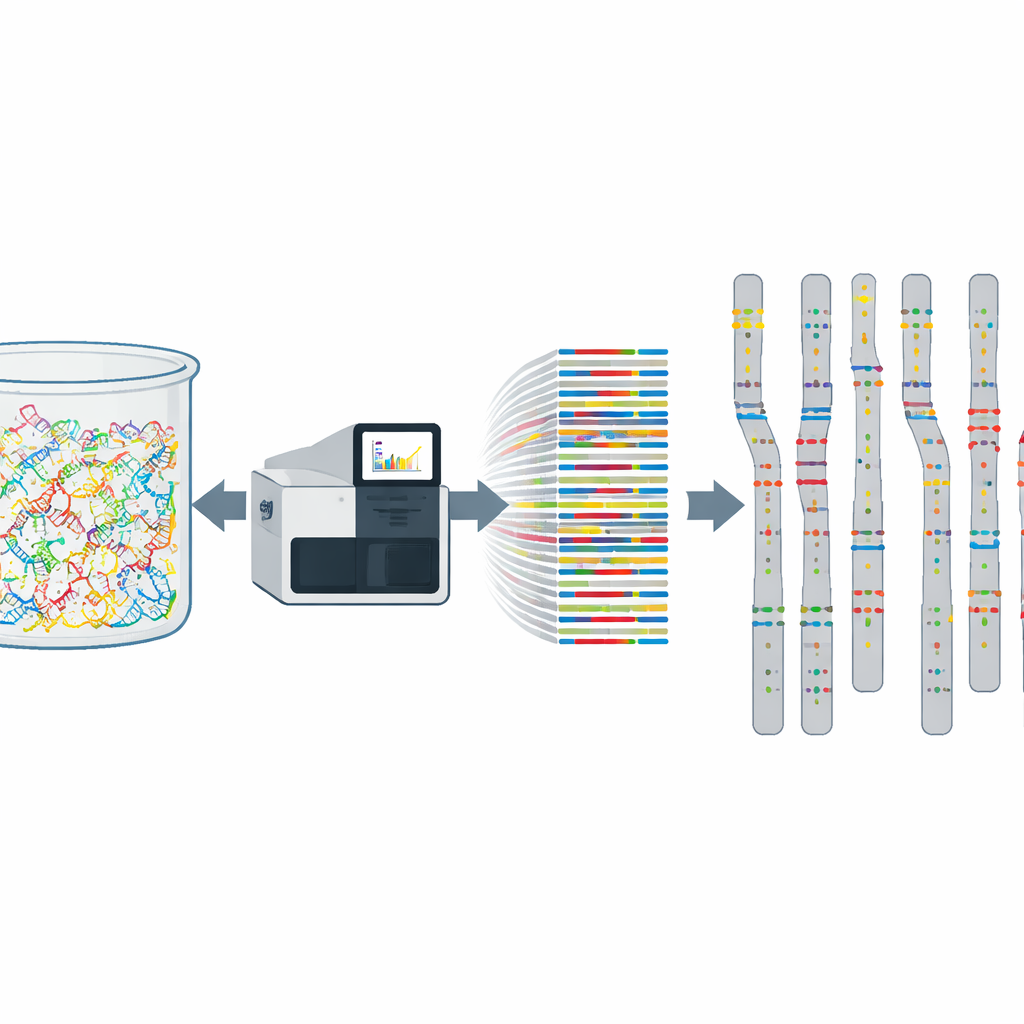
DNA-Pooling hat Vor- und Nachteile. Zwar schützt es die Identität einzelner Personen und reduziert Kosten, macht es aber schwieriger, sehr seltene Veränderungen zu erkennen und zu bestätigen, dass ein schwaches Signal nicht nur ein Maschinenfehler ist. Um dem zu begegnen, bauten die Autorinnen und Autoren starke Sicherheitsmaßnahmen in ihre Studie ein. Sie verlangten, dass jede gemeldete genetische Variante von mindestens 20 Sequenzierungsreads gestützt wird und in mindestens drei der zehn unabhängigen Pools auftaucht. Für eine hochvertrauenswürdige Teilmenge forderten sie Tausende von Gesamtreads über die Pools hinweg. Außerdem prüften sie, ob das Muster der Variantenfrequenzen in jedem Pool mit den anderen übereinstimmt, und verglichen ihre Ergebnisse mit globalen Datenbanken und kleineren zypriotischen Studien. Die starke statistische Übereinstimmung zeigte, dass der Pooling‑Ansatz die Häufigkeit jeder Variante mit hoher Präzision messen kann.
Was die DNA Zyprerinnen und Zyprer hervorhebt
Aus den gepoolten Daten katalogisierte das Projekt mehr als vier Millionen genetische Varianten, darunter über 100.000, die in großen internationalen Ressourcen wie gnomAD und ClinVar nicht auftauchen. Viele dieser Unterschiede sind klinisch relevant. Manche Genveränderungen, die mit Blutkrankheiten oder Blutungsneigungen in Verbindung stehen, sind beispielsweise in Zypern um mehrere Dutzend Mal häufiger als in globalen Datensätzen, was darauf hindeutet, dass sie in nationale Screening‑Programme aufgenommen werden sollten. Umgekehrt fanden die Forschenden auch Varianten, die weltweit extrem selten scheinen, sich aber bei gesunden zypriotischen Spendern als relativ häufig erweisen. Ohne lokale Daten könnten solche Veränderungen fälschlich als krankheitsverursachend eingestuft werden, nur weil sie andernorts so selten sind.
Risikowerte und Gentests neu denken
Die neue Karte zeigt außerdem, dass manche risikosteigernden Varianten, die global häufig sind, in Zypern viel seltener vorkommen und umgekehrt. Diese Diskrepanz hat praktische Folgen. Viele moderne Instrumente, wie polygenetische Risikoscores, die die Wahrscheinlichkeit schätzen, an Krebs oder Herzkrankheiten zu erkranken, setzen voraus, dass die zugrunde liegenden Variantenfrequenzen in der Zielpopulation denen der Referenzpopulation ähneln, mit der das Instrument erstellt wurde. Die Zyprer‑Daten zeigen, dass diese Annahme oft nicht gilt. Folglich können Risikoscores und diagnostische Panels, die auf fremden Daten basieren, das Risiko für zypriotische Patientinnen und Patienten überschätzen oder unterschätzen, sofern sie nicht mithilfe dieser neuen lokalen Referenz nachkalibriert werden.
Wie diese Ressource die künftige Gesundheitsversorgung prägen kann
Für Nicht‑Fachleute lautet die Quintessenz: Dieses Projekt verwandelt den genetischen Hintergrund Zyperns von einer Lücke in eine detaillierte Karte. Die Datenbank unter cyprusgenome.org ermöglicht es Klinikerinnen, Klinikern und Forschenden zu prüfen, ob eine genetische Variante lokal wirklich selten und verdächtig ist oder schlicht ein harmloses Merkmal zypriotischer Abstammung, das globale Studien übersehen haben. Diese Klarheit kann Fehlinterpretationen verhindern, intelligentere nationale Screening‑Strategien leiten und die Grundlage für genauere, an die Insel angepasste Risikovorhersagewerkzeuge legen. Wenn weitere Sequenzierungen und zusätzliche Datenschichten wie Profile von Immungenen und Messungen der Genaktivität ergänzt werden, ist diese Ressource darauf angelegt, zu einem Eckpfeiler für Präzisionsmedizin und Gesundheitsplanung in Zypern zu werden.
Zitation: Antoniades, A., Chi, J., Brown, C. et al. Population genetic variation characterised through serial independent pool-seq: the Cyprus Genome Project. Sci Rep 16, 14215 (2026). https://doi.org/10.1038/s41598-026-44707-x
Schlüsselwörter: Cyprus-Genom, Populationsgenetik, Pooling von DNA-Sequenzen, seltene Varianten, Präzisionsmedizin