Clear Sky Science · nl
Een verbeterde genoomassemblage op chromosoomniveau en uitgebreide annotatie van het modelascidia Ciona savignyi
Waarom een klein zeediertje ertoe doet
Op het eerste gezicht lijkt de zakpijp Ciona savignyi een eenvoudig, zakvormig dier dat zich vastklampt aan steigers en scheepshuid. Toch zit dit bescheiden organisme dicht bij de evolutionaire wortel van alle gewervelde dieren, inclusief de mens. Omdat het makkelijk te kweken is, snel ontwikkelt en opmerkelijk goed in staat is nieuwe omgevingen te koloniseren, is Ciona savignyi een krachtig model geworden om te begrijpen hoe complexe lichamen ontstaan en hoe leven zich aan snelle milieuveranderingen aanpast. Deze studie levert een veel scherper genetisch blauwdruk voor deze soort, wat de deur opent naar preciezer werk in disciplines variërend van ontwikkelingsbiologie tot invasie-ecologie.
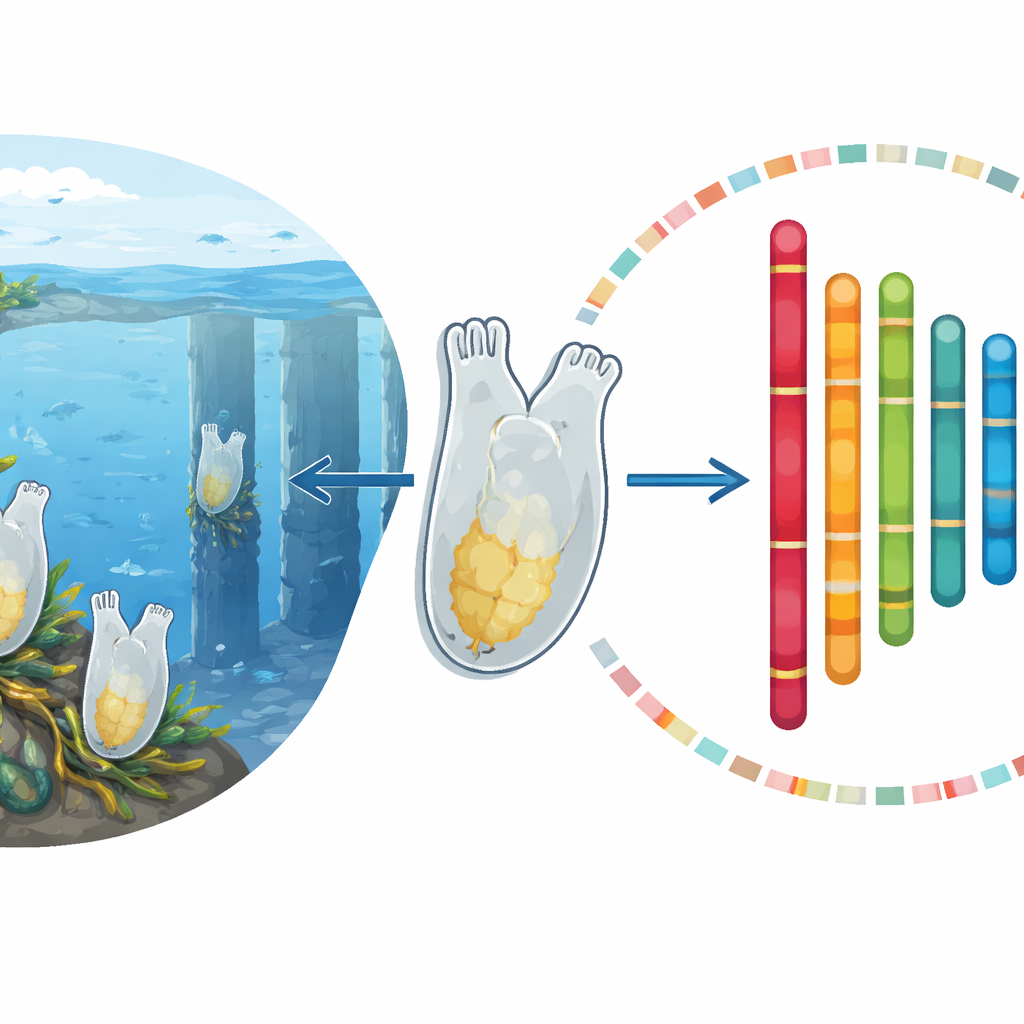
Een eenvoudig dier met een groot verhaal
Ciona savignyi behoort tot de tunicata, de naaste ongewervelde verwanten van de gewervelden. Hun kikkervisachtige larven hebben een stijve staaf en een zenuwkabel die lijken op de vroege wervelkolom en het ruggenmerg in gewervelde embryo’s. Omdat deze dieren transparante, snel ontwikkelende embryo’s en compacte genomen hebben, dienen ze al lange tijd als heldere, gestroomlijnde systemen om te onderzoeken hoe complexe lichaamsplannen ontstaan. Veel tunicaten, waaronder Ciona-soorten, verspreiden zich ook snel over de wereld en verdragen grote schommelingen in temperatuur en zoutgehalte. Dat maakt ze natuurlijke proefcases om te bestuderen hoe organismen omgaan met de milieuschokken die nu gepaard gaan met klimaatverandering en mondiale handel.
De noodzaak van een beter genetisch kaart
Onderzoekers bestuderen Ciona savignyi al jaren, maar de eerdere genoomkaart was gefragmenteerd en onvolledig. Een belangrijkere reden is dat individuen van deze soort een uitzonderlijk grote hoeveelheid genetische variatie dragen, wat het technisch lastig maakt om DNA-fragmenten aan elkaar te zetten. Het vorige referentiegenoom, algemeen gebruikt sinds 2008, was in honderden stukken gebroken. Dit beperkte het vermogen van wetenschappers om eigenschappen zoals stressbestendigheid, snelle acclimatie of verschillen tussen populaties te koppelen aan specifieke DNA-streken. Een duidelijker genoom op chromosoomschaal was nodig om Ciona savignyi tot een echt modern genomisch model te maken.
Het samenstellen van de genoompuzzel
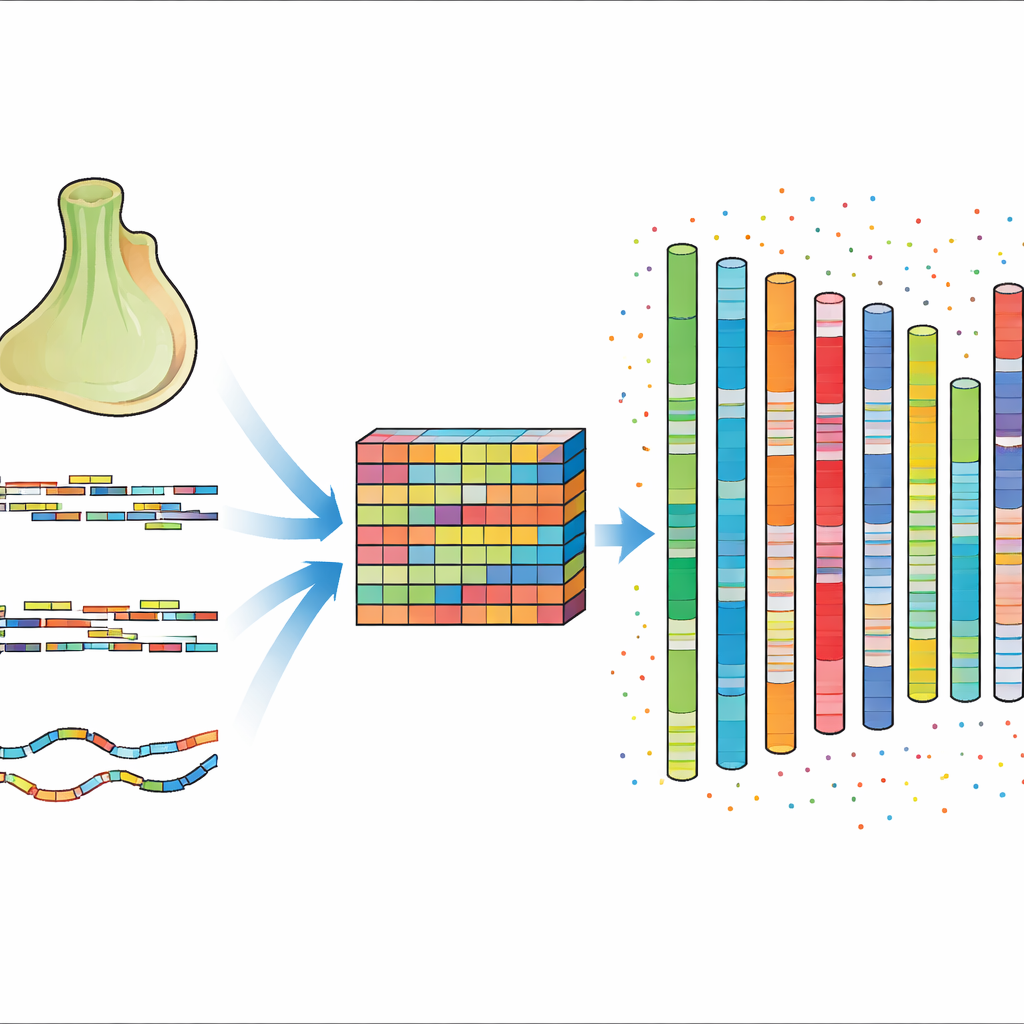
Om dit op te lossen combineerden de auteurs meerdere geavanceerde-sequencingbenaderingen. Ze gebruikten zeer nauwkeurige korte DNA-reads om de algemene samenstelling van het genoom te tellen en te karakteriseren, lange reads om lastige, repetitieve gebieden te overspannen, en een techniek genaamd Hi-C die onthult welke delen van het DNA dicht bij elkaar liggen in de celkern. Ze sequenceden ook lange RNA-strekken van meerdere dieren om vast te leggen welke genen actief zijn en hoe ze zijn opgebouwd. Door deze data zorgvuldig te reinigen, samen te stellen en te polijsten, en vervolgens de Hi-C-informatie te gebruiken om de stukken te ordenen en oriënteren, bouwden ze een aaneengesloten genoom van ongeveer 200 miljoen DNA-letters dat netjes is gerangschikt in 13 chromosomen.
Wat het nieuwe genoom onthult
De verbeterde assemblage is niet alleen continuër, maar ook rijker aan biologische details. Bijna 96 procent van de sequentie kon op chromosomen worden geplaatst, en de typische aaneengesloten stretch van geassembleerd DNA is nu vele malen langer dan in de vorige versie. Verrassend genoeg bestaat bijna 45 procent van het genoom uit herhaalde elementen, zoals mobiele DNA-segmenten die zichzelf kunnen kopiëren en verplaatsen. De auteurs identificeerden 15.327 eiwitcoderende genen, waarvan meer dan 96 procent gekoppeld kon worden aan bekende of voorspelde functies via grote openbare databanken. Ze brachten ook duizenden niet-coderende RNA-genen in kaart die betrokken zijn bij taken zoals eiwitsynthese en genregulatie, wat een dieper inzicht geeft in hoe dit compacte genoom is georganiseerd en gecontroleerd.
Waarom deze bron het verschil maakt
Voor niet-specialisten is de belangrijkste conclusie dat wetenschappers nu een veel duidelijkere en betrouwbaardere kaart van het DNA van Ciona savignyi hebben. Dit maakt nauwkeurige vergelijkingen met andere chordaten mogelijk om na te gaan hoe gewervelde kenmerken zijn geëvolueerd, en stelt onderzoekers in staat om genetische veranderingen te lokaliseren die ten grondslag liggen aan het indrukwekkende vermogen van de soort om nieuwe en stressvolle omgevingen te overleven. Praktisch gezien verandert de nieuwe genoomassemblage dit bescheiden zakpijpje in een nog krachtiger model om evolutie, ontwikkeling en omgevingsadaptatie te onderzoeken — met inzichten die ons uiteindelijk helpen onze eigen oorsprong en de snel veranderende zeeën van onze planeet beter te begrijpen.
Bronvermelding: Huang, X., Zhan, A. An Improved Chromosome-Level Genome Assembly and Comprehensive Annotation of the Model Ascidian Ciona savignyi. Sci Data 13, 617 (2026). https://doi.org/10.1038/s41597-026-06990-1
Trefwoorden: Ciona savignyi, genoomassemblage, tunicaat, omgevingsadaptatie, invasieve soort