Clear Sky Science · fr
Assemblage d’un génome amélioré au niveau des chromosomes et annotation complète du modèle ascidien Ciona savignyi
Pourquoi une minuscule créature marine compte
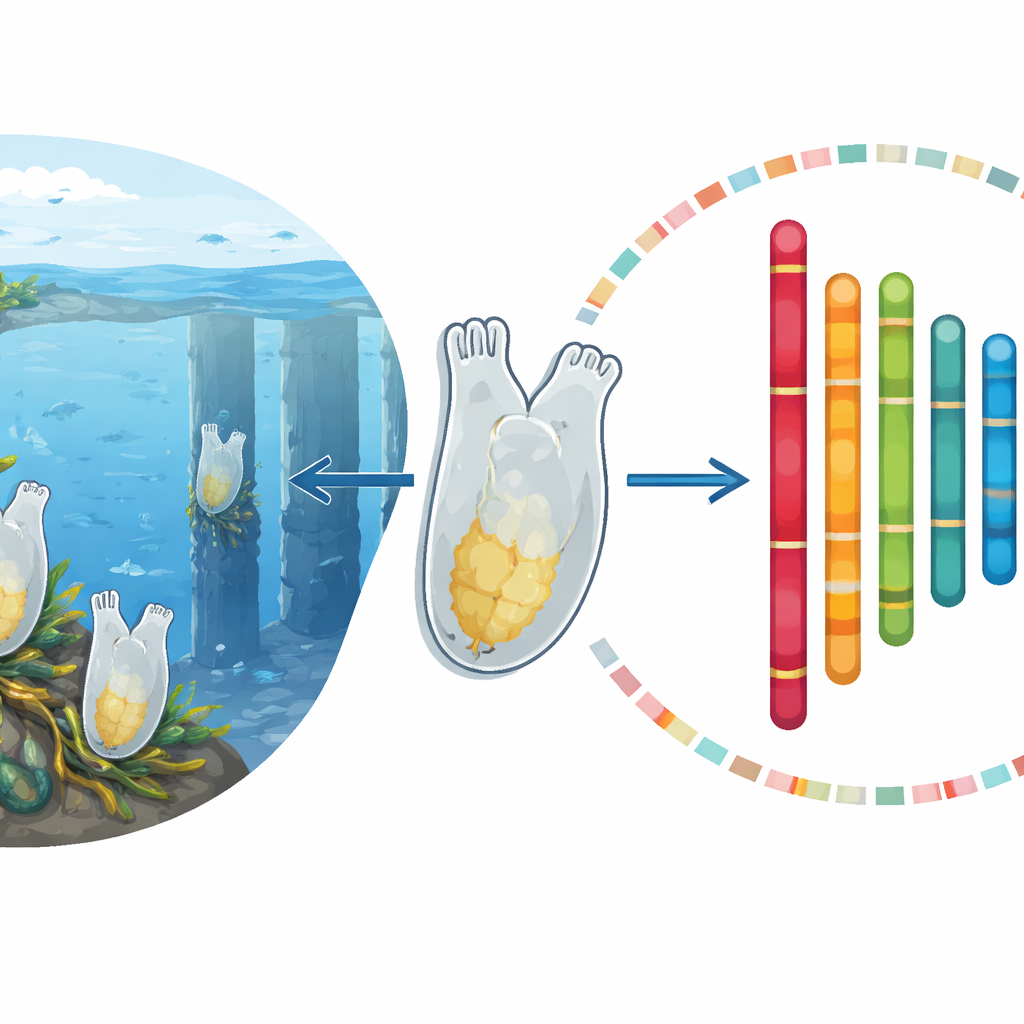
À première vue, l’ascidie Ciona savignyi ressemble à un animal simple en forme de sac accroché aux quais et aux coques de bateaux. Pourtant, cette créature modeste occupe une position proche de la racine évolutive de tous les animaux à colonne vertébrale, y compris les humains. Facile à élever, à développement rapide et remarquablement douée pour coloniser de nouveaux milieux, Ciona savignyi est devenue un modèle puissant pour comprendre comment des corps complexes évoluent et comment la vie s’adapte aux changements environnementaux rapides. Cette étude fournit un plan génétique beaucoup plus précis pour cette espèce, ouvrant la voie à des travaux plus fins dans des domaines allant de la biologie du développement à l’écologie des invasions.
Un animal simple avec une grande histoire
Ciona savignyi appartient aux tunicates, les plus proches parents invertébrés des vertébrés. Leurs larves en forme de têtard possèdent une tige rigide et un cordon nerveux qui évoquent la colonne et la moelle épinière embryonnaires des vertébrés. Parce que ces animaux ont des embryons transparents, à développement rapide, et des génomes compacts, ils servent depuis longtemps de systèmes clairs et épurés pour étudier comment apparaissent des plans corporels complexes. De nombreuses tuniciers, y compris les espèces de Ciona, se répandent également rapidement dans le monde, tolérant de fortes variations de température et de salinité. Cela en fait des cas d’étude naturels pour examiner comment les organismes font face aux bouleversements environnementaux associés au changement climatique et au commerce mondial.
La nécessité d’une carte génétique plus précise
Les chercheurs étudient Ciona savignyi depuis des années, mais sa carte génomique antérieure était fragmentée et incomplète. Une des raisons majeures est que les individus de cette espèce présentent une quantité exceptionnellement élevée de variation génétique, ce qui complique techniquement l’assemblage des fragments d’ADN. Le génome de référence précédent, largement utilisé depuis 2008, était morcelé en centaines de morceaux. Cela limitait la capacité des scientifiques à relier des caractères tels que la tolérance au stress, l’acclimatation rapide ou les différences entre populations à des segments d’ADN précis. Un génome plus clair, à l’échelle des chromosomes, était nécessaire pour faire de Ciona savignyi un modèle génomique véritablement moderne.
Assembler le puzzle du génome
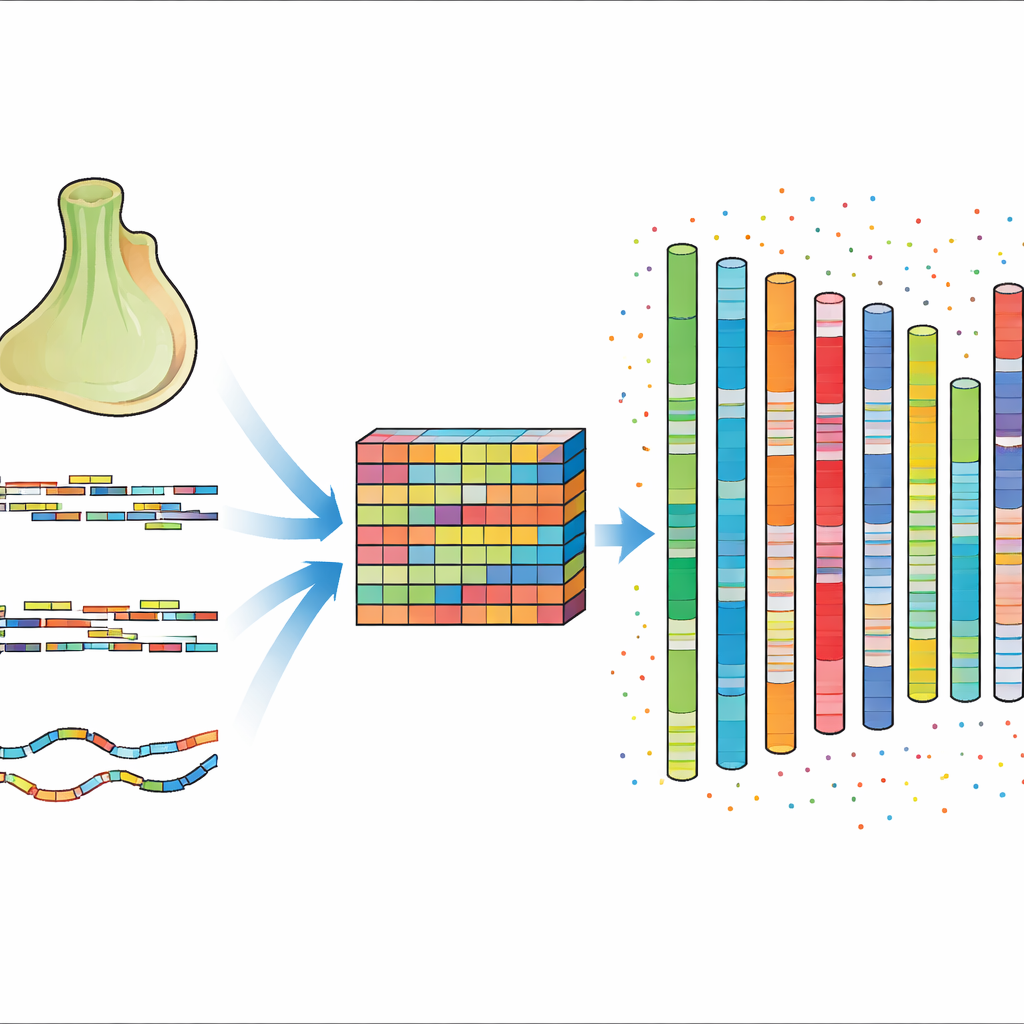
Pour résoudre ce problème, les auteurs ont combiné plusieurs approches de séquençage de pointe. Ils ont utilisé des lectures d’ADN courtes et très précises pour estimer et caractériser le contenu global du génome, des lectures longues pour couvrir des régions difficiles et répétitives, et une technique appelée Hi-C qui révèle quelles parties de l’ADN se trouvent proches les unes des autres dans le noyau cellulaire. Ils ont aussi séquencé de longs segments d’ARN provenant de plusieurs individus pour capturer quels gènes sont actifs et comment ils sont structurés. En nettoyant, assemblant et polissant soigneusement ces données, puis en utilisant les informations Hi-C pour ordonner et orienter les fragments, ils ont construit un génome contigu d’environ 200 millions de lettres d’ADN, organisé en 13 chromosomes.
Ce que révèle le nouveau génome
La nouvelle assemblée est non seulement plus continue, elle est aussi plus riche en détails biologiques. Près de 96 pour cent des séquences ont pu être positionnées sur les chromosomes, et la longueur typique des tranches continues d’ADN assemblé est maintenant plusieurs fois supérieure à celle de la version précédente. De façon surprenante, presque 45 pour cent du génome est constitué d’éléments répétitifs, comme des segments d’ADN mobiles qui peuvent se copier et se déplacer. Les auteurs ont identifié 15 327 gènes codant des protéines, plus de 96 pour cent étant associés à des fonctions connues ou prédites via de larges bases de données publiques. Ils ont également répertorié des milliers de gènes d’ARN non codants impliqués dans des tâches telles que la synthèse des protéines et la régulation génique, offrant une vision plus profonde de l’organisation et du contrôle de ce génome compact.
Pourquoi cette ressource change la donne
Pour le non-spécialiste, l’essentiel est que les scientifiques disposent désormais d’une carte de l’ADN de Ciona savignyi beaucoup plus claire et fiable. Cela permet des comparaisons précises avec d’autres chordés pour retracer l’évolution des caractéristiques des vertébrés, et cela aide les chercheurs à identifier les changements génétiques à l’origine de l’impressionnante capacité de l’espèce à survivre dans des environnements nouveaux et stressants. En termes pratiques, cette nouvelle assemblée génomique transforme cette humble ascidie en un modèle encore plus puissant pour explorer l’évolution, le développement et l’adaptation environnementale — offrant des insights qui, en fin de compte, nous aident à mieux comprendre nos propres origines et les océans en rapide transformation de la planète.
Citation: Huang, X., Zhan, A. An Improved Chromosome-Level Genome Assembly and Comprehensive Annotation of the Model Ascidian Ciona savignyi. Sci Data 13, 617 (2026). https://doi.org/10.1038/s41597-026-06990-1
Mots-clés: Ciona savignyi, assemblage du génome, tunicat, adaptation environnementale, espèce invasive