Clear Sky Science · de
Eine verbesserte, chromosomenskalige Genomassemblierung und umfassende Annotation des Modell-Tuniziers Ciona savignyi
Warum ein winziges Meereswesen wichtig ist
Auf den ersten Blick wirkt der Seesack Ciona savignyi wie ein einfaches, beutelförmiges Tier, das an Docks und Schiffsrümpfen hängt. Doch dieses bescheidene Lebewesen sitzt nahe der evolutionären Wurzel aller Wirbeltiere, einschließlich des Menschen. Weil es sich leicht züchten lässt, schnell entwickelt und bemerkenswert gut darin ist, neue Lebensräume zu besiedeln, ist Ciona savignyi zu einem starken Modell geworden, um zu verstehen, wie komplexe Körper entstehen und wie Leben sich schnell verändernden Umweltbedingungen anpasst. Diese Studie liefert einen deutlich schärferen genetischen Bauplan für die Art und ebnet den Weg für präzisere Arbeiten in Feldern von der Entwicklungsbiologie bis zur Invasionsökologie.
Ein einfaches Tier mit großer Geschichte
Ciona savignyi gehört zu den Tunicaten, den nächsten wirbellosen Verwandten der Wirbeltiere. Ihre laichähnlichen Larven besitzen eine starre Stange und ein Nervenseil, die an das frühe Rückgrat und das Rückenmark in Wirbeltier-Embryonen erinnern. Da diese Tiere transparente, schnell entwickelnde Embryonen und kompakte Genome haben, dienen sie seit langem als klare, schlanke Systeme, um zu erforschen, wie komplexe Körperpläne entstehen. Viele Tunicate, einschließlich Ciona-Arten, breiten sich außerdem rasch weltweit aus und tolerieren große Schwankungen von Temperatur und Salzgehalt. Das macht sie zu natürlichen Modellfällen, um zu untersuchen, wie Organismen mit den Umweltumwälzungen umgehen, die heute mit Klimawandel und globalem Handel einhergehen.
Der Bedarf an einer besseren genetischen Karte
Forscherinnen und Forscher untersuchen Ciona savignyi seit Jahren, doch die frühere Genomkarte war fragmentiert und unvollständig. Ein Hauptgrund dafür ist, dass Individuen dieser Art ungewöhnlich viel genetische Variation tragen, was das Zusammenfügen von DNA-Fragmenten technisch erschwert. Das bisherige Referenzgenom, das seit 2008 weit verbreitet genutzt wird, war in Hunderte Stücke zerteilt. Das schränkte die Möglichkeit ein, Merkmale wie Stressresistenz, schnelle Akklimatisierung oder Unterschiede zwischen Populationen bestimmten DNA-Regionen zuzuordnen. Eine klarere, chromosomenskalige Genomkarte war nötig, um Ciona savignyi zu einem wirklich modernen genomischen Modell zu machen.
Das Genom-Puzzle zusammensetzen
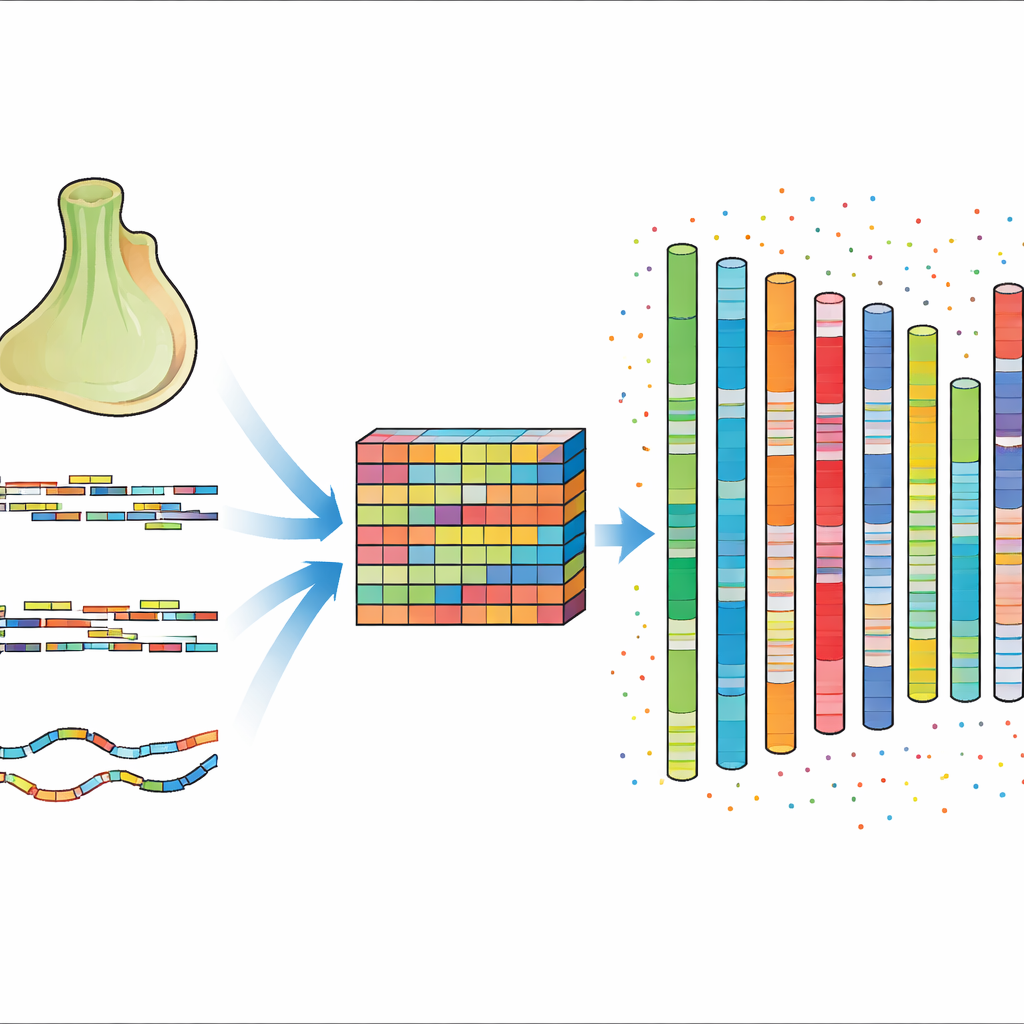
Um dies zu erreichen, kombinierten die Autorinnen und Autoren mehrere hochmoderne Sequenzieransätze. Sie verwendeten hochpräzise kurze DNA-Lesungen, um den Gesamtgehalt des Genoms zu quantifizieren und zu charakterisieren, lange Lesungen, um schwierige, repetitive Regionen zu überbrücken, sowie eine Methode namens Hi-C, die zeigt, welche DNA-Teile im Zellkern nah beieinander liegen. Außerdem sequenzierten sie lange RNA-Abschnitte aus mehreren Tieren, um erfassten, welche Gene aktiv sind und wie sie strukturiert sind. Durch sorgfältiges Bereinigen, Assemblieren und Polieren dieser Daten und anschließendem Einsatz der Hi-C-Informationen zur Anordnung und Orientierung der Stücke bauten sie ein zusammenhängendes Genom mit etwa 200 Millionen DNA-Basenpaaren, das ordentlich auf 13 Chromosomen angeordnet ist.
Was das neue Genom offenbart
Die verbesserte Assemblierung ist nicht nur kontinuierlicher, sie enthält auch mehr biologische Details. Nahezu 96 Prozent der Sequenz konnten auf Chromosomen platziert werden, und die typische zusammenhängende Länge des assemblierten DNA-Materials ist nun vielfach größer als in der vorherigen Version. Überraschenderweise besteht fast 45 Prozent des Genoms aus wiederholten Elementen, etwa mobilen DNA-Segmenten, die sich kopieren und bewegen können. Die Autorinnen und Autoren identifizierten 15.327 proteinkodierende Gene, von denen mehr als 96 Prozent über große öffentliche Datenbanken mit bekannten oder vorhergesagten Funktionen verknüpft sind. Sie katalogisierten außerdem Tausende nichtkodierender RNA-Gene, die an Aufgaben wie Proteinsynthese und Genregulation beteiligt sind, und bieten damit einen tieferen Einblick, wie dieses kompakte Genom organisiert und kontrolliert wird.
Warum diese Ressource die Regeln ändert
Für Nicht-Fachleute ist die zentrale Erkenntnis, dass Wissenschaftlerinnen und Wissenschaftler nun eine weitaus klarere und verlässlichere Karte der DNA von Ciona savignyi besitzen. Das ermöglicht präzise Vergleiche mit anderen Chordatieren, um nachzuzeichnen, wie wirbeltierliche Merkmale entstanden sind, und erlaubt es Forschenden, genetische Veränderungen zu identifizieren, die der beeindruckenden Fähigkeit der Art zugrunde liegen, in neuen und stressigen Umgebungen zu überleben. Praktisch verwandelt die neue Genomassemblierung diesen unscheinbaren Seesack in ein noch leistungsfähigeres Modell zur Erforschung von Evolution, Entwicklung und Umweltanpassung — und liefert Einsichten, die uns letztlich helfen, unsere eigenen Ursprünge und die rasch wechselnden Meere unseres Planeten besser zu verstehen.
Zitation: Huang, X., Zhan, A. An Improved Chromosome-Level Genome Assembly and Comprehensive Annotation of the Model Ascidian Ciona savignyi. Sci Data 13, 617 (2026). https://doi.org/10.1038/s41597-026-06990-1
Schlüsselwörter: Ciona savignyi, Genomassemblierung, Tunicat, Umweltanpassung, invasive Art