Clear Sky Science · it
Validazione e applicazione di un saggio qPCR quantitativo standardizzato per la valutazione dei geni di resistenza agli antimicrobici nelle acque superficiali
Perché contano i piccoli geni nelle acque selvagge
Quando percorri un sentiero in un parco nazionale e vedi ruscelli limpidi e impetuosi, sembrano intatti dall'intervento umano. Ma anche in luoghi remoti, tracce microscopiche dei nostri antibiotici possono manifestarsi come geni che rendono i batteri più difficili da eliminare. Questo studio pone una domanda semplice ma importante: possiamo misurare in modo affidabile questi geni di resistenza agli antibiotici nelle acque superficiali e usare quelle informazioni per capire quanto l'attività umana stia influenzando anche i paesaggi più protetti?
Cercare segnali di allarme nell'acqua che scorre
Gli antibiotici salvano vite, ma il loro uso intensivo in medicina e agricoltura ha favorito l'evoluzione di difese nei batteri. Quelle istruzioni difensive sono scritte nel DNA come geni di resistenza agli antibiotici. Quando persone o animali rilasciano batteri, o quando le acque reflue raggiungono i fiumi, questi geni possono diffondersi nell'ambiente, talvolta arrivando in luoghi che sembrano incontaminati. Scienziati e gestori delle terre pubbliche hanno bisogno di metodi per monitorare questi segnali genetici di allarme in laghi e ruscelli, così da individuare cambiamenti precocemente e valutare se siano dovuti all'afflusso di visitatori, a inquinamento storico o a processi naturali di fondo.
Creare un test genetico standardizzato
Il team di ricerca ha sviluppato una piastra di test genetico unica basata sulla PCR quantitativa, un metodo in grado di contare sequenze di DNA specifiche. Il loro pannello mirava a 47 marcatori genetici batterici differenti, inclusi molti noti geni di resistenza e alcuni utili per tracciare l'origine della contaminazione, come quelli umani, aviari o da animali al pascolo. Hanno progettato o adattato con cura i primer del DNA—brevi sequenze che dicono alla macchina PCR cosa copiare—e poi hanno verificato che ciascuno corrispondesse realmente al gene previsto confrontandoli con i principali database di riferimento. Per valutare l'affidabilità del test, lo hanno eseguito su DNA proveniente da 41 isolati batterici clinici e hanno confrontato i risultati con il sequenziamento genomico completo. L'accordo tra il test rapido e il sequenziamento molto più dettagliato è stato estremamente elevato, con sensibilità e specificità intorno al 98 percento.
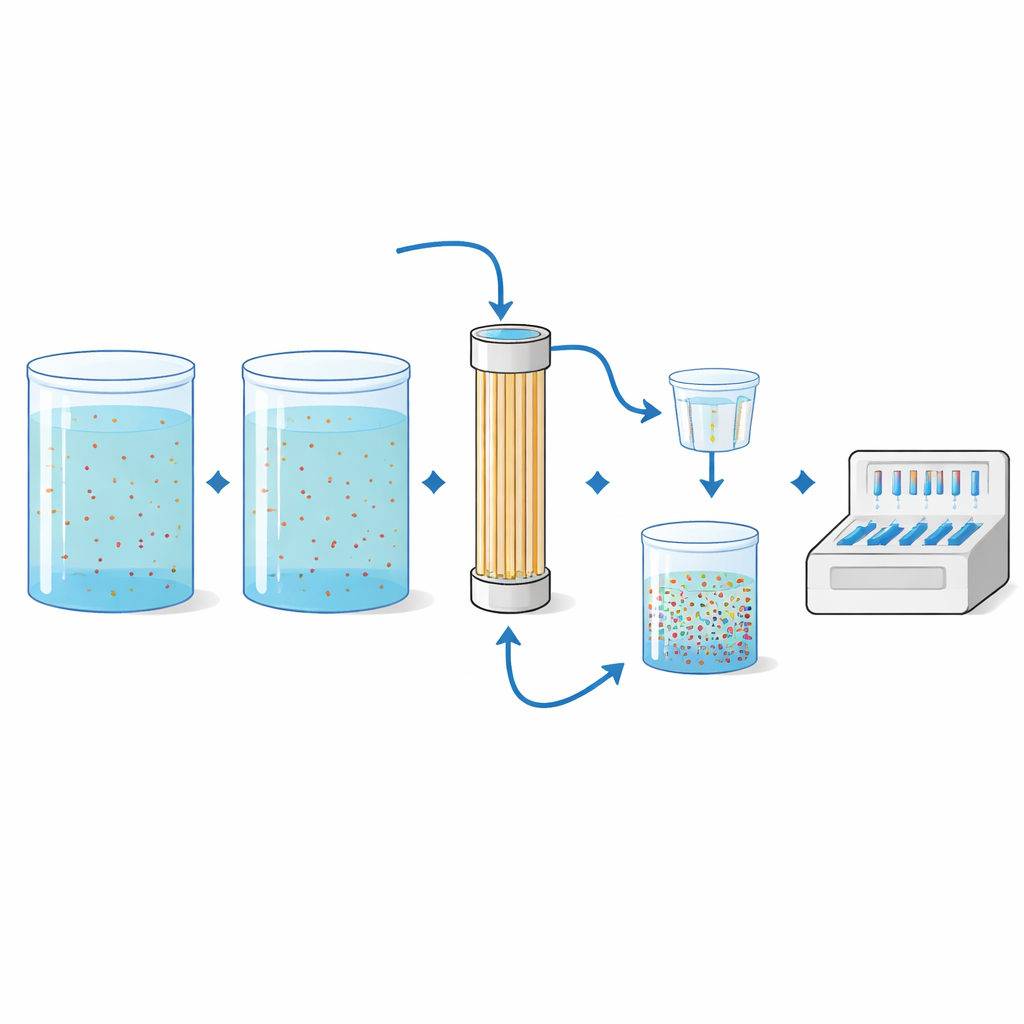
Concentrare segnali rari da grandi volumi
I geni di resistenza nei ruscelli selvaggi possono essere estremamente rari, quindi il team aveva bisogno di un modo per «ingrandire» tracce minime in grandi quantità d'acqua. Hanno utilizzato l'ultrafiltrazione a fibre cave, una tecnologia presa in prestito dalla dialisi e dal trattamento delle acque potabili. Grandi volumi—fino a 50 litri in questo studio—venivano pompati attraverso una cartuccia piena di sottili fibre cave che intrappolano i microrganismi. Il materiale trattenuto veniva quindi risciacquato dal filtro, ulteriormente concentrato su membrane più piccole e infine analizzato con il pannello PCR. In prove di laboratorio controllate, gli scienziati hanno inoculato acqua sterile con batteri noti portatori di otto diversi geni di resistenza a varie concentrazioni e volumi. Il metodo ha rilevato in modo affidabile molti dei geni inoculati, specialmente quando si filtravano volumi maggiori, e i rapporti misurati tra geni di resistenza e DNA batterico totale corrispondevano strettamente alle aspettative.
Cosa possono rivelare i parchi dell'Alaska
Armato di questo approccio, il team si è rivolto a tre parchi nazionali dell'Alaska che differiscono per l'afflusso di visitatori: Denali, Kenai Fjords e Wrangell–St. Elias. In ciascun parco hanno campionato due ruscelli, uno vicino a campeggi, strade o vecchi siti minerari e uno in una località più remota. Da questi corsi d'acqua hanno filtrato diversi campioni da 20 e 50 litri, coltivato alcuni batteri per testare quali potessero crescere in presenza di antibiotici e utilizzato il pannello PCR insieme al sequenziamento del DNA di marcatori batterici generali per vedere come si distribuivano i geni di resistenza e le comunità microbiche più ampie. In tutti e sei i siti hanno rilevato con alta confidenza 19 geni di resistenza distinti. Alcuni, come i geni associati ad antibiotici comuni quali sulfamidici e tetracicline, erano abbastanza diffusi, mentre altri legati a farmaci ospedalieri potenti sono apparsi in un numero limitato di campioni.
Impronte umane in ruscelli freddi e limpidi
Il parco con il maggior afflusso di visitatori, Denali, ha mostrato la più ampia varietà di geni di resistenza nel complesso. Tuttavia, il ruscello che si è distinto per la maggiore abbondanza di DNA di resistenza è stato Exit Creek nel Kenai Fjords National Park, che scorre sotto un centro visitatori e un punto di partenza per i sentieri molto frequentati. Lì, la proporzione di geni di resistenza rispetto al DNA batterico totale era significativamente più alta rispetto a tutti gli altri siti campionati. Per contro, Wrangell–St. Elias, con molti meno visitatori, ha mostrato un numero inferiore di tipi di geni di resistenza, e alcuni schemi hanno suggerito altre influenze come l'estrazione storica del rame. La maggior parte dei gruppi batterici identificati tramite il sequenziamento ampio non erano patogeni umani classici, e un solo isolato coltivato da tutti i siti ha mostrato una resistenza chiara nei test di laboratorio tradizionali, sottolineando che molti geni di resistenza possono risiedere in microrganismi ambientali piuttosto che in batteri chiaramente patogeni.
Cosa significa per proteggere persone e parchi
Questo lavoro dimostra che è possibile utilizzare una combinazione standardizzata e applicabile sul campo di filtrazione a grande volume e test genetici mirati per monitorare i geni di resistenza agli antibiotici nelle acque superficiali, anche dove la contaminazione è bassa. Confrontando sia la frequenza di comparsa dei geni di resistenza sia la loro abbondanza, i gestori possono cominciare a distinguere tra livelli naturali di fondo e probabili influenze umane dovute a visitatori, acque reflue o inquinamento residuo. Sebbene la presenza di geni di resistenza da sola non provi un rischio sanitario immediato, tracciarli nel tempo offre un sistema di allerta precoce e un modo per valutare quanto bene i parchi stiano proteggendo sia gli ecosistemi sia le comunità a valle in un mondo in cui la resistenza agli antibiotici è una preoccupazione in crescita.
Citazione: Scott, L.C., Ahlstrom, C.A., Woksepp, H. et al. Validation and application of a standardized quantitative PCR assay for the assessment of antimicrobial resistance genes in surface water. Sci Rep 16, 11597 (2026). https://doi.org/10.1038/s41598-026-35635-x
Parole chiave: resistenza agli antimicrobici, acque superficiali, parchi nazionali, monitoraggio qPCR, qualità dell'acqua