Clear Sky Science · fr
Validation et application d'un test de qPCR standardisé pour l'évaluation des gènes de résistance aux antimicrobiens dans les eaux de surface
Pourquoi de petits gènes dans les eaux sauvages comptent
Quand vous randonnez dans un parc national et que vous voyez des ruisseaux clairs et vifs, ils semblent intacts et loin de l'empreinte humaine. Mais même dans des sites reculés, des traces microscopiques de nos antibiotiques peuvent apparaître sous forme de gènes rendant les bactéries plus difficiles à tuer. Cette étude pose une question simple mais cruciale : peut-on mesurer de manière fiable ces gènes de résistance aux antibiotiques dans les eaux de surface, et utiliser ces données pour comprendre dans quelle mesure l'activité humaine affecte même nos paysages les mieux protégés ?
À la recherche de signaux d'alerte dans l'eau courante
Les antibiotiques sauvent des vies, mais leur usage intensif en médecine et en agriculture a favorisé l'évolution de défenses chez les bactéries. Ces instructions de défense sont écrites dans l'ADN sous forme de gènes de résistance aux antibiotiques. Quand des personnes ou des animaux éliminent des bactéries, ou quand des eaux usées se déversent dans les cours d'eau, ces gènes peuvent se répandre dans l'environnement, parfois jusqu'à des lieux qui paraissent vierges. Les scientifiques et les gestionnaires des terres publiques ont besoin de moyens pour surveiller ces signaux génétiques dans les lacs et les ruisseaux afin de détecter tôt les changements et d'évaluer si l'utilisation par les visiteurs, une pollution historique ou des processus naturels en sont la cause.
Concevoir un test génétique standardisé
L'équipe de recherche a développé une plaque de test génétique unique basée sur la PCR quantitative, une méthode capable de compter des séquences d'ADN spécifiques. Leur panel ciblait 47 marqueurs géniques bactériens différents, incluant de nombreux gènes de résistance connus et quelques marqueurs permettant de tracer l'origine de la contamination, comme humaine, aviaire ou liée au pâturage. Ils ont soigneusement conçu ou adapté des amorces d'ADN — de courtes séquences qui indiquent à la machine PCR ce qu'il faut copier — puis vérifié que chacune correspondait réellement au gène visé en comparant aux principales bases de référence. Pour évaluer la fiabilité du test, ils l'ont appliqué à l'ADN de 41 isolats bactériens cliniques et ont comparé les résultats au séquençage de génome complet. La concordance entre le test rapide et le séquençage beaucoup plus détaillé a été extrêmement élevée, avec une sensibilité et une spécificité proches de 98 %.
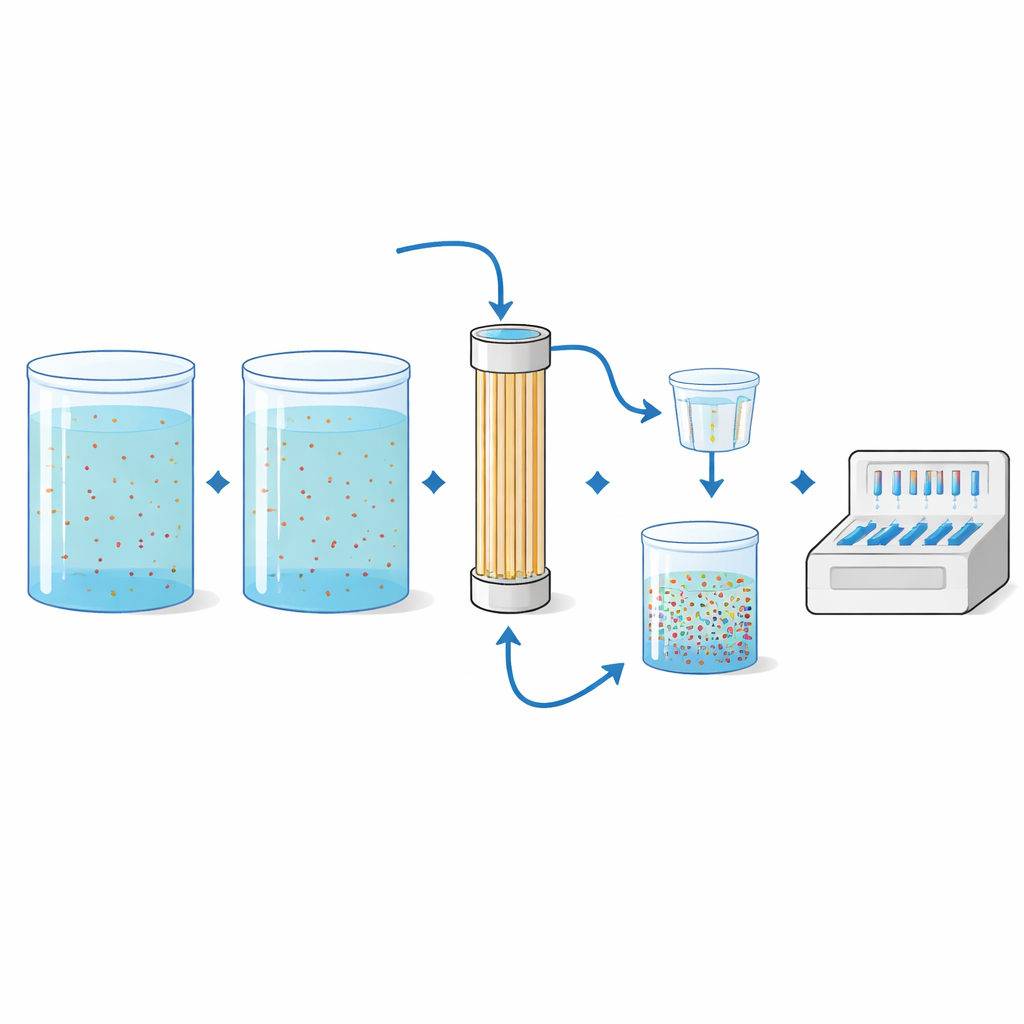
Concentrer des signaux rares à partir de grands volumes
Les gènes de résistance dans les ruisseaux sauvages peuvent être extraordinairement rares, si bien que l'équipe avait besoin d'une méthode pour « zoomer » sur de minuscules traces dans une grande quantité d'eau. Ils ont utilisé l'ultrafiltration à fibres creuses, une technologie empruntée à l'hémodialyse et au traitement de l'eau potable. De grands volumes — jusqu'à 50 litres dans cette étude — étaient pompés à travers une cartouche remplie de fines fibres creuses qui retiennent les microbes. Le matériel piégé était ensuite rincé hors du filtre, concentré davantage sur des membranes plus petites, puis enfin analysé avec le panel PCR. Dans des essais en laboratoire contrôlés, les scientifiques ont ajouté à de l'eau stérile des bactéries connues portant huit gènes de résistance à plusieurs concentrations et volumes. La méthode détectait de façon fiable beaucoup des gènes ajoutés, en particulier lorsque de plus grands volumes d'eau étaient filtrés, et les proportions mesurées de gènes de résistance par rapport à l'ADN bactérien total correspondaient étroitement aux attentes.
Ce que les parcs de l'Alaska peuvent révéler
Armée de cette approche, l'équipe s'est tournée vers trois parcs nationaux en Alaska qui diffèrent par leur fréquentation : Denali, Kenai Fjords et Wrangell–St. Elias. Dans chaque parc, ils ont échantillonné deux ruisseaux, l'un situé près de campings, de routes ou d'anciennes mines, et l'autre dans un endroit plus isolé. À partir de ces cours d'eau, ils ont filtré plusieurs échantillons de 20 et 50 litres, cultivé certaines bactéries pour tester celles qui pouvaient croître en présence d'antibiotiques, et utilisé le panel PCR ainsi que le séquençage d'indicateurs bactériens généraux pour examiner la distribution des gènes de résistance et des communautés microbiennes plus larges. Parmi les six sites, ils ont détecté avec une grande confiance 19 gènes de résistance distincts. Certains, comme des gènes liés à des antibiotiques courants tels que les sulfamides et les tétracyclines, étaient assez répandus, tandis que d'autres, associés à des médicaments puissants utilisés en milieu hospitalier, n'apparaissaient que dans quelques échantillons.
Empreintes humaines dans des ruisseaux froids et clairs
Le parc le plus fréquenté, Denali, présentait la plus grande diversité de gènes de résistance au total. Pourtant, le ruisseau qui se distinguait par la plus grande abondance d'ADN de résistance était Exit Creek, dans le parc national de Kenai Fjords, qui coule sous un centre d'accueil et un départ de sentier très fréquentés. Là, la proportion de gènes de résistance par rapport à l'ADN bactérien total était significativement plus élevée que sur tous les autres sites échantillonnés. En revanche, Wrangell–St. Elias, avec bien moins de visiteurs, montrait moins de types de gènes de résistance, et certains schémas laissaient entrevoir d'autres influences possibles, comme l'ancienne exploitation du cuivre. La plupart des groupes bactériens identifiés par le séquençage large n'étaient pas des agents pathogènes humains classiques, et un seul isolat cultivé provenant de tous les sites a montré une résistance évidente lors des tests de laboratoire traditionnels, ce qui souligne que de nombreux gènes de résistance peuvent résider dans des microbes environnementaux plutôt que dans des bactéries clairement pathogènes.
Ce que cela signifie pour la protection des personnes et des parcs
Ce travail montre qu'il est possible d'utiliser une combinaison standardisée et opérationnelle sur le terrain de filtration de grands volumes et de tests génétiques ciblés pour surveiller les gènes de résistance aux antibiotiques dans les eaux de surface, même lorsque la contamination est faible. En comparant à la fois la fréquence d'apparition des gènes de résistance et leur abondance, les gestionnaires peuvent commencer à distinguer entre des niveaux de fond naturels et une influence humaine probable liée aux visiteurs, aux eaux usées ou à une pollution historique. Si la présence de gènes de résistance n'indique pas à elle seule une menace sanitaire immédiate, leur suivi dans le temps offre un système d'alerte précoce et un moyen d'évaluer l'efficacité de la protection des écosystèmes et des communautés situées en aval, dans un monde où la résistance aux antibiotiques est un enjeu croissant.
Citation: Scott, L.C., Ahlstrom, C.A., Woksepp, H. et al. Validation and application of a standardized quantitative PCR assay for the assessment of antimicrobial resistance genes in surface water. Sci Rep 16, 11597 (2026). https://doi.org/10.1038/s41598-026-35635-x
Mots-clés: résistance aux antimicrobiens, eaux de surface, parcs nationaux, surveillance par qPCR, qualité de l'eau