Clear Sky Science · it
Screening dell’intera proteina e profilazione multimodale delle cellule CD4+ specifiche per antigene a risoluzione single-cell
Perché è importante per la salute e l’oncologia
Il nostro sistema immunitario si affida a cellule helper che coordinano gli attacchi contro virus e tumori, ma gli scienziati hanno faticato a monitorare queste cellule in dettaglio. Questo studio introduce un metodo di laboratorio potente in grado di individuare rare cellule T helper nel sangue, determinare con precisione ciò che riconoscono e leggerne il comportamento cellula per cellula. Il lavoro potrebbe affinare la progettazione dei vaccini e sostenere nuove terapie cellulari per infezioni come COVID-19 e per tumori associati al papillomavirus umano (HPV).
Trovare i direttori d’orchestra immunitari
Le cellule T helper, dette anche cellule CD4+, fungono da direttori d’orchestra del sistema immunitario. Rispondono quando altre cellule mostrano loro brevi porzioni di virus o proteine tumorali e, a loro volta, aiutano le cellule B produttrici di anticorpi, le cellule T citotossiche e altri difensori a svolgere il proprio compito. Studiare questi direttori è stato difficile perché ciascuna cellula riconosce un frammento proteico leggermente diverso e gli strumenti per trovarle nel sangue o ne alterano lo stato naturale o possono testare solo un numero limitato di bersagli per volta. Gli autori si sono proposti di costruire un metodo capace di esplorare proteine intere, catturare direttamente le cellule helper dal sangue e leggere contemporaneamente i loro programmi genetici e i loro recettori T in un’unica analisi.

Costruire una libreria proteica per le cellule helper
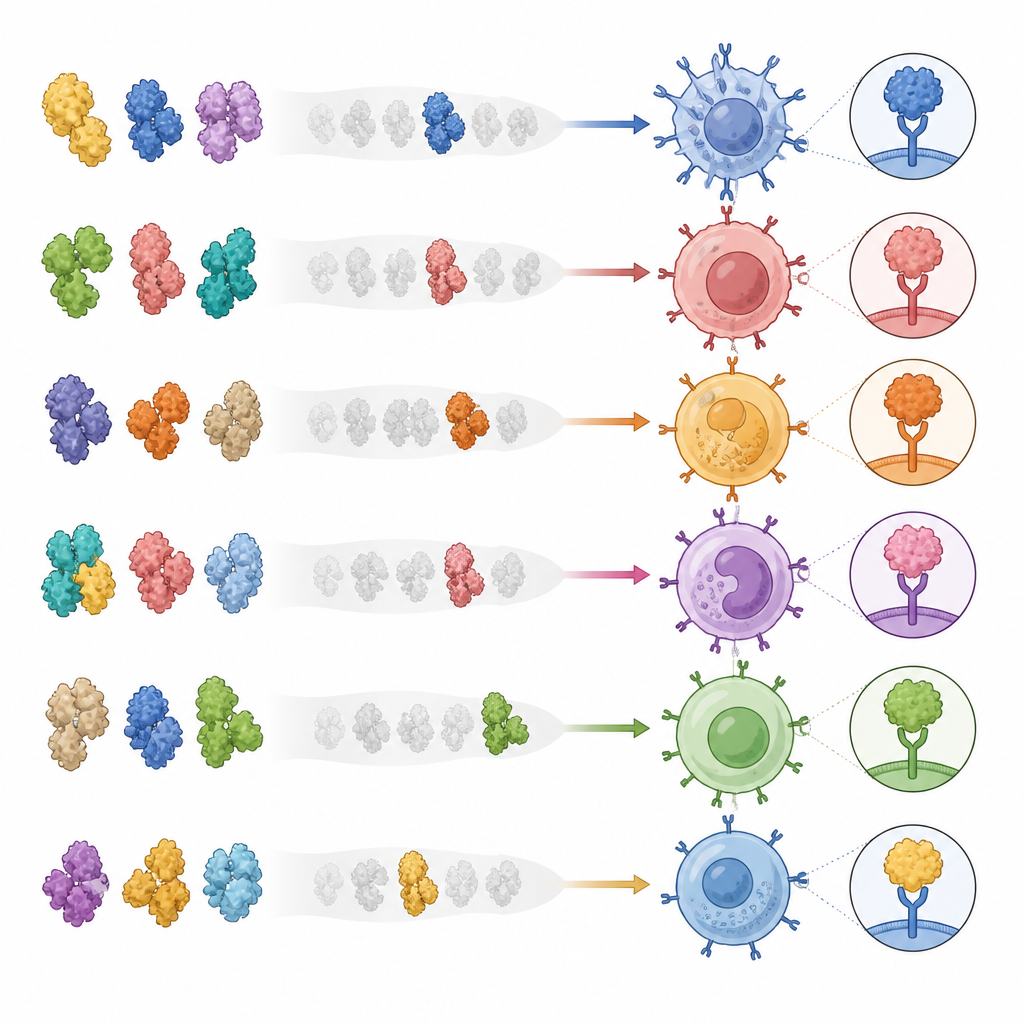
Il gruppo ha ingegnerizzato una vasta libreria di complessi proteici artificiali che imitano ciò che le cellule presentano alle cellule T helper. Ogni complesso contiene un frammento proteico specifico di un virus o di una proteina tumorale in una conformazione fissa, legato a una molecola umana di presentazione. Collegando le parti in una singola catena, hanno reso più semplice la produzione su larga scala di centinaia di complessi distinti in colture cellulari umane senza dover sintetizzare ogni peptide separatamente. Hanno dimostrato che questi complessi legano solo le cellule T helper corrispondenti, funzionano attraverso diversi tipi di geni HLA comuni e possono rilevare anche cellule rare nel sangue a frequenze molto basse. È importante che il legame a questi complessi predicesse anche la risposta delle stesse cellule T quando i bersagli erano presentati su cellule viventi, non solo in test artificiali.
Monitorare le cellule helper contro COVID-19 nel tempo
Con questa piattaforma, i ricercatori hanno scandagliato l’intero dominio di legame del recettore (RBD) della proteina spike di SARS-CoV-2, insieme ad altre regioni virali, in campioni di sangue di 22 persone che avevano avuto COVID-19. Usando codici a barre e sequenziamento single-cell, hanno catturato 2.188 cellule T helper specifiche per il virus e hanno appreso, per ciascuna cellula, quale frammento virale riconosceva, quale gene HLA lo presentava, com’era fatto il suo recettore T e quali geni stava esprimendo. Hanno osservato un mix ricco di stati cellulari, incluse cellule con caratteristiche di memoria, effettrici, regolatorie e simili a cellule esauste. Nel tempo, le risposte tendevano a spostarsi verso cellule di memoria effettrici, ma in modo differente rispetto a quanto osservato in precedenti studi sulle cellule T citotossiche. Il team ha creato un “punteggio di immunogenicità” che combina quante persone e cloni di cellule T rispondevano a un dato frammento virale, quanto quei cloni si espandessero e quanto a lungo persistevano. Punteggi più alti per frammenti del RBD della spike erano correlati a livelli anticorpali successivamente più elevati, suggerendo che queste cellule helper possano sostenere una qualità migliore degli anticorpi.
Esplorare le cellule helper HPV per la terapia del cancro
I ricercatori si sono poi rivolti al cancro, concentrandosi su HPV-16, una causa importante di tumori cervicali e altri tumori. Hanno costruito una libreria che ricopriva a tasselli due proteine HPV, E6 ed E7, usando frammenti di diversa lunghezza per sondare come le regioni “flanking” intorno a un nucleo centrale influenzino il riconoscimento da parte delle cellule T helper. Hanno applicato questa libreria a pazienti con lesioni precancerose che avevano ricevuto vaccini terapeutici contro l’HPV e hanno identificato dozzine di cellule T helper specifiche per HPV. Da queste, hanno selezionato un pannello di recettori delle cellule T per test più approfonditi. Alcuni recettori hanno mostrato risposte forti e selettive quando trasferiti in cellule T umane, producendo molteplici segnali utili e uccidendo cellule bersaglio caricate con frammenti HPV o con la proteina E6 a lunghezza intera, mostrando al contempo poca o nessuna reazione verso proteine umane simili o verso un ampio pannello di altri tipi di geni HLA. Un recettore in particolare, chiamato H2 nello studio, è emerso come candidato promettente per future terapie cellulari ingegnerizzate.
Cosa significa per vaccini e terapie future
Per i non specialisti, il messaggio chiave è che gli autori hanno costruito una sorta di “motore di ricerca immunitario” per le cellule T helper. Può analizzare proteine intere di virus o tumori, isolare le rare cellule che riconoscono pezzi specifici e rivelare contemporaneamente come si comportano e come potrebbero essere impiegate. Nel caso di COVID-19, questo approccio ha collegato certi frammenti della spike sia a forti risposte delle cellule helper sia a livelli anticorpali più elevati, offrendo indizi per perfezionare i vaccini. Nelle patologie correlate a HPV, ha identificato recettori di cellule helper che appaiono potenti e sufficientemente sicuri da considerare per immunoterapie antitumorali mirate. Pur richiedendo ulteriori lavori per estendere il metodo ad altri tipi di geni HLA e a coorti di pazienti più vaste, questa piattaforma apre una strada pratica per mappare e, in futuro, indirizzare il braccio helper del sistema immunitario in molte malattie.
Citazione: Zhang, R., Qi, J., McKasson, M. et al. Whole-protein screening and multi-modal profiling of antigen-specific CD4+ T cells at single-cell resolution. Nat Commun 17, 3979 (2026). https://doi.org/10.1038/s41467-026-72396-7
Parole chiave: Cellule T CD4, profilazione single-cell, immunità SARS-CoV-2, immunoterapia HPV, recettori delle cellule T