Clear Sky Science · it
Caratteristiche molecolari ad alto rischio possono oscurare la complessità genomica nella predizione degli esiti della leucemia linfatica cronica; spunti da trial clinici nel Regno Unito
Perché questa storia sul cancro del sangue è importante
La leucemia linfatica cronica (LLC) è la forma più comune di leucemia negli adulti, eppure i pazienti possono conviverci per anni oppure vederla diventare aggressiva molto prima. I medici hanno a lungo considerato quanto il DNA del tumore appaia disordinato—la sua “complessità genomica”—per stimare quali pazienti potrebbero avere esiti peggiori. Questo studio pone una domanda cruciale per pazienti e clinici: è davvero necessario misurare quanto sia caotico l’intero genoma, o bastano poche caratteristiche specifiche ad alto rischio per dirci la maggior parte di ciò che serve sapere sugli esiti futuri?
Oltre un genoma ingarbugliato
I ricercatori hanno analizzato cellule del cancro del sangue di 495 persone con LLC precedentemente non trattata che hanno partecipato a tre ampi trial britannici di chemioterapia e chemo‑immunoterapia. Invece di concentrarsi soltanto sul disordine genetico complessivo, hanno anche misurato tre marcatori più precisi: se un gene immunitario chiave chiamato IGHV fosse mutato o non mutato, la lunghezza dei telomeri cromosomici e quale “epitipo” di metilazione del DNA le cellule presentassero, indicatore dell’origine da linfociti B naive o da linfociti B con memoria. Hanno inoltre catalogato difetti genetici specifici e guadagni o perdite cromosomiche noti per guidare la LLC.
Livelli diversi di alterazione del DNA
I pazienti sono stati raggruppati in base al numero di alterazioni del numero di copie—ampie perdite o guadagni di DNA—presenti nelle loro cellule tumorali: bassa complessità genomica (zero‑due cambiamenti), intermedia (tre‑quattro) o alta (cinque o più). I tumori ad alta complessità avevano molta più probabilità di mostrare IGHV non mutato, danni al gene TP53 (un guardiano critico del danno al DNA), telomeri corti e alcune perdite cromosomiche caratteristiche, come parti dei cromosomi 11 e 13. I tumori a complessità intermedia mostravano spesso alterazioni di ATM e BIRC3, geni coinvolti nella risposta al danno del DNA e nella sopravvivenza cellulare. Al contrario, i tumori con meno cambiamenti del DNA risultavano arricchiti per trisomia 12 (una copia extra del cromosoma 12) e mutazioni di NOTCH1, uno schema precedentemente collegato a una biologia della malattia in parte diversa.
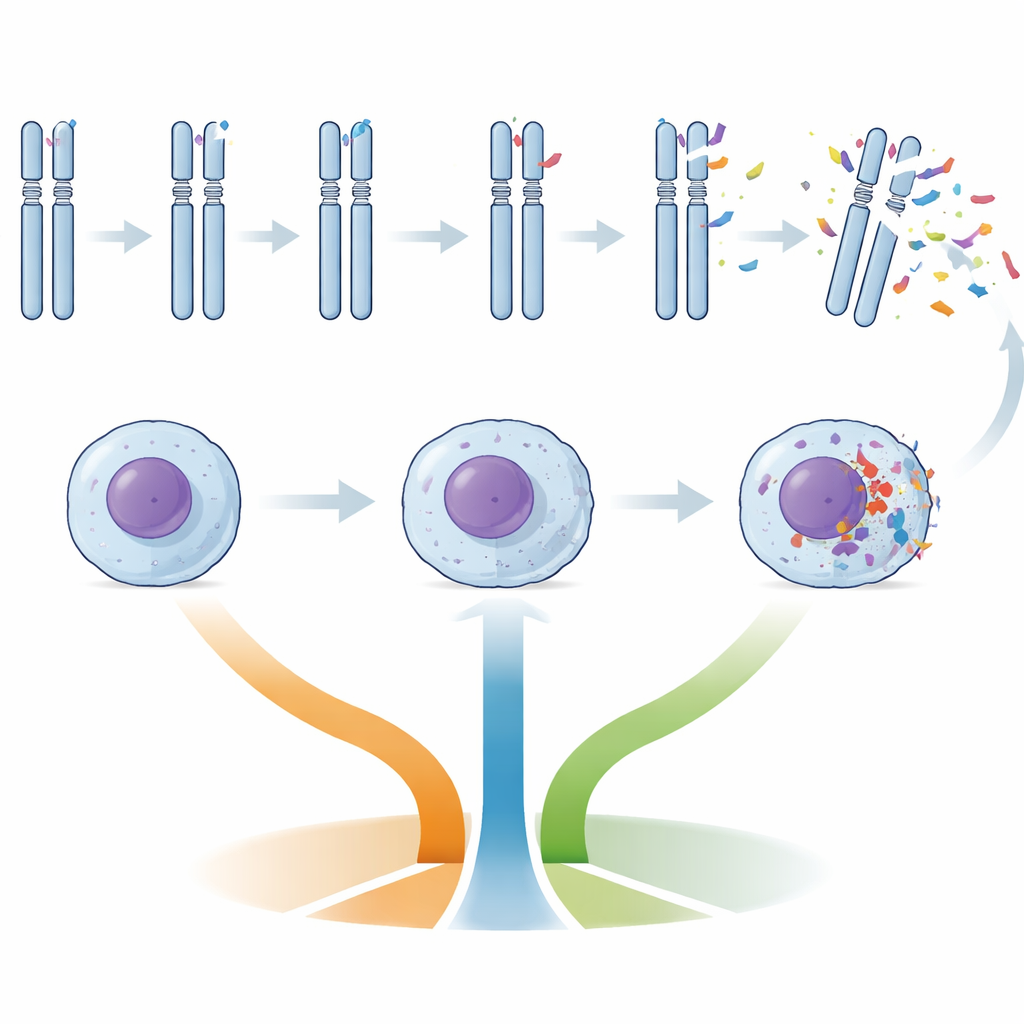
Telomeri, identità cellulare e rischio
I telomeri—i cappucci protettivi alle estremità dei cromosomi—si accorciano man mano che le cellule si dividono. In questo studio la lunghezza dei telomeri si è chiaramente correlata al rischio: i pazienti con i telomeri più corti tendevano a rientrare nel gruppo ad alta complessità e avevano esiti peggiori. Gli “epitipi” di metilazione del DNA hanno aggiunto un ulteriore livello informativo: i tumori il cui schema di metilazione somigliava a quello dei linfociti B naive (n‑CLL) erano più spesso associati a caratteristiche avverse. Insieme, IGHV non mutato, telomeri corti ed epitipo naive‑like co‑occorrevano frequentemente con danni a TP53 negli stessi pazienti, delineando un quadro coerente di una forma biologicamente aggressiva di LLC, indipendentemente dal numero totale di cambiamenti del DNA presenti.
Quali marcatori predicono davvero il futuro?
A prima vista, i pazienti i cui tumori presentavano genomi altamente complessi recidivavano prima e morivano prima rispetto a quelli con meno cambiamenti del DNA. Ma quando il gruppo ha costruito modelli statistici più sofisticati che consideravano molti fattori contemporaneamente, l’elevata complessità genomica spesso perdeva potere come predittore indipendente. Al contrario, caratteristiche specifiche—disfunzione di TP53, IGHV non mutato, telomeri corti ed epitipi di metilazione naive‑like—sono emerse come gli indicatori più forti e costanti di minore sopravvivenza libera da progressione e sopravvivenza globale. In uno dei tre trial l’alta complessità aggiungeva ancora qualche valore prognostico, ma in generale sembrava essere un segno visibile di problemi più profondi piuttosto che il fattore determinante fondamentale.
Cosa significa per i pazienti e per l’assistenza
Per le persone che convivono con la LLC, questi risultati suggeriscono che un pannello mirato di marcatori ad alto rischio può essere più informativo di una misura ampia di quanto il genoma appaia disordinato. L’alta complessità genomica sembra catturare il risultato finale dell’accumulo di cambiamenti pericolosi—soprattutto danni a TP53, rapido ricambio cellulare che porta all’accorciamento dei telomeri e un’origine cellulare che si comporta più come un linfocita B naive immaturo. Mentre i nuovi farmaci mirati stanno rimodellando il trattamento della LLC, lo studio sostiene che costruire modelli di rischio attorno a queste caratteristiche specifiche, e validarli in pazienti trattati con terapie moderne, potrebbe affinare la capacità dei medici di prevedere chi avrà una malattia più indolente e chi invece necessita di monitoraggio più stretto e di trattamenti più precoci e intensivi.
Citazione: Parker, H., Carr, L., Norris, K. et al. High-risk molecular features may eclipse genomic complexity in predicting chronic lymphocytic leukemia outcomes; UK clinical trial insights. Leukemia 40, 816–826 (2026). https://doi.org/10.1038/s41375-026-02906-5
Parole chiave: leucemia linfatica cronica, complessità genomica, TP53, lunghezza dei telomeri, metilazione del DNA