Clear Sky Science · es
Las características moleculares de alto riesgo pueden eclipsar la complejidad genómica al predecir la evolución de la leucemia linfocítica crónica; perspectivas de ensayos clínicos del Reino Unido
Por qué importa esta historia sobre cáncer sanguíneo
La leucemia linfocítica crónica (LLC) es la leucemia más habitual en adultos; sin embargo, algunos pacientes pueden convivir con ella durante años mientras que en otros progresa a una forma agresiva mucho antes. Durante tiempo, los médicos han observado cuánto parece estar desordenado el ADN de un cáncer—su “complejidad genómica”—para estimar qué pacientes pueden tener peor pronóstico. Este estudio plantea una cuestión clave para pacientes y clínicos: ¿realmente necesitamos medir cuán caótico es todo el genoma, o bastan unas pocas características de alto riesgo para revelar la mayor parte de lo que necesitamos saber sobre los resultados futuros?
Más allá de un genoma enmarañado
Los investigadores examinaron células de cáncer sanguíneo de 495 personas con LLC previamente no tratada que participaron en tres grandes ensayos del Reino Unido sobre quimioterapia y quimioinmunoterapia. En lugar de centrarse únicamente en el desorden genético global, midieron también tres marcadores más precisos: si un gen inmunitario clave llamado IGHV estaba mutado o no, la longitud de los extremos cromosómicos (telómeros) y qué “epitipo” de metilación del ADN presentaban las células, lo que refleja si el cáncer se originó en células B de tipo naïve o en células B con rasgos de memoria. También catalogaron fallos genéticos específicos y ganancias o pérdidas cromosómicas conocidas por impulsar la LLC.
Diferentes niveles de alteración del ADN
Los pacientes se agruparon según cuántas alteraciones del número de copias—grandes ganancias o pérdidas de ADN—presentaban sus células tumorales: baja complejidad genómica (cero a dos cambios), intermedia (tres a cuatro) o alta (cinco o más). Los cánceres de alta complejidad eran mucho más propensos a mostrar IGHV no mutado, daño en el gen TP53 (un encargado crítico de la respuesta al daño del ADN), telómeros cortos y ciertas pérdidas cromosómicas características, como fragmentos de los cromosomas 11 y 13. Los cánceres de complejidad intermedia con frecuencia presentaban alteraciones en ATM y BIRC3, genes implicados en la respuesta al daño del ADN y la supervivencia celular. En contraste, los cánceres con menos cambios de ADN mostraron enriquecimiento de la trisomía 12 (una copia adicional del cromosoma 12) y mutaciones en NOTCH1, un patrón vinculado previamente a una biología de la enfermedad algo distinta.
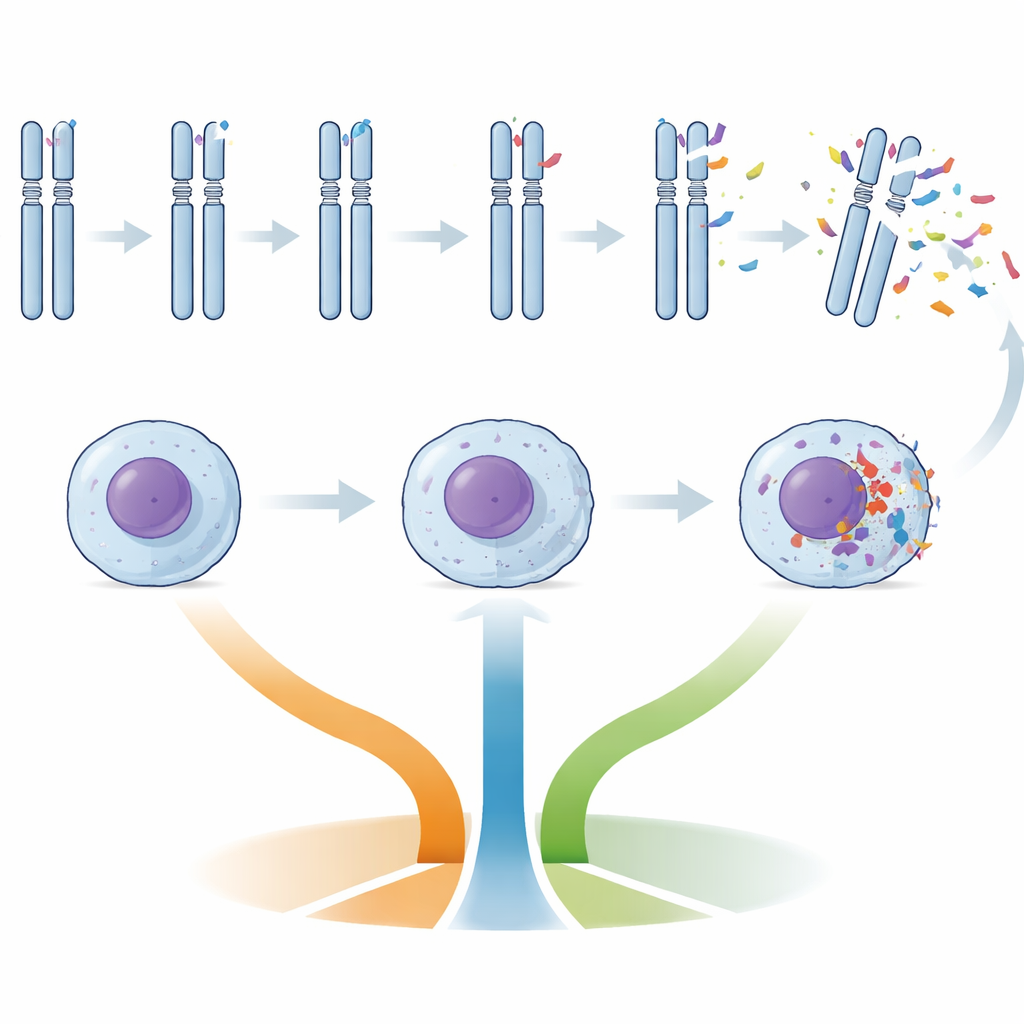
Telómeros, identidad celular y riesgo
Los telómeros—las tapas protectoras en los extremos cromosómicos—se acortan a medida que las células se dividen. En este estudio, la longitud de los telómeros se relacionó claramente con el riesgo: los pacientes con los telómeros más cortos tendían a agruparse en el grupo de alta complejidad y tenían peores resultados. Los “epitipos” de metilación del ADN aportaron otra capa de información: los cánceres cuya pauta de metilación se asemejaba a las células B naïve (n‑CLL) se asociaron con mayor frecuencia a rasgos adversos. En conjunto, IGHV no mutado, telómeros cortos y epitipo de tipo naïve con frecuencia coincidían con daño en TP53 en los mismos pacientes, dibujando un cuadro coherente de una forma biológicamente agresiva de LLC, independientemente del número total de cambios en el ADN.
¿Qué marcadores predicen realmente el futuro?
A primera vista, los pacientes cuyos cánceres mostraban genomas muy complejos recaían antes y fallecían antes que aquellos con menos cambios de ADN. Pero cuando el equipo construyó modelos estadísticos más sofisticados que consideraron muchos factores a la vez, la alta complejidad genómica con frecuencia perdió su poder como predictor independiente. En su lugar, características concretas—alteración de TP53, IGHV no mutado, telómeros cortos y patrones de metilación de tipo naïve—surgieron como los indicadores más sólidos y consistentes de peor supervivencia libre de progresión y supervivencia global. En uno de los tres ensayos, la alta complejidad aún añadió algo de valor pronóstico, pero en general pareció ser un signo visible de problemas más profundos en lugar del motor fundamental.
Qué significa esto para pacientes y cuidados
Para las personas con LLC, estos hallazgos sugieren que un panel focalizado de marcadores de alto riesgo podría ser más informativo que una medida amplia de cuánto se ve desordenado el genoma. La alta complejidad genómica parece capturar el resultado final de la acumulación de cambios peligrosos—especialmente el daño a TP53, la rápida renovación celular que conduce al acortamiento de los telómeros y un origen celular que se comporta más como una célula B inmadura de tipo naïve. A medida que los fármacos dirigidos más recientes remodelan el tratamiento de la LLC, el estudio sostiene que construir modelos de riesgo alrededor de estas características específicas, y validarlos en pacientes que reciben terapias modernas, podría afinar la capacidad de los médicos para predecir qué enfermedad probablemente permanecerá tranquila y cuál puede requerir seguimiento más estrecho y un tratamiento más intensivo y precoz.
Cita: Parker, H., Carr, L., Norris, K. et al. High-risk molecular features may eclipse genomic complexity in predicting chronic lymphocytic leukemia outcomes; UK clinical trial insights. Leukemia 40, 816–826 (2026). https://doi.org/10.1038/s41375-026-02906-5
Palabras clave: leucemia linfocítica crónica, complejidad genómica, TP53, longitud de los telómeros, metilación del ADN